Clear Sky Science · it
Disfunzione dell’ecosistema intestinale nella malattia di Parkinson: decifrare i collegamenti metagenoma-metaboloma fecale per nuovi pannelli diagnostici
Perché l’intestino conta in una malattia cerebrale
La malattia di Parkinson è solitamente pensata come un disturbo cerebrale che causa tremori, rigidità e rallentamento dei movimenti. Tuttavia questo studio suggerisce che indizi importanti della malattia potrebbero nascondersi in un luogo inaspettato: le nostre feci. Analizzando con cura le piccole molecole e i microrganismi presenti nelle feci di persone con Parkinson e di volontari sani, i ricercatori mostrano che l’ecosistema intestinale è alterato nella malattia di Parkinson—e che questa alterazione potrebbe essere trasformata in un test non invasivo per aiutare a diagnosticare la condizione con maggiore precisione.
Uno sguardo ravvicinato all’impronta chimica intestinale
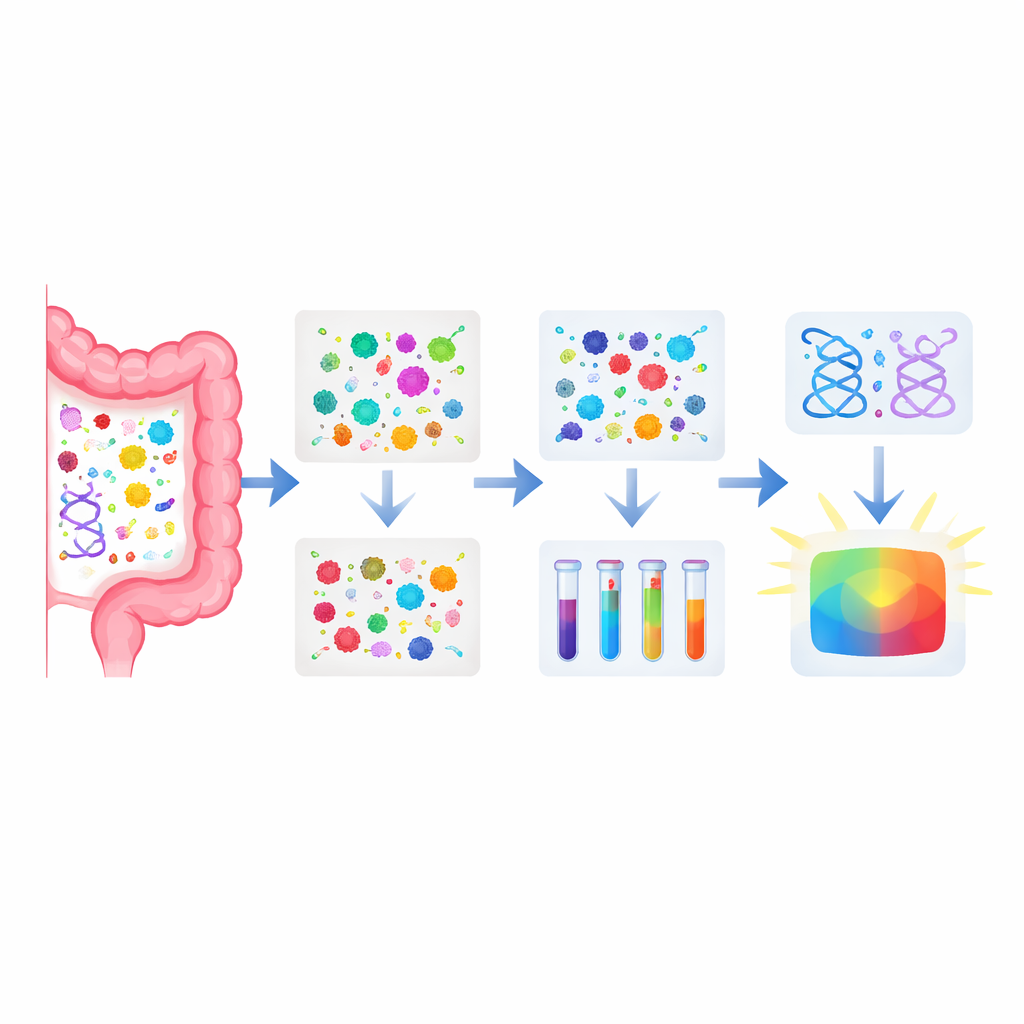
Il team ha raccolto campioni di feci da oltre 130 persone con malattia di Parkinson e più di 110 adulti sani in Cina. Utilizzando una tecnica di laboratorio sensibile che misura le piccole molecole, hanno costruito un dettagliato “impronta chimica” di ciascun campione. Hanno identificato 33 molecole fecali che differivano nettamente tra i due gruppi. La maggior parte di queste era ridotta nelle persone con Parkinson e apparteneva a famiglie coinvolte nella degradazione e nell’utilizzo degli amminoacidi (i mattoni delle proteine), degli zuccheri, dei grassi e di composti legati all’energia. Un elemento di rilievo è stato l’acido acetico, un acido grasso a catena corta prodotto dai batteri intestinali, che risultava significativamente ridotto nei pazienti con Parkinson.
Collegamenti tra chimica intestinale e sintomi quotidiani
Le molecole alterate non erano solo misure astratte; alcune erano strettamente correlate alla gravità della malattia. Livelli più elevati di un acido grasso chiamato acido pentadecanoico erano associati a punteggi peggiori nei test motori e a deficit cognitivi di memoria e pensiero nelle scale standard per il Parkinson, anche dopo aver corretto per età, sesso e stile di vita. Altre molecole legate agli amminoacidi, come triptofano e metionina, tendevano a essere più basse nei pazienti con problemi motori quotidiani più gravi. Queste connessioni suggeriscono che ciò che accade nell’intestino può rispecchiarsi nel cervello e nel corpo, influenzando potenzialmente sia i sintomi motori sia quelli non motori.
Costruire un test per il Parkinson basato sulle feci
Delle 33 molecole alterate, i ricercatori hanno utilizzato metodi di apprendimento automatico per selezionarne un sottoinsieme che funzionasse meglio insieme per la diagnosi. Sono giunti a un pannello di 12 metaboliti fecali, molti dei quali legati ai cicli energetici e al metabolismo degli amminoacidi. Questo pannello di 12 molecole riusciva a distinguere i pazienti con Parkinson dalle persone sane con buona accuratezza in un gruppo di addestramento, e ha funzionato in modo simile in un gruppo di test separato. Poiché la raccolta delle feci è non invasiva e relativamente semplice, un pannello del genere potrebbe un giorno integrare l’esame clinico, riducendo le diagnosi errate e permettendo di rilevare la malattia più precocemente.
Quando microbi e molecole raccontano la stessa storia
Lo studio è andato oltre combinando questi dati chimici con un precedente sequenziamento approfondito del DNA dei microbi intestinali su un sottogruppo degli stessi partecipanti. Abbinando i geni microbici ai metaboliti fecali, il team ha scoperto oltre 200 collegamenti tra funzioni batteriche specifiche e particolari molecole. Molte di queste connessioni convergevano sul metabolismo degli amminoacidi, in particolare su vie che coinvolgono glicina, serina, treonina, fenilalanina, tirosina e triptofano. Nelle persone con Parkinson, i geni che normalmente aiutano a processare questi amminoacidi erano spesso ridotti, e anche i metaboliti correlati risultavano più bassi, mentre alcune specie batteriche legate a queste vie erano più abbondanti, segnalando uno spostamento disturbato ma coordinato nell’ecosistema intestinale.
Combinare i segnali per una rilevazione più precisa
Elemento cruciale, gli autori hanno testato se unendo informazioni microbiche e chimiche si potesse migliorare la diagnosi. Hanno fuso il loro pannello di 12 molecole con un precedente “indice della malattia di Parkinson” basato su 25 geni microbici. Nel gruppo con entrambi i tipi di dati, il modello combinato ha distinto i pazienti con Parkinson dai controlli sani con precisione molto elevata, superando sia i soli microbi intestinali sia i soli metaboliti. Questo supporta l’idea che le intuizioni più potenti derivano dal considerare l’intestino come un ecosistema completo—microbi, loro geni e le molecole che producono—invece di studiare ogni livello in isolamento.
Cosa significa per i pazienti e per il futuro
Per il lettore non specialista, il messaggio principale è che la malattia di Parkinson lascia un’impronta chiara nell’intestino, alterando sia la composizione microbica sia le piccole molecole che questi producono, in particolare quelle legate agli amminoacidi e all’uso di energia. Pur non potendo questo studio dimostrare che questi cambiamenti intestinali causino il Parkinson, esso fornisce forti evidenze che essi sono strettamente intrecciati con la malattia e i suoi sintomi. Se confermati e perfezionati in gruppi più ampi e diversificati, i marcatori combinati basati sull’intestino potrebbero offrire ai medici un semplice test fecale per supportare la diagnosi e forse monitorare la progressione della malattia. A lungo termine, comprendere questa connessione gut–brain potrebbe anche aprire la strada a nuovi trattamenti che mirano a ripristinare un ecosistema intestinale più sano.
Citazione: Qian, Y., Xu, S., He, X. et al. Gut ecosystem dysfunction in parkinson’s disease: deciphering faecal metabolome-metagenome links for novel diagnostic panels. npj Parkinsons Dis. 12, 91 (2026). https://doi.org/10.1038/s41531-026-01299-7
Parole chiave: Malattia di Parkinson, microbioma intestinale, metabolomica fecale, metabolismo degli amminoacidi, biomarcatori non invasivi