Clear Sky Science · it
Valutazione comparativa completa degli strumenti di binning metagenomico svela fattori chiave per migliorare il recupero dei genomi
Perché i piccoli vicini del tuo intestino meritano uno sguardo più attento
I microbi che vivono nei nostri intestini, nei suoli e negli oceani modellano silenziosamente la nostra salute, i sistemi alimentari e il clima. Tuttavia la maggior parte di essi non può essere coltivata in laboratorio, quindi gli scienziati si affidano al sequenziamento del DNA per osservare questi mondi nascosti. Questo studio pone una domanda apparentemente semplice ma dalle grandi conseguenze: quando convertiamo dati grezzi di DNA in genomi provvisori di microbi, quali strumenti computazionali funzionano meglio e in quali condizioni hanno successo o falliscono?
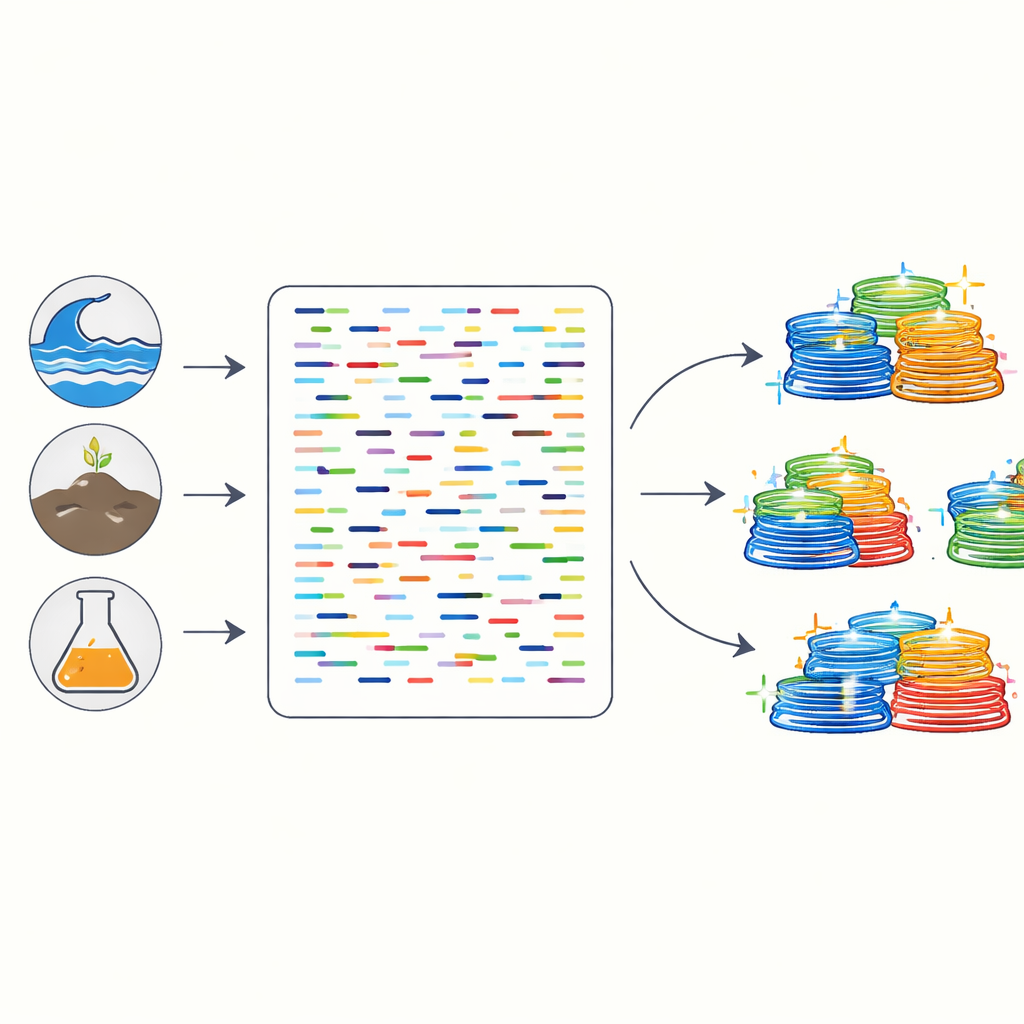
Ricomporre i genomi da un puzzle genetico
I moderni sequenziatori trasformano una manciata di suolo o un campione fecale in miliardi di brevi frammenti di DNA mescolati provenienti da centinaia o migliaia di specie. I ricercatori prima assemblano questi pezzi in tratti più lunghi chiamati contig, poi utilizzano strumenti di “binning” per raggruppare i contig che probabilmente provengono dallo stesso microbo, formando ciò che è noto come genomi assemblati da metagenomi. Esistono molti programmi di binning diversi, basati su idee matematiche e di machine learning distinte. Gli autori hanno confrontato in modo sistematico nove strumenti popolari, più tre metodi che raffinano e combinano i loro risultati, utilizzando una miscela di comunità simulate e dati reali di DNA provenienti da campioni umani intestinali, oceanici e del suolo.
Come la complessità della comunità e la profondità di sequenziamento influenzano i risultati
Il gruppo ha scoperto che due caratteristiche fondamentali di un dataset influenzano fortemente il successo del binning: il numero di specie presenti e la profondità di sequenziamento del campione. Quando le comunità contenevano solo poche decine di specie, la maggior parte degli strumenti si comportava ragionevolmente bene. Ma man mano che il numero di specie saliva a centinaia o migliaia—livelli più vicini ai veri microbiomi intestinali o del suolo—molti metodi più vecchi vacillavano, non riuscendo a recuperare genomi completi. Maggiore sequenziamento aiutava sempre, specialmente oltre circa 7 gigabase per campione, ma non poteva salvare completamente gli strumenti non progettati per gestire elevata complessità. Al contrario, una nuova generazione di programmi di binning basati su reti neurali manteneva alte prestazioni in queste comunità affollate, in particolare quando erano disponibili abbondanti dati di sequenziamento.
Algoritmi più intelligenti e il problema nascosto dei chimeri
Una scoperta rilevante è che strumenti basati su reti neurali come COMEBin, SemiBin2 e VAMB (soprattutto quando sfruttano informazioni provenienti da più campioni contemporaneamente) hanno costantemente recuperato più genomi di alta qualità rispetto agli approcci tradizionali. Tuttavia, gli autori hanno anche guardato oltre i conteggi semplici e hanno valutato quanti genomi ricostruiti fossero “chimerici”—ibridi artificiali costruiti per errore da pezzi di specie diverse. Usando un controllo specializzato per questo tipo di contaminazione, hanno mostrato che i tassi di chimerismo variavano ampiamente tra gli strumenti. Alcuni metodi che sembravano efficaci dalle misure standard in realtà producevano molti genomi ibridi, mentre altri, inclusi certi strumenti basati su reti neurali, mantenevano livelli di chimerismo relativamente bassi. Ciò evidenzia che i controlli di qualità devono andare oltre la semplice completezza e i tassi di errore.
Perché molti campioni e letture accoppiate contano
Lo studio ha affrontato anche due scelte pratiche per i progetti sul microbioma: quanti campioni raggruppare quando si esegue il binning “multi-campione” e se usare il sequenziamento single-end più economico o le più informative letture paired-end. Per gli strumenti che possono apprendere dai pattern di copertura attraverso più campioni, le prestazioni miglioravano con l’aumentare del numero di campioni—ma solo fino a circa 20. Usarne meno dava poco vantaggio, e usarne molti di più poteva persino peggiorare i risultati o sprecare risorse computazionali. Separatamente, gli autori hanno mostrato che i dataset sequenziati con letture single-end producevano costantemente assemblaggi peggiori e molti meno genomi di qualità rispetto ai dati paired-end, anche quando la quantità totale di DNA sequenziata era simile, perché l’assenza dell’informazione di accoppiamento porta a contig più frammentati.
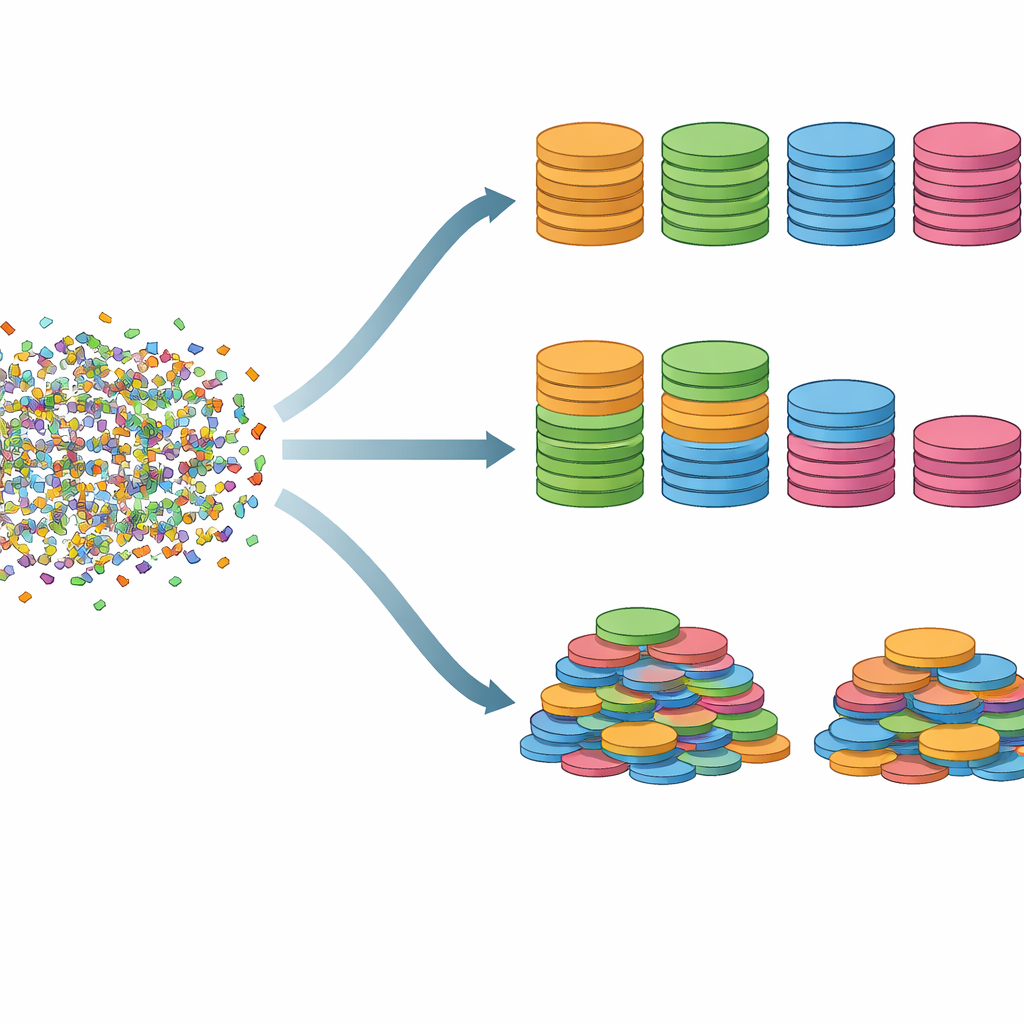
Combinare strumenti per costruire cataloghi microbici migliori
Poiché diversi programmi tendono a eccellere su microbi differenti, gli autori hanno testato se un approccio ensemble potesse fare meglio di qualsiasi singolo strumento. Integrando i bin genomici di tre metodi basati su reti neurali tra i migliori e poi raffinando il risultato con un attento post-processing, hanno recuperato oltre il 30% in più di genomi di alta qualità rispetto alle pipeline più vecchie e ampiamente usate che combinano strumenti di binning tradizionali. Questi genomi aggiuntivi non erano solo ripetizioni: hanno ampliato l’albero della vita rappresentato nei dati e includevano regioni difficili da catturare come i geni 16S dell'RNA ribosomiale, importanti per nominare e collocare i microbi nell’albero filogenetico microbico.
Cosa significa questo per i futuri studi sul microbioma
Per i non specialisti, il messaggio principale è semplice: il modo in cui convertiamo le letture di DNA grezze in genomi provvisori influisce profondamente su ciò che riteniamo viva in un dato ambiente. Questo lavoro di benchmarking mostra che un sequenziamento più profondo, letture paired-end, l’uso accurato di circa 20 campioni correlati e strumenti di binning moderni basati su reti neurali—idealmente combinati in una strategia ensemble—possono aumentare notevolmente sia il numero sia l’affidabilità dei genomi microbici recuperati. Di conseguenza, ciò significa mappe più accurate delle comunità invisibili che influenzano i nostri corpi e il pianeta, e una base più solida per future scoperte in medicina, ecologia e biotecnologia.
Citazione: Kim, J., Kim, N., Cha, J.H. et al. Comprehensive benchmarking of metagenomic binning tools reveals key factors for improved genome recovery. Nat Commun 17, 3467 (2026). https://doi.org/10.1038/s41467-026-71521-w
Parole chiave: metagenomica, microbioma, ricostruzione del genoma, strumenti di machine learning, studio di benchmarking