Clear Sky Science · fr
Assemblage du génome au niveau des chromosomes, quasi télomère-à-télomère, de Rhodiola yunnanensis (Crassulaceae)
La médecine de montagne rencontre l’ADN moderne
Hautes dans les montagnes du sud‑ouest de la Chine pousse Rhodiola yunnanensis, une plante succulente robuste prisée en médecine traditionnelle pour des composés censés aider l’organisme à supporter le stress et les environnements rudes. Cette étude fournit le plan génétique le plus détaillé à ce jour pour cette espèce peu connue, offrant aux scientifiques une référence puissante pour explorer comment elle survit à l’air raréfié et au froid, et comment elle produit ses ingrédients chimiques recherchés. 
Une plante résistante dans un habitat hostile
La plupart des espèces du groupe Rhodiola vivent sur des pentes balayées par les vents en haute altitude où les températures varient fortement, le rayonnement solaire est intense et l’oxygène se fait rare. Leurs tiges souterraines épaisses et leurs feuilles charnues stockent l’eau et l’énergie, leur permettant de traverser ces extrêmes. Ces mêmes tissus sont riches en molécules spécifiques, notamment la salidroside et la rosavin, qui ont attiré l’attention tant des traditions herboristes que des laboratoires modernes. Pourtant, les différentes espèces de Rhodiola produisent des quantités très variables de ces composés, et jusqu’à présent, les scientifiques manquaient d’une carte génétique complète pour comprendre pourquoi et pour retracer comment ces plantes se sont adaptées à la vie au‑dessus des nuages.
Construire un plan génétique complet
Pour créer une carte quasi complète du génome de Rhodiola yunnanensis, les chercheurs ont d’abord collecté des feuilles d’une plante sauvage poussant à environ 3 400 mètres dans les montagnes Hengduan du Sichuan, en Chine. Ils ont extrait de l’ADN de haute qualité et l’ont séquencé en utilisant plusieurs technologies. De longs fragments d’ADN ont été lus par un appareil portable capable de lire de très longues séquences en une seule fois, tandis qu’une autre plateforme a produit un grand nombre de lectures plus courtes et très précises. Une troisième approche, appelée Hi‑C, a capturé la manière dont les morceaux d’ADN se positionnent les uns par rapport aux autres à l’intérieur du noyau cellulaire, fournissant un guide pour assembler les fragments en chromosomes complets.
Des fragments aux chromosomes
À l’aide de programmes informatiques spécialisés, l’équipe a d’abord assemblé les lectures longues en séquences continues d’ADN et a éliminé les copies dupliquées qui apparaissent parce que chaque plante porte deux versions de son génome. Ils ont ensuite poli ces séquences avec les lectures courtes plus précises pour corriger les erreurs. Enfin, ils ont utilisé les données de contacts Hi‑C pour organiser et orienter les morceaux en 11 longues structures correspondant aux chromosomes. Le résultat est un génome d’environ 643 millions de « lettres », dont presque la totalité est ancrée dans des unités de taille chromosomique. Dans de nombreux cas, chaque chromosome s’étend presque sans interruption d’une extrémité à l’autre, et des éléments typiques comme les télomères aux extrémités et les centromères au centre peuvent être clairement repérés. 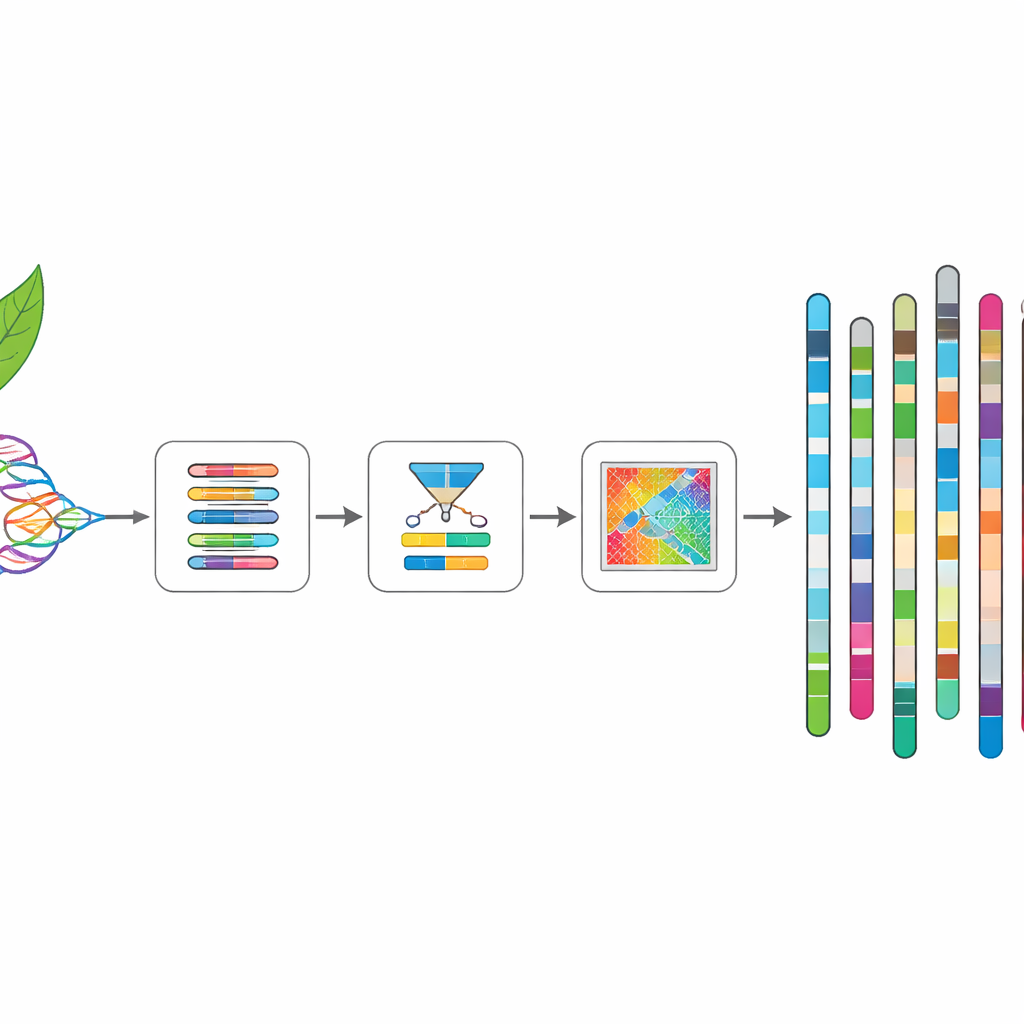
Ce que révèle le génome
Une fois le génome assemblé, les chercheurs se sont attelés à identifier ses parties fonctionnelles. Ils ont constaté qu’environ les deux tiers de l’ADN sont constitués de séquences répétées, en particulier d’un type courant connu sous le nom d’éléments à répétition terminale longue. Sur ce fond répété, ils ont prédit 36 495 gènes codant pour des protéines, la grande majorité étant étayée par des molécules d’ARN réellement observées dans les feuilles, les tiges et les fruits. La plupart de ces gènes ont pu être rattachés à des familles et des fonctions connues chez d’autres plantes, y compris plus de 1 600 facteurs de transcription — des commutateurs clés qui activent ou désactivent d’autres gènes. L’équipe a également répertorié des milliers de gènes d’ARN non codants, qui participent à la traduction et à la régulation de l’information génétique.
Une nouvelle base pour des découvertes futures
Des tests approfondis montrent que ce génome est à la fois très complet et précis, répondant aux références modernes de qualité. Pour les non‑spécialistes, l’essentiel est que nous disposons désormais d’une carte génétique fiable, quasi bout‑à‑bout, de Rhodiola yunnanensis. Cette ressource aidera les chercheurs à découvrir comment cette plante alpine fait face au froid, à l’intensité lumineuse et au faible apport en oxygène, et comment elle synthétise ses composés médicinaux précieux au niveau moléculaire. À son tour, ces connaissances pourraient éclairer la conservation de ces plantes de montagne menacées, guider la sélection pour une culture durable et soutenir les efforts visant à recréer les ingrédients utiles de Rhodiola dans des microbes ou des cultures, réduisant ainsi la pression sur les populations sauvages.
Citation: Wang, M., Du, P., Tong, C. et al. A near telomere-to-telomere chromosome-level genome assembly of Rhodiola yunnanensis (Crassulaceae). Sci Data 13, 707 (2026). https://doi.org/10.1038/s41597-026-07044-2
Mots-clés: Rhodiola yunnanensis, plantes médicinales, assemblage du génome, adaptation en haute altitude, métabolites spécialisés des plantes