Clear Sky Science · de
Eine nahezu telomeren‑zu‑telomeren Chromosomen‑Ebene Genomassemblierung von Rhodiola yunnanensis (Crassulaceae)
Bergmedizin trifft moderne DNA
Hoch in den Bergen Südwestchinas wächst Rhodiola yunnanensis, eine robuste Sukkulente, die in der traditionellen Medizin wegen Verbindungen geschätzt wird, denen man zutraut, dem Körper bei Stress und rauer Umgebung zu helfen. Diese Studie liefert den bislang detailliertesten genetischen Bauplan für diese wenig bekannte Art und bietet Wissenschaftlern eine leistungsfähige Referenz, um zu erforschen, wie sie dünne Luft und Kälte überlebt und wie sie ihre begehrten chemischen Inhaltsstoffe herstellt. 
Eine zähe Pflanze in rauer Heimat
Die meisten Arten der Gattung Rhodiola leben an windgepeitschten, hochgelegenen Hängen, wo die Temperaturen stark schwanken, das Sonnenlicht intensiv ist und nur wenig Sauerstoff vorhanden ist. Ihre dicken unterirdischen Rhizome und fleischigen Blätter speichern Wasser und Energie und helfen ihnen, diese Extreme zu überstehen. Diese Gewebe sind außerdem reich an speziellen Molekülen, darunter Salidrosid und Rosavin, die sowohl traditionelle Heilkenntnisse als auch moderne Labore interessieren. Dennoch produzieren verschiedene Rhodiola‑Arten sehr unterschiedliche Mengen dieser Verbindungen, und bislang fehlte ein vollständiger genetischer Plan, um zu verstehen, warum das so ist und wie diese Pflanzen sich an das Leben über den Wolken angepasst haben.
Erstellung eines nahezu vollständigen genetischen Bauplans
Um eine nahezu vollständige Karte des Genoms von Rhodiola yunnanensis zu erstellen, sammelten die Forschenden zunächst Blätter von einer Wildpflanze, die in etwa 3.400 Metern Höhe in den Hengduan‑Bergen der Provinz Sichuan, China, wächst. Sie isolierten hochwertige DNA und sequenzierten sie mit mehreren Technologien. Lange DNA‑Fragmente wurden mit einem tragbaren Gerät erfasst, das sehr lange Abschnitte in einem Stück lesen kann, während eine andere Plattform eine sehr große Anzahl kürzerer, sehr genauer Reads lieferte. Ein dritter Ansatz, genannt Hi‑C, erfasste, wie DNA‑Stücke im Zellkern nebeneinander liegen, und lieferte so eine Anleitung zum Zusammensetzen der Fragmente zu vollständigen Chromosomen.
Von Fragmenten zu Chromosomen
Mithilfe spezialisierter Computerprogramme setzte das Team zunächst die langen Reads zu kontinuierlichen DNA‑Abschnitten zusammen und entfernte doppelte Kopien, die dadurch entstehen, dass jede Pflanze zwei Versionen ihres Genoms trägt. Anschließend polierten sie diese Abschnitte mit den genaueren kurzen Reads, um Fehler zu korrigieren. Schließlich nutzten sie die Hi‑C‑Kontaktinformationen, um die Stücke zu 11 langen Strukturen anzuordnen und zu orientieren, die den Chromosomen entsprechen. Das Ergebnis ist ein Genom von etwa 643 Millionen „Buchstaben“, wobei nahezu der gesamte Inhalt in chromosomengroße Einheiten verankert ist. In vielen Fällen verläuft jedes Chromosom nahezu ununterbrochen von einem Ende zum anderen, und typische Merkmale wie Telomere an den Spitzen und Centromere in der Mitte sind deutlich erkennbar. 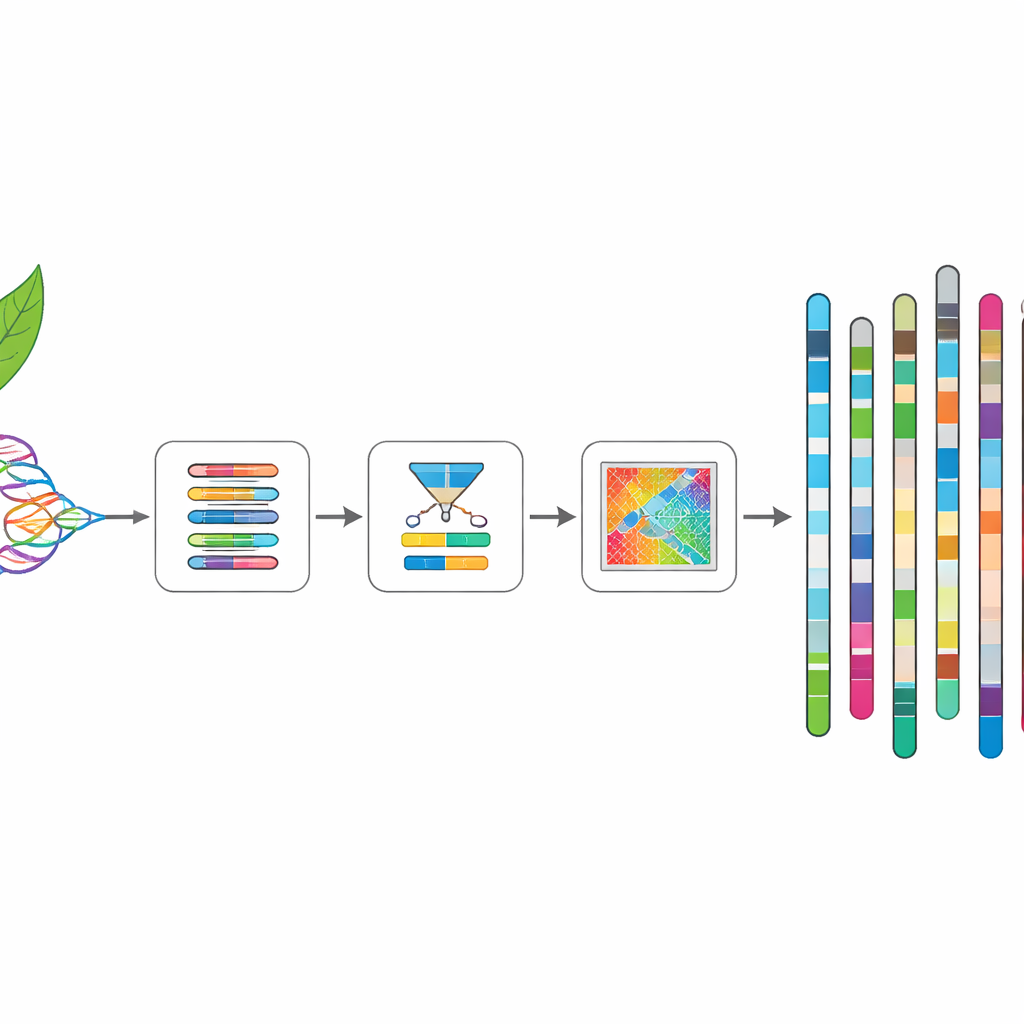
Was das Genom im Inneren offenbart
Sobald das Genom assembliert war, machten sich die Forschenden daran, seine funktionalen Teile zu identifizieren. Sie fanden heraus, dass etwa zwei Drittel der DNA aus wiederholten Sequenzen bestehen, insbesondere aus einem häufigen Typ, den man als Long‑Terminal‑Repeat‑Elemente (LTRs) kennt. Auf diesem wiederholten Hintergrund sagten sie 36.495 proteinkodierende Gene voraus, wobei die große Mehrheit durch tatsächlich in Blättern, Stängeln und Früchten nachgewiesene RNA‑Moleküle gestützt wird. Die meisten dieser Gene konnten bekannten Familien und Funktionen aus anderen Pflanzen zugeordnet werden, darunter mehr als 1.600 Transkriptionsfaktoren – zentrale Schalter, die andere Gene ein‑ oder ausschalten. Das Team katalogisierte außerdem Tausende nicht‑kodierender RNA‑Gene, die bei der Übersetzung und Regulation genetischer Information helfen.
Eine neue Grundlage für zukünftige Entdeckungen
Umfangreiche Tests zeigen, dass dieses Genom sowohl sehr vollständig als auch genau ist und moderne Qualitätsmaßstäbe erfüllt. Für Nicht‑Spezialisten bedeutet das: Wir haben jetzt eine verlässliche, nahezu durchgehende genetische Karte von Rhodiola yunnanensis. Diese Ressource wird Forschenden dabei helfen, zu entschlüsseln, wie diese alpine Pflanze mit Kälte, intensiver Beleuchtung und Sauerstoffarmut umgeht und wie sie ihre wertvollen medizinischen Verbindungen auf molekularer Ebene synthetisiert. Dieses Wissen kann wiederum den Schutz dieser bedrohten Bergpflanzen informieren, Zuchtprogramme für nachhaltigen Anbau leiten und Bemühungen unterstützen, nützliche Rhodiola‑Inhaltsstoffe in Mikroben oder Kulturpflanzen nachzubilden, wodurch der Druck auf wildwachsende Bestände verringert werden könnte.
Zitation: Wang, M., Du, P., Tong, C. et al. A near telomere-to-telomere chromosome-level genome assembly of Rhodiola yunnanensis (Crassulaceae). Sci Data 13, 707 (2026). https://doi.org/10.1038/s41597-026-07044-2
Schlüsselwörter: Rhodiola yunnanensis, Heilpflanzen, Genomassemblierung, Anpassung an große Höhen, Pflanzliche Sekundärmetaboliten