Clear Sky Science · fr
Assemblage du génome au niveau des chromosomes du porc indigène sud-africain Kolbroek, Sus scrofa domesticus
Un petit porc robuste au grand récit génétique
Le porc Kolbroek ne ressemble peut-être pas à un animal high-tech, mais ce robuste porc d’élevage sud-africain porte une boîte à outils génétique qui aide les petits exploitants à faire face à la chaleur, aux parasites et aux aliments de faible qualité. Jusqu’à présent, son ADN n’avait jamais été cartographié en détail. Cette étude livre le premier génome complet au niveau chromosomique du Kolbroek, créant un plan qui peut aider à conserver la race, révéler ses traits utiles et orienter une production de porc plus durable dans les régions confrontées à des conditions environnementales difficiles.
Pourquoi ce porc local est important
L’Afrique du Sud importe une grande partie de son porc, et les grandes exploitations commerciales tendent à utiliser des races exotiques qui grandissent vite et donnent de grandes portées. En revanche, les petits éleveurs s’appuient souvent sur des porcs indigènes comme le Kolbroek. Ces porcs sont plus petits et moins prolifiques, mais ils sont bien adaptés à la chaleur locale, aux maladies et aux aliments bon marché, y compris les plantes fibreuses et les céréales riches en tanins comme le sorgho rouge. Les enquêtes génétiques antérieures ont montré que les porcs indigènes d’Afrique australe possèdent une riche diversité génétique, mais ils sont aussi menacés : les croisements avec des animaux commerciaux peuvent diluer leurs traits uniques, et l’absence de programmes d’élevage structurés fait de la consanguinité un problème croissant.
Une carte génétique pour protéger une race patrimoniale
Pour sauvegarder le Kolbroek et mieux exploiter ses atouts, les éleveurs ont besoin d’un génome de référence de haute qualité — une liste complète et ordonnée de son ADN pouvant être comparée à d’autres porcs. Les génomes porcins commerciaux existants, comme celui de la race Duroc, ne reflètent pas fidèlement les animaux indigènes sud-africains, rendant les tests génétiques moins fiables. Le nouveau génome du Kolbroek change la donne. Il fournit une vue détaillée des chromosomes de l’animal, permettant aux chercheurs d’identifier les régions d’ADN qui déterminent des traits importants comme la résistance aux maladies, la tolérance à la chaleur et la capacité à se développer avec des fourrages grossiers. Il jette aussi les bases pour concevoir des tests génétiques adaptés aux porcs africains, plutôt que de s’appuyer sur des outils développés à partir de races européennes et asiatiques.
Comment le génome a été construit
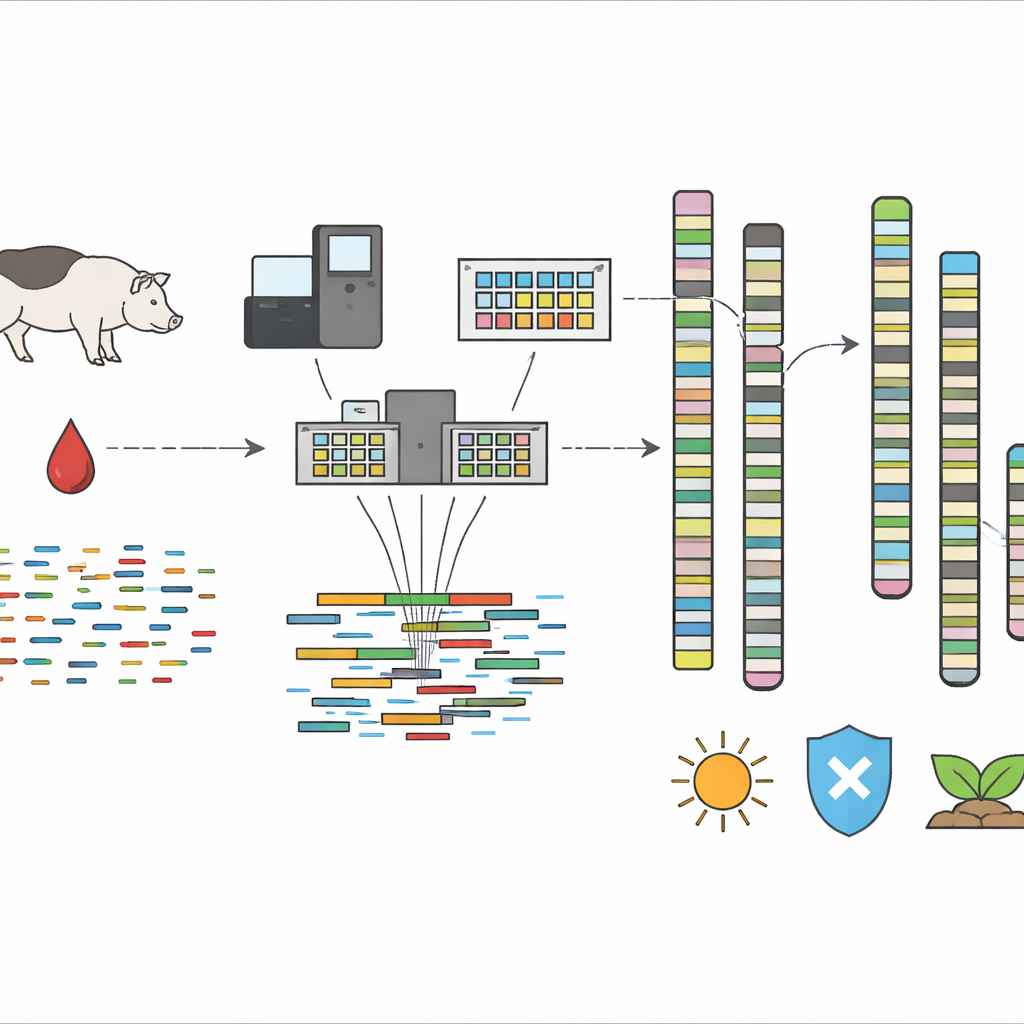
Les chercheurs ont commencé avec une seule truie Kolbroek pure provenant d’un élevage en Afrique du Sud. À partir d’un échantillon sanguin prélevé avec soin, ils ont extrait de très longs brins d’ADN et les ont séquencés avec deux technologies avancées. L’une, connue sous le nom de séquençage HiFi, lit de longues portions d’ADN avec une grande précision. L’autre, Omni-C, capture la manière dont l’ADN se replie à l’intérieur de la cellule, aidant à relier des fragments distants pour reconstituer des chromosomes entiers. Un pipeline d’assemblage spécialisé, développé par le Vertebrate Genome Project et exécuté sur la plateforme de calcul Galaxy Europe, a rabouté des milliards de fragments d’ADN, éliminé des contaminations comme des séquences mitochondriales errantes et arrangé les pièces en 19 échafaudages à l’échelle des chromosomes plus des fragments additionnels.
Ce que révèle l’ADN
Le génome final s’étend sur environ 2,6 milliards de lettres d’ADN, d’une taille et d’une structure semblables à celles d’autres porcs domestiques. Les contrôles de qualité ont montré que plus de 95 % des gènes attendus sont présents et correctement assemblés. L’équipe a constaté que les éléments répétés — des segments d’ADN qui apparaissent de nombreuses fois dans le génome — constituent environ 38 % de l’ADN du Kolbroek, un schéma qui correspond à celui d’autres mammifères. En utilisant un outil de prédiction de gènes basé sur l’apprentissage automatique, ils ont identifié 22 025 gènes codant pour des protéines. Lors de la comparaison du génome du Kolbroek avec les références porcines standard, ils ont observé que ses chromosomes s’alignent globalement, mais présentent aussi des différences structurelles et des variantes génétiques uniques qui sous-tendent probablement ses adaptations particulières aux environnements africains.
De la carte d’ADN à de meilleurs porcs et de meilleures exploitations
En transformant l’ADN du Kolbroek en un génome public et de haute qualité, cette étude fournit aux éleveurs et aux scientifiques un nouvel outil puissant. Cet assemblage peut servir à concevoir des tests génétiques locaux abordables, à rechercher des variantes liées à la fertilité, à la croissance, à la qualité de la viande et à la résilience, et à inclure les porcs sud-africains dans les efforts mondiaux de « pangenome » qui visent à capturer la diversité complète de l’espèce. Concrètement, cela signifie que les futurs programmes d’élevage pourront viser à améliorer la productivité sans perdre la robustesse et l’adaptation environnementale du Kolbroek — contribuant à préserver un patrimoine génétique unique et à rendre la production porcine plus durable pour les petits et grands élevages.»}irst.
Citation: Smith, R.M., Molotsi, A.H., Nesengani, L.T. et al. A chromosome-level genome assembly of the South African indigenous, Kolbroek pig, Sus scrofa domesticus. Sci Data 13, 635 (2026). https://doi.org/10.1038/s41597-026-07002-y
Mots-clés: Porc Kolbroek, assemblage du génome, bétail indigène, élevage porcin, Afrique du Sud