Clear Sky Science · fr
Examiner les archives zooarchéologiques à travers le temps et l’espace pour l’ADN des agents pathogènes anciens
Pourquoi les vieux os d’animaux comptent pour notre santé
La plupart des maladies infectieuses dangereuses actuelles proviennent d’animaux ou continuent de circuler entre animaux et humains. Pourtant, notre compréhension de la façon dont ces maladies sont apparues dans le passé lointain reste étonnamment floue. Cette étude se tourne vers une archive inhabituelle — des milliers d’années d’os et de dents d’animaux — pour déterminer quels microbes infectaient le bétail et les animaux sauvages anciens, quelle était leur répartition et ce que cela peut révéler sur les racines profondes des maladies zoonotiques modernes qui sautent entre animaux et humains.
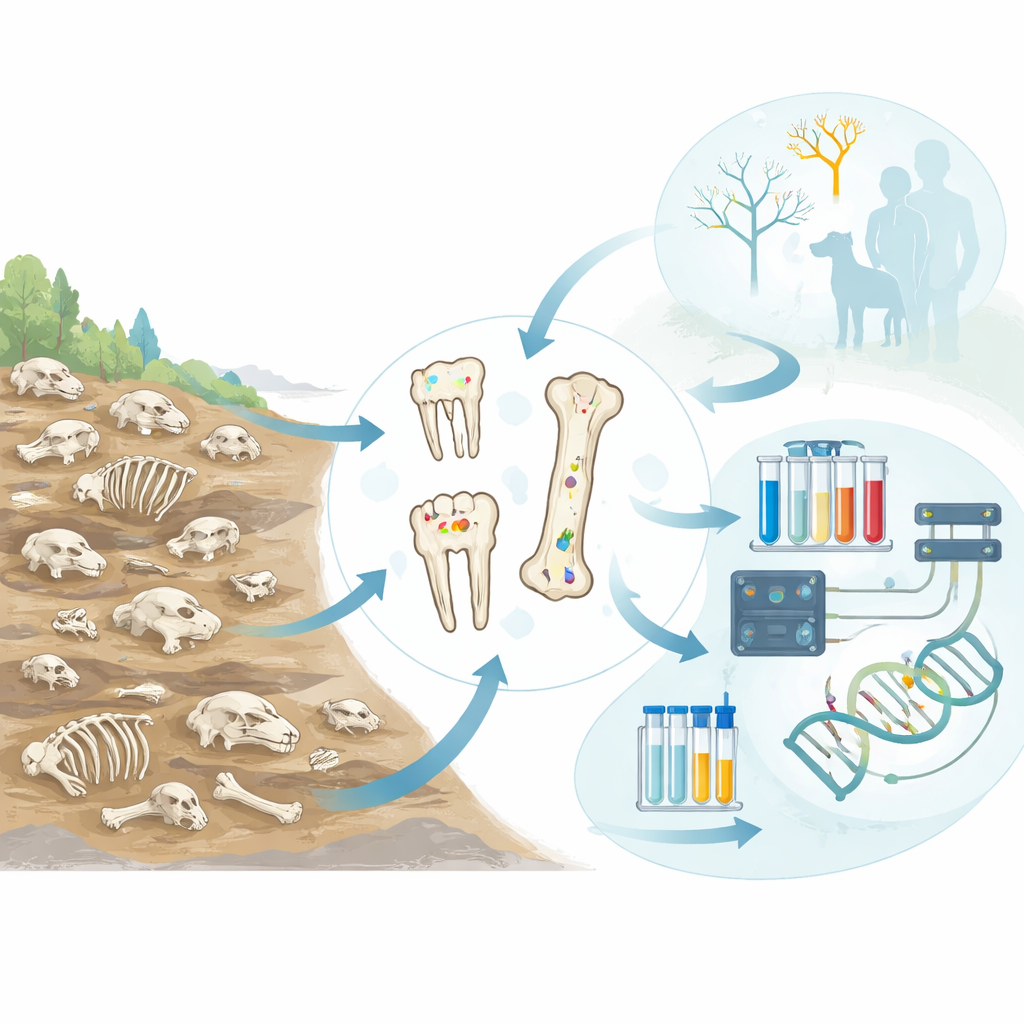
À la recherche d’indices dans les os enfouis
Les chercheurs ont rassemblé 346 os et dents provenant d’au moins 328 animaux individuels, mis au jour sur 34 sites archéologiques s’étendant de l’Europe à l’Asie centrale et couvrant environ les 5800 dernières années, du Néolithique au Moyen Âge. La plupart des spécimens provenaient d’animaux domestiqués tels que bovins, ovins, porcs, caprins et chiens, mais quelques espèces sauvages ont été incluses lorsqu’elles jouaient un rôle majeur dans les économies passées. Plutôt que d’échantillonner au hasard, l’équipe s’est concentrée sur des os montrant des signes visibles de maladie — comme une nouvelle formation osseuse anormale, des piqûres ou des lésions — ainsi que sur des dents, qui peuvent parfois conserver des traces d’infections transmises par le sang.
Lire les empreintes ADN cachées
Dans des laboratoires propres spécialisés, l’équipe a foré de petites quantités de poudre dans chaque os ou dent et en a extrait l’ADN restant. Elle a ensuite utilisé le séquençage à haut débit pour capturer des millions de courts fragments d’ADN par spécimen. L’ADN humain a été filtré, et les fragments génétiques restants ont été comparés à une vaste base de référence de bactéries et autres microbes. Un ensemble strict de critères — comme des motifs caractéristiques de dégradation de l’ADN ancien et une couverture large du génome d’un microbe — a aidé à distinguer les infections anciennes authentiques de la contamination moderne.
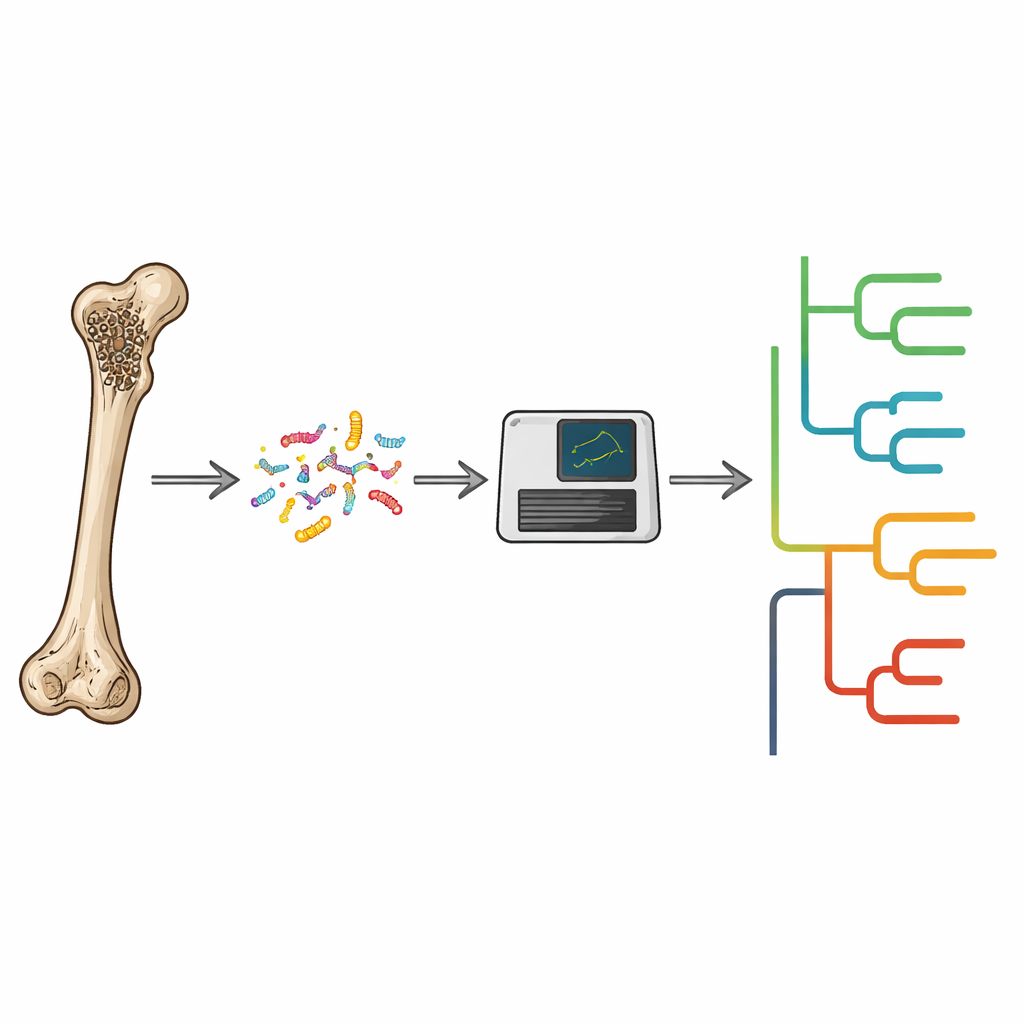
Microbes anciens issus du bétail et de leurs voisins
Sur les 346 spécimens, 55 ont fourni des preuves génétiques solides pour au moins une espèce bactérienne pathogène ou opportuniste, aboutissant à 116 « détections » distinctes de pathogènes représentant 29 types de microbes. Ceux-ci allaient de bactéries bien connues pour causer des maladies, comme Salmonella enterica, à des microbes qui vivent normalement sans danger dans la bouche ou l’intestin mais peuvent provoquer des maladies dans certaines conditions. De façon importante, les os présentant des lésions visibles étaient bien plus susceptibles de contenir de l’ADN de pathogène que des os apparemment sains, démontrant que l’inspection paléopathologique attentive est un moyen puissant de choisir des échantillons prometteurs. Le site de Tilla Bulak, dans l’Ouzbékistan actuel, se distingue : bien qu’il ait fourni moins d’un tiers des spécimens, il représentait plus de la moitié des détections de pathogènes réussies, ce qui suggère que les conditions d’inhumation locales et la pression pathologique passée influencent ce qui se conserve dans les archives.
Retracer des proches anciens de pathogènes modernes
Pour deux bactéries associées au bétail — Erysipelothrix rhusiopathiae, qui infecte les porcs, les bovins et parfois les humains, et Streptococcus lutetiensis, une cause de mammite chez les animaux laitiers — les chercheurs ont récupéré suffisamment d’ADN pour placer les souches anciennes sur des arbres évolutifs aux côtés de génomes modernes. Une dent de bovin d’environ 4000 ans provenant de Russie portait une souche d’E. rhusiopathiae qui se situe sur une branche profonde de l’arbre de l’espèce, regroupée avec, mais distincte de, la diversité moderne. De même, trois spécimens d’ovins et de caprins de l’âge du Bronze de Tilla Bulak ont livré des génomes de S. lutetiensis formant un groupe ancien serré positionné à la base des lignées actuelles. Ces positionnements soutiennent l’authenticité de l’ADN ancien et montrent que ces pathogènes étaient déjà répandus et génétiquement diversifiés dans les troupeaux préhistoriques bien avant d’être reconnus par la médecine vétérinaire moderne.
Une nouvelle fenêtre sur l’histoire profonde des maladies
En combinant la pathologie des os d’animaux, l’archéologie et l’ADN ancien, cette étude montre que le dossier zooarchéologique peut révéler bien plus que l’alimentation et la domestication : il peut aussi cartographier l’histoire ancienne des infections qui affectent encore aujourd’hui les humains et les animaux. Le travail confirme que les os visiblement malades sont des cibles particulièrement riches pour l’ADN de pathogènes et démontre comment même des génomes fragmentaires et de faible couverture peuvent être placés dans le paysage évolutif plus large. Ce faisant, il ouvre une voie vers une perspective « One Health » étendue sur des millénaires, où l’interaction à long terme entre les personnes, leurs animaux et leurs microbes partagés peut être tracée à travers le temps et l’espace.
Citation: W. Runge, A.K., Light-Maka, I., Massy, K. et al. Probing the zooarchaeological record across time and space for ancient pathogen DNA. Nat Commun 17, 3469 (2026). https://doi.org/10.1038/s41467-026-71543-4
Mots-clés: ADN ancien, zooarchéologie, maladies zoonotiques, pathogènes du bétail, One Health