Clear Sky Science · fr
Euglena gracilis comme plateforme de criblage à haut débit pour l’activité antibactérienne, la cytotoxicité et la perméabilité membranaire dans un test unique et économique
Pourquoi une minuscule cellule verte compte
Les infections bactériennes mortelles deviennent de plus en plus difficiles à traiter à mesure que davantage de germes contournent nos antibiotiques actuels. Pourtant, la découverte de nouveaux médicaments est lente, coûteuse et souvent frustrante. Cette étude présente un assistant étonnamment simple : Euglena gracilis, un micro-organisme commun des mares. En observant comment cette minuscule cellule verte change de couleur, les chercheurs ont mis au point un test en une étape capable de repérer rapidement des candidats antibiotiques prometteurs, d’éliminer ceux qui sont toxiques et de vérifier s’ils peuvent franchir plusieurs barrières biologiques — le tout dans le même essai abordable.
Un simple changement de couleur aux grandes implications
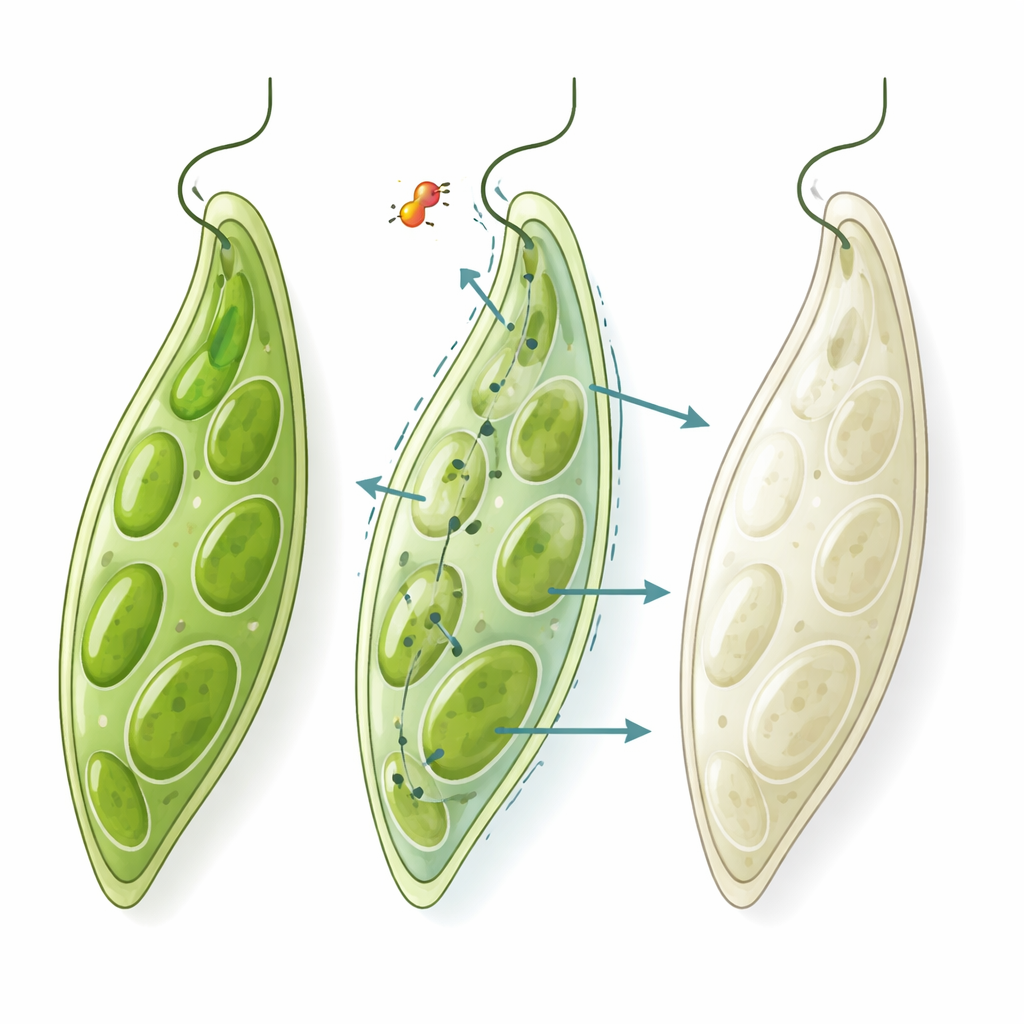
Euglena ressemble à une petite pantoufle verte au microscope. Sa couleur provient des chloroplastes, les mêmes structures de capture de lumière que l’on trouve dans les cellules végétales. Il y a longtemps, ces chloroplastes provenaient de bactéries et conservent encore certains traits bactériens. Cette particularité les rend vulnérables à plusieurs antibiotiques, qui peuvent endommager ou éliminer les chloroplastes et faire passer Euglena du vert au blanc — un processus appelé blanchiment. Dans le même temps, Euglena est un organisme alimentaire flexible : il peut subsister sur des nutriments dissous même lorsqu’il perd ses chloroplastes. Cela signifie que si un composé provoque le blanchiment d’Euglena mais que les cellules restent vivantes et continuent de se diviser, il cible probablement une fonction de type antibactérien sans être largement toxique pour des cellules complexes comme les nôtres.
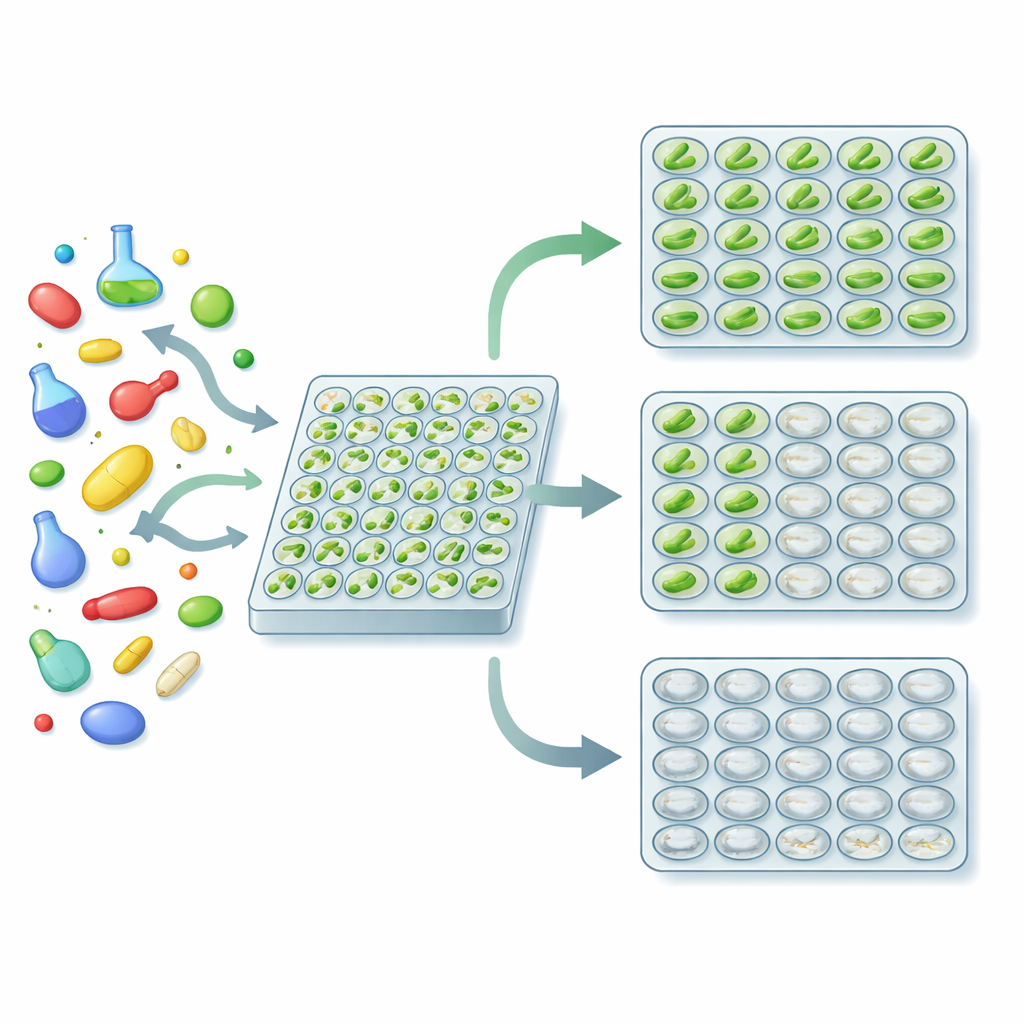
Trois résultats en un seul test simple
Les auteurs ont transformé cette biologie en un criblage pratique à haut débit. Ils ont cultivé Euglena dans des plaques standard de 96 puits, ajouté un composé test différent dans chaque puits et attendu quelques jours. À la fin, chaque puits tombait de façon fiable dans l’un des trois états visibles : vert (le composé n’a pas eu d’effet notable), blanc mais trouble (les cellules ont survécu mais perdu leurs chloroplastes, suggérant une activité antibactérienne), ou clair (les cellules ont été tuées, suggérant une toxicité générale). À l’aide d’un lecteur de plaques mesurant combien de lumière les puits absorbent à différentes longueurs d’onde, l’équipe a défini des seuils numériques permettant de distinguer automatiquement ces états. Un rapport particulier entre la lumière absorbée dans les régions rouge et verte du spectre signale le blanchiment, tandis que l’intensité globale du signal indique si la culture a poussé ou non.
Mettre le criblage à l’épreuve
Pour vérifier si cette approche fonctionnait au-delà de la théorie, les chercheurs ont d’abord soumis Euglena à une bibliothèque commerciale de 79 composés bien caractérisés. Leur système basé sur la couleur a séparé clairement les médicaments connus pour tuer les cellules de ceux qui interfèrent spécifiquement avec des processus de type bactérien. Huit composés ont déclenché le blanchiment sans anéantir les cultures. La plupart étaient des antibiotiques classiques qui bloquent la production de protéines ou d’ADN chez les bactéries, couvrant plusieurs familles chimiques distinctes. Fait important, tous les médicaments d’une même classe n’ont pas forcément provoqué le blanchiment d’Euglena, révélant que l’héritage bactérien du chloroplaste ne recoupe qu’en partie celui des bactéries modernes. Quelques composés ont produit des motifs inhabituels d’absorption de la lumière parce qu’ils étaient eux-mêmes colorés, rappelant aux utilisateurs que des molécules fortement teintées peuvent nécessiter une vérification manuelle des résultats.
Découvrir des signaux dans les produits naturels
L’équipe a ensuite appliqué l’essai à 88 produits naturels rares isolés de myxobactéries et de champignons, organismes connus pour produire des molécules chimiquement exotiques. Dix-huit composés ont empêché la croissance d’Euglena, cohérent avec des actions connues sur la production d’énergie, l’architecture cellulaire ou les mécanismes d’autophagie. De façon frappante, un composé — l’argyrine C, un peptide cyclique provenant de myxobactéries — a provoqué un fort blanchiment plutôt qu’une mort nette. L’argyrine C est déjà connue pour bloquer un facteur d’élongation protéique impliqué dans la synthèse des protéines au sein des mitochondries, les centrales énergétiques de la cellule qui elles aussi descendent de bactéries. Son effet de blanchiment chez Euglena confirme que l’essai peut détecter des mécanismes de type antibactérien qui vont au-delà des drogues ciblant habituellement le ribosome ou l’ADN.
Promesses et limites de l’approche
Ce criblage basé sur la couleur manquera certains types d’antibiotiques importants. Par exemple, les médicaments qui attaquent la paroi cellulaire bactérienne n’ont rien sur quoi s’accrocher dans les chloroplastes et laissent donc Euglena verte. Même parmi les composés qui bloquent la production protéique, seulement environ 40 % ont provoqué le blanchiment, soulignant la distance évolutive entre les chloroplastes et les agents pathogènes modernes. En revanche, la méthode est exceptionnellement peu coûteuse, robuste et facile à mettre à l’échelle. Euglena pousse dans un milieu simple au sel et à l’éthanol sans sérum animal, peut être maintenue pendant des semaines avec un entretien minimal et ne nécessite qu’un équipement de laboratoire basique. Parce que son chloroplaste dérive d’un ancêtre à Gram négatif, l’essai est particulièrement adapté pour trouver des médicaments capables de pénétrer les membranes multiples typiques de certaines des bactéries résistantes les plus préoccupantes aujourd’hui.
Ce que cela signifie pour les antibiotiques futurs
Pour un observateur non spécialiste, ce travail montre comment observer un organisme unicellulaire passer du vert au blanc peut aider à orienter la recherche des antibiotiques de demain. L’essai Euglena n’est pas une solution unique face à la résistance aux médicaments, mais constitue un filtre précoce puissant : en une étape il met en évidence des molécules qui semblent antibactériennes, paraissent relativement sûres pour les cellules complexes et peuvent traverser plusieurs barrières membranaires. Ces candidats peuvent ensuite être soumis à des essais plus approfondis directement dans des bactéries pathogènes et des cellules animales. Alors que les infections multi-résistantes continuent d’augmenter dans le monde, des outils de criblage intelligents et peu coûteux comme celui-ci pourraient accélérer la découverte en permettant aux scientifiques de concentrer des ressources rares sur les pistes les plus prometteuses.
Citation: Pereira, L., Löffler, LS., H. Kirsch, S. et al. Euglena gracilis as a high-throughput screening platform for antibacterial activity, cytotoxicity and membrane permeability in a one-step and cost-effective assay. J Antibiot 79, 376–385 (2026). https://doi.org/10.1038/s41429-026-00911-5
Mots-clés: découverte d’antibiotiques, criblage à haut débit, Euglena gracilis, résistance aux médicaments, produits naturels