Clear Sky Science · es
Identificación y análisis funcional bioinformático de polimorfismos nuevos y conocidos en el gen de la miostatina de la oveja montés de los Cárpatos ucranianos
Por qué importan los genes musculares en las ovejas de montaña
Las ovejas que pastan en las alturas de los Cárpatos ucranianos son algo más que ganado pintoresco. Son una raza local resistente que alimenta familias, sostiene culturas tradicionales y debe seguir siendo productiva en un clima duro. Este estudio examina el ADN de estos animales centrado en un único gen potente llamado miostatina, que ayuda a controlar cuánto músculo desarrolla un animal. Al descubrir pequeñas diferencias en este gen y usar modelos informáticos para predecir sus efectos, los investigadores esperan sentar las bases para una cría más inteligente y sostenible—producir ovejas que crezcan bien sin perder la resiliencia ganada con el tiempo.
Un freno clave al crecimiento muscular
La miostatina actúa como un pedal de freno para el crecimiento muscular en muchos mamíferos, incluidos humanos, bovinos y ovinos. Cuando este freno se debilita o se rompe, los animales pueden desarrollar músculos inusualmente voluminosos, un rasgo que ya se ha vinculado a mutaciones específicas de la miostatina en algunas razas de ganado y ovejas. Pero muchos cambios en el ADN dentro y alrededor del gen de la miostatina se encuentran en tramos denominados «no codificantes» que no alteran directamente la proteína. En su lugar, pueden afectar sutilmente cuánto se activa el gen, cuándo y en qué tejidos. Dado que el tamaño muscular influye fuertemente en el rendimiento cárnico y la eficiencia alimentaria, incluso cambios pequeños en esta capa reguladora pueden tener grandes consecuencias económicas y biológicas.
Una mirada cercana a un segmento de ADN poco visible
El equipo se centró en el intrón 1, una porción no codificante dentro del gen de la miostatina que ha atraído creciente atención en la investigación ganadera. Recolectaron sangre de 54 ovejas puras de los Cárpatos ucranianos y secuenciaron un tramo de 1.062 pares de bases de este intrón. En él hallaron nueve cambios de una sola letra del ADN, conocidos como polimorfismos de nucleótido único o SNP. Ocho de estos ya se habían descrito previamente en otras razas; uno, situado 283 bases después del primer exón, era totalmente nuevo. La mayoría de las letras alteradas eran raras y aparecían solo en animales portadores de una copia del cambio y una copia normal, lo que refuerza que esta región está generalmente bastante conservada en esta raza.
Patrones de variación en una raza tradicional
Al reconstruir segmentos de ADN más largos (haplotipos) que combinan varios SNP, los investigadores mostraron que una versión «de referencia» del intrón 1 dominaba la población, representando casi el 88 por ciento de todos los haplotipos. Las variantes restantes estaban distribuidas en un puñado de combinaciones raras. En comparación con otras razas estudiadas anteriormente, las ovejas montés de los Cárpatos ucranianos muestran por tanto una diversidad inusualmente baja en esta porción de la miostatina, con la mayoría de los animales portando la misma secuencia estándar. El SNP recién descubierto destacó: a diferencia de los demás, mostró los tres genotipos posibles en el rebaño y se apartó de las simples expectativas de apareamiento aleatorio, lo que sugiere fuerzas evolutivas recientes o una estructura poblacional sutil.
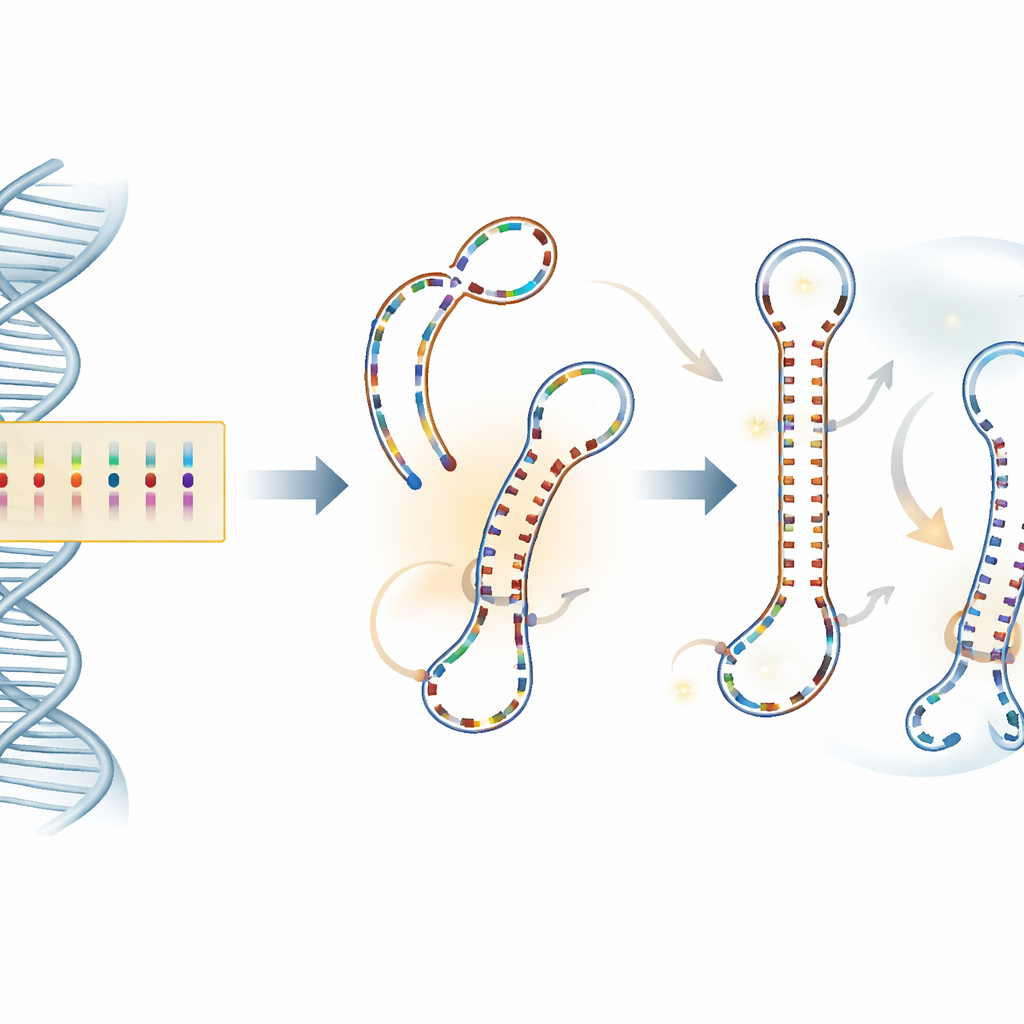
Lo que los ordenadores revelan sobre el comportamiento molecular
Encontrar variación es solo el primer paso; la pregunta más difícil es si alguno de estos cambios en el ADN realmente importa para el funcionamiento del gen. Para abordarlo, el equipo utilizó varias capas de análisis bioinformático. Modelaron cómo cada SNP podría alterar el plegamiento y la estabilidad de la larga copia de ARN producida a partir del gen, qué tan cercanos están los cambios a sitios de unión para proteínas reguladoras conocidas y si segmentos del intrón podrían plegarse en estructuras en horquilla que podrían servir como precursores de microARN—pequeñas moléculas de ARN que afinan la actividad génica. Para la horquilla más prometedora, que se solapa con un SNP en particular (c.373+607G>A), fueron más allá y ejecutaron simulaciones detalladas de dinámica molecular, siguiendo cómo alelos diferentes hacían que la estructura del ARN se flexionara, compactara o doblara a lo largo del tiempo en un entorno acuoso simulado.
Dos candidatos destacados para herramientas de cría futuras
De entre estas pruebas, dos SNP emergieron como especialmente interesantes: el ya conocido c.373+607G>A y el recién identificado c.373+283T>C. Ambos se predicen que modifican la estabilidad del ARN de la miostatina de maneras que podrían influir en cómo se procesa y expresa el gen. La variante 607 también parece alterar el comportamiento tridimensional de una horquilla candidata para microARN, lo que podría afectar si se produce tal molécula reguladora o la eficiencia con que se genera. Aunque ninguna de estas predicciones demuestra que los SNP cambien por sí solos la musculatura o el crecimiento, proporcionan objetivos concretos para futuros trabajos de laboratorio y estudios de asociación en granjas.
De las pistas del ADN a mejores ovejas de montaña
Por ahora, esta investigación no afirma que ninguna variante en particular dará carcasas más pesadas o corderos de crecimiento más rápido. En su lugar, ofrece un mapa: un primer catálogo de la variación del intrón 1 de la miostatina en la oveja montés de los Cárpatos ucranianos y una lista jerarquizada de cambios con más probabilidad de tener efectos biológicos reales. Con este mapa, estudios futuros pueden probar cómo estos marcadores genéticos se relacionan con el crecimiento, la calidad de la carne y la adaptación a las condiciones de montaña. En última instancia, combinar el conocimiento tradicional sobre esta raza local con la selección basada en ADN podría ayudar a los pastores a mejorar la producción cárnica preservando la resiliencia y el valor cultural de sus rebaños.
Cita: Buslyk, T., Peka, M., Saienko, A. et al. Identification and bioinformatic functional analysis of novel and known polymorphisms in the myostatin gene of Ukrainian Carpathian Mountain sheep. Sci Rep 16, 14628 (2026). https://doi.org/10.1038/s41598-026-44326-6
Palabras clave: miostatina, genética ovina, crecimiento muscular, selección asistida por marcadores, oveja montés de los Cárpatos ucranianos