Clear Sky Science · de
Identifizierung und bioinformatische Funktionsanalyse bekannter und neuer Polymorphismen im Myostatingen der ukrainischen Karpatenbergschafe
Warum Muskelgene bei Bergschafen wichtig sind
Die Schafe, die hoch in den ukrainischen Karpaten weiden, sind mehr als malerisches Vieh. Sie sind eine robuste lokale Rasse, die Familien ernährt, traditionelle Kulturen stützt und in einem harten Klima leistungsfähig bleiben muss. Diese Studie blickt in die DNA dieser Tiere und konzentriert sich auf ein einziges mächtiges Gen namens Myostatin, das mitbestimmt, wie viel Muskelmasse ein Tier aufbaut. Indem die Forscher winzige Unterschiede in diesem Gen aufdecken und mit Computermodellen ihre möglichen Folgen vorhersagen, wollen sie die Grundlage für klügere, nachhaltigere Zucht legen — Schafe zu produzieren, die gut wachsen, ohne ihre hart erarbeitete Widerstandsfähigkeit zu verlieren.
Eine zentrale Bremse für Muskelwachstum
Myostatin wirkt wie ein Bremsfuß für das Muskelwachstum bei vielen Säugetieren, darunter Menschen, Rinder und Schafe. Wenn diese Bremse abgeschwächt oder aufgehoben ist, können Tiere ungewöhnlich kräftige Muskeln entwickeln — ein Merkmal, das bereits mit bestimmten Myostatin‑Mutationen in einigen Rassen von Rindern und Schafen verknüpft wurde. Viele DNA‑Veränderungen im und um das Myostatin‑Gen liegen jedoch in sogenannten „nicht‑kodierenden“ Bereichen, die das Protein selbst nicht direkt verändern. Stattdessen können sie subtil beeinflussen, wie stark das Gen angeschaltet wird, wann und in welchen Geweben. Da die Muskelgröße den Fleischansatz und die Futtereffizienz stark beeinflusst, können selbst kleine Änderungen in dieser Regulationsschicht große ökonomische und biologische Folgen haben.
Ein genauer Blick auf ein verborgenes DNA‑Segment
Das Team richtete den Fokus auf Intron 1, einen nicht‑kodierenden Abschnitt innerhalb des Myostatin‑Gens, der in der Nutztierforschung zunehmende Aufmerksamkeit findet. Sie entnahmen Blutproben von 54 reinrassigen ukrainischen Karpatenbergschafen und sequenzierten eine 1.062 Basenpaare lange Strecke dieses Introns. Darin identifizierten sie neun Einzelbuchstaben‑DNA‑Veränderungen, sogenannte Einzel‑Nukleotid‑Polymorphismen (SNPs). Acht davon waren bereits zuvor in anderen Rassen berichtet worden; eine, gelegen 283 Basen nach dem ersten Exon, war völlig neu. Die meisten veränderten Basen waren selten und traten nur bei Tieren auf, die eine Kopie der Veränderung und eine normale Kopie trugen, was bestätigt, dass dieser Bereich in dieser Rasse insgesamt recht konserviert ist.
Variationsmuster in einer traditionellen Rasse
Durch die Rekonstruktion längerer DNA‑Segmente (Haplotypen), die mehrere SNPs kombinieren, zeigten die Forscher, dass eine „Referenz“‑Version von Intron 1 die Population dominierte und fast 88 Prozent aller Haplotypen ausmachte. Die übrigen Varianten verteilten sich auf einige wenige seltene Kombinationen. Im Vergleich zu früher untersuchten Rassen zeigen die ukrainischen Karpatenbergschafe damit eine ungewöhnlich geringe Diversität in diesem Abschnitt von Myostatin, wobei die meisten Tiere dieselbe Standardsequenz tragen. Der neu entdeckte SNP stach heraus: Im Gegensatz zu den anderen zeigte er alle drei möglichen Genotypen in der Herde und wich von den einfachen Erwartungen zufälliger Paarung ab, was auf jüngste evolutionäre Kräfte oder eine subtile Populationsstruktur hindeutet.
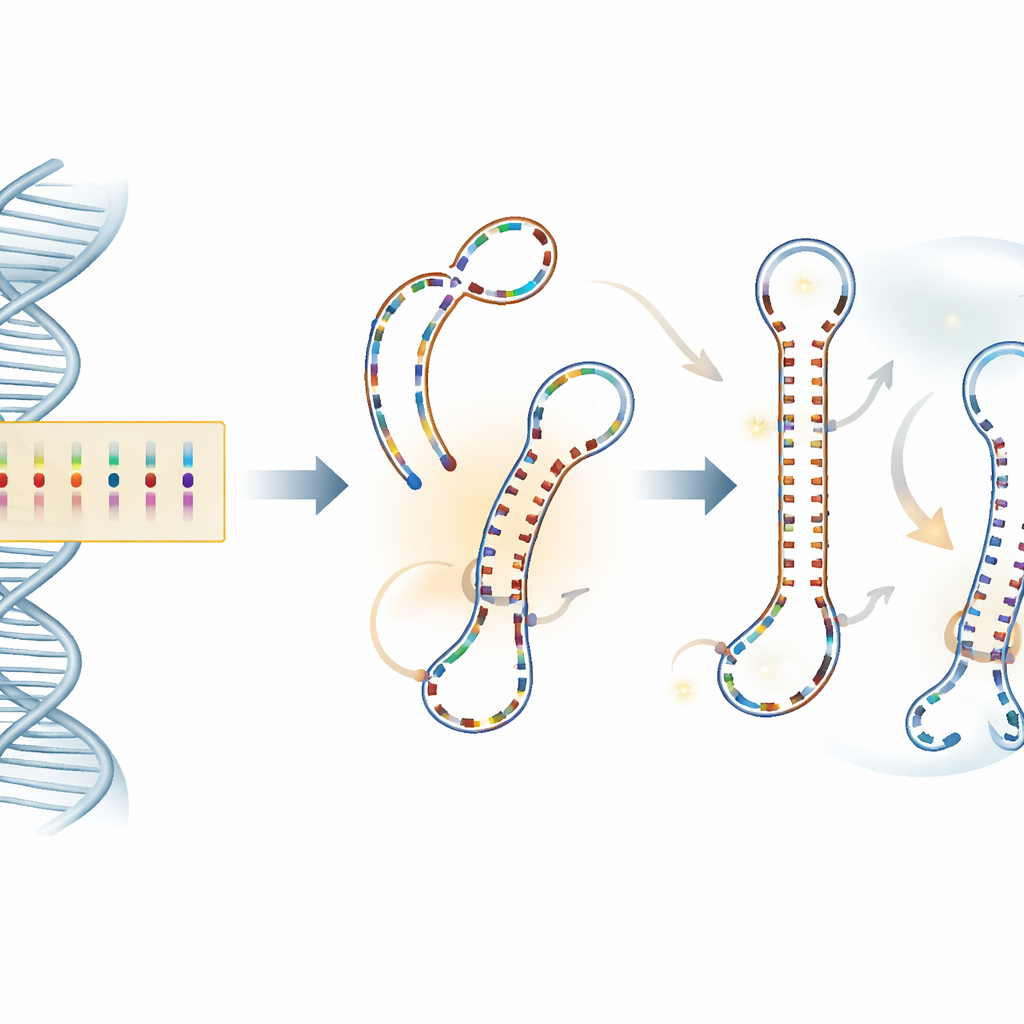
Was Computer über molekulares Verhalten zeigen
Variation zu finden ist nur der erste Schritt; die schwierigere Frage ist, ob irgendeine dieser DNA‑Veränderungen tatsächlich das Verhalten des Gens beeinflusst. Um dies zu prüfen, nutzte das Team mehrere Ebenen bioinformatischer Analyse. Sie modellierten, wie jeder SNP die Faltung und Stabilität der langen RNA‑Kopie beeinflussen könnte, die vom Gen erzeugt wird, wie nahe die Veränderungen an Bindungsstellen bekannter regulatorischer Proteine liegen und ob Segmente des Introns Haarnadelstrukturen (Hairpins) bilden könnten, die als Vorläufer für Mikro‑RNAs dienen — winzige RNA‑Moleküle, die die Genaktivität feinabstimmen. Für das vielversprechendste Hairpin, das mit einem bestimmten SNP (c.373+607G>A) überlappt, gingen sie noch weiter und führten detaillierte Molekulardynamik‑Simulationen durch, um zu verfolgen, wie verschiedene Allele die RNA‑Struktur in einer simulierten wässrigen Umgebung im Laufe der Zeit biegen, kompaktieren oder flexen ließen.
Zwei herausragende Kandidaten für künftige Zuchtwerkzeuge
In diesen Tests traten zwei SNPs als besonders interessant hervor: der bereits bekannte c.373+607G>A und der neu identifizierte c.373+283T>C. Beide werden dahingehend vorhergesagt, die Stabilität der Myostatin‑RNA so zu verändern, dass dies die Verarbeitung und Expression des Gens beeinflussen könnte. Die Variante bei Position 607 scheint zudem das dreidimensionale Verhalten eines potenziellen Mikro‑RNA‑Hairpins zu verändern, was beeinflussen könnte, ob ein solches regulatorisches Molekül überhaupt gebildet wird oder wie effizient es hergestellt wird. Obwohl keine dieser Vorhersagen beweist, dass die SNPs allein Muskeln oder Wachstum verändern, liefern sie greifbare Ziele für zukünftige Laboruntersuchungen und feldbasierte Assoziationsstudien.
Von DNA‑Hinweisen zu besseren Bergschafen
Vorerst behauptet diese Forschung nicht, dass eine bestimmte Variante schwerere Schlachtkörper oder schneller wachsende Lämmer liefert. Stattdessen bietet sie eine Karte: ein erstes Verzeichnis der Variation in Myostatin‑Intron 1 bei ukrainischen Karpatenbergschafen und eine Rangliste der Veränderungen, die am ehesten reale biologische Effekte haben könnten. Mit dieser Karte können künftige Studien prüfen, wie diese genetischen Marker mit Wachstum, Fleischqualität und Anpassung an Gebirgsbedingungen zusammenhängen. Letztlich könnte die Kombination traditionellen Wissens über diese lokale Rasse mit DNA‑basierter Auswahl Schäfern helfen, die Fleischproduktion zu verbessern und gleichzeitig die Widerstandsfähigkeit und den kulturellen Wert ihrer Herden zu bewahren.
Zitation: Buslyk, T., Peka, M., Saienko, A. et al. Identification and bioinformatic functional analysis of novel and known polymorphisms in the myostatin gene of Ukrainian Carpathian Mountain sheep. Sci Rep 16, 14628 (2026). https://doi.org/10.1038/s41598-026-44326-6
Schlüsselwörter: Myostatin, Schafgenetik, Muskulaturwachstum, markerunterstützte Zucht, ukrainische Karpatenbergschafe