Clear Sky Science · es
Inhibición de Ddx3x en la corteza prefrontal medial induce un fenotipo tipo autista en ratones mediante la alteración de la plasticidad sináptica
Cuando un gen modifica la conducta social
¿Por qué ciertos cambios genéticos provocan diferencias en la conducta social, en el aprendizaje y en las respuestas sensoriales que etiquetamos como autismo? Este estudio se centra en un gen concreto, DDX3X, y plantea una pregunta simple pero potente: ¿qué ocurre en el cerebro cuando este gen no funciona correctamente? Mediante el estudio de células cerebrales en cultivo y de ratones diseñados experimentalmente, los autores trazan un recorrido desde una pequeña falla molecular hasta alteraciones en el cableado cerebral y, finalmente, comportamientos parecidos al autismo.
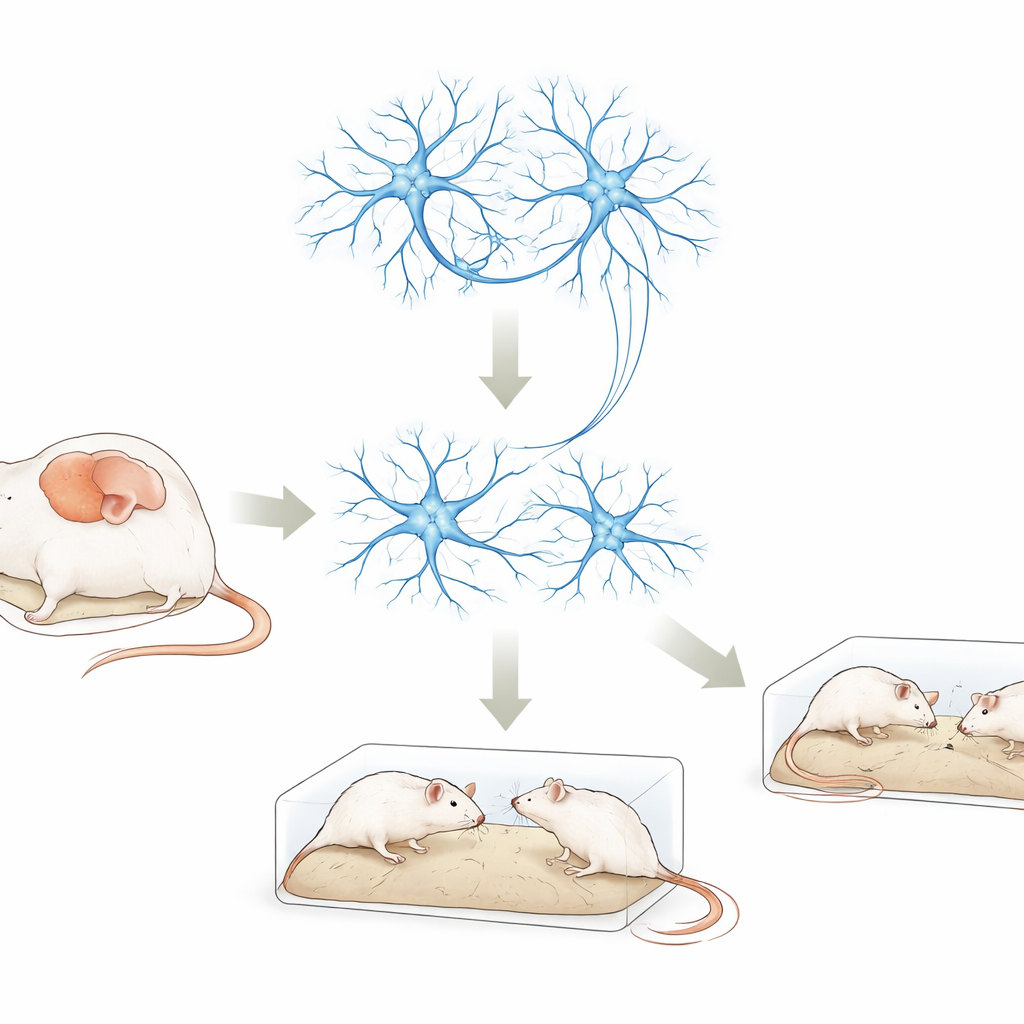
Un gen clave del cerebro bajo la lupa
DDX3X es un gen que ayuda a las células a manejar el ARN, la copia operativa de nuestro código genético usada para fabricar proteínas. Se detectan cada vez más variaciones de DDX3X en personas con autismo, discapacidad intelectual y retraso del desarrollo. Sin embargo, no quedaba claro cómo estos cambios perturban la función cerebral. En este trabajo, los científicos redujeron la actividad de la versión murina del gen, llamada Ddx3x, en dos contextos: células neuronales en cultivo y una región cerebral específica en ratones vivos, la corteza prefrontal medial. Esta región participa intensamente en la interacción social, la toma de decisiones y la memoria—habilidades que con frecuencia se ven afectadas en el autismo.
De células de crecimiento más lento a cambios sociales en ratones
Cuando el equipo disminuyó los niveles de Ddx3x en células neuronales cultivadas en el laboratorio, las células crecieron más despacio y formaron conexiones con menos facilidad que las células normales. En ratones, emplearon un virus inofensivo como herramienta de entrega para reducir Ddx3x únicamente en las neuronas de la corteza prefrontal medial. A esos ratones se les sometió a una batería de pruebas de comportamiento. En comparación con los animales de control, los ratones con reducción de Ddx3x se movían con normalidad y no mostraban ansiedad inusual en campo abierto, pero manifestaron un menor interés por un ratón desconocido, se sintieron menos atraídos por una nueva pareja social y obtuvieron peores resultados en un laberinto que exige memoria cuando el intervalo de retención era mayor. También mostraron más comportamientos repetitivos de excavación y enterramiento—paralelos de dos rasgos centrales del autismo: dificultades sociales y rutinas repetitivas.
Cambios ocultos en el paisaje proteico del cerebro
Para ver qué cambiaba dentro de las células, los investigadores realizaron estudios proteómicos a gran escala tanto en las células en cultivo como en la corteza prefrontal medial de los ratones. Encontraron cientos de proteínas cuyos niveles variaron cuando Ddx3x fue reducido. Muchas de las proteínas más afectadas participaban en la forma en que las sinapsis—las uniones donde se comunican las neuronas—se adaptan y se fortalecen con el tiempo, una propiedad conocida como plasticidad sináptica. Vías relacionadas con el fortalecimiento de conexiones ligado al aprendizaje, la transmisión química mediada por glutamato y GABA (las principales señales excitadoras e inhibitorias del cerebro), y el metabolismo hormonal y energético mostraron indicios de estar atenuadas. Tanto en las células como en el tejido cerebral, también observaron alteraciones coincidentes en los sistemas que pliegan correctamente las proteínas nuevas y etiquetan las proteínas desgastadas para su eliminación, lo que sugiere un fallo generalizado en el control de calidad proteico.
Conexiones entre neuronas debilitadas
Examinando más de cerca la estructura de las sinapsis, el equipo utilizó microscopios de alta resolución para observar las neuronas de la región cerebral afectada. Hallaron que los ratones con Ddx3x reducido presentaban menos espinas dendríticas—las pequeñas protuberancias en las ramas neuronales donde se sitúan las sinapsis excitadoras—especialmente las espinas maduras en forma de hongo que son cruciales para conexiones fuertes y estables. La densidad postsináptica, una zona rica en proteínas que ancla receptores y moléculas de señalización, era más fina y de menor tamaño. Registros eléctricos en cortes cerebrales mostraron que las señales excitadoras llegaban con menos frecuencia, aunque su fuerza individual no cambiaba. En conjunto, estos hallazgos apuntan a una red cerebral con menos puntos de comunicación y de menor eficacia, más que a una red totalmente silenciosa.
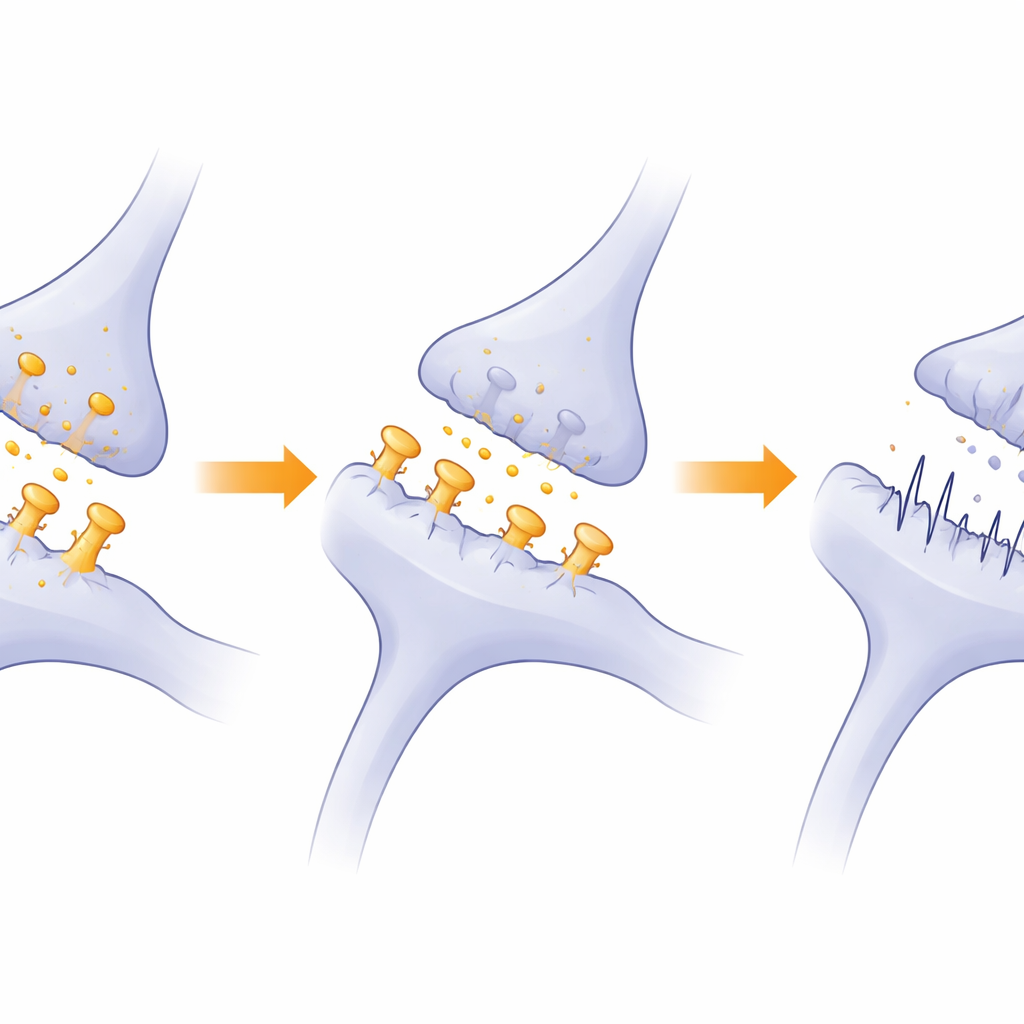
Cómo el desequilibrio proteico alterado puede alimentar rasgos autistas
Más allá de las sinapsis individuales, el estudio pone de relieve un problema más profundo: la maquinaria que mantiene el equilibrio de las proteínas sinápticas parece estar suprimida cuando Ddx3x es bajo. Los sistemas que pliegan proteínas recién sintetizadas y los que degradan las dañadas—especialmente la vía ubiquitina–proteasoma—mostraron menor actividad. Dado que las sinapsis dependen de una renovación constante y un ajuste fino de sus componentes proteicos, esta desaceleración puede erosionar gradualmente la fuerza y la flexibilidad sináptica. Los autores proponen que esta combinación de menos espinas maduras, señalización amortiguada y deficiente mantenimiento proteico en la corteza prefrontal medial contribuye a explicar los cambios sociales y cognitivos observados en sus ratones. En términos sencillos, cuando DDX3X falla, los circuitos cerebrales que sostienen la conducta social y el aprendizaje no pueden construir ni mantener las conexiones necesarias, orientando el desarrollo hacia una trayectoria similar al autismo.
Cita: Zhuang, H., Cao, X., Tang, X. et al. Knockdown of Ddx3x in mPFC induces autistic-like phenotype in mice via altered synaptic plasticity. Transl Psychiatry 16, 216 (2026). https://doi.org/10.1038/s41398-026-03945-3
Palabras clave: DDX3X, trastorno del espectro autista, plasticidad sináptica, corteza prefrontal medial, sistema ubiquitina-proteasoma