Clear Sky Science · pt
Características genômicas e moleculares convergentes preveem risco de metástase metacrônica em carcinoma de células claras do rim
Por que alguns cânceres renais retornam
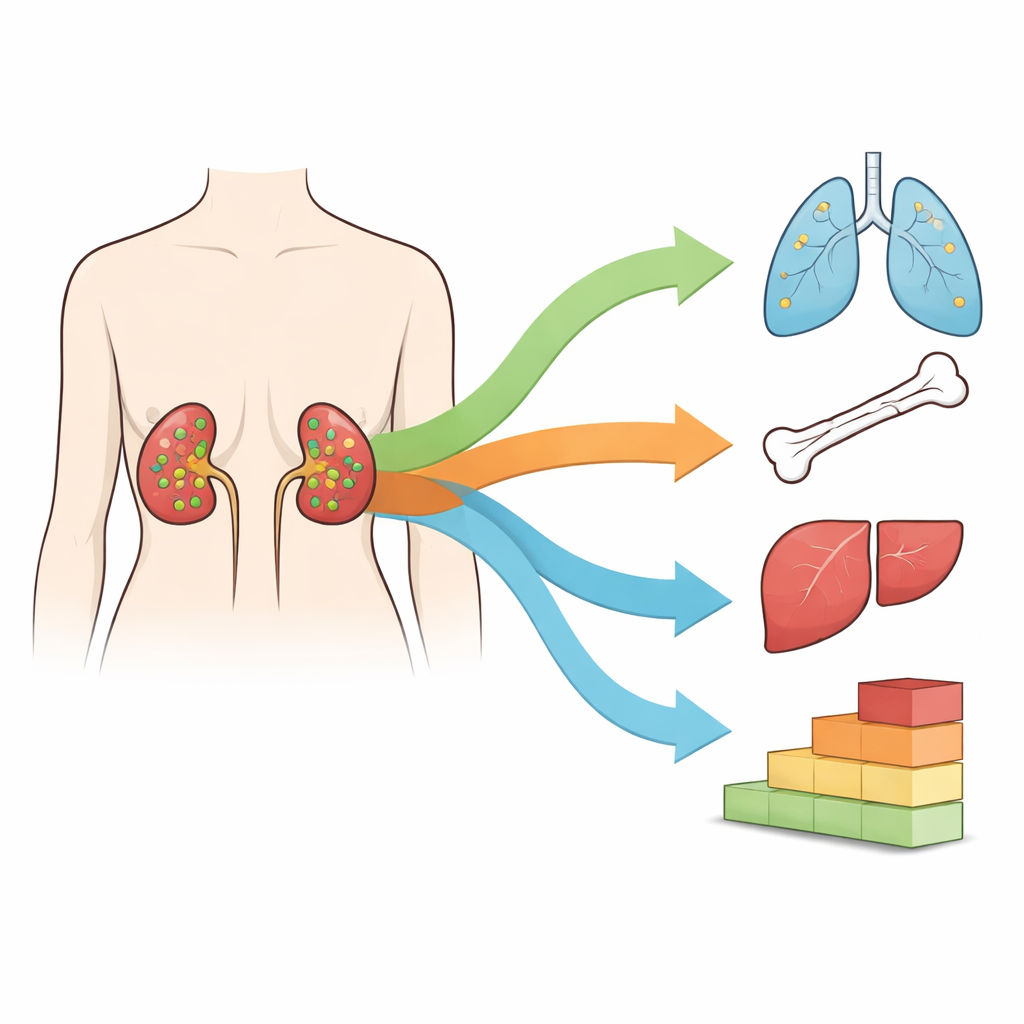
Para muitas pessoas com carcinoma de células claras do rim, a forma mais comum de câncer renal, a cirurgia para remover o tumor renal parece curar a doença. Ainda assim, em cerca de um em cada três casos, o câncer reaparece meses ou anos depois em outras partes do corpo. Essa disseminação tardia, conhecida como metástase metacrônica, é difícil de prever e ainda mais difícil de tratar. O estudo resumido aqui faz uma pergunta prática com consequências que mudam vidas: podemos ler o DNA e o RNA de um tumor no momento da cirurgia para dizer quais pacientes têm mais probabilidade de enfrentar uma recaída perigosa?
Acompanhando pacientes por anos, não meses
Os pesquisadores reanalisaram dados de 192 pessoas cujos tumores renais já haviam sido profundamente perfilados por grandes projetos oncológicos. De forma crucial, acrescentaram acompanhamento de longo prazo, monitorando quem desenvolveu metástases e quando, por até oito anos. Isso permitiu dividir os tumores em três grupos: aqueles que já estavam se espalhando ou o fizeram rapidamente, aqueles que nunca se espalharam durante o seguimento e aqueles que pareciam localizados a princípio, mas geraram novos tumores mais tarde. Como os dois últimos grupos podem parecer semelhantes em exames de imagem e ao microscópio, comparar seus padrões moleculares ofereceu uma maneira de descobrir sinais de alerta ocultos que os testes clínicos comuns deixam passar.
Uma região cromossômica frágil como sinal de alerta precoce
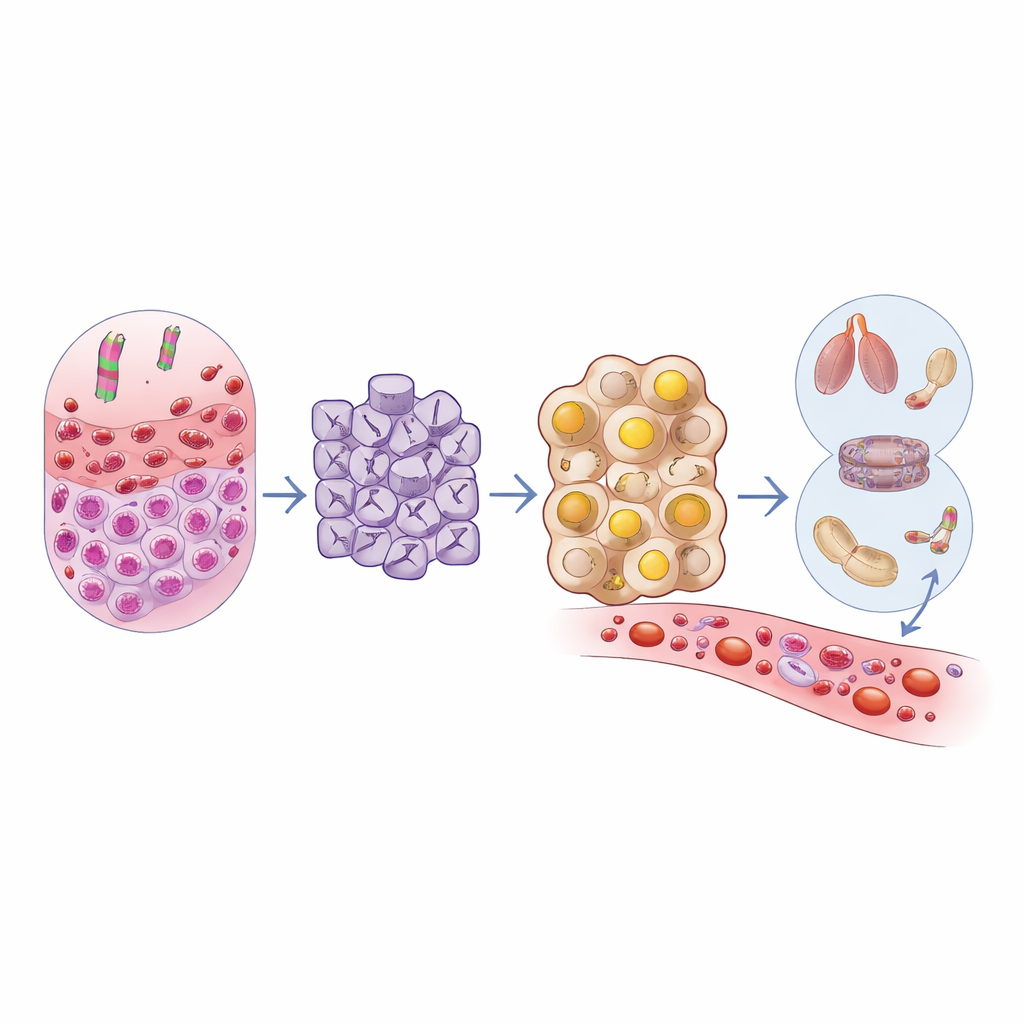
No nível do DNA, a equipe procurou ganhos e perdas de grandes segmentos cromossômicos. Eles descobriram que tumores que mais tarde produziram metástases apresentavam maior probabilidade de ter perdido um trecho no braço curto do cromossomo 1, em uma banda chamada 1p31–36. Nessa região, muitos genes mostraram tanto redução do número de cópias quanto menor atividade, sugerindo que a perda física do DNA estava silenciando-os diretamente. Vários desses genes, incluindo CYP4A11, estão envolvidos na degradação de moléculas gordurosas, sugerindo que esse dano cromossômico pode reorganizar a forma como as células tumorais processam combustível e blocos de construção. Esse padrão de perda coordenada de DNA e silenciamento gênico distinguiu tumores que viriam a metastizar de outros mais indolentes que nunca se espalharam.
Como células tumorais e seus vizinhos mudam
Como uma amostra tumoral em bloco mistura células cancerosas com células de suporte e imunes, os autores usaram métodos computacionais para “desmisturar” os dados e estimar quais genes estavam ativos em cada compartimento. Nas próprias células cancerosas, tumores que mais tarde se espalharam mostraram redução da atividade de genes que ajudam as células a manter uma arquitetura ordeira e firmemente conectada. Um ator-chave, PATJ, que ajuda a manter a polaridade e as junções estreitas que mantêm as células epiteliais alinhadas, foi fortemente rebaixado e também se localiza na região vulnerável 1p. Ao mesmo tempo, as células cancerosas exibiram amortecimento amplo de múltiplas rotas de degradação de ácidos graxos, consistente com uma mudança em direção ao armazenamento de gorduras como gotículas dentro das células — uma característica desse tipo de câncer. No microambiente circundante, os pesquisadores observaram sinais reduzidos de certos tipos de células imunes, incluindo células T reguladoras e um tipo pró-inflamatório de macrófago, sugerindo que o panorama imune local em tumores de alto risco está incomumente esgotado de tipos celulares potencialmente protetores.
De sinais moleculares a um escore de risco prático
Para transformar essas descobertas em algo que clínicos pudessem eventualmente usar, a equipe construiu um modelo estatístico que combina a atividade de apenas cinco genes: FKBP15, SLC31A1, CPT2, PATJ e CALR. Os cinco surgiram como fortes preditores individuais de metástase tardia. Usando validação cruzada, onde o modelo é repetidamente treinado em parte dos dados e testado no restante, essa assinatura de cinco genes separou com mais precisão pacientes de alto e baixo risco do que vários painéis gênicos existentes para câncer renal projetados para recorrência ou sobrevida. Pacientes com escores mais altos na assinatura de cinco genes tiveram períodos livres de doença mais curtos, enquanto aqueles com escores baixos tendiam a permanecer livres de metástase por mais tempo. O desempenho do modelo também foi apoiado quando aplicado a um grupo independente de pacientes.
O que isso significa para pacientes e cuidados futuros
Para uma pessoa prestes a se submeter à cirurgia por câncer renal, a maior incógnita é se o tumor removido já "plantou sementes" em outros locais que emergirão depois. Este estudo sugere que certas características ocultas — perda de uma região cromossômica específica, enfraquecimento da ordem estrutural da célula e supressão das vias de queima de gorduras — marcam tumores com maior probabilidade de disseminação tardia. Ao destilar esses padrões em um teste compacto de cinco genes, o trabalho aponta para um acompanhamento mais personalizado: pacientes identificados como de alto risco poderiam ser monitorados mais de perto ou considerados para tratamentos adicionais, enquanto pacientes de baixo risco poderiam evitar terapias desnecessárias. Embora o modelo ainda precise de testes clínicos prospectivos, os resultados oferecem um quadro molecular mais claro do porquê alguns carcinomas renais de células claras retornam e como podemos melhor antecipar e prevenir esse desfecho.
Citação: M. Naeini, M., Pang, M., Rohatgi, N. et al. Convergent genomic and molecular features predict risk of metachronous metastasis in clear cell renal cell carcinoma. Commun Med 6, 205 (2026). https://doi.org/10.1038/s43856-026-01436-6
Palavras-chave: câncer renal, risco de metástase, genômica do câncer, microambiente tumoral, metabolismo de ácidos graxos