Clear Sky Science · pt
Integração de metabolômica e aprendizado de máquina com análise in silico para identificar biomarcadores precoces e interações moleculares na lesão renal aguda associada à sepse
Por que detectar o risco renal cedo é importante
Em unidades de terapia intensiva, muitos pacientes com infecções graves (sepse) desenvolvem subitamente problemas renais severos. Atualmente, os médicos dependem de um resíduo sanguíneo chamado creatinina para detectar esse dano, mas a creatinina só aumenta depois que os rins já foram lesionados. Este estudo fez uma pergunta crucial: sinais químicos ocultos no sangue podem revelar que a lesão renal relacionada à sepse está prestes a ocorrer com um dia de antecedência, dando aos médicos a chance de agir mais cedo?
Procurando pistas químicas ocultas no sangue
Os pesquisadores acompanharam cinquenta adultos em uma unidade de terapia intensiva com sepse. Alguns desenvolveram lesão renal aguda dentro de dois dias, enquanto outros não. Importante: as amostras de sangue foram coletadas logo após o diagnóstico de sepse, antes de os rins apresentarem falha evidente. Em vez de testar alguns marcadores conhecidos, a equipe usou um método amplo de “impressão química” para rastrear mais de mil pequenas moléculas no sangue, conhecidas coletivamente como metabólitos. Essas moléculas refletem como o organismo usa e transforma nutrientes e energia, e podem mudar rapidamente quando órgãos estão sob estresse.
De milhares de sinais a um punhado de marcadores-chave
A análise computacional mostrou que pacientes que mais tarde desenvolveram lesão renal apresentavam um padrão químico sanguíneo distintamente diferente daqueles que não desenvolveram. De 1.425 características, 634 metabólitos específicos puderam ser identificados de forma confiável, e 150 desses diferiram fortemente entre os dois grupos de pacientes. Muitas das alterações indicaram distúrbios no processamento de aminoácidos e gorduras, especialmente vias envolvendo o aminoácido fenilalanina e a molécula similar a uma vitamina NAD+, essencial para a produção de energia nas células. Para transformar esses dados extensos em algo clinicamente útil, os pesquisadores usaram métodos de aprendizado de máquina projetados para filtrar muitas variáveis e selecionar as mais informativas.
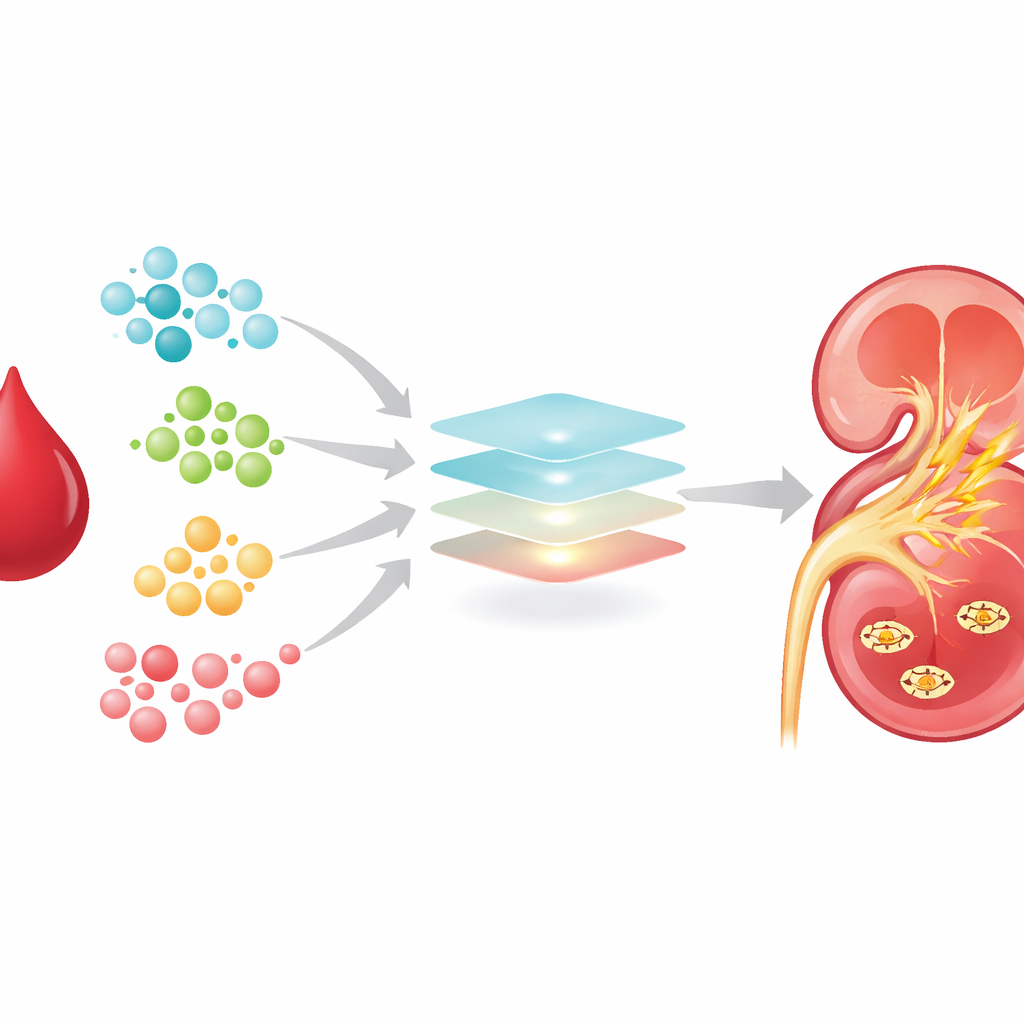
Um painel de alerta com cinco moléculas
Dois algoritmos computacionais independentes convergiram para um pequeno conjunto de cinco metabólitos que foram especialmente eficazes em distinguir pacientes que desenvolveriam ou não lesão renal. Foram eles: ácido sebácico, um tipo de acilcarnitina, acetato de metila, ácido treônico (um produto de degradação da vitamina C) e uma molécula chamada 1‑RDN, intimamente ligada à produção de NAD+. Todos os cinco estavam aumentados em pacientes rumo à lesão renal. Quando a equipe construiu um modelo preditivo usando apenas essas cinco moléculas e o testou em um rigoroso esquema “leave-one-out”, o melhor modelo separou corretamente pacientes de alto e baixo risco com alta precisão, superando medidas tradicionais como creatinina e marcadores inflamatórios comuns.
Como metabolismo e estresse renal podem estar conectados
Além da predição, o padrão de metabólitos conta uma história sobre o que pode estar ocorrendo dentro dos rins durante a sepse inicial. O aumento de acilcarnitina e ácido sebácico sugere que as células renais estão com dificuldade para queimar gorduras corretamente, levando a déficits de energia. Níveis crescentes de 1‑RDN indicam tentativas estressadas de reconstruir o NAD+, o cofator que auxilia o manejo de combustível e energiza as mitocôndrias, as fábricas de energia celular. O acúmulo de ácido treônico indica que o organismo está usando intensamente as defesas de vitamina C contra danos oxidativos. O acetato de metila, formado a partir da acetona, pode agravar ainda mais o estresse oxidativo e drenar energia. Em conjunto, essas mudanças desenham o quadro de rins presos em um ciclo de queima de gordura defeituosa, colapso energético e lesão oxidativa mesmo antes de os testes convencionais sinalizarem problema.
Uma ponte molecular possível entre química e dano
Para aprofundar, a equipe usou simulações de acoplamento molecular para verificar se algum dos metabólitos-chave poderia interagir fisicamente com proteínas conhecidas por atuar na doença renal. Encontraram que 1‑RDN poderia ligar‑se firmemente à fenilalanina hidroxilase, uma enzima que ajuda a processar o aminoácido fenilalanina e está presente não apenas no fígado, mas também no tecido renal. Isso levanta a possibilidade de que mudanças na química relacionada ao NAD+ possam alterar diretamente o manejo de aminoácidos no próprio rim, vinculando o estresse energético a alterações em moléculas sinalizadoras derivadas da fenilalanina. Embora essa ideia ainda precise ser testada em experimentos de laboratório e em modelos animais, ela oferece um ponto de partida concreto para explorar como disrupções metabólicas podem desencadear dano estrutural renal.
O que isso pode significar para o cuidado futuro
Este trabalho sugere que um simples exame de sangue medindo um pequeno painel de metabólitos poderia alertar os médicos, com até um dia de antecedência, quais pacientes com sepse estão à beira de uma lesão renal aguda. Embora a abordagem atual dependa de instrumentos laboratoriais sofisticados e ainda não esteja pronta para uso à beira do leito, as moléculas identificadas poderiam virar ensaios direcionados mais rápidos no futuro. Se validadas em estudos maiores e multicêntricos, tais provas poderiam permitir que os clínicos ajustassem medicamentos, calibrassem melhor o manejo de fluidos e pressão arterial, e considerassem terapias protetoras antes que os rins atinjam um ponto sem volta, potencialmente melhorando a sobrevivência e a recuperação de alguns dos pacientes mais graves.
Citação: Xu, W., Zhang, Z., Gu, F. et al. Integrating metabolomics and machine learning with in silico analysis to identify early biomarkers and molecular interactions in sepsis-associated acute kidney injury. Sci Rep 16, 10963 (2026). https://doi.org/10.1038/s41598-026-45255-0
Palavras-chave: sepse, lesão renal aguda, metabolômica, biomarcadores, aprendizado de máquina