Clear Sky Science · pt
Desenho racional e avaliação antibacteriana de novos derivados de piranopirazol: um estudo combinado experimental e in silico
Por que novas moléculas contra germes importam
Infecções resistentes a antibióticos estão aumentando em todo o mundo, tornando doenças antes rotineiras mais difíceis e, por vezes, impossíveis de tratar. Este estudo explora uma nova classe de moléculas sintetizadas em laboratório, chamadas piranopirazóis, projetadas para atuar como novas armas antibacterianas. Usando uma combinação de química verde e modelagem computacional avançada, os pesquisadores colocaram uma questão premente: podemos projetar racionalmente pequenas moléculas que tanto eliminem bactérias nocivas quanto se comportem como fármacos reais e seguros dentro do organismo?
Construindo novas moléculas de forma mais limpa
A equipe começou sintetizando uma família de compostos à base de piranopirazol usando reações multicomponentes, nas quais vários reagentes simples são combinados em um único recipiente. Essa estratégia reduz resíduos e evita condições severas, alinhando-se a abordagens mais verdes da química. Uma molécula intermediária central serviu como um núcleo flexível que, quando reagiu com diferentes pequenos reagentes como ácidos orgânicos, aminas e nitrilas, produziu um painel diversificado de estruturas relacionadas. Cada etapa nessas vias reacionais foi confirmada por ferramentas analíticas padrão que decodificam como os átomos estão conectados, assegurando que as arquiteturas moleculares pretendidas foram realmente construídas.
Colocando os compostos à prova contra germes
Com os compostos em mãos, as novas moléculas foram testadas em laboratório contra quatro bactérias de importância clínica: duas espécies Gram-positivas (Staphylococcus aureus e Bacillus subtilis) e duas Gram-negativas (Escherichia coli e Pseudomonas aeruginosa). Os pesquisadores mediram quão bem cada composto inibia o crescimento bacteriano examinando as claras “zonas de inibição” que produziriam em placas de ágar, usando o antibiótico comum cloranfenicol como referência. Vários compostos, incluindo variantes rotuladas 2b, 3a, 5b, 6b, 7b e 8b, mostraram forte atividade, por vezes aproximando-se ou até superando o fármaco de referência para cepas específicas. Notavelmente, algumas moléculas eram mais eficazes contra bactérias Gram-positivas, enquanto outras funcionavam melhor em espécies Gram-negativas, ressaltando como pequenos ajustes estruturais podem alterar a potência antibacteriana e a seletividade.
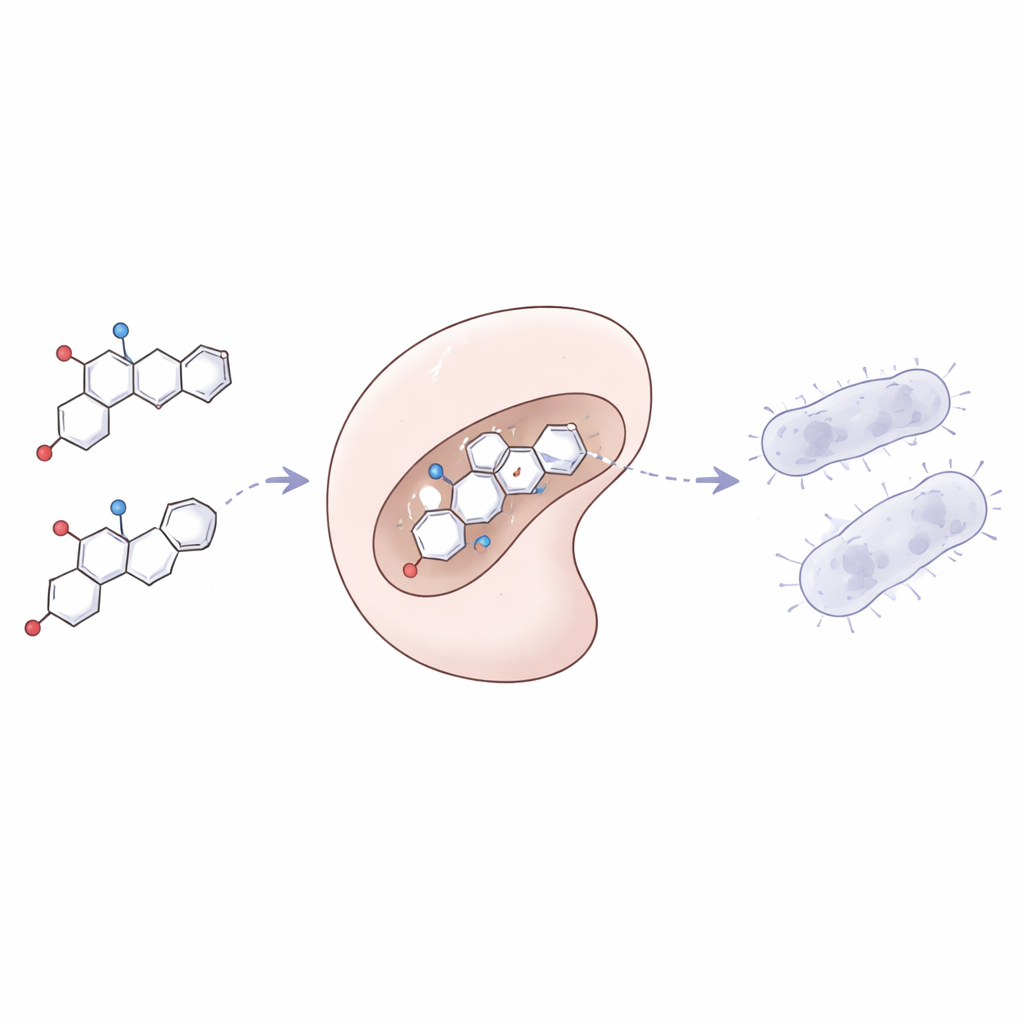
Perscrutando o comportamento eletrônico e o alvo enzimático
Para entender por que alguns piranopirazóis tiveram desempenho superior, a equipe utilizou cálculos de química quântica para sondar como os elétrons estão distribuídos nas moléculas. Eles focaram em dois níveis de energia-chave que controlam quão facilmente uma molécula pode doar ou aceitar elétrons, o que por sua vez influencia como ela reage com alvos biológicos. Compostos com lacunas menores entre esses níveis tendiam a ser mais reativos e correlacionaram com efeitos antibacterianos mais fortes. Mapas eletrostáticos codificados por cores revelaram ainda quais partes de cada molécula eram mais positivamente ou negativamente carregadas, destacando as regiões mais propensas a se ligar a proteínas. O principal alvo proteico foi a tirosil-tRNA sintetase, uma enzima bacteriana essencial envolvida na construção de novas proteínas. Simulações de docking computacional mostraram que vários piranopirazóis se encaixam firmemente no sítio ativo dessa enzima, formando múltiplas interações estabilizadoras e obtendo energias de ligação muito favoráveis na faixa nanomolar.
Das previsões computacionais ao comportamento parecido com fármacos
Projetar um bom antibiótico não é apenas matar bactérias; a molécula também precisa se deslocar pelo organismo, ser absorvida e evitar toxicidade excessiva. Por isso, os pesquisadores realizaram previsões in silico de ADME e toxicidade para estimar propriedades como absorção intestinal, distribuição e potenciais efeitos adversos. Muitas das moléculas mais promissoras atenderam a critérios amplamente usados de “caráter de fármaco”, incluindo a Regra dos Cinco de Lipinski, e foram previstas como tendo alta absorção intestinal. O risco geral de toxicidade foi modelado como baixo a moderado, e a maioria dos compostos foi classificada como não mutagênica e não citotóxica, embora alguns tenham mostrado indícios de possíveis efeitos hepáticos que exigiriam estudos adicionais. Combinados com os dados de docking e eletrônicos, esses resultados ajudaram a identificar um subconjunto de piranopirazóis com o melhor equilíbrio entre potência, seletividade e segurança prevista.
O que isso significa para futuros antibióticos
Em termos simples, este trabalho mostra que é possível projetar e afinar deliberadamente novas moléculas antibacterianas ao emparelhar química sintética inteligente com ferramentas computacionais poderosas. O arcabouço do piranopirazol, especialmente quando decorado com aneis aromáticos, átomos de halogênio e grupos ciano, pode penetrar defesas bacterianas, ligar-se firmemente a uma enzima bacteriana vital e interferir na produção de proteínas. Embora esses compostos ainda estejam em estágio inicial pré-clínico, eles oferecem um ponto de partida promissor para desenvolver futuros fármacos que possam ajudar a combater infecções resistentes a antibióticos. Os próximos passos envolverão testar como se comportam em organismos vivos, refinar sua segurança e explorar sua eficácia contra cepas multirresistentes difíceis de tratar.
Citação: Abdelatty, M.M., Makhlouf, A.A., Moustapha, M.E. et al. Rational design and antibacterial assessment of novel pyranopyrazole derivatives: a combined experimental and in silico study. Sci Rep 16, 11621 (2026). https://doi.org/10.1038/s41598-026-37625-5
Palavras-chave: resistência a antibióticos, piranopirazol, projeto de fármacos, docking molecular, agentes antibacterianos