Clear Sky Science · pl
O polinomach współwskaźnikowych topologicznych do modelowania predykcyjnego właściwości fizykochemicznych leków przeciwwirusowych
Dlaczego matematyka może przyspieszyć poszukiwania leków na Ebolę
Odnalezienie nowych leków przeciwwirusowych zwykle jest powolne i kosztowne, ponieważ każdą obiecującą cząsteczkę trzeba najpierw zsyntetyzować i przebadać w laboratorium. Niniejsze badanie eksploruje skrót: wykorzystanie pomysłów z matematyki i teorii grafów do „odczytania” struktury leku jak kodu kreskowego i przewidzenia jego zachowania bez przygotowywania ani jednego związku chemicznego. Praca koncentruje się na lekach proponowanych przeciwko wirusowi Ebola i pokazuje, jak starannie zaprojektowane, numeryczne odciski palców cząsteczek mogą prognozować istotne właściwości fizyczne, ważne dla działania leku w organizmie.
Przekształcanie cząsteczek w proste obrazy
Rdzeniem tego podejścia jest sposób przerysowania cząsteczki jako prostej sieci: atomy stają się węzłami, a wiązania chemiczne — krawędziami je łączącymi. Gdy lek jest reprezentowany jako sieć, autorzy obliczają wskaźniki topologiczne — liczby oddające cechy takie jak liczba rozgałęzień cząsteczki, jak ciasno są połączone atomy, czy jak symetryczny jest ogólny kształt. Wskaźniki te kondensują złożoną, trójwymiarową strukturę do kilku wartości opisowych, co umożliwia szybkie porównywanie i analizowanie wielu cząsteczek na komputerze.
Nowe odciski molekularne z dodatkowymi szczegółami
Opierając się na wcześniejszych pracach, badacze wprowadzają i analizują rodzinę udoskonalonych wskaźników zwanych współ-wskaźnikami topologicznymi, pochodzącymi z dwóch konstrukcji matematycznych znanych jako wielomiany CoM i CoNM. Zamiast brać pod uwagę tylko atomy bezpośrednio połączone wiązaniem, te nowe deskryptory uwzględniają także pary atomów, które nie są bezpośrednio połączone, lecz wciąż wpływają na siebie poprzez strukturę całości. CoM skupia się na liczbie wiązań zbiegających się przy każdym atomie, podczas gdy CoNM śledzi „sąsiedztwo” wokół każdego atomu. Kodując tę bogatszą informację w zwarte polinomy, metoda może wygenerować wiele różnych wskaźników w jednym kroku, oferując bardziej zniuansowany odcisk każdej cząsteczki bez dużych kosztów obliczeniowych.
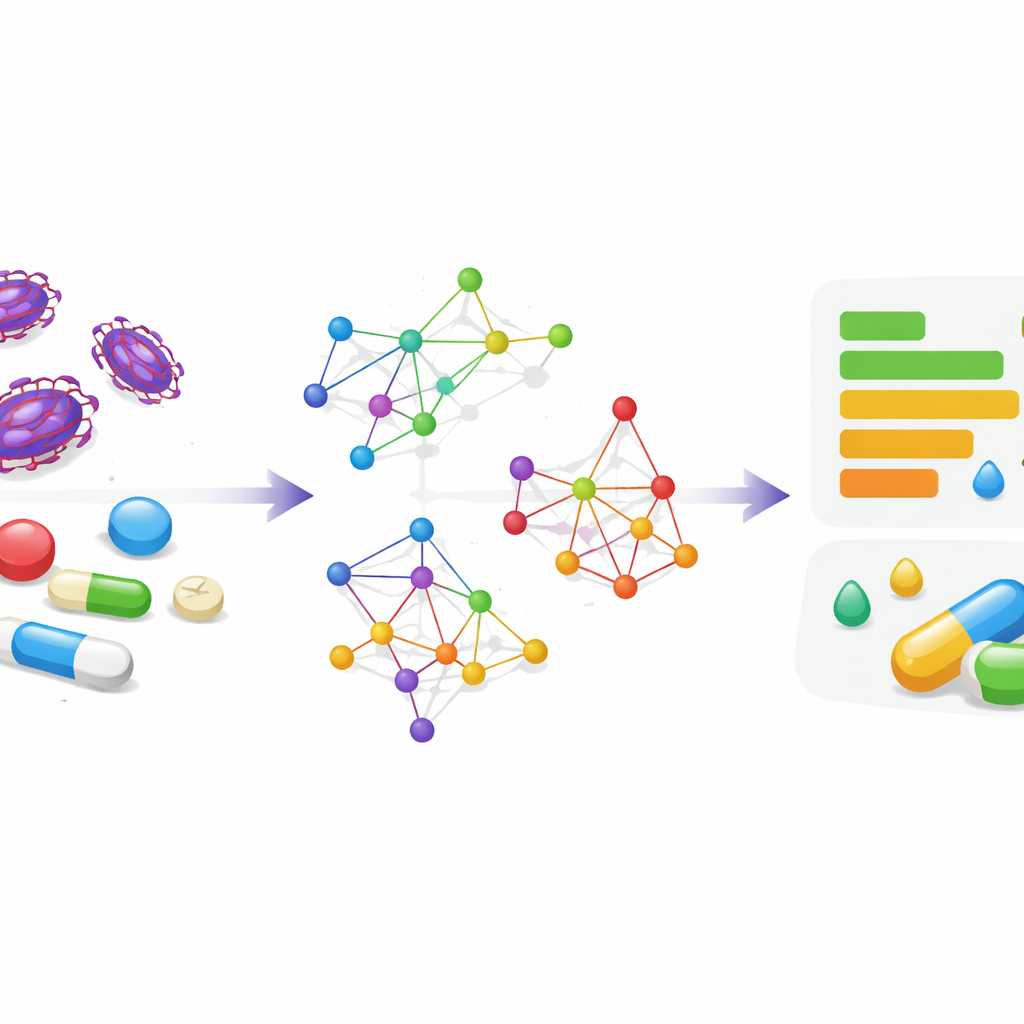
Testowanie metody na kandydatach na leki przeciwko Ebola
Zespół zastosował swoje ramy do ośmiu leków przeciwwirusowych omawianych w kontekście leczenia Eboli, w tym Galidesiviru, Chlorku chinoliny (Chloroquine), Favipiraviru, Amodiaquinu, Azytromycyny, Brincidofowiru, Clomiphenu i Remdesiviru. Dla każdego leku policzono zestaw współ-wskaźników opartych na stopniach węzłów i sąsiedztwach oraz porównano je z danymi eksperymentalnymi zaczerpniętymi z bazy ChemSpider. Badane właściwości fizyczne obejmowały objętość molową, refrakcyjność molową, polaryzowalność (jak łatwo elektrony cząsteczki ulegają zniekształceniu), napięcie powierzchniowe, ogólną złożoność strukturalną, stopień lipofilności lub hydrofilności (LogP), gęstość i współczynnik załamania światła. W praktyce postawiono pytanie: czy te matematyczne odciski mogą zastąpić czasochłonne pomiary?
Znajdowanie najlepszych powiązań między strukturą a zachowaniem
Aby zbadać te powiązania, autorzy zbudowali modele Ilościowo-Struktura–Właściwość (QSPR) — równania wiążące każdy topologiczny współ-wskaźnik z daną właściwością fizyczną. Wypróbowali trzy rodziny modeli: proste dopasowania liniowe, dopasowania logarytmiczne i dopasowania kwadratowe. Wiele właściwości wykazało silne korelacje z wybranymi wskaźnikami, z współczynnikami korelacji często bliskimi jedności, co oznacza, że przewidywania bardzo dobrze śledziły dane eksperymentalne. Niektóre deskryptory, takie jak współ-wskaźnik łączności atom-wiązanie oraz różne indeksy oparte na sąsiedztwach, powtarzalnie wyrastały na najpewniejszych predyktorów kluczowych cech, takich jak objętość molowa, refrakcyjność molowa, polaryzowalność i złożoność strukturalna. Dla bardziej subtelnych cech, takich jak równowaga olej–woda i gęstość, modele nieliniowe — zwłaszcza logarytmiczne i kwadratowe — lepiej uchwyciły zależności niż proste proste linie, podkreślając, że związek między strukturą a właściwością często ma charakter krzywoliniowy, a nie liniowy.
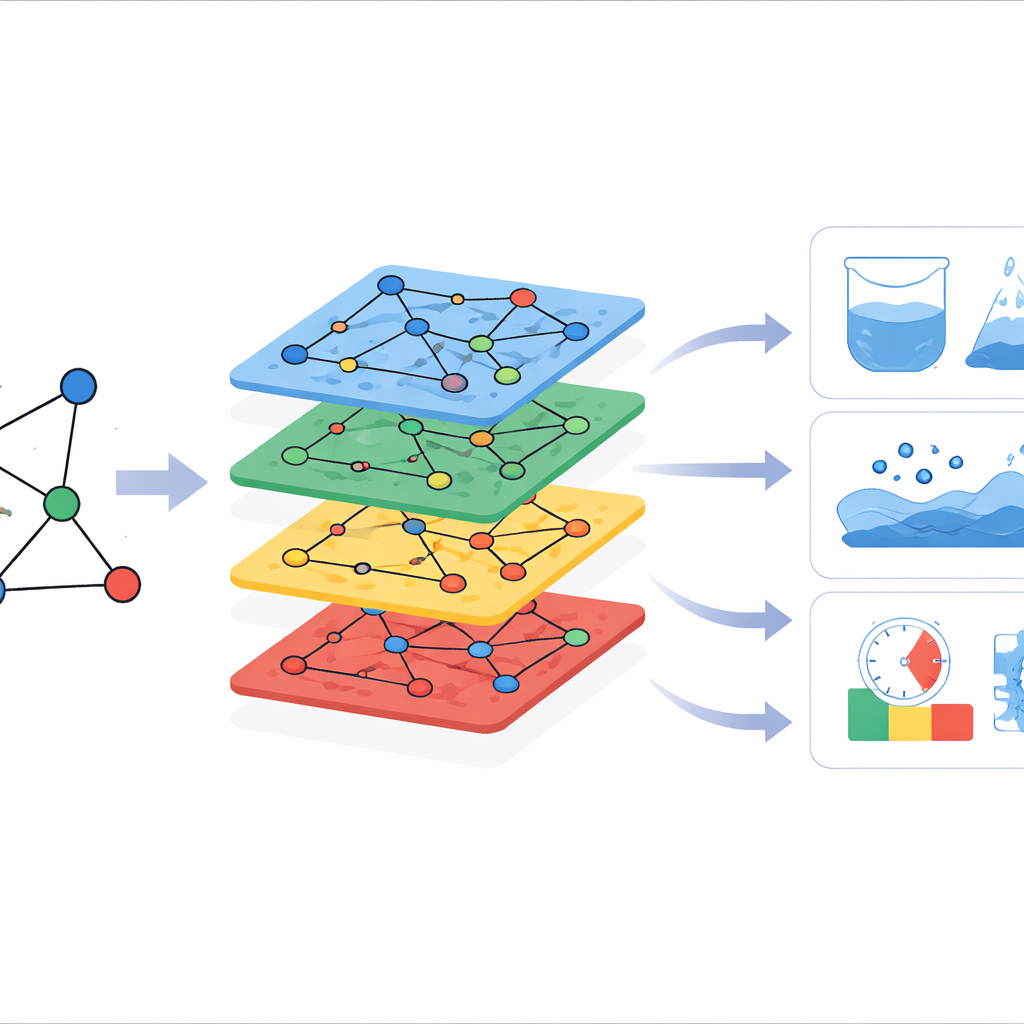
Co to oznacza dla przyszłych odkryć leków
Podsumowując, badanie pokazuje, że starannie zaprojektowane współ-wskaźniki topologiczne, generowane z wielomianów CoM i CoNM, mogą służyć jako skuteczne substytuty pomiarów laboratoryjnych właściwości leków przeciwwirusowych. Dzięki dokładnemu przewidywaniu zachowania kandydatów molekularnych, te narzędzia matematyczne pomagają naukowcom szybko filtrować duże biblioteki związków, skupiać eksperymenty na najbardziej obiecujących kandydatach i dopracowywać projekty molekularne przed syntezą. Chociaż nie zastępują testów biologicznych, takie deskryptory oferują szybki, niskokosztowy sposób poruszania się po przestrzeni chemicznej — co jest szczególnie cenne w reakcji na szybko rozwijające się zagrożenia, takie jak Ebola i inne pojawiające się choroby zakaźne.
Cytowanie: Meharban, S., Ullah, A., Zaman, S. et al. On topological co-index polynomials for predictive modeling of the physicochemical properties of antiviral drugs. Sci Rep 16, 12456 (2026). https://doi.org/10.1038/s41598-026-43640-3
Słowa kluczowe: Leki przeciwwirusowe przeciwko Ebola, wskaźniki topologiczne, modelowanie QSPR, teoria grafów molekularnych, komputerowe projektowanie leków