Clear Sky Science · pl
Pomiar genomu diploidalnego Acrossocheilus wenchowensis zbliżony do telomer-do-telomeru
Dlaczego ta ryba potoku górskiego ma znaczenie
Acrossocheilus wenchowensis, czasem nazywany słodkowodnym okoniem, może wyglądać jak zwykła ryba rzeczna, ale w południowych Chinach ceniona jest zarówno jako pokarm, jak i gatunek ozdobny. Żyje w chłodnych potokach górskich, ma smaczne mięso bogate w korzystne tłuszcze i wykazuje wyraźne różnice wzrostu między samcami a samicami — cechy te czynią ją atrakcyjną do hodowli. Aby zrozumieć i w końcu zarządzać tymi cechami, naukowcy potrzebują kompletnej instrukcji dla tej ryby: jej genomu. Badanie to dostarcza jeden z najbardziej kompletnych genomów ryb dostępnych do tej pory, złożony niemal od jednego końca chromosomu do drugiego.
Kompletny podręcznik od początku do końca
Autorzy postawili sobie za cel zbudowanie genomu A. wenchowensis zbliżonego do „telomer-do-telomeru”. Telomery to ochronne czapeczki na końcach chromosomów, a odczytanie sekwencji od jednego końca do drugiego bez przerw jest złotym standardem jakości genomu. Wykorzystując kilka nowoczesnych technologii sekwencjonowania DNA, zmontowali dwa kompletne zestawy chromosomów — po jednym pochodzącym od każdego z rodziców w tym gatunku diploidalnym. Każdy zestaw, czyli haplotyp, obejmuje około 860–870 milionów nukleotydów, z długimi, ciągłymi odcinkami, które zdecydowanie przewyższają wcześniejsze genomy ryb. Dla większości chromosomów zespół był w stanie odtworzyć sekwencję od jednego telomeru do drugiego, pozostawiając jedynie garstkę drobnych luk.
Odnajdywanie ukrytych kotwic genomu
Ponad samo ułożenie sekwencji DNA, badacze szukali kluczowych cech strukturalnych organizujących chromosomy. Odkryli powtarzającą się sekwencję DNA o długości 262 zasad, która występuje raz na każdym chromosomie i oznacza centromer — centralny punkt kotwiczenia niezbędny do prawidłowego rozdziału chromosomów podczas podziału komórki. Ten repeat pochodzi z mobilnego elementu genetycznego, co ujawnia, jak „skaczące” DNA przyczyniło się do ukształtowania kręgosłupa chromosomów. Wokół tych centromerów genów jest niewiele, podczas gdy inne elementy powtarzalne gromadzą się gęsto — wzorzec znany także u ludzi i innych zwierząt. Posiadanie takiego poziomu szczegółu dla genomu ryby jest rzadkie i otwiera możliwość badania, jak struktura chromosomów wpływa na cechy w toku ewolucji.
Wypatrując różnic między dwoma zestawami chromosomów
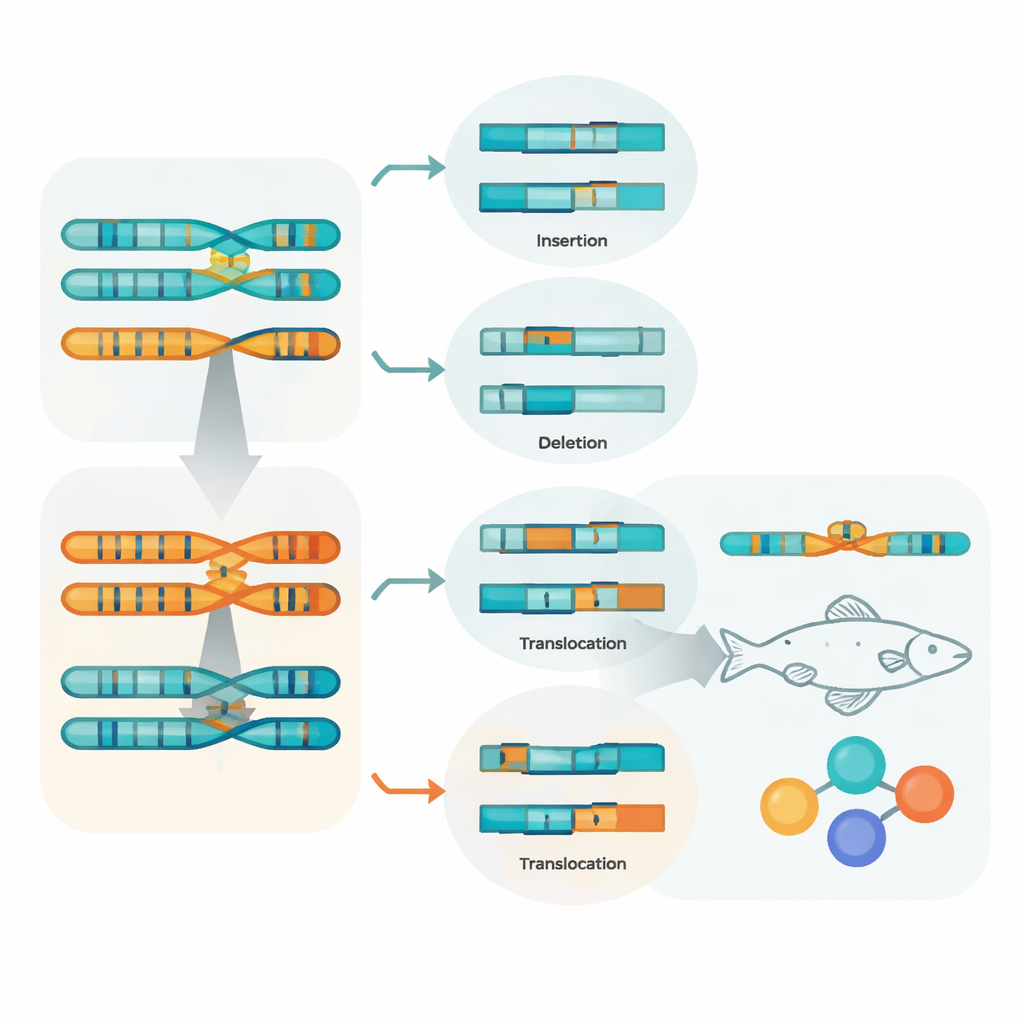
Dzięki zachowaniu oddzielnych dwóch haplotypów rodzicielskich, zespół mógł bezpośrednio je porównać i skatalogować różnice. Stwierdzili miliony pojedynczych zmian nukleotydowych, setki tysięcy niewielkich insercji i delecji oraz tysiące większych przearanżowań, takich jak odwrócenia fragmentów, duplikacje, przemieszczania lub zmiany w liczbie kopii. Wiele z tych zmian pokrywa się z mobilnymi elementami genetycznymi, co sugeruje, że te ruchome sekwencje są głównymi motorami zmian strukturalnych. Gdy warianty zachodziły na geny, większość leżała w obrębie samych genów, a wiele małych insercji lub delecji przewidywano jako zmieniające białka. Ta szczegółowa mapa pokazuje, ile zmienności może istnieć nawet w genomie pojedynczego osobnika.
Śledzenie historii rodzinnej i regionalnych różnic
Posiadając ten genom referencyjny, autorzy porównali A. wenchowensis z pokrewnymi karpiami i kiełbiami. Ich analizy sugerują, że jego rodzaj, Acrossocheilus, rozdzielił się z bliskiego kuzynowskiego rodzaju Onychostoma około 13,7 miliona lat temu, a A. wenchowensis oddzielił się od swego bliskiego krewnego A. fasciatus około 5,25 miliona lat temu. Zespół przebadał także ponownie sekwencjonując 80 ryb z czterech regionów rzecznych w Chinach. Dane genetyczne wykazały, że większość populacji jest stosunkowo podobna i wymienia geny, ale jedna grupa z Longyan (LY) wyróżnia się znacznie większym dystansem genetycznym od pozostałych. Wzorzec ten wskazuje na ograniczone mieszanie się i lokalną adaptację, co może mieć praktyczne konsekwencje dla zarządzania dzikimi zasobami i programów hodowlanych.
Co to oznacza dla akwakultury i biologii
Dla osób niebędących specjalistami kluczową wiadomością jest to, że naukowcy stworzyli wyjątkowo kompletny plan budowy komercyjnie i ekologicznie istotnej słodkowodnej ryby. To źródło pokazuje, gdzie zaczynają się i kończą jej chromosomy oraz gdzie mają kotwice; jak różnią się dwa rodzicielskie zestawy DNA; jak gatunek wpisuje się w szersze drzewo rodowe ryb; oraz jak populacje rozsiane po Chinach różnią się genetycznie. Taka wiedza stanowi fundament do przyszłych badań nad determinacją płci, wzrostem oraz adaptacją do zmieniających się warunków środowiskowych. Z czasem ten genom może pomóc hodowcom opracować bardziej wydajne, zrównoważone linie akwakulturalne i wspomóc konserwatorów w ochronie różnorodności genetycznej ryb potoków górskich.
Cytowanie: Xue, L., Luo, M., Wang, H. et al. Near telomere-to-telomere diploid genome assembly of Acrossocheilus wenchowensis. Sci Data 13, 452 (2026). https://doi.org/10.1038/s41597-026-06752-z
Słowa kluczowe: genom ryby, telomer do telomeru, słodkowodny okoń, genetyka populacji, akwakultura