Clear Sky Science · pl
Analiza porównawcza genomu dostarcza podstaw do zdefiniowania biosyntezy salwinoryny A w Salvia divinorum
Roślina halucynogenna z obietnicą medyczną
Salvia divinorum, czasem nazywana „szałwią wróżbitów”, jest znana z wywoływania krótkotrwałych, lecz intensywnych halucynacji po spożyciu liści. Ten sam związek odpowiadający za te doświadczenia — salwinoryna A — jest dziś badany jako wzorzec do opracowywania nowych leków przeciwbólowych, przeciwdepresyjnych i wspomagających leczenie uzależnień. Badanie stawia pozornie proste pytanie o dużych implikacjach: jak roślina syntetyzuje salwinorynę A i jak ewoluowała ta ścieżka chemiczna? Odpowiedź może pozwolić naukowcom odtworzyć związek i pokrewne molekuły w kontrolowanych systemach, bez polegania na trudnej w uprawie roślinie.
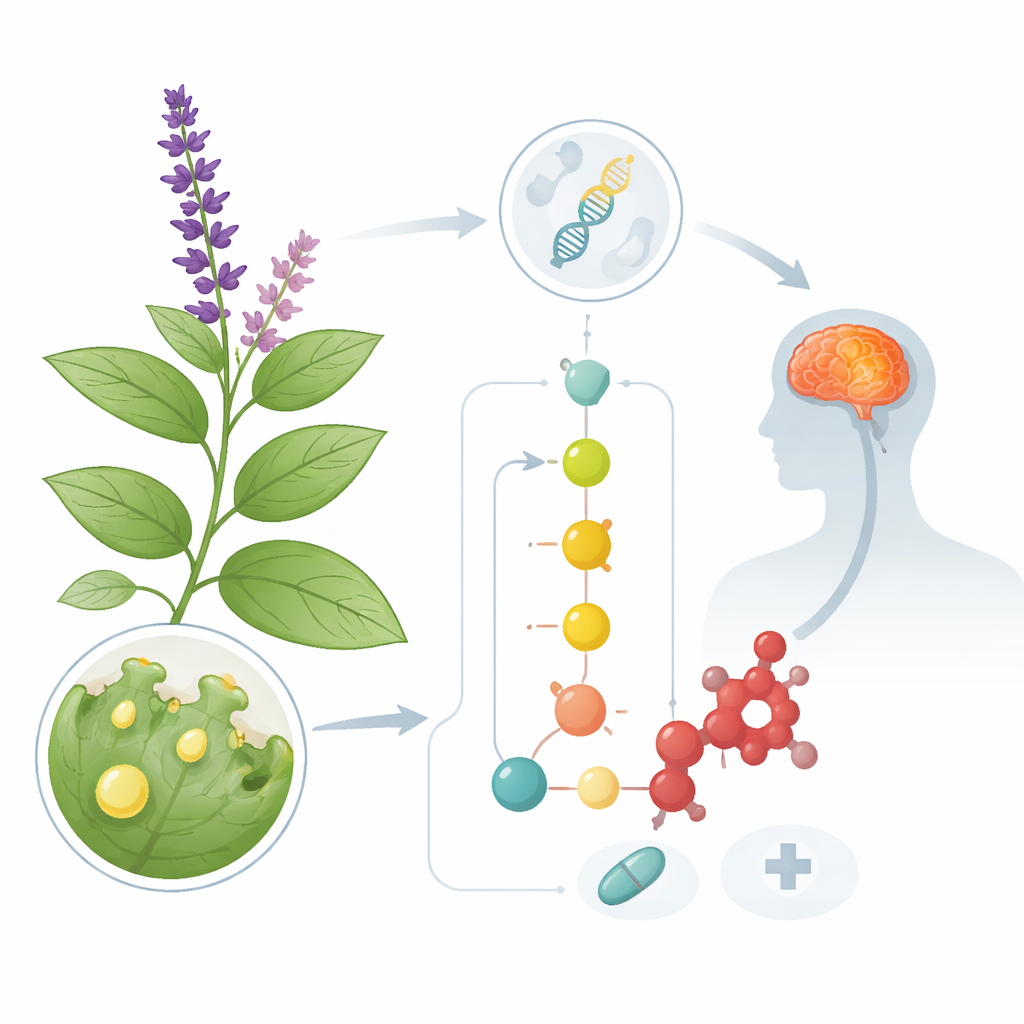
Od świętej rośliny do obiektu badań
Salvia divinorum rośnie naturalnie w lasach mglistych stanu Oaxaca w Meksyku, gdzie od dawna jest stosowana przez uzdrowicieli Mazateków w obrzędach. Współczesna farmakologia wykazała, że salwinoryna A oddziałuje na specyficzne białko w mózgu — receptor opioidowy kappa — gdzie może tłumić pewne rodzaje bólu i zmniejszać nagradzające działanie substancji uzależniających. Niestety roślina jest rzadka, trudna w uprawie i daje jedynie niewielkie ilości związku. Całkowita synteza chemiczna jest możliwa, ale zbyt skomplikowana i kosztowna do zastosowań na dużą skalę. Aby udostępnić salwinorynę A jako praktyczny lek, badacze potrzebują szczegółowej mapy wewnętrznej linii montażowej rośliny, tak aby ścieżkę można było odbudować w mikrobach lub innych uprawach.
Czytanie instrukcji rośliny
Zespół wygenerował wysokiej jakości genom na poziomie chromosomów dla Salvia divinorum — pełny spis jej instrukcji DNA. Następnie porównano ten genom z genomami kilku krewnych z rodziny szałwiowatych, w tym kulinarnego rozmarynu i chia, a także blisko spokrewnionych gatunków ozdobnych i leczniczych. Porównania ujawniły, kiedy różne linie szałwi rozdzieliły się od siebie na przestrzeni dziesiątek milionów lat i uwydatniły epizody duplikacji całego genomu, w których cały zestaw genów został skopiowany. Takie zdarzenia duplikacyjne są powszechnym silnikiem innowacji u roślin, ponieważ dodatkowe kopie genów mogą ewoluować nowe funkcje bez zakłócania starych.
Budowanie ścieżki chemicznej krok po kroku
Salwinoryna A należy do rodziny cząsteczek zwanych furanoklerodanowymi diterpenoidami, które roślina wytwarza w drobnych „fabrykach” na powierzchni liścia zwanych gruczołowatymi włoskami (trichomami). Wcześniejsze prace zidentyfikowały już pierwsze etapy tej ścieżki, które budują podstawowy szkielet węglowy z prostych jednostek wyjściowych. Nakładając dane o aktywności genów z trichomów na nowy genom, autorzy mogli wskazać dodatkowe geny włączone tam, gdzie powstaje salwinoryna A. Skoncentrowali się na dwóch głównych grupach enzymów: białkach cytochromu P450, które wprowadzają atomy tlenu w precyzyjnych pozycjach na szkielecie węglowym, oraz metylotransferazach, które przyłączają małe grupy metylowe.
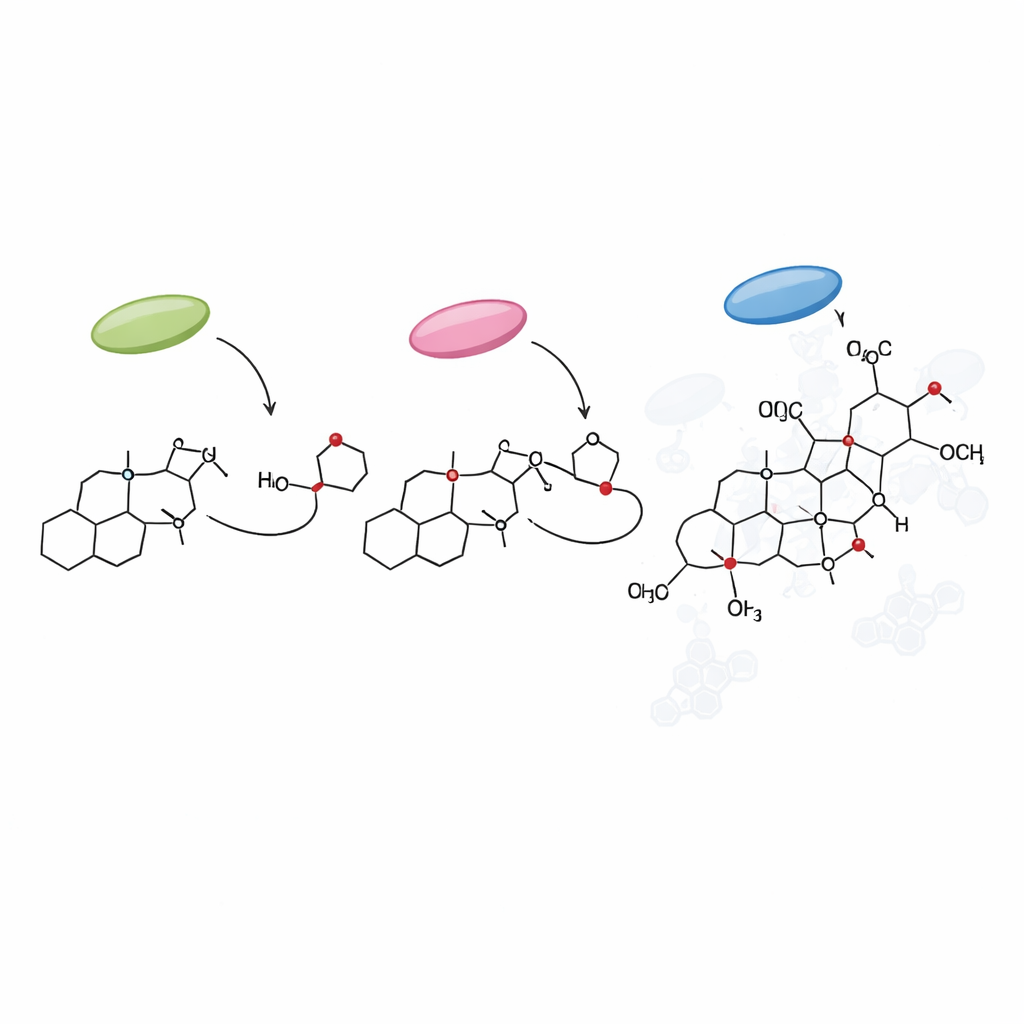
Nowe enzymy formujące rdzeń salwinoryny
Poprzez połączenie ewolucyjnego detektywistycznego podejścia i praktycznych eksperymentów w liściach tytoniu, badacze odkryli kilka brakujących kroków w ścieżce. Pokazali, że jeden enzym P450, nazwany zakonotowo annonene synthase, prawdopodobnie pojawił się po duplikacji całego genomu specyficznej dla amerykańskich szałwii i został przekształcony z starszego enzymu działającego na inną klasę związków roślinnych. Drugi klaster enzymów P450 z rodziny CYP728D okazał się przeprowadzać serię precyzyjnych utlenień, przekształcając pośrednik zwany kwasem hardwickiowym w „divinatoriny”, kluczowe pośrednie związki na drodze do salwinoryny A. Inny enzym, metylotransferaza z rodziny SABATH, potwierdzono jako odpowiedzialny za metylację konkretnej grupy karboksylowej — subtelna modyfikacja chemiczna wydająca się unikalna dla Salvia divinorum i kluczowa dla zakończenia jednego z głównych pośredników.
Jak ewolucja ukształtowała silny produkt naturalny
Śledząc położenie tych genów w genomie i ich relacje z odpowiednikami w innych gatunkach szałwii, badanie pokazuje, że biosynteza salwinoryny A nie pojawiła się nagle. Zamiast tego powstała stopniowo, gdy skopiowane geny były przetasowywane, lokalnie ponownie kopiowane i przesuwane do nowych ról, zwłaszcza w trichomach liści. Niektóre krewniaki produkują pokrewne klerodany, lecz brak im całego zestawu wyspecjalizowanych enzymów obecnych w Salvia divinorum, co podkreśla, jak niewielkie, specyficzne dla linii zmian mogą dać bardzo różne profile chemiczne. Zrozumienie tego ewolucyjnego „majsterkowania” dostarcza mapy drogowej do odkrycia pozostałych nieznanych kroków i do racjonalnej modyfikacji ścieżki w celu stworzenia nowych, potencjalnie terapeutycznych molekuł.
Od ewolucji roślin do przyszłych leków
Autorzy konkludują, że posiadając kompletny genom i niemal ukończoną ścieżkę biosyntezy salwinoryny A, stworzono podstawy do produkcji tego związku — oraz jego ulepszonych wariantów — bez polegania na dziko rosnących lub szklarniowych roślinach. W praktyce przybliża to badaczy do zaprojektowania drożdży, bakterii lub innych upraw do wytwarzania furanoklerodanów na dużą skalę. Dla osób niebędących specjalistami kluczowy wniosek jest taki, że czytając i porównując genomy roślin, naukowcy mogą zarówno odtworzyć, jak potężne produkty naturalne ewoluowały, jak i ponownie wykorzystać te same instrukcje genetyczne do opracowania nowej generacji terapii przeciw bólowi, uzależnieniom i zaburzeniom psychicznym.
Cytowanie: Li, H., Sun, Y., Xu, W. et al. Comparative genome analysis provides a foundation for defining salvinorin A biosynthesis in Salvia divinorum. Nat Commun 17, 3414 (2026). https://doi.org/10.1038/s41467-026-70885-3
Słowa kluczowe: Salvia divinorum, salwinoryna A, specjalizowany metabolizm roślinny, genomika porównawcza, odkrywanie leków z naturalnych produktów