Clear Sky Science · it
Potenziali biomarcatori del sarcoma di Ewing identificati tramite un’analisi paneuropea su campioni raccolti prospetticamente
Perché questo studio sul cancro infantile è importante
Il sarcoma di Ewing è un tumore raro ma aggressivo che colpisce principalmente bambini e giovani adulti, spesso originando nelle ossa e diffondendosi rapidamente ai polmoni o ad altre ossa. I medici possono valutare l’estensione della malattia, ma faticano ancora a prevedere quali pazienti avranno un buon esito e quali correranno il rischio maggiore di recidiva, anche quando ricevono la stessa chemioterapia moderna. Questo studio paneuropeo si è proposto di trovare segnali biologici all’interno del DNA e dell’RNA del tumore che possano aiutare a personalizzare il trattamento, come la pressione arteriosa guida le cure cardiovascolari. 
Uno sguardo più ravvicinato nei tumori del sarcoma di Ewing
Il team di ricerca ha raccolto 335 campioni tumorali da pazienti con sarcoma di Ewing di nuova diagnosi trattati in grandi trial clinici europei nel corso di due decenni. Tutti i campioni sono stati prelevati prima della chemioterapia e processati con protocolli condivisi in biobanche specializzate. Invece di concentrarsi su una singola mutazione, gli scienziati hanno misurato dieci diversi “biomarcatori”. Alcuni erano geni individuali o piccoli RNA regolatori, come MIR34A, STEAP1, EZH2, DKK2 e LGALS3BP, valutati mediante colorazione di sezioni tumorali o PCR quantitativa. Altri riflettevano cambiamenti più ampi nel genoma, come guadagni o perdite di interi bracci cromosomici (ad esempio 1q o 16q), piccole cancellazioni che interessano una regione genica chiamata ADAM3A, la percentuale complessiva del genoma alterata e l’estensione della perdita di eterozigosi nel genoma, ossia la perdita delle coppie normali di copie geniche.
Collegare i segnali tumorali agli esiti dei pazienti
Per ciascun biomarcatore, gli investigatori si sono posti due domande: come si relazionava a caratteristiche cliniche consolidate (come età, dimensione del tumore, localizzazione pelvica o presenza di metastasi alla diagnosi) e quanto prevedeva la sopravvivenza. Per farlo hanno raggruppato i pazienti in categorie “alte” o “basse” per ogni marker e utilizzato modelli statistici che tengono conto di altri fattori di rischio. Hanno inoltre calcolato le dimensioni dell’effetto per valutare quanto ogni segnale fosse clinicamente rilevante, non solo se superasse una soglia di P‑value. Lo studio ha rilevato che la maggior parte dei marcatori era solo debolmente correlata tra loro, suggerendo che catturassero aspetti diversi della biologia tumorale piuttosto che riflettere un singolo cambiamento sottostante.
Il caos genomico come segnale di allarme
I segnali più potenti provenivano da marcatori che catturavano quanto il DNA del tumore fosse diventato disordinato. Una alta percentuale del genoma alterata (PGA) e un’ampia perdita di eterozigosi erano entrambe associate a un rischio chiaramente più elevato di eventi come recidiva e morte, anche dopo aggiustamento per metastasi, dimensione del tumore e altri fattori noti. I pazienti i cui tumori mostravano cambiamenti di numero di copie più diffusi o LOH tendevano ad avere tumori pelvici, rispondere meno bene alla chemioterapia a livello istologico e avevano maggior probabilità di morire durante il follow‑up. I guadagni di 1q e le perdite di 16q spesso si presentavano insieme e si correlavano con questa instabilità genomica più ampia, rafforzando l’idea che squilibri del DNA su larga scala, più che singole mutazioni puntiformi, contribuiscano alla malattia aggressiva. 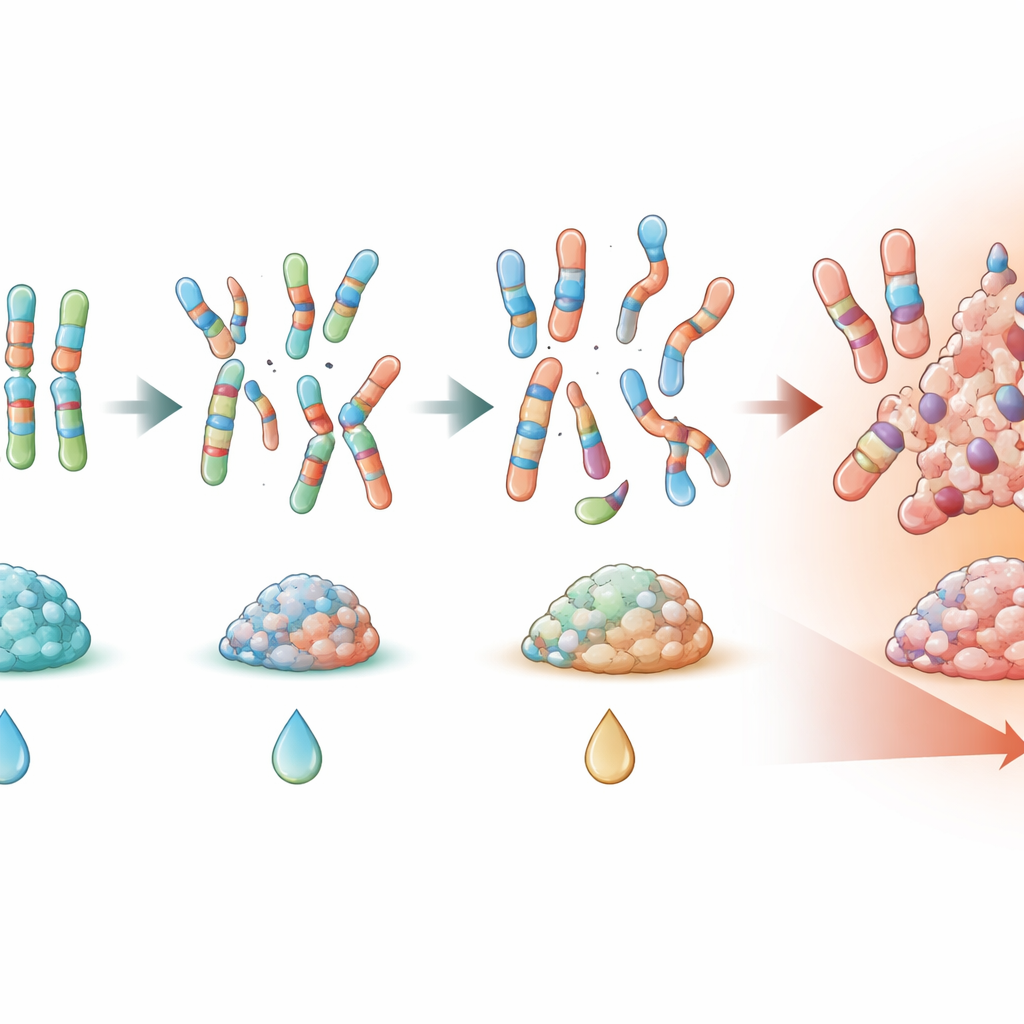
Un segnale protettivo da un piccolo RNA
In contrasto con i marcatori del caos genomico, un’espressione più alta di MIR34A, un piccolo RNA regolatorio precedentemente collegato alla morte cellulare e alla sensibilità alla chemioterapia, era associata a esiti migliori. I pazienti con tumori ricchi di MIR34A hanno sperimentato meno recidive e decessi, e questo effetto è rimasto forte anche dopo l’aggiustamento per fattori clinici standard. Studi di laboratorio precedenti hanno mostrato che MIR34A può silenziare geni che promuovono la divisione cellulare, la sopravvivenza e la diffusione; questo ampio dataset clinico supporta ora il suo ruolo come influenza oncosoppressiva nel sarcoma di Ewing. Una forte espressione membranosa della proteina di superficie STEAP1 è risultata anch’essa associata a migliore sopravvivenza nei pazienti con malattia localizzata, mentre un’espressione elevata di EZH2 era più comune nei pazienti già metastatici alla diagnosi, sebbene EZH2 di per sé non abbia predetto chiaramente la sopravvivenza in questa coorte.
Cosa significa per le cure future
Nel complesso, l’analisi paneuropea suggerisce che tre marcatori emergono come particolarmente informativi per la prognosi del sarcoma di Ewing: ampia perdita di eterozigosi, elevata frazione del genoma alterata e bassi livelli di MIR34A. I tumori con DNA fortemente frammentato e privi di questo RNA protettivo hanno maggior probabilità di comportarsi in modo aggressivo, mentre quelli con genomi più ordinati e livelli più alti di MIR34A tendono a seguire un decorso più favorevole. Pur non essendo ancora parte della pratica clinica di routine, questi marcatori offrono una strada verso test su sangue o tessuto che potrebbero aiutare i medici a identificare i bambini che necessitano di terapie intensificate e quelli che potrebbero evitare tossicità aggiuntive, avvicinando così la terapia veramente personalizzata per questo cancro difficile.
Citazione: Ranft, A., Richter, G.H.S., Diaz-Martin, J. et al. Potential biomarkers of Ewing sarcoma identified through a Europe-wide analysis of prospectively collected samples. Sci Rep 16, 11613 (2026). https://doi.org/10.1038/s41598-026-43071-0
Parole chiave: Sarcoma di Ewing, biomarcatori del cancro, instabilità genomica, oncologia pediatrica, prognosi