Clear Sky Science · it
Traiettoria genomica distinta nelle infezioni invasive da Salmonella Typhimurium ST313
Perché questa storia di infezioni del sangue è importante
In molte regioni a basso reddito, in particolare nell’Africa subsahariana, una forma pericolosa di Salmonella non si limita a causare intossicazione alimentare: invade il flusso sanguigno, provocando malattie gravi e molte vittime ogni anno. Questo studio pone una domanda urgente: come si è evoluto e diffuso nel mondo un particolare tipo genetico di questo batterio, chiamato ST313, e perché alcuni rami diventano più difficili da trattare? Tracciando l’albero genealogico del microbo in oltre 3.000 genomi, i ricercatori rivelano come l’uso di antibiotici, i movimenti umani e sottili cambiamenti nel DNA stiano rimodellando una minaccia importante per la salute pubblica.
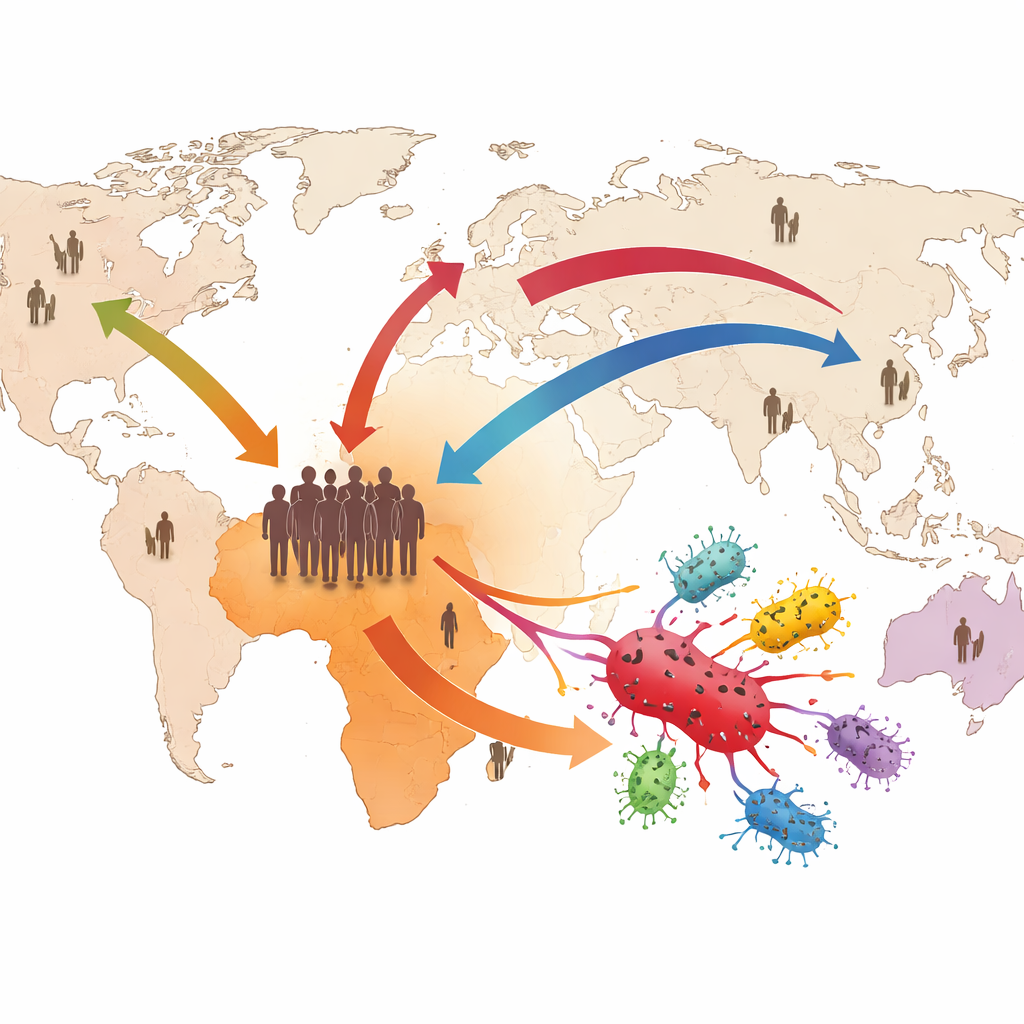
Uno sguardo più attento su un peso silenzioso a livello globale
Le infezioni invasive da Salmonella non tifoidea si verificano quando batteri che di solito causano malattie intestinali riescono a entrare nel sangue o in altri siti normalmente sterili, come il liquido cerebrale. Queste infezioni sono particolarmente pericolose per i bambini piccoli, gli anziani, le persone con HIV e chi è malnutrito. I ricercatori hanno assemblato il più ampio set di dati globale finora: oltre 11.000 di queste infezioni invasive e, all’interno di esso, 3.115 genomi del tipo ST313 di Salmonella Typhimurium raccolti tra il 1966 e il 2023. La maggior parte dei campioni ST313 proveniva dal sangue e la maggior parte dai pazienti africani, sottolineando quanto questo patogeno sia legato alla malattia ematica grave su quel continente.
Nuovi rami nell’albero familiare della Salmonella
Confrontando minuscole differenze nel DNA tra tutti i genomi ST313, il team ha mappato come questo batterio si suddivide in diverse linee principali e quando probabilmente sono emerse. Sono emerse due nuove varianti: una linea principale fino ad ora non riconosciuta (chiamata L4) e un nuovo sottoramo all’interno della linea dominante 2 (denominato 2.4). L4 sembra essersi sviluppata secoli fa in Asia prima di spostarsi in Africa, dove oggi mantiene una popolazione consistente. Al contrario, il sottoramo 2.4 è un ramo recente in rapida espansione nell’Africa orientale, in particolare in Kenya. L’analisi mostra inoltre che diverse linee si sono mosse più volte tra i continenti, probabilmente facilitate dai viaggi e dal commercio moderni, con la maggior parte delle dispersioni a lunga distanza che avvengono da o verso l’Africa.
Gli antibiotici come forze evolutive nascoste
Uno dei segnali più forti nei dati è come l’uso di antibiotici abbia indirizzato il successo o il declino delle linee. Lavori precedenti avevano mostrato che la resistenza al cloramfenicolo aveva aiutato una linea (L2) a rimpiazzare un’altra (L1) intorno al 2001. Questo studio va oltre catalogando i geni di resistenza e i loro vettori mobili – plasmidi, trasposoni e virus che trasferiscono DNA tra i batteri. I ricercatori rilevano che L2, e in particolare il suo sottoramo 2.4, porta un pesante carico di geni di resistenza, inclusi quelli che degradano farmaci moderni come le cefalosporine a spettro esteso e l’azitromicina. Nel frattempo, la più anziana L1 ha acquisito resistenza solo più tardi, per poi iniziare a perdere elementi chiave di resistenza dopo il 2005 in Malawi, in coincidenza con cambiamenti nelle politiche terapeutiche locali – e la sua popolazione è diminuita poco dopo. Questo suggerisce che quando certi antibiotici escono dall’uso, i batteri che sostengono un “costo” per mantenere resistenze non necessarie possono perdere terreno.
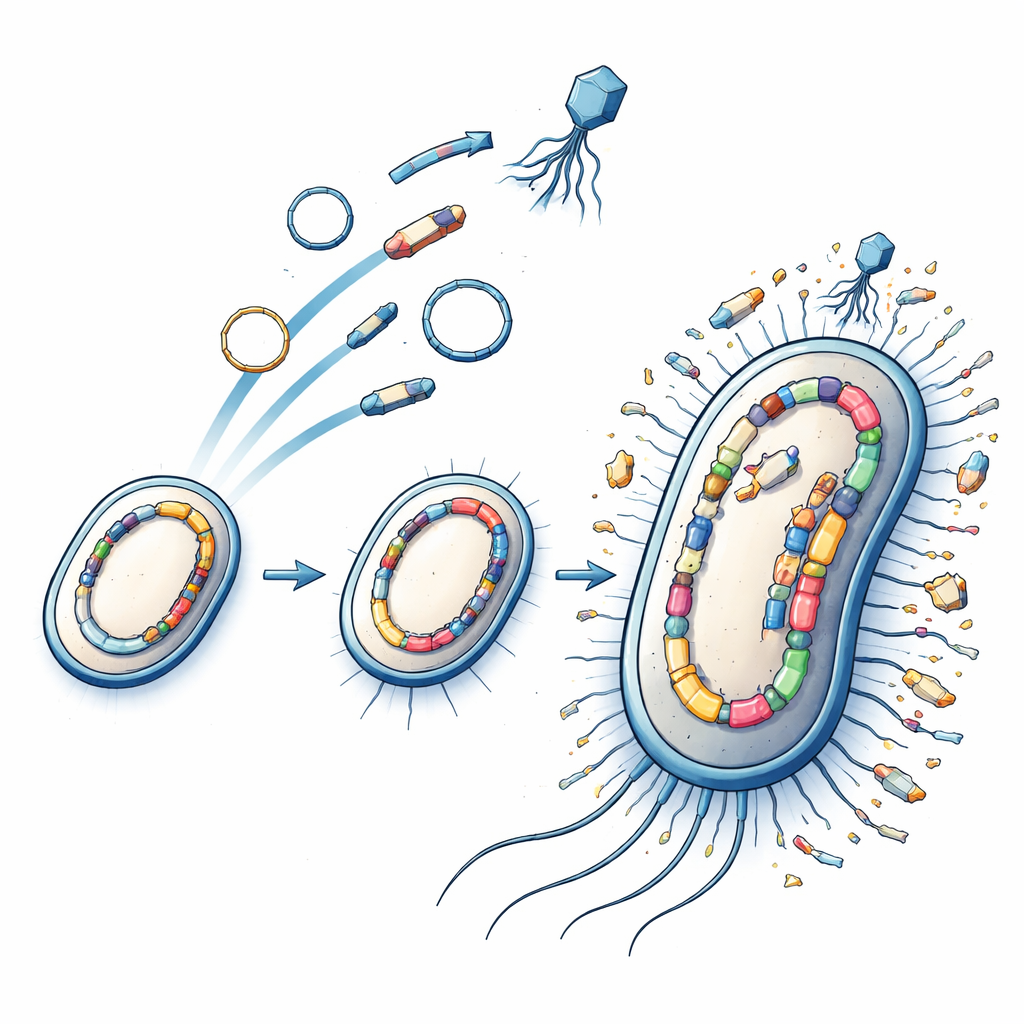
Manomissioni del genoma che aumentano l’invasività
La resistenza ai farmaci è solo una parte della storia. Gli autori hanno anche seguito come altri cambiamenti genetici possano rendere ST313 più incline a lasciare l’intestino e invadere il sangue. Hanno misurato un “indice di invasività” basato su quali geni sono intatti, danneggiati o mancanti, riflettendo un modello più ampio di degradazione del genoma osservato nei patogeni adattati all’ospite. Alcune linee, come L3, mostrano punteggi particolarmente elevati, mentre L4 e L5 sembrano associare una resistenza moderata a un’aumentata invasività. Un’analisi del pan‑genoma – sostanzialmente un censimento di tutti i geni presenti tra i ceppi – ha rivelato centinaia di geni accessori la cui presenza si associa al successo di linee specifiche. Molti di questi geni appartengono a percorsi di riparazione del DNA e a elementi mobili, suggerendo che gli stessi meccanismi che spostano i geni di resistenza potrebbero anche mettere a punto la capacità del batterio di sopravvivere nell’organismo umano.
Cosa significa per la sorveglianza e le cure future
Nel complesso, i risultati dipingono ST313 come un patogeno il cui destino è strettamente legato al comportamento umano: quali antibiotici vengono usati, come le persone si spostano oltre i confini e quanto bene i sistemi sanitari monitorano le infezioni. Un sottoramo altamente resistente e in rapida crescita (2.4) e una linea di lunga data ma ora in espansione (L4) hanno entrambi acquisito kit genetici che possono favorire l’invasione del sangue e il fallimento dei trattamenti. Per i non specialisti, il messaggio chiave è che le politiche sugli antibiotici e la sorveglianza globale non si limitano a reagire all’evoluzione batterica: contribuiscono a plasmarla. Monitorare queste linee, soprattutto in Africa ma anche nei paesi che ricevono viaggiatori e importazioni alimentari, sarà essenziale per scegliere farmaci efficaci, progettare vaccini futuri e ridurre i decessi dovuti alle infezioni invasive da Salmonella.
Citazione: Jia, C., Zhou, H., Cao, Q. et al. Distinct genomic trajectory among invasive Salmonella Typhimurium ST313 infections. Nat Commun 17, 3693 (2026). https://doi.org/10.1038/s41467-026-70196-7
Parole chiave: Salmonella invasiva, resistenza antimicrobica, epidemiologia genomica, evoluzione batterica, sorveglianza sanitaria globale