Clear Sky Science · fr
Évaluation de l’immunogénicité et cartographie des épitopes du protéome du VASV par profilage des anticorps sériques avec des bibliothèques de phages portant des antigènes du VASV
Pourquoi cela compte pour les agriculteurs et la sécurité alimentaire
La fièvre porcine africaine est une maladie virale mortelle du porc qui a décimé des cheptels et ébranlé le marché mondial du porc, en particulier dans les pays à forte population porcine comme la Chine. En l’absence d’un vaccin sûr et efficace, les flambées sont principalement maîtrisées par des abattages massifs, ce qui est dévastateur pour les éleveurs et les prix des denrées. Cette étude pose une question simple mais essentielle : que « voit » exactement le système immunitaire du porc lorsqu’il combat ce virus, et comment ces connaissances peuvent-elles être traduites en meilleurs tests et, à terme, en vaccins ?
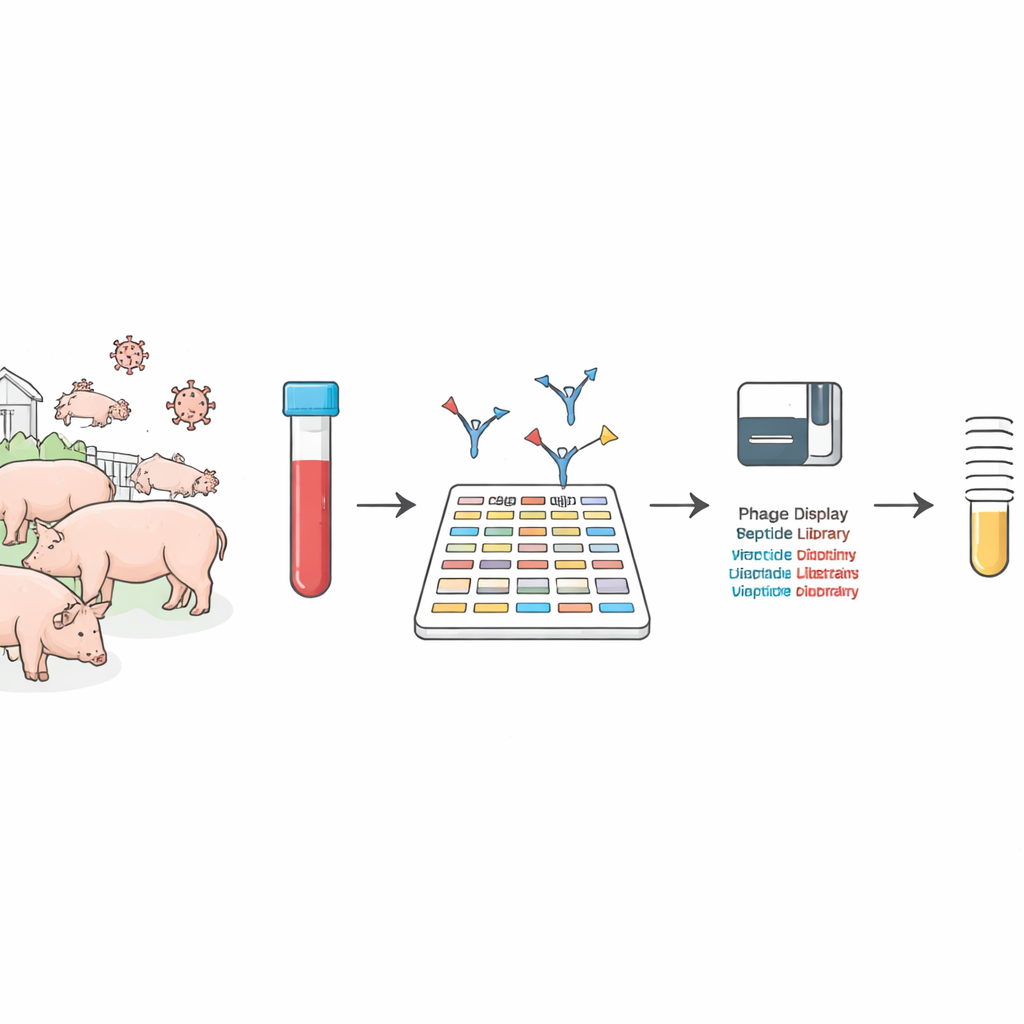
Lire le système immunitaire comme un code‑barres
Les chercheurs ont utilisé une méthode à haut débit appelée phage display séquencé pour examiner en profondeur les anticorps présents dans le sang de porc. Plutôt que de tester une protéine virale à la fois, ils ont construit deux immenses collections de phages inoffensifs, chacun affichant à sa surface un petit fragment du virus de la fièvre porcine africaine ou d’autres virus courants chez le porc. Lorsqu’un sérum porcin est mélangé à ces collections, les anticorps s’accrochent aux fragments qu’ils reconnaissent. En séquençant les fragments capturés, l’équipe a pu reconstruire, en une seule passe, l’ensemble du paysage des cibles du système immunitaire porcin.
Suivre l’infection de la crise à la récupération
L’équipe a analysé le sang de 100 porcs, certains jamais infectés et d’autres à différents stades de la fièvre porcine africaine : début, phase intermédiaire et rétablissement. Ils ont constaté que les porcs en phase aiguë et précoce ne reconnaissaient que quelques fragments viraux, tandis que les animaux qui avaient survécu et récupéré présentaient un profil étendu et riche de reconnaissance par les anticorps à travers de nombreuses protéines virales. Cet « étalement » de la réponse suggère que le contrôle à long terme du virus dépend de l’atteinte de nombreuses cibles à la fois, et non d’une ou deux protéines célèbres. Leurs cartes ont aussi confirmé la fiabilité de la méthode en recoupant de nombreuses régions virales déjà répertoriées dans des bases de données publiques.
Dénicher une cible virale jusque‑là méconnue
Au‑delà de la confirmation de protéines bien étudiées, la découverte la plus marquante a été une protéine virale jusque‑là peu connue nommée DP238L. Des anticorps dirigés contre DP238L réapparaissaient systématiquement chez les porcs ayant récupéré de l’infection. En comparant les séquences virales de 169 souches différentes, les scientifiques ont trouvé que DP238L est fortement conservée — c’est‑à‑dire qu’elle change très peu au fil de l’évolution du virus — et qu’elle est largement reconnue par les anticorps porcins. Les prédictions structurelles suggèrent que la majeure partie de DP238L est exposée et accessible au système immunitaire, et des « cartes thermiques » d’anticorps ont montré des réponses fortes le long de la plupart de sa longueur, la désignant comme une candidate de choix pour les vaccins et les tests diagnostiques.
Transformer les cartes d’épitope en outils opérationnels
Pour passer des cartes informatiques à l’utilisation pratique, l’équipe a produit DP238L en bactérie et testé si de vrais sérums porcins la reconnaissaient. Le sang des porcs infectés se liait fortement à la protéine DP238L purifiée, tandis que le sang des porcs sains ne le faisait pas, confirmant que DP238L se comporte comme un marqueur d’infection authentique. Les chercheurs ont également assemblé deux courts segments hautement réactifs d’autres protéines virales en une seule protéine « multi‑épitope » et ont montré que le sérum de porcs infectés reconnaissait aussi ce chimère. Enfin, ils ont immunisé des porcs avec DP238L et observé une réponse anticorps forte et durable ainsi qu’un profil équilibré de molécules de signalisation immunitaire, ce qui suggère que cette protéine peut déclencher en toute sécurité une réaction immunitaire robuste.
Ce que cela signifie pour les tests et les vaccins
Pour un lecteur non spécialiste, ce travail revient à dresser une carte détaillée des cibles que le virus présente au système immunitaire du porc, puis à tester lesquelles sont à la fois stables et faciles à atteindre. L’étude identifie 29 protéines virales clés et localise les régions les plus réactives dans chacune d’elles, DP238L se distinguant comme une cible particulièrement prometteuse. Ces observations peuvent orienter la conception de tests sanguins plus sensibles reposant sur plusieurs fragments viraux forts et conservés plutôt que sur un seul, rendant le diagnostic plus fiable à travers différentes souches virales. Elles fournissent également une feuille de route pour développer des vaccins ciblés et plus sûrs visant à reproduire la réponse immunitaire large et multi‑cibles observée chez les porcs survivants — une étape essentielle pour réduire les abattages, protéger les moyens de subsistance des agriculteurs et stabiliser l’approvisionnement mondial en porc.
Citation: Ma, L., Weng, Z., Zhang, Y. et al. Immunogenicity assessment and epitope mapping of the ASFV proteome by profiling serum antibodies with ASFV antigen phage libraries. Commun Biol 9, 448 (2026). https://doi.org/10.1038/s42003-026-09709-5
Mots-clés: Fièvre porcine africaine, immunité porcine, épîtopes viraux, conception de vaccins, diagnostic sérologique