Clear Sky Science · fr
Cadre de sélection de gènes hybride en deux étapes LASSO–HHO pour un diagnostic précis de la maladie d’Alzheimer
Pourquoi cette recherche compte pour la santé cérébrale
La maladie d’Alzheimer prive les personnes de leur mémoire et de leur autonomie, et nous manquons encore d’outils simples et largement disponibles pour la détecter tôt. Les techniques de laboratoire modernes peuvent mesurer l’activité de dizaines de milliers de gènes à partir d’un tout petit échantillon de tissu cérébral ou de sang, mais ce flot de données est difficile à transformer en réponses claires pour les cliniciens. Cet article présente une méthode intelligente en deux étapes pour trier ces informations génétiques et extraire un petit ensemble de gènes capable de diagnostiquer la maladie d’Alzheimer avec une très grande précision, tout en restant suffisamment rapide et pratique pour une utilisation réelle.
Transformer une aiguille dans une botte de foin de gènes en quelques indices
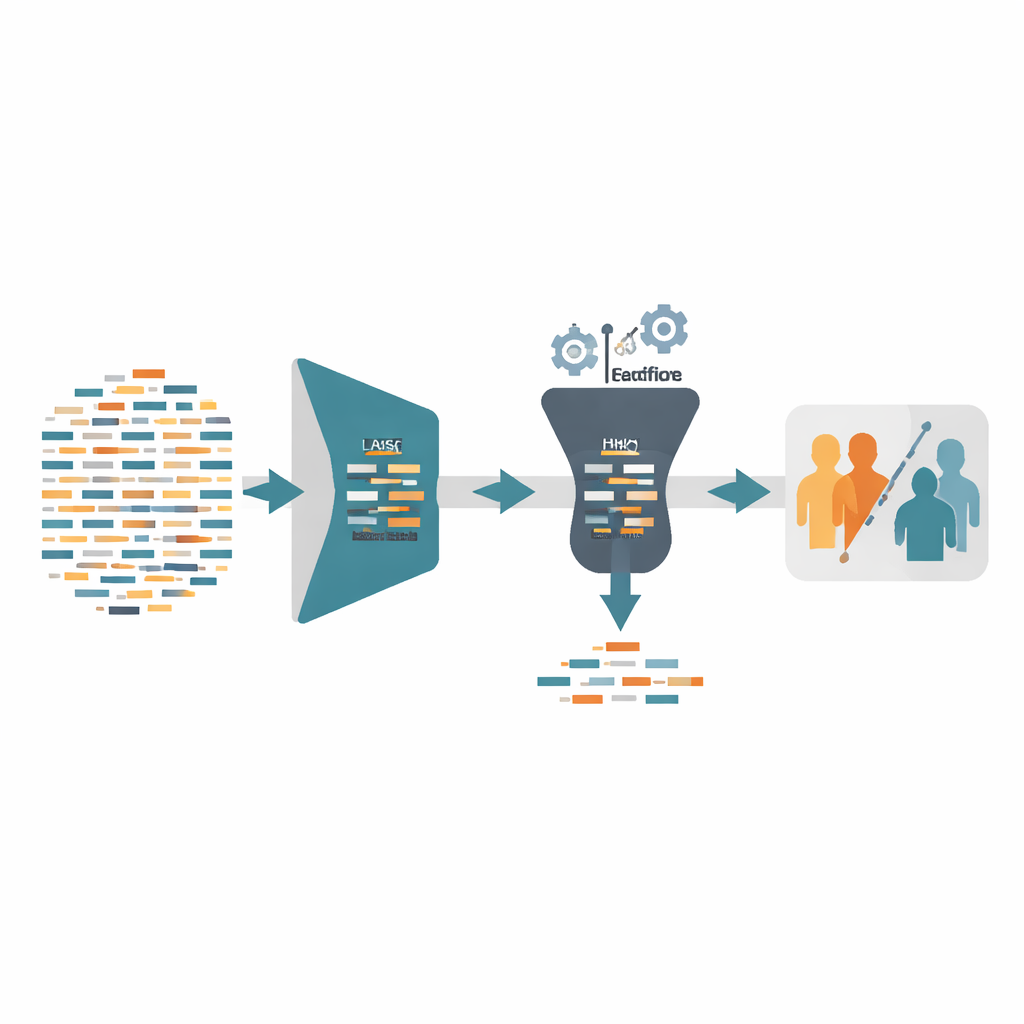
Chaque jeu de données d’expression génique d’Alzheimer utilisé dans cette étude contient plus de 20 000 gènes mais seulement quelques centaines de patients. Ce déséquilibre revient à essayer d’identifier une personne à partir de milliers de questions, avec des réponses provenant d’un petit groupe de volontaires : il est facile d’interpréter à tort du bruit aléatoire. Les auteurs s’attaquent à ce problème en appliquant d’abord une technique appelée LASSO, qui agit comme un filtre puissant. Elle ramène la plupart des signaux géniques à zéro et conserve uniquement ceux qui aident réellement à distinguer les personnes atteintes d’Alzheimer des témoins sains. À elle seule, cette première passe réduit souvent la liste des gènes de plus de 99 %, diminuant radicalement la complexité et le risque de surapprentissage, tout en préservant suffisamment d’information pour prédire la maladie.
Une seconde passe intelligente lorsqu’elle est nécessaire
Après cet élagage initial, le cadre lance conditionnellement une seconde étape basée sur une stratégie de recherche inspirée de la nature appelée Harris Hawks Optimization. Ici, chaque « faucon » représente un sous-ensemble possible de gènes, et les faucons ajustent répétitivement leurs positions pour chasser des combinaisons qui améliorent le diagnostic. Crucialement, cette étape n’est pas toujours utilisée. Si le LASSO seul atteint déjà au moins 99 % de précision et que l’ensemble de gènes sélectionné compte moins de 40 gènes, le processus s’arrête là. Sinon, la recherche basée sur les faucons affine davantage les gènes survivants, guidée par une règle de notation qui récompense fortement une haute précision diagnostique tout en favorisant un nombre réduit de gènes. Cette conception adaptative évite de gaspiller du temps de calcul lorsque la solution plus simple est déjà suffisante.
Mettre la méthode à l’épreuve
Les auteurs ont évalué leur cadre — nommé LHGS — sur quatre jeux de données publics d’Alzheimer provenant de différentes régions cérébrales et équipes de recherche. Ils ont entraîné un classificateur d’apprentissage automatique standard appelé machine à vecteurs de support en utilisant seulement les gènes sélectionnés, et ont jugé la performance avec des mesures courantes telles que la précision, la précision positive et le rappel. Dans certains jeux de données, le LASSO seul suffisait pour atteindre une précision parfaite ou quasi parfaite : un jeu de données n’a nécessité que trois gènes pour séparer correctement tous les échantillons Alzheimer et sains. Dans des jeux de données plus difficiles, l’ajout de la recherche basée sur les faucons a porté la précision à 100 % tout en maintenant l’ensemble final entre environ 11 et 37 gènes. Comparée à une série d’autres méthodes d’optimisation populaires, l’approche en deux étapes était à la fois plus précise et bien plus rapide, car la recherche lourde n’a lieu que dans l’espace fortement réduit créé par le LASSO.
Découvrir des marqueurs géniques prometteurs
Au-delà de la construction d’un bon prédicteur, l’étude met aussi en avant des gènes concrets qui pourraient jouer un rôle important dans la biologie de l’Alzheimer. En examinant l’ampleur de la contribution de chaque gène lors de l’étape LASSO, les auteurs ont identifié une courte liste de gènes constamment influents dans chaque jeu de données. Certains, tels que TRPM7 et des gènes impliqués dans la signalisation du stress, le contrôle de l’inflammation et la communication synaptique, sont déjà associés à la santé cérébrale et à la neurodégénérescence. D’autres sont moins bien compris, suggérant de nouvelles pistes pour des études de laboratoire. Le fait qu’un diagnostic fiable puisse être obtenu avec seulement quelques dizaines, voire quelques gènes, laisse entendre que des tests futurs pourraient se concentrer sur des panels ciblés et compacts plutôt que sur des puces larges et coûteuses.

Ce que cela signifie pour le futur du diagnostic de l’Alzheimer
Pour un non-spécialiste, le message principal est qu’il devient possible de lire la « signature » moléculaire de l’Alzheimer à partir d’un nombre étonnamment réduit de gènes, choisis parmi des dizaines de milliers par un processus soigneux en deux étapes. Le cadre LHGS montre que l’on peut combiner un filtre statistique rapide avec une seconde passe sélective pour obtenir à la fois précision et rapidité, rendant l’approche plus adaptée à des usages cliniques ultérieurs. Si les auteurs soulignent que leurs résultats doivent être confirmés sur des cohortes plus larges et plus variées, et que des expériences antérieures peuvent avoir légèrement surestimé les performances, ce travail ouvre la voie à des tests génétiques sanguins ou tissulaires capables de signaler précocement la maladie d’Alzheimer à l’aide d’un ensemble compact et bien choisi de marqueurs géniques.
Citation: Asiry, O., El-Gawady, A., Eltoukhy, M.M. et al. LASSO–HHO two-stage hybrid gene selection framework for accurate Alzheimer’s disease diagnosis. Sci Rep 16, 13393 (2026). https://doi.org/10.1038/s41598-026-48742-6
Mots-clés: Diagnostic de la maladie d’Alzheimer, expression génique, sélection de caractéristiques, apprentissage automatique, biomarqueurs