Clear Sky Science · fr
Reconstruction 3D à grande surface des tissus cornéens par microscopie confocale à mise au point oscillante
Voir l’œil en trois dimensions
La fenêtre transparente à l’avant de votre œil, la cornée, regorge de nerfs délicats et de cellules immunitaires qui peuvent révéler des signes précoces de maladies comme le diabète, la sclérose en plaques, ou même le COVID long. Les médecins utilisent déjà un type spécial de microscope posé délicatement sur l’œil pour observer ces structures, mais ils les voient généralement comme des tranches plates. Cette étude présente une nouvelle méthode pour transformer des milliers de ces tranches en une carte tridimensionnelle détaillée sur une large zone de la cornée, ouvrant la voie au suivi de cellules minuscules et des modifications nerveuses en santé et en maladie.
Pourquoi les images plates ne suffisent pas
La microscopie confocale in vivo standard produit des images très nettes de la cornée, mais chaque image ne capture qu’une petite zone et une seule profondeur. Les médecins assemblent souvent de nombreuses images pour créer des mosaïques bidimensionnelles plus larges afin d’examiner le réseau nerveux cornéen ou de compter les cellules immunitaires. Cependant, les nerfs et les cellules immunitaires sont véritablement tridimensionnels : ils se ramifient, se courbent et se déplacent non seulement latéralement mais aussi en profondeur ou vers la surface. Avec les méthodes actuelles, le mouvement en profondeur reste largement invisible. Les reconstructions 3D existantes sont limitées à des zones très petites, de l’ordre de la taille d’une image unique, ce qui est trop restreint pour suivre de nombreuses cellules ou pour capturer la pleine variabilité de la couche nerveuse.
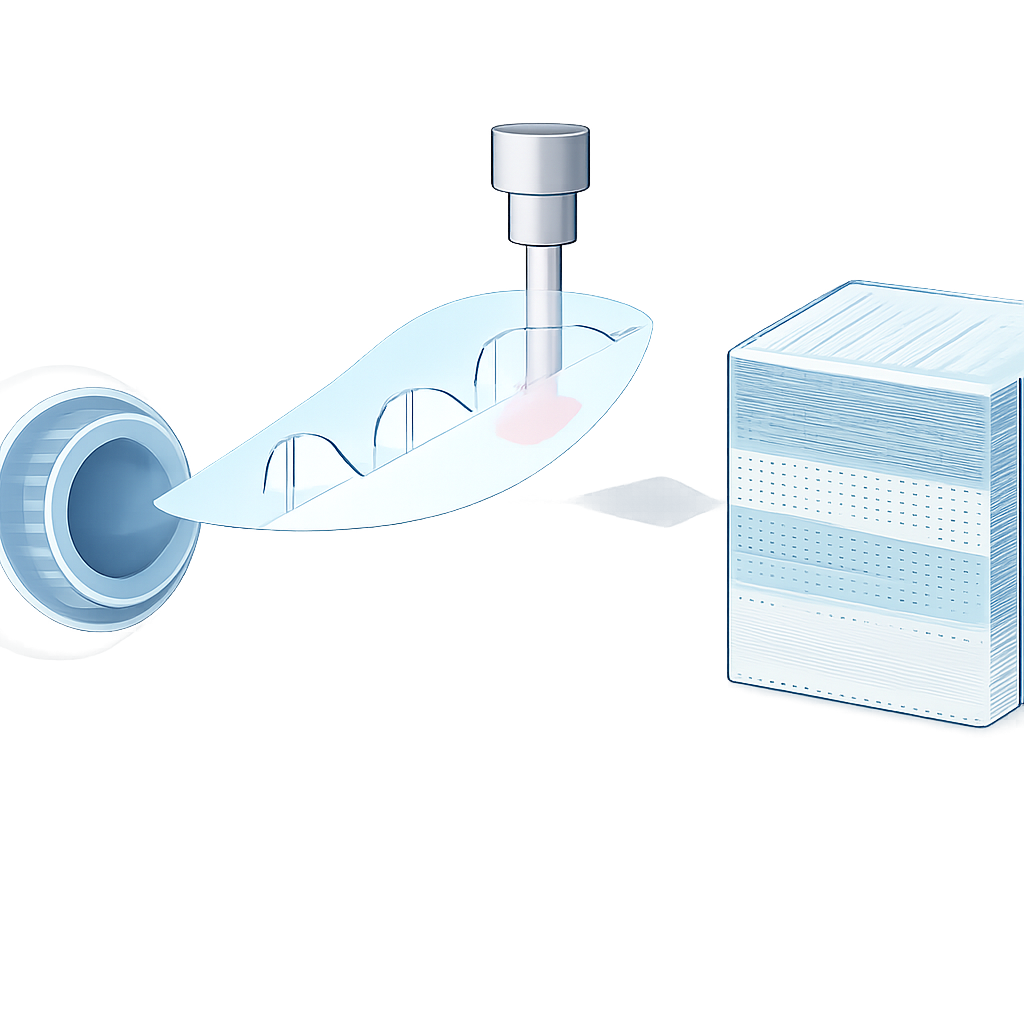
Balayer une région cornéenne large et profonde
L’équipe de recherche part d’un système de microscope confocal personnalisé qui touche doucement l’œil avec une pointe couverte, tandis qu’un second dispositif guide le regard du patient le long d’un trajet planifié. Pendant que l’œil se déplace lentement, le microscope balaie une vaste zone de la cornée. Dans le même temps, la mise au point du microscope est continuellement déplacée de haut en bas selon un motif triangulaire à travers le tissu. Autrement dit, au lieu d’imager une seule couche plate, le système scanne à plusieurs reprises une pile de profondeurs pendant qu’il parcourt la cornée, couvrant à la fois le plexus nerveux sous-basal et les couches voisines. Les données brutes sont des milliers de petites images partiellement chevauchantes acquises à différentes positions et profondeurs lors de ce balayage oscillant.
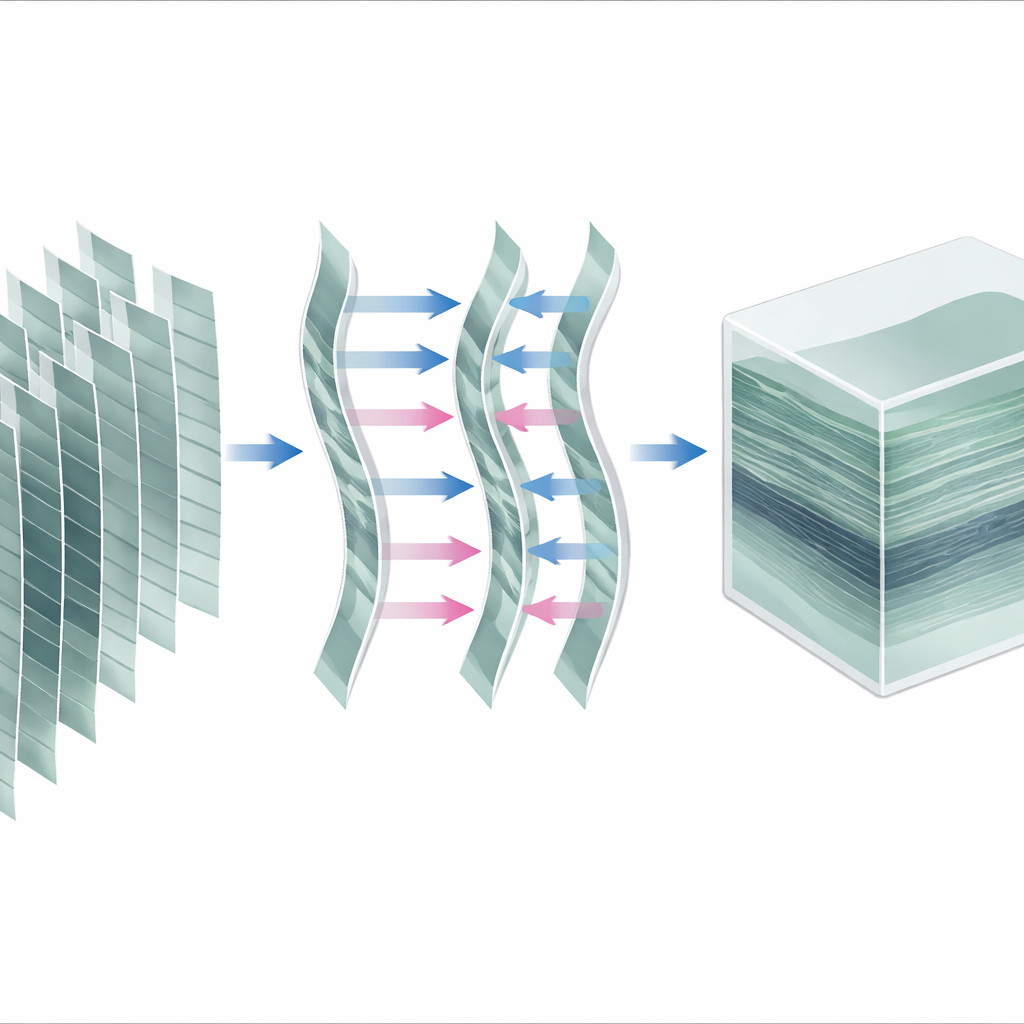
Transformer des tranches mobiles en un volume solide
Pour transformer ces images en un bloc tridimensionnel propre du tissu, les auteurs conçoivent une chaîne de traitement étape par étape. D’abord, ils corrigent les mouvements latéraux de l’œil, veillant à ce que chaque image soit placée sur une grille commune, comme si l’œil était resté parfaitement immobile. Ensuite, ils divisent le balayage continu en nombreuses « piles » de mise au point courtes, chacune couvrant un passage complet de la mise au point d’avant en arrière ou inversement. Pour chaque pile, ils attribuent une valeur de profondeur à chaque image en se basant sur la position de mise au point enregistrée et interpolent entre les tranches pour remplir une grille tridimensionnelle régulière de petits cubes, ou voxels. Enfin, ils moyennent toutes les piles qui se chevauchent dans l’espace pour les fusionner en un volume unique de la région scannée.
Corriger les mouvements subtils en profondeur
Parce que l’œil et la cornée sont souples et que la respiration et d’autres petits mouvements peuvent intervenir, le tissu peut se déplacer légèrement vers ou loin du microscope pendant le balayage. Pour gérer cela, les auteurs introduisent deux méthodes de raffinement de complexité croissante. La méthode la plus simple traite chaque pile de mise au point comme un bloc rigide et aligne les piles le long de l’axe de profondeur en utilisant une registration d’images tridimensionnelle, résolvant un système d’équations pour positionner chaque pile à la profondeur la plus cohérente. La méthode la plus avancée va plus loin, découpant les piles en sous-piles plus petites et estimant comment la profondeur du tissu évolue de façon continue dans le temps. Cela leur permet de compenser des effets d’étirement ou de compression à l’intérieur des piles, reconstituer effectivement une trajectoire de mouvement axial et corriger chaque image individuellement avant la fusion finale.
Quelle est l’efficacité et pourquoi cela compte
L’équipe a testé les trois variantes de reconstruction sur des jeux de données provenant de 15 personnes présentant différentes formes de sécheresse oculaire. L’inspection visuelle des coupes à travers les volumes reconstruits a montré une qualité similaire entre les méthodes, ce qui suggère que, dans ce montage particulier, les erreurs de profondeur importantes étaient déjà limitées. Cependant, une mesure objective spécialisée de la qualité d’image conçue pour les images confocales a détecté de petites mais significatives améliorations lorsque la correction du mouvement en profondeur était appliquée, en particulier avec la méthode la plus avancée. Bien que cette correction de haute précision exige beaucoup plus de temps de calcul, les auteurs la recommandent pour les projets qui effectueront des analyses automatisées ou des mesures détaillées sur les volumes.
De l’outil de recherche aux usages cliniques futurs
En termes simples, ce travail montre comment transformer un balayage oculaire rapide et large en une carte tridimensionnelle stable d’une vaste région cornéenne. Pour des applications comme le suivi des cellules immunitaires lorsqu’elles migrent près de la couche nerveuse, ou la caractérisation de l’évolution du réseau nerveux cornéen au fil du temps ou en réponse à un traitement, cette combinaison de large couverture et de profondeur complète est cruciale. Le même flux de travail peut être adapté pour se concentrer sur différentes couches cornéennes, et il pourrait devenir essentiel pour les futures versions du microscope qui ne touchent plus l’œil du tout, où le mouvement en profondeur est plus prononcé. À terme, de telles reconstructions 3D détaillées pourraient aider les médecins à détecter plus tôt les lésions nerveuses, surveiller les réponses aux thérapies plus précisément et mieux comprendre comment la surface de l’œil reflète des maladies ailleurs dans le corps.
Citation: Allgeier, S., Bohn, S., Mikut, R. et al. Large-area 3D reconstruction of corneal tissues from oscillating focus confocal microscopy. Sci Rep 16, 12693 (2026). https://doi.org/10.1038/s41598-026-48735-5
Mots-clés: imagerie cornéenne, microscopie confocale, reconstruction 3D, nerfs cornéens, cellules immunitaires