Clear Sky Science · fr
Aperçus mécanistiques de la désagrégation des fibrilles d’amyloïde-β par l’EPPS via des simulations de dynamique moléculaire par échange de réplicas
Pourquoi cette recherche compte
La maladie d’Alzheimer prive progressivement les personnes de leur mémoire et de leur autonomie ; l’un de ses signes distinctifs est l’accumulation dans le cerveau de fibres protéiques collantes appelées plaques amyloïdes. Une petite molécule de laboratoire appelée EPPS a montré chez la souris qu’elle aide à éliminer ces plaques et à améliorer la mémoire, mais la manière dont elle attaque les fibres au niveau microscopique restait mystérieuse. Cette étude utilise des simulations informatiques avancées pour observer, atome par atome, comment l’EPPS se fixe à ces fibres nuisibles et commence à les écarter, fournissant des indices susceptibles d’orienter la conception de futurs médicaments contre Alzheimer.
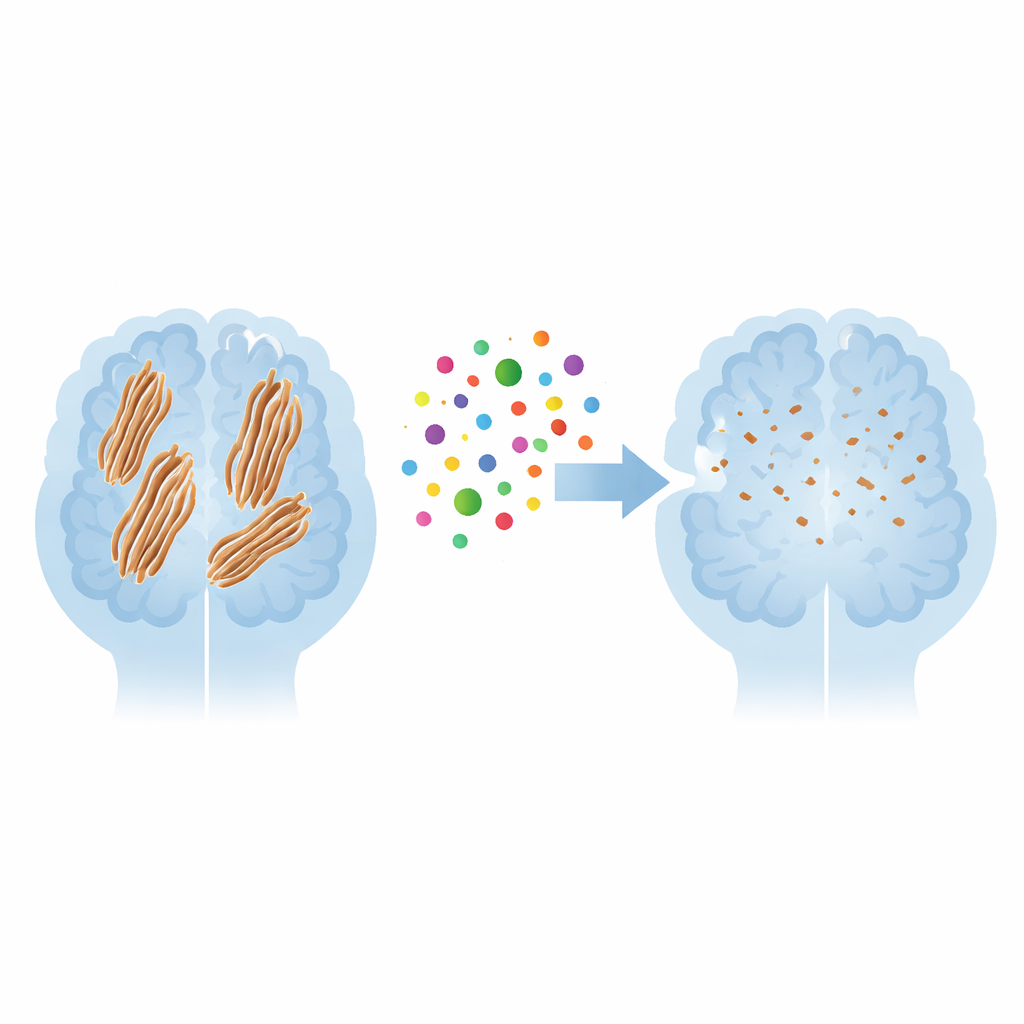
Le problème des amas protéiques tenaces
Dans la maladie d’Alzheimer, des fragments d’une protéine appelée amyloïde-β peuvent se replier en structures plates en feuillets qui s’empilent en assemblages longs et en corde connus sous le nom de fibrilles. Ces fibrilles s’emmêlent pour former les plaques observées dans le cerveau des malades et sont supposées endommager les neurones voisins. La stabilité de ces fibres résulte d’une combinaison de régions hydrophobes qui s’attirent et d’arrières-squelettes alignés qui se relient par de nombreux faibles liaisons hydrogène, comme les dents d’une fermeture éclair. Parce que ces forces sont si nombreuses et puissantes, une fois formées, les fibrilles sont notoirement difficiles à séparer, ce qui explique pourquoi trouver des moyens de les déstabiliser constitue un enjeu thérapeutique majeur.
Un examen plus rapproché de la rencontre entre l’EPPS et la fibre
Pour sonder l’interaction entre l’EPPS et les fibres amyloïdes, les chercheurs ont eu recours à la dynamique moléculaire par échange de réplicas, une technique de simulation puissante qui leur permet d’explorer de nombreux mouvements et conformations possibles des molécules au fil du temps. Ils ont commencé avec une mini-fibrille préassemblée composée de cinq brins amyloïdes empilés entourés d’eau et de sel dissous, puis ajouté un nombre égal de molécules d’EPPS placées au hasard autour. En exécutant plusieurs simulations à des températures étroitement espacées proches de la température corporelle, ils ont pu suivre où l’EPPS préfère se lier et comment sa présence modifie le mouvement des brins protéiques, capturant des événements précoces encore difficiles à observer expérimentalement.
Où l’EPPS s’accroche en premier
Les simulations ont révélé que l’EPPS n’est pas attiré de manière uniforme sur l’ensemble de la fibre. Au contraire, il est fortement attiré par les brins les plus externes, en particulier à des sites spécifiques chargés négativement à la surface de la protéine. Là, la partie chargée positivement de l’EPPS forme des contacts ioniques serrés, agissant presque comme un aimant s’emboîtant sur une vis exposée au bord de la fibre. Ces zones d’accrochage privilégiées sont plus accessibles à l’eau environnante que l’intérieur densément empaqueté, ce qui explique pourquoi l’EPPS pénètre rarement le cœur du faisceau. Une fois fixé, l’EPPS a tendance à caler sa queue flexible entre des brins voisins, se positionnant de façon à perturber le compactage régulier en feuillets qui rigidifie la fibrille.

Comment le tiraillement en bordure desserre tout le faisceau
La liaison aux extrémités a des conséquences étendues. L’équipe a mesuré l’amplitude de mouvement de chaque partie de la fibre au cours des simulations et a constaté que les segments périphériques devenaient nettement plus mobiles peu après la fixation de l’EPPS. Cette augmentation de la mobilité ne resta pas confinée aux brins externes ; avec le temps, elle se propagea vers l’intérieur, indiquant que la perturbation créée en surface se répercute à travers la structure. Une analyse détaillée montra que le nombre de liaisons hydrogène stabilisantes entre brins adjacents diminuait, en particulier là où la queue de l’EPPS s’était glissée entre eux, et que des portions de la protéine perdaient leur caractère ordonné en feuillet. Dans certaines régions, les conformations privilégiées des arrières-squelettes changèrent substantiellement, signe que les brins se pliaient et se tordaient en s’éloignant de l’arrangement serré propre à la fibrille.
Implications pour les futurs traitements contre Alzheimer
Pris ensemble, les simulations présentent l’EPPS comme un petit saboteur stratégique : il cible des points chargés accessibles à l’extérieur des fibres amyloïdes, utilise une forte attraction électrique pour s’ancrer, puis exploite sa structure flexible pour écarter les brins voisins et éroder la colle interne de la fibre. Bien que les simulations informatiques aient été trop courtes pour capturer la désintégration complète des fibrilles, la perte d’ordre et de liaisons observée suggère fortement qu’une attaque prolongée par l’EPPS conduirait à terme à leur désassemblage. Pour les non-spécialistes, le message clé est que l’EPPS ne dissout pas simplement les plaques de manière vague ; il suit un plan d’action microscopique précis qui peut maintenant éclairer la conception de nouvelles molécules, plus puissantes, destinées à assouplir et à éliminer les dépôts protéiques liés à Alzheimer.
Citation: Choi, KE., Pae, A.N. & Cho, NC. Mechanistic insights into the disaggregation of amyloid-β fibrils by EPPS via replica-exchange molecular dynamics simulations. Sci Rep 16, 13034 (2026). https://doi.org/10.1038/s41598-026-42391-5
Mots-clés: Maladie d’Alzheimer, plaques amyloïdes, agrégation protéique, simulations moléculaires, conception de médicaments