Clear Sky Science · es
Análisis de ATAC-seq de un solo núcleo resuelve características de cromatina y transcripción del carcinoma fibrolamelar
Mirando dentro de un cáncer de hígado raro
El carcinoma fibrolamelar es una forma rara de cáncer de hígado que suele afectar a adolescentes y adultos jóvenes; para muchos pacientes, la cirugía es la única esperanza. Sin embargo, este tumor no está compuesto únicamente por células cancerosas: es una comunidad compleja de muchos tipos celulares que interactúan en un entorno compartido. Este estudio utiliza tecnologías de una sola célula de vanguardia para acercarse a esa comunidad, revelando qué células impulsan cambios moleculares clave y apuntando a nuevas formas de atacar la enfermedad.
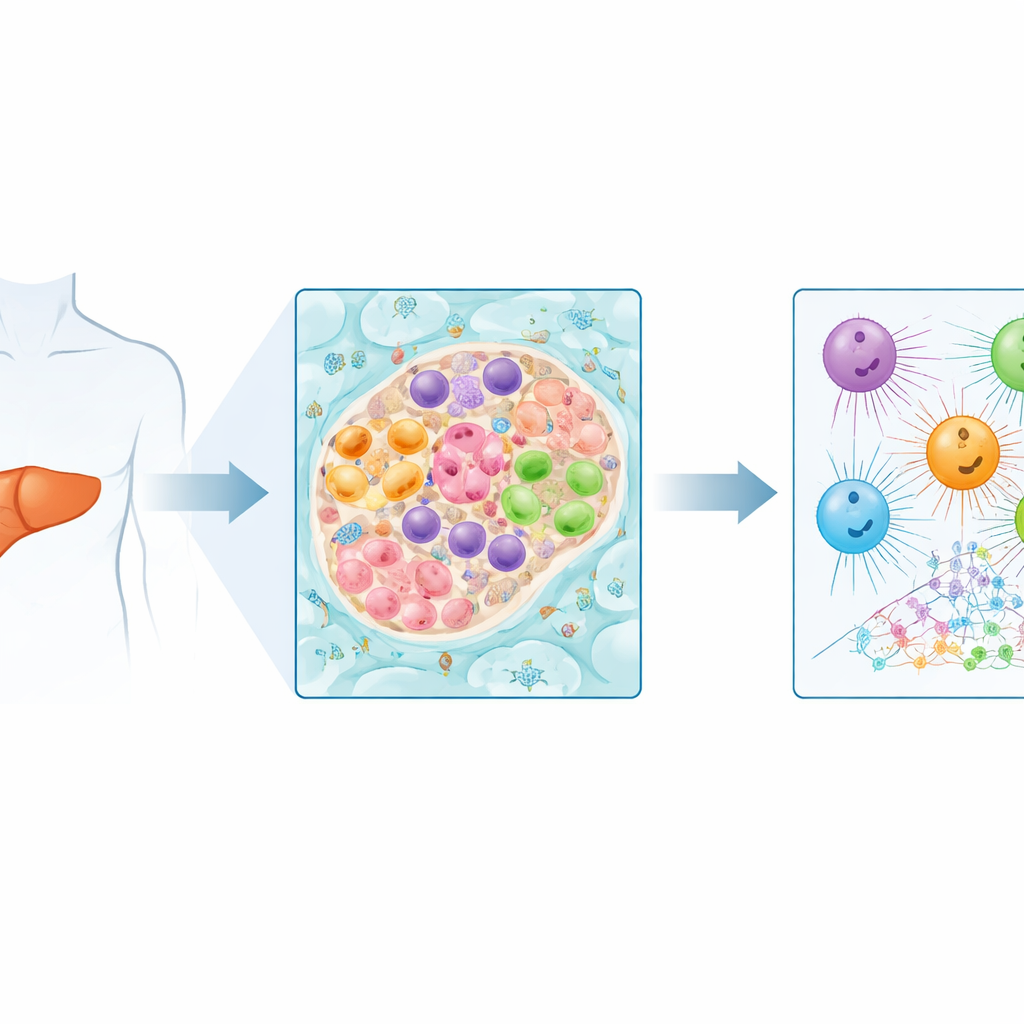
Por qué este cáncer es tan desafiante
El carcinoma fibrolamelar se diferencia de los cánceres de hígado más comunes. Suele aparecer en personas sin enfermedad hepática subyacente y se caracteriza por bandas gruesas de tejido similar a la cicatriz que atraviesan el tumor. Casi todos los pacientes comparten una fusión de ADN distintiva que crea una proteína anómala, DNAJ-PKAc, capaz de iniciar tumores en modelos animales. Pero bloquear directamente esta proteína ha resultado difícil porque proteínas similares son esenciales para la función normal de la célula. Como resultado, los investigadores se centran cada vez más en las vías y los tipos celulares downstream que esta proteína de fusión altera, con la esperanza de encontrar puntos de ataque más precisos.
Analizar cada célula una por una
Estudios previos a gran escala midieron la actividad génica y la actividad de la cromatina (cómo se empaqueta el ADN) mezclando todas las células de un tumor. Ese enfoque es potente pero oculta los roles de tipos celulares individuales, como las células tumorales, las células de los vasos sanguíneos y las células de soporte formadoras de cicatriz. En este trabajo, los autores aíslan núcleos individuales de muestras tumorales congeladas y de tejido hepático no canceroso cercano. Aplican ATAC-seq de un solo núcleo, que mapea regiones abiertas del ADN donde residen elementos regulatorios, y RNA-seq de un solo núcleo, que mide qué genes están activos. Métodos computacionales sofisticados agrupan los núcleos en clústeres que coinciden con tipos celulares hepáticos conocidos y comparan cómo difieren esas células entre tejido tumoral y normal.
Diferentes células, distintos roles moleculares
La visión de una sola célula revela que muchas señales moleculares reportadas previamente en el carcinoma fibrolamelar en realidad provienen de distintos tipos celulares dentro del tumor. Por ejemplo, tres pequeños ARN regulatorios antes considerados simplemente marcadores tumorales muestran patrones claramente distintos: la actividad de miR-190b se concentra en células epiteliales hepáticas cancerosas, miR-10b se altera principalmente en células de vasos sanguíneos, y miR-199b está elevada en células estrelladas activadas, que son actores clave en la fibrosis. Esto significa que los modelos sencillos centrados solo en células cancerosas no bastan para estudiar todas estas moléculas. El equipo también mapea regiones de ADN donde es probable que se unan ciertos factores de transcripción, las proteínas que controlan la actividad génica. Las redes que involucran miembros de la familia AP-1 y proteínas CREB parecen reconfiguradas en tipos celulares específicos, mientras que las señales relacionadas con la función hepática normal están disminuidas en las células tumorales.
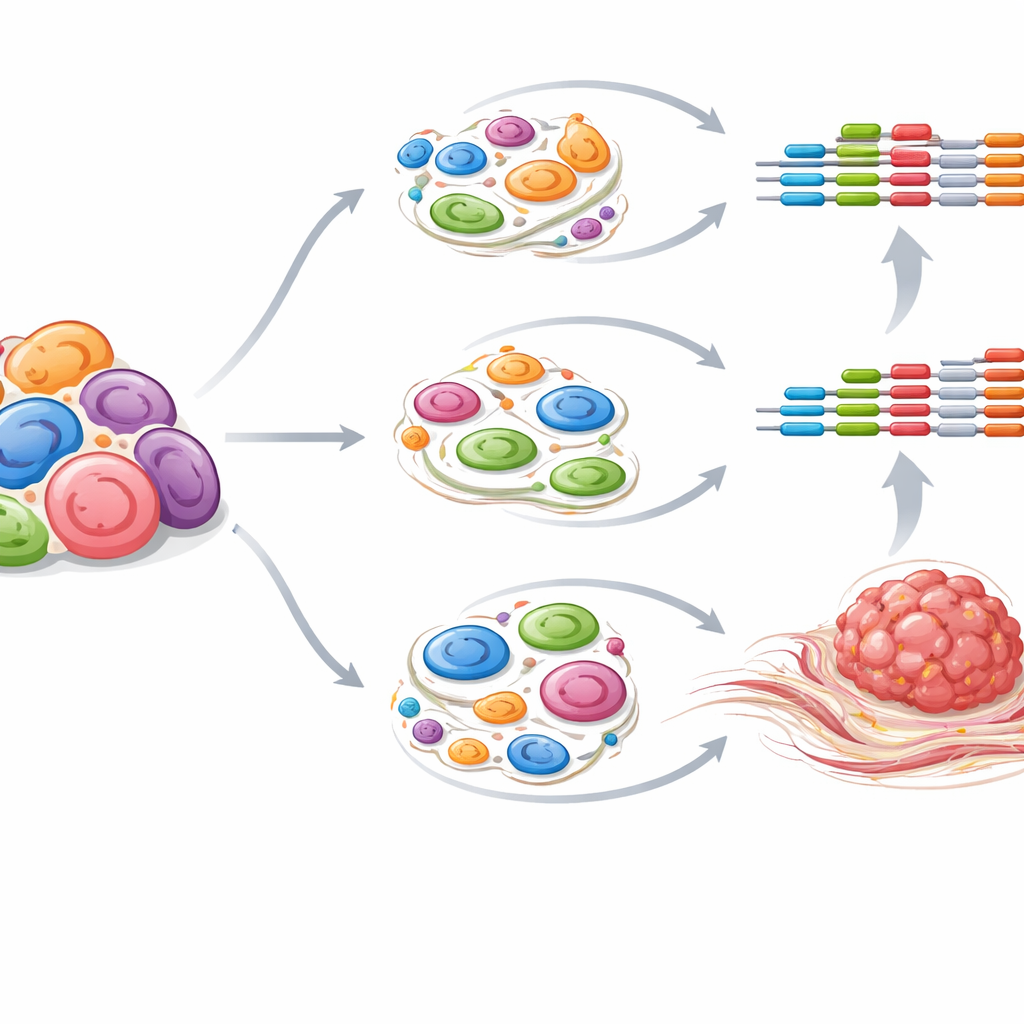
Interruptores de control ocultos y la cicatrización tumoral
Al integrar sus datos de cromatina de una sola célula con mediciones previas a granel de elementos regulatorios activos, los investigadores asignan potentes “superenhancers” a tipos celulares particulares. Muchos de estos centros de control del ADN se encuentran cerca de genes que están inusualmente activos en el carcinoma fibrolamelar. Un ejemplo destacado es CDH11, un gen vinculado previamente con fibrosis y supresión inmune en otras enfermedades. El estudio encuentra que distintos superenhancers cercanos a CDH11 están activos tanto en células tumorales como en células estrelladas activadas, y que el propio CDH11 se expresa en ambos. Análisis adicionales de la comunicación célula a célula sugieren que las células estrelladas actúan como hubs para la señalización TGFβ, una vía conocida por impulsar la cicatrización. En conjunto, esto apunta a una red convergente en la que CDH11 y ciertos microARNs ayudan a alimentar la formación del denso tejido fibroso que caracteriza a este cáncer.
Qué significa esto para futuros tratamientos
Este trabajo ofrece un mapa de alta resolución del paisaje regulador en el carcinoma fibrolamelar, desglosado por tipo celular. Para el público general, el mensaje clave es que el comportamiento del tumor no puede explicarse solo por las células cancerosas; las células de soporte y los vasos sanguíneos desempeñan papeles cruciales, y distintas moléculas actúan en diferentes “barrios” celulares. Al identificar qué genes, interruptores de control y vías de señalización están activos en qué células, el estudio destaca candidatos como CDH11, microARNs específicos y redes de factores de transcripción que podrían ser dirigidos de forma más segura y eficaz que la propia proteína de fusión original. Aunque hacen falta más validaciones y muestras emparejadas de pacientes, este atlas de una sola célula proporciona una guía valiosa para diseñar futuras terapias contra este raro y formidable cáncer de hígado.
Cita: Farghli, A.R., Sherman, M.S., Shui, B. et al. Single-nucleus ATAC-seq analysis resolves chromatin and transcriptional features of fibrolamellar carcinoma. Sci Rep 16, 14360 (2026). https://doi.org/10.1038/s41598-026-44899-2
Palabras clave: carcinoma fibrolamelar, secuenciación de una sola célula, accesibilidad de la cromatina, microambiente tumoral, cáncer de hígado