Clear Sky Science · es
L-asparaginasa de Streptomyces koyangensis: predicción computacional de una interacción de doble mecanismo con BCL-2 en la leucemia linfoblástica aguda
Por qué importa una enzima bacteriana en la leucemia infantil
La leucemia linfoblástica aguda (LLA) es el cáncer más frecuente en la infancia, y uno de sus fármacos clave es una enzima llamada L-asparaginasa. Este medicamento priva de alimento a las células leucémicas al eliminar un aminoácido que ellas no pueden sintetizar. Pero las versiones actuales, producidas a partir de bacterias comunes como Escherichia coli, pueden provocar reacciones alérgicas intensas y otros efectos adversos. Este estudio explora si una L-asparaginasa procedente de otro microbio, Streptomyces koyangensis, podría ofrecer una opción más segura y potente —e incluso atacar las células leucémicas mediante dos mecanismos en lugar de uno—.
Un giro nuevo en un fármaco conocido
Las células leucémicas dependen de un nutriente llamado asparagina, presente en la sangre, para crecer y dividirse. Las L-asparaginasas estándar actúan degradando este nutriente, de modo que las células cancerosas quedan esencialmente privadas de alimento, mientras que las células sanas, que pueden sintetizar su propia asparagina, lo toleran mucho mejor. Lamentablemente, los fármacos actuales son proteínas bacterianas grandes que el sistema inmunitario suele reconocer como invasores, provocando reacciones alérgicas y en ocasiones forzando la interrupción del tratamiento. Los investigadores buscaron fuentes alternativas de la enzima —dos especies de Streptomyces y la palmera datilera (una planta)— para determinar si alguna podría ser más adecuada para terapia.
Usar ordenadores para explorar moléculas invisibles
En lugar de ir directamente a animales de laboratorio o pacientes, el equipo construyó primero modelos computacionales detallados de cada enzima candidata. Examinaron rasgos físicos básicos como tamaño, estabilidad y cuán hidrofílica o hidrofóbica es cada enzima —características que influyen en cuánto puede durar un fármaco en el organismo y en su propensión a agregarse o degradarse. Luego emplearon varios métodos de simulación independientes para predecir cómo estas enzimas podrían unirse a proteínas clave relacionadas con la leucemia dentro o en la superficie de las células cancerosas. Al comparar distintos algoritmos y ejecutar simulaciones físicas prolongadas del movimiento molecular, pudieron evaluar si el “acoplamiento” predicho entre enzima y proteína cancerosa era fuerte y estable en el tiempo.
Encontrando un socio prometedor en Streptomyces
En todas estas pruebas, la L-asparaginasa de Streptomyces koyangensis destacó de forma consistente. Los ensayos de acoplamiento computacional sugirieron que se une muy fuertemente a una proteína llamada BCL-2, que con frecuencia está sobreexpresada en las células leucémicas y actúa como una guardia que impide su muerte. Simulaciones posteriores mostraron que la enzima y BCL-2 forman una superficie de contacto amplia y ajustada, mantenida por numerosos enlaces de hidrógeno e interacciones electrostáticas e hidrofóbicas favorables. El complejo permaneció notablemente estable durante una prueba virtual de “estrés” de 100 nanosegundos, con solo pequeñas oscilaciones en la conformación y una energía de unión calculada fuertemente negativa —indicadores de que esta asociación probablemente resistiría en la práctica. En contraste, las enzimas procedentes de las otras fuentes mostraron interacciones más débiles y menos estables.
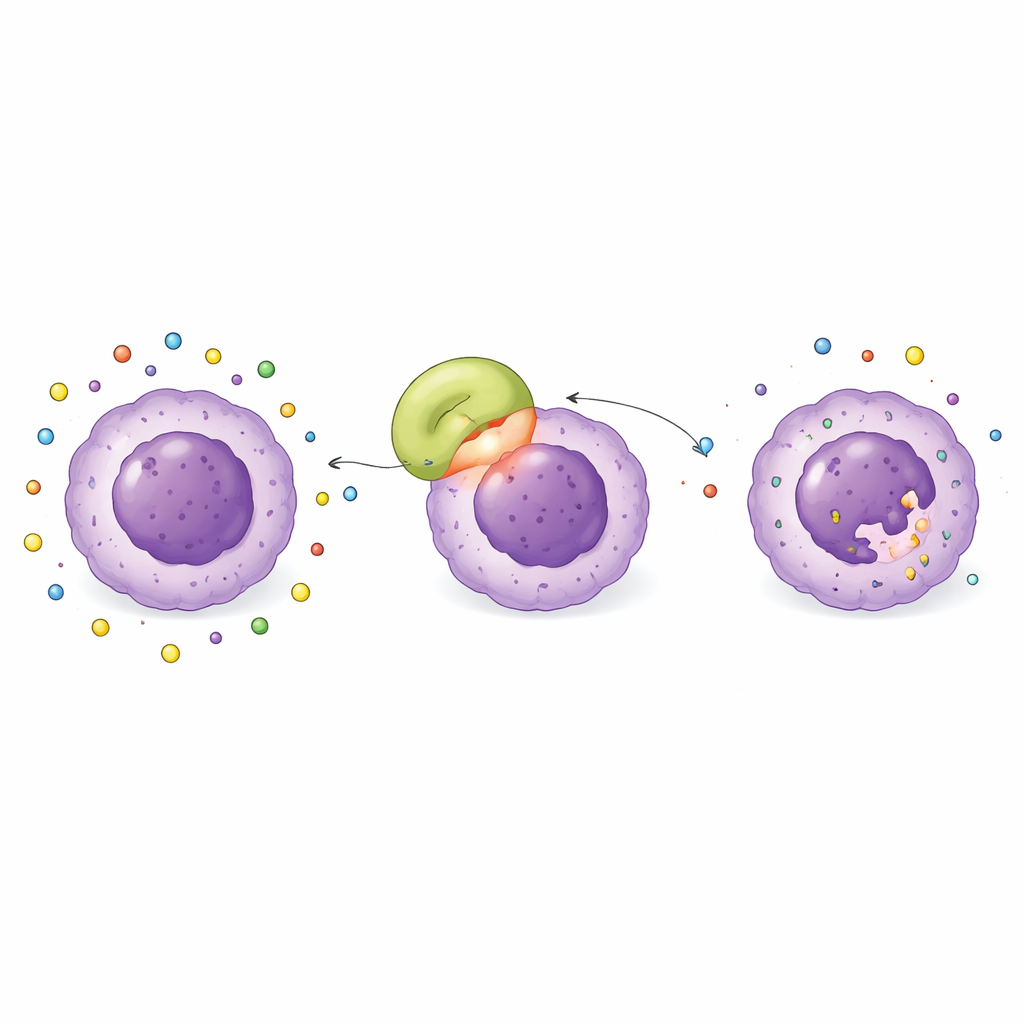
Un posible doble golpe contra las células leucémicas
Estos hallazgos sugieren que la L-asparaginasa de Streptomyces koyangensis podría no solo privar de asparagina a las células leucémicas, sino también unirse directamente a BCL-2, debilitando potencialmente las defensas de las células frente a la muerte programada. En principio, eso equivaldría a un doble golpe: cortar un nutriente vital a la vez que se desactiva un escudo clave de supervivencia. El estudio incluso identificó aminoácidos “puntos calientes” en la enzima que resultan cruciales para esta unión, proporcionando objetivos claros para futuros ajustes destinados a equilibrar potencia y seguridad. Dado que las enzimas de Streptomyces pueden provocar menos reacciones inmunitarias que las fuentes bacterianas estándar, este candidato podría en última instancia abordar tanto la resistencia como los problemas de efectos secundarios observados con la terapia actual.
Qué significa esto y qué sigue
Para el público no especializado, la conclusión es que los ordenadores potentes pueden ahora cribar y diseñar posibles fármacos contra el cáncer antes de que lleguen a un tubo de ensayo. Aquí, una batería exhaustiva de simulaciones apunta a la L-asparaginasa de Streptomyces koyangensis como un tratamiento prometedor de nueva generación para la LLA, con la posibilidad intrigante de un mecanismo dual —privación de nutrientes más ataque directo a una proteína de supervivencia. Sin embargo, el trabajo realizado hasta ahora es completamente virtual. Los autores subrayan que son esenciales experimentos de laboratorio con la enzima purificada, células leucémicas y modelos animales para confirmar si esta acción doble predicha realmente ocurre y es segura. Si esos estudios tienen éxito, esta enzima de origen microbiano podría ayudar a perfeccionar el tratamiento de la leucemia e inspirar búsquedas computacionales similares para fármacos biológicos más inteligentes y precisos.
Cita: Solanki, G., Prajapati, C., Gadhvi, R. et al. Streptomyces koyangensis L-asparaginase: computational prediction of dual-mechanism BCL-2 interaction in acute lymphoblastic leukemia. Sci Rep 16, 12675 (2026). https://doi.org/10.1038/s41598-026-42798-0
Palabras clave: leucemia linfoblástica aguda, L-asparaginasa, BCL-2, Streptomyces koyangensis, diseño computacional de fármacos