Clear Sky Science · de
Schnelles Screening von tierischen Coronaviren in Nutztieren und Wildtieren mit einem Silizium-Photonik-Biosensor
Warum die Beobachtung tierischer Viren wichtig ist
In einer Welt, in der Menschen, Nutztiere und Wildtiere zunehmend zusammenrücken, können Viren, die in Tieren entstehen, leichter auf Menschen überspringen. Coronaviren sind ein typisches Beispiel: Mehrere große Ausbrüche, einschließlich COVID-19, lassen sich auf tierische Wirte zurückverfolgen. Dieser Artikel beschreibt einen neuen chipbasierten Sensor, der eine breite Palette tierischer Coronaviren in Fledermäusen und Hühnern schnell erkennen kann, ohne die normalerweise erforderlichen langen Laborverfahren. Durch schnellere und einfachere Viruskontrollen könnte diese Technologie unsere Frühwarnsysteme gegen künftige Pandemien stärken.

Ein wachsender Verkehrsstau zwischen Tieren und Menschen
Das moderne Leben hat den Kontakt zwischen Menschen, Nutztieren und Wildtieren stark intensiviert. Erweiterte Landwirtschaft, globaler Handel und die Rodung natürlicher Lebensräume bringen Arten zusammen, die früher selten aufeinandertrafen. Coronaviren gedeihen in diesem dichten Umfeld, weil sie leicht mutieren und genetisches Material austauschen können, was ihnen erlaubt, sich an neue Wirte anzupassen. Fledermäuse, einige Nutztierarten und andere Wildtiere können viele Coronavirus-Stämme still tragen. Diese Viren in Tieren zu erkennen, bevor sie auf Menschen überspringen, ist entscheidend. Goldstandard-Tests wie PCR sind jedoch langsam, erfordern komplexe Geräte und müssen in spezialisierten Laboren durchgeführt werden. Das macht routinemäßiges Screening einer großen Zahl von Tieren im Feld schwierig und teuer.
Ein lichtbasierter Chip als Virendetektor
Das Forschungsteam entwickelte einen winzigen Siliziumchip, der Licht nutzt, um das genetische Material von Coronaviren direkt nachzuweisen, ohne Verstärkung oder chemische Marker. Auf dem Chip verlaufen sehr kleine Leitbahnen, sogenannte Wellenleiter, die einen Lichtstrahl gleichzeitig in zwei verschiedenen Modulationen führen. Die Oberfläche dieser Wellenleiter ist mit kurzen DNA-Strängen beschichtet, die darauf ausgelegt sind, passende Coronavirus-RNA aus Tierproben zu binden. Wenn virale RNA an diese Stränge bindet, ändert sich subtil, wie sich Licht in den Wellenleitern ausbreitet. Das interferometrische Design des Geräts wandelt diese Änderung in ein messbares Signal in Echtzeit um, sodass der Chip selbst winzige Mengen an virusbezogenem Material innerhalb von Minuten erkennen kann.
Den Chip so entwerfen, dass er viele Coronavirus-Typen erfasst
Um Säugetiere und Vögel abzudecken, bauten die Wissenschaftler zwei Versionen des Sensors. Eine zielt auf einen hochkonservierten Abschnitt des Replikationsgens, der von Alpha- und Betacoronaviren genutzt wird und in Fledermäusen und vielen anderen Säugetieren verbreitet ist. Die andere konzentriert sich auf eine stabile Region nahe dem vorderen Bereich des Genoms bei Gammacoronaviren, die häufig Geflügel betreffen. Sie passten sorgfältig an, wie viele DNA-Sonden auf der Chipoberfläche sitzen, und mischten sie mit flexiblen Abstandshaltermolekülen, damit sie für Bindungen zugänglich bleiben. Außerdem optimierten sie den Salzgehalt und fügten eine kleine Menge Formamid hinzu, ein Lösungsmittel, das hilft, RNA-Stränge zu strecken, sodass sie sich leichter mit den Sonden paaren können. Ein Regenerationsschritt ermöglicht es dem Chip, gebundene RNA zwischen den Tests freizusetzen, sodass dasselbe Gerät mehrfach wiederverwendet werden kann.
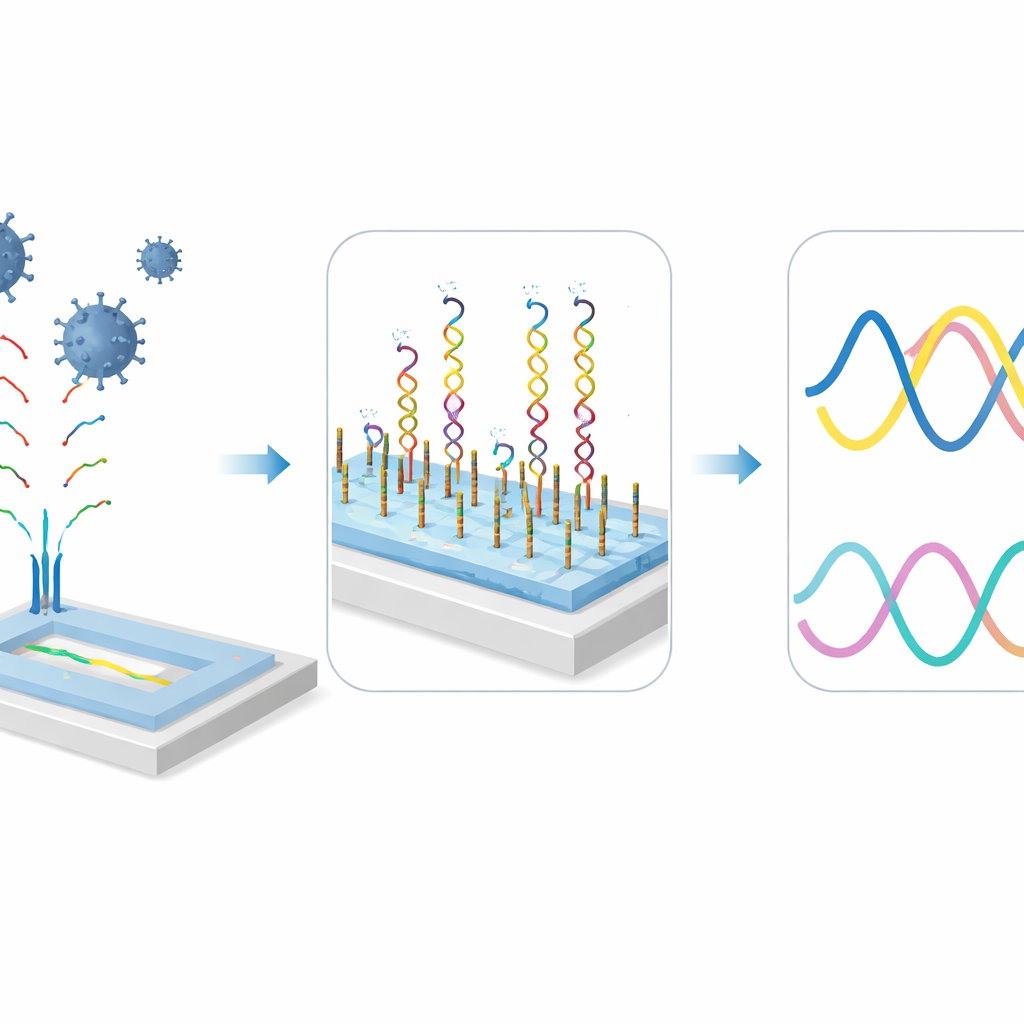
Wie gut der neue Sensor funktioniert
In kontrollierten Tests mit synthetischen viralen Fragmenten und längeren im Labor hergestellten RNA-Molekülen konnte der Chip sehr niedrige Konzentrationen nachweisen, in manchen Fällen bis hin zu wenigen Kopien viraler RNA pro Mikroliter. Seine Messungen stimmten eng mit denen der Standard-PCR überein, aber die Auslesezeit betrug etwa 20–25 Minuten statt mehreren Stunden. Das Team prüfte den Sensor dann an realen Proben: Fledermauskot und Tupferproben von Hühnern, die mit einem häufigen Geflügel-Coronavirus infiziert waren. Bei Fledermäusen identifizierte der Sensor die meisten positiven und negativen Proben korrekt, wobei die Leistung bei sehr niedrigen Infektionsniveaus mäßig war. Bei Hühnern waren die Ergebnisse stärker, mit hoher Sensitivität und Spezifität über ein breites Spektrum an Viruslasten, was zeigt, dass der Chip infizierte Vögel zuverlässig ohne Verstärkungsschritt erkennen kann.
Was das für künftige Ausbrüche bedeuten könnte
Obwohl das derzeitige Setup noch eine grundlegende Laborhandhabung zur RNA-Extraktion benötigt, ist der Chip selbst kompakt, mit Standard-Mikroelektronikverfahren herstellbar und für die Massenproduktion zu niedrigen Kosten ausgelegt. Die Autoren argumentieren, dass ähnliche Geräte, wenn Optik und Fluidik weiter miniaturisiert und automatisiert werden, näher an Höfe, Märkte und Wildtierüberwachungsstellen gebracht werden könnten. Dort könnten sie als schnelle, routinemäßige Screenings für tierische Coronaviren dienen und die PCR ergänzen, anstatt sie zu ersetzen. Für nicht spezialisierte Leser ist die wichtigste Erkenntnis, dass dieser lichtbasierte Chip ein schnelles, wiederverwendbares und skalierbares Werkzeug bietet, um tierische Viren dort zu beobachten, wo sie entstehen, und so unsere Chancen zu verbessern, gefährliche Stämme zu erkennen, bevor sie zur nächsten menschlichen Pandemie werden.
Zitation: Serrano, B., Soler, M., Courtillon, C. et al. Rapid screening of animal coronaviruses in livestock and wildlife using a silicon photonics biosensor. npj Biosensing 3, 26 (2026). https://doi.org/10.1038/s44328-026-00091-0
Schlüsselwörter: Überwachung von Coronaviren, Silizium-Photonik-Biosensor, tierische Reservoirs, schnelle Diagnostik, One Health