Clear Sky Science · de
Untersuchung uncharakterisierter Gene in Saccharomyces cerevisiae mithilfe von Robot-Wissenschaftlern
Warum das für die Alltagsbiologie wichtig ist
Wir sprechen oft davon, den vollständigen genetischen Bauplan eines Organismus zu haben, aber bei vielen Genen wissen wir noch immer nicht, welche Funktion sie tatsächlich erfüllen. Diese Studie geht dieses Rätsel bei Backhefe an, einem Arbeitspferd der Wissenschaft und Industrie, indem sie automatisierte „Roboter-Wissenschaftler“ mit Computermodellen kombiniert. Die Forschenden zeigen, wie dieser Ansatz die Rolle eines zuvor unerforschten Gens aufdecken kann, das an der Umschaltung der Energiequelle beteiligt ist — ein Wechsel, der Wachstum, Stoffwechsel und letztlich die Fähigkeit der Zellen, mit sich ändernden Umgebungen umzugehen, beeinflusst.
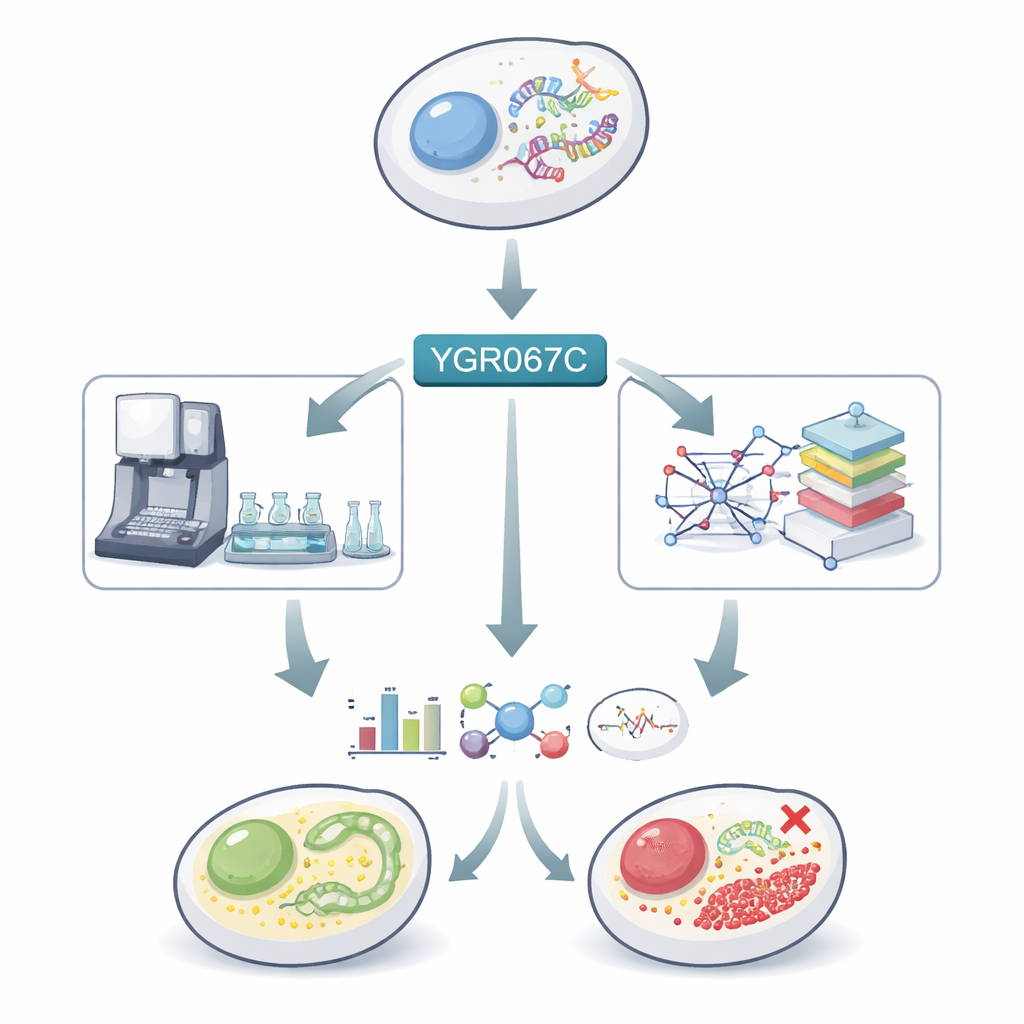
Ein verborgenes Gen in einem sehr vertrauten Organismus
Backhefe wird seit Jahrzehnten untersucht, doch fast 900 ihrer etwa 6.000 Gene sind noch schlecht verstanden. Eines davon, YGR067C genannt, produziert ein Protein mit einem strukturellen Motiv, das typisch für Genregulatoren ist, was darauf hindeutet, dass es andere Gene steuern könnte. Frühere Arbeiten legten nahe, dass Veränderungen in diesem Gen der Hefe geholfen haben, sich an das Wachsen auf ungewöhnlichen Nahrungsquellen wie Methanol anzupassen. Die Autorinnen und Autoren vermuteten daher, dass YGR067C an der Steuerung der Umschaltung vom Verbrennen von Zucker zum Verbrennen des Alkohols Ethanol beteiligt sein könnte — ein wichtiger metabolischer „Gangwechsel“, den die Hefe vornimmt, wenn der Glukosevorrat erschöpft ist.
Roboter und Modelle als Treiber der Experimente
Um diese Idee zu prüfen, nutzte das Team eine automatisierte Laborplattform mit dem Spitznamen Eve. Eve kultivierte normale Hefe und einen Stamm, bei dem YGR067C gelöscht war, in winzigen Vertiefungen mit Nährmedium, das nur eine kleine Menge Glukose enthielt, und zwang die Kulturen so durch das klassische zweiphasige Wachstumsverhalten: zunächst eine Phase des Zuckerabbaus, dann eine Phase des Ethanolabbaus. Der Roboter verfolgte sorgfältig das Wachstum und entnahm zu gewählten Zeiten Proben. Diese Proben wurden dann auf drei Ebenen analysiert: welche Gene aktiv waren (Transkriptomik), welche kleinen Moleküle vorhanden waren (Metabolomik) und wie schnell bzw. dicht die Kulturen wuchsen. Parallel dazu verwendeten die Forschenden zwei Typen von Computermodellen des Hefestoffwechsels, um vorherzusagen, was passieren sollte, wenn die Funktion des Gens gestört ist — nicht nur in den direkt mit der Atmung verbundenen Pfaden, sondern auch im weiteren Netz der Reaktionen innerhalb der Zelle.
Was passiert, wenn das Gen entfernt wird
Die Daten zeigten, dass die Entfernung von YGR067C sowohl Wachstum als auch die innere Chemie verändert. Der Mutant wuchs etwas schneller und erreichte unter den getesteten Bedingungen eine höhere Zelldichte als der normale Stamm, was darauf hindeutet, dass weniger Energie in bestimmte kostenintensive zelluläre Maschinerien investiert wurde. Während der Zuckerabbauphase waren viele Gene, die an wichtigen Energiewegen in den Mitochondrien beteiligt sind — wie der Zitratzyklus, die oxidative Phosphorylierung und der Glyoxylatzyklus — im Mutanten weniger aktiv. Gleichzeitig gab es Hinweise darauf, dass der Zuckerabbau selbst aktiver war, und zwei Bestandteile einer zellulären „Protonenpumpe“, die zur Aufrechterhaltung des Säuregleichgewichts beiträgt, waren stärker exprimiert, was mit einer höheren Produktion saurer Nebenprodukte der Fermentation übereinstimmt.
Andauernde Effekte in der Ethanol-Verbrennungsphase
Nachdem sich die Kulturen auf die Nutzung von Ethanol umgestellt hatten, verblassten die Unterschiede in der Genaktivität zwischen den beiden Stämmen weitgehend, doch Unterschiede in den Metaboliten wurden deutlich. Im Mutanten häuften sich mehrere verwandte Moleküle, die zelluläre Reduktionskraft tragen und speichern — einschließlich verschiedener Formen von NAD — in höheren Konzentrationen an, ebenso wie einige Aminosäuren wie Glutamat und Asparagin. Pfadanalyse deuteten auf weiterreichende Veränderungen in der Aminosäuresynthese, im Vitaminstoffwechsel und in lipidbezogenen Wegen hin. Zusammengenommen deuten diese Befunde darauf hin, dass zwar die genregulatorische Aktivität von YGR067C am stärksten ist, wenn Glukose vorhanden ist, die metabolischen Folgen seines Fehlens jedoch in die Ethanol-Nutzungsphase hineinwirken und die Art und Weise verändern, wie die Zelle Energieerzeugung, Bausteinsynthese und Wachstum ausbalanciert.
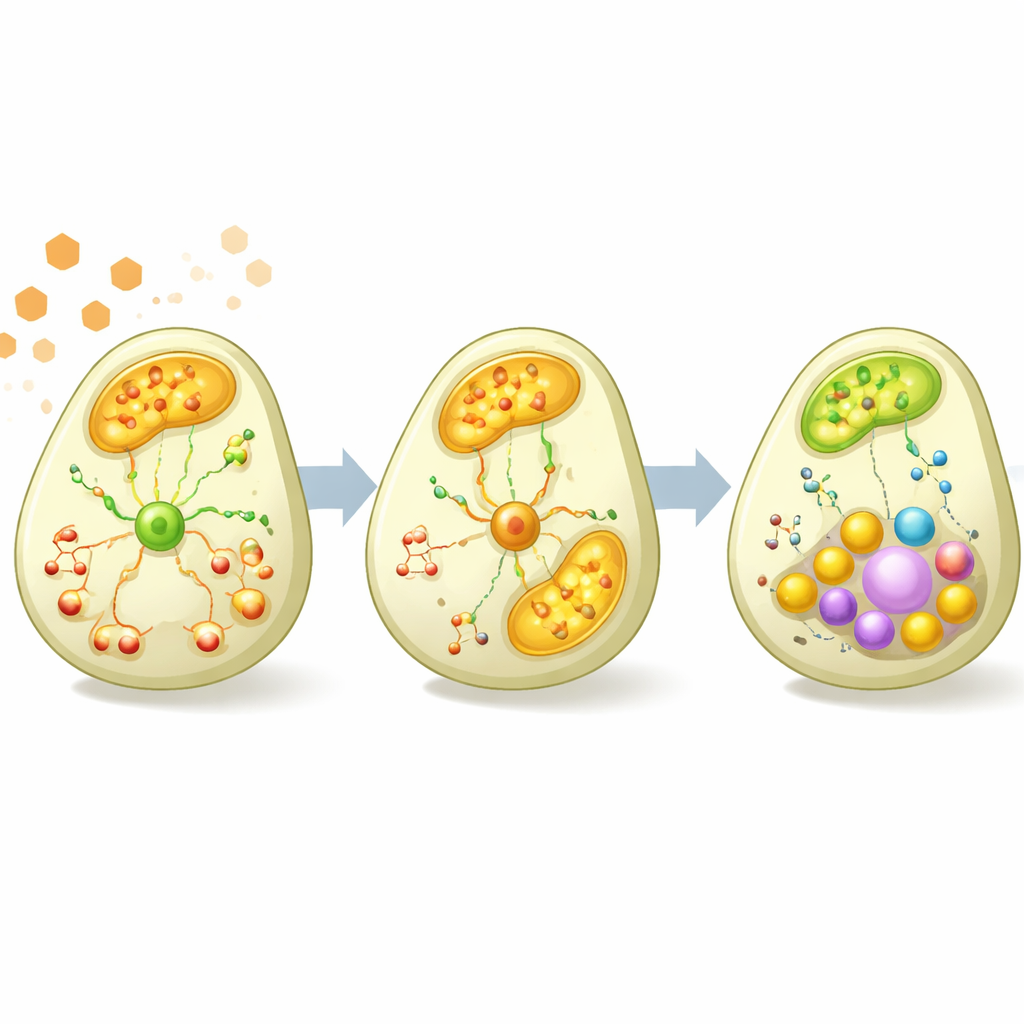
Was uns das über das Gen und das große Ganze sagt
Durch die Kombination automatisierter Experimente mit mehrschichtigen Messungen und mehreren Modellierungsstrategien kommt die Studie zu einer klaren, intuitiven Kernaussage für Nicht-Fachleute: YGR067C hilft, die Maschinerie der Hefe zum Verbrennen von Ethanol über die Atmung einzuschalten und feinzujustieren, wenn der Zucker knapp wird. Fehlt das Gen, stützen sich die Zellen stärker auf einfache Zuckerfermentation, investieren weniger in mitochondriale Energiewege und zeigen Folgeänderungen bei wichtigen energietragenden Molekülen und der Aminosäuresynthese, während sie unter den getesteten Bedingungen etwas schneller wachsen. Ebenso wichtig ist, dass die Arbeit eine allgemeine Vorgehensweise aufzeigt, wie vage Hypothesen über unbekannte Gene in konkrete, prüfbare Vorhersagen verwandelt werden können — ein Ansatz, der skaliert werden könnte, um viele der verbleibenden „unbekannten“ Gene in Hefe und anderen Organismen zu entschlüsseln.
Zitation: Bjurström, E.Y., Gower, A.H., Lasin, P. et al. Investigating uncharacterised genes in Saccharomyces cerevisiae using robot scientists. Sci Rep 16, 10999 (2026). https://doi.org/10.1038/s41598-026-46236-z
Schlüsselwörter: Hefegenetik, Diauxie, Stoffwechsel, robotisches Labor, Genregulation