Clear Sky Science · de
Transkriptom-Analyse und Resekquenzierung enthüllen immunbezogene Gene und molekulare Marker, die mit Aeromonas salmonicida-Resistenz bei Salmo trutta fario assoziiert sind
Warum robuste Forellen für Bergflüsse wichtig sind
Hohe Gebirgsflüsse auf dem Tibetischen Hochplateau beherbergen einzigartige Fischbestände, von denen lokale Gemeinschaften in Bezug auf Nahrung und Einkommen abhängen. Eine dieser Arten, die Bachforelle Salmo trutta fario, wird in der Region inzwischen kultiviert, leidet jedoch erheblich unter Verlusten durch eine bakterielle Kiemenerkrankung verursacht durch Aeromonas salmonicida. Diese Studie stellte eine praktische Frage mit großen ökologischen und wirtschaftlichen Auswirkungen: Können wir die Fische identifizieren, die von Natur aus besser gegen diese Infektion gewappnet sind, und dieses genetische Wissen nutzen, um widerstandsfähigere Bestände für zukünftige Betriebe zu züchten? 
Fische auf dem Dach der Welt unter Druck
Der Yarlung Zangbo und seine Nebenflüsse durchqueren das, was manchmal als Dach der Welt bezeichnet wird. Wasserkraftprojekte und andere menschliche Aktivitäten erhöhen den Druck auf diese kalten, schnellen Flüsse und machen den Schutz der Fischbestände dringlicher. Vor mehr als einem Jahrhundert eingeführte Bachforellen sind zu einer wichtigen Aquakulturart geworden, doch Ausbrüche der bakteriellen Kiemenerkrankung können große Bestände vernichten. Anstatt sich nur auf Medikamente oder Impfstoffe zu verlassen, prüften die Autoren, ob die Forellen selbst genetische Hinweise liefern, die erklären, warum einige Infektionen überleben, während andere daran sterben — und damit die Möglichkeit eröffnen, von Natur aus robustere Fische zu züchten.
Beobachtung, wie Gene auf Infektion reagieren
Das Team setzte zunächst Hunderte von Forellen dem krankheitserregenden Bakterium aus. Je nachdem, ob sie erkrankten, starben oder gesund blieben, wurden die Fische als anfällig, resistent oder als unbehandelte Kontrollen eingeteilt. Aus einem wichtigen Immunorgan, der Kopfniere, bestimmten die Forschenden, welche Gene in jeder Gruppe hoch- oder herunterreguliert wurden, mithilfe einer Methode, die Tausende von RNA-Botschaften gleichzeitig erfasst. Sie fanden Tausende von Genen mit veränderter Aktivität nach der Infektion, insbesondere solche, die an Immunalarmen, Zellkommunikation und Stressreaktionen beteiligt sind. Mehrere Gene stachen hervor, darunter interferonstimulierbare Gene und Schaltstellen in zwei wichtigen Abwehrwegen, den PI3K- und NF-kappa-B-Signalwegen, die gemeinsam steuern, wie Immunzellen auf Eindringlinge reagieren.
Verknüpfung von DNA-Varianten mit robusteren Forellen
Allein die Genaktivität kann nicht vollständig erklären, warum einige Forellen Krankheiten abwehren. Um tiefer zu graben, sequenzierten die Wissenschaftler größtenteils die DNA aus den Lebern resistenter und anfälliger Fische und suchten nach winzigen Buchstabenunterschieden, sogenannten Single-Nucleotide-Polymorphismen (SNPs). Anschließend überlagerten sie diese DNA-Varianten mit der Liste der infektionssensitiven Gene. Diese kombinierte Sichtweise hob 104 SNPs in immunrelevanten Genen hervor, die über nahezu alle Chromosomen hinweg deutliche Unterschiede zwischen resistenten und anfälligen Gruppen zeigten. Aus diesen wählten sie sechs SNP-Stellen als vielversprechendste Marker aus, viele davon in oder in der Nähe von Genen, die mit den PI3K- und NF-kappa-B-Regulationssystemen verbunden sind. 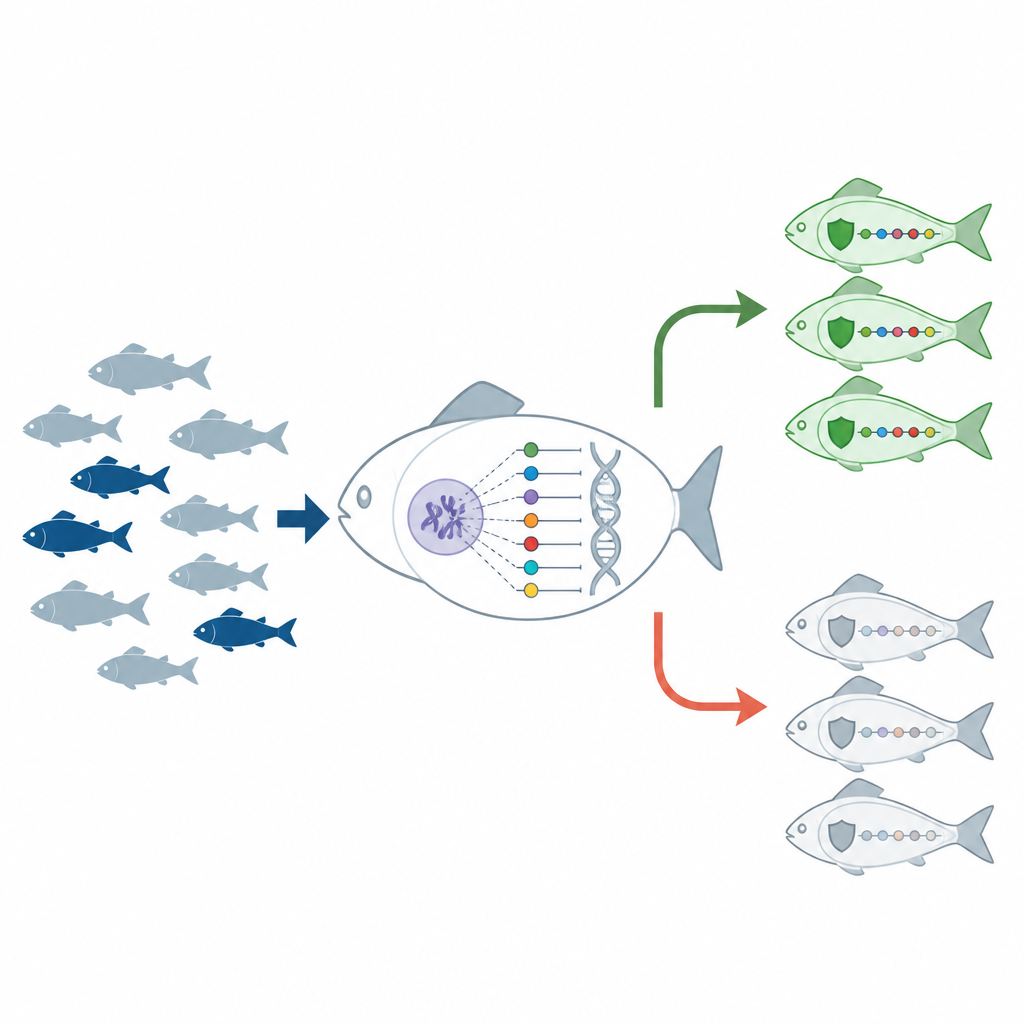
Prüfung eines genetischen Screening-Tools
Um zu testen, ob diese DNA-Marker Fische in der Praxis nach ihrer Widerstandskraft sortieren können, setzten die Forschenden eine neue Gruppe von 360 Forellen dem Bakterium aus. Nach dem Ausbruch nutzten sie eine Labormethode namens Multiplex-PCR, um alle sechs SNPs gleichzeitig aus einem kleinen Flossenstück abzulesen. In der anfälligen Gruppe trugen die meisten Fische SNP-Kombinationen, die mit Schwäche verbunden waren, während in der resistenten Gruppe die meisten das entgegengesetzte Muster zeigten. Insgesamt klassifizierte der Gentest etwa 88 Prozent der Fische korrekt, und die Übereinstimmung zwischen DNA-Muster und Überleben war statistisch signifikant. Rund 15 Prozent der gesamten Population trugen ein vollständig resistentes Genotypmuster, was darauf hindeutet, dass bereits eine krankheitsresistente Linie im Entstehen begriffen ist.
Was das für künftige Forellenzuchten bedeutet
Für Nicht-Spezialisten ist die Kernaussage einfach: Indem man beobachtet, welche Gene während einer Infektion hochfahren, und die Forellen-DNA nach kleinen, konsistenten Unterschieden durchsucht, haben Wissenschaftler eine kurze Liste genetischer Marker identifiziert, die robuste Fische von anfälligen unterscheiden. Diese Marker könnten es Züchtern ermöglichen, junge Forellen zu screenen, bevor sie je mit Krankheit in Kontakt kommen, und schrittweise Bestände aufzubauen, die weniger Verluste erleiden und weniger Behandlungen benötigen. Zwar sind weitere Untersuchungen in größeren und unterschiedlichen Populationen nötig, doch die Studie zeigt, wie sorgfältige genetische Spurensuche eine gesündere Aquakultur fördern und den Schutz von Fischen in einigen der höchsten Flusssysteme der Welt unterstützen kann.
Zitation: Zhou, J., Sun, S., Wang, W. et al. Transcriptome and resequencing reveal immune-related genes and molecular markers associated with Aeromonas salmonicida resistance in Salmo trutta fario. Sci Rep 16, 14909 (2026). https://doi.org/10.1038/s41598-026-45045-8
Schlüsselwörter: Bachforelle, Fischkrankheitsresistenz, Aquakulturgenetik, Aeromonas salmonicida, SNP-Marker