Clear Sky Science · de
Untersuchung exosombezogener Gene als potenzielle Biomarker bei primärer immunthrombozytopenie mittels Transkriptomik und vorläufiger experimenteller Validierung
Warum diese Blutungsstörung wichtig ist
Leichte Blutergüsse oder häufige Nasenbluten können manchmal auf ein verborgenes Problem mit den Blutplättchen hinweisen — den winzigen Zellfragmenten, die bei der Blutgerinnung helfen. Die primäre immunthrombozytopenie (ITP) ist eine solche Erkrankung, bei der das Immunsystem fälschlich die Thrombozyten zerstört. Ärzte stellen die Diagnose ITP bislang meist durch Ausschluss anderer Ursachen, weil es keinen einfachen, spezifischen Labortest gibt. Diese Studie untersucht, ob winzige Partikel namens Exosomen und die mit ihnen verbundenen Gene den Weg zu besseren Bluttests und möglicherweise neuen Therapien weisen könnten.
Kleine Transporter mit großer Botschaft
Exosomen sind mikroskopische Bläschen, die von Zellen freigesetzt werden und Proteine sowie genetisches Material durch den Blutkreislauf transportieren — sie fungieren als Kuriere zwischen Zellen. Frühere Arbeiten deuteten darauf hin, dass Exosomen bei ITP Signale enthalten könnten, die das Gleichgewicht des Immunsystems stören und die Thrombozytenbildung im Knochenmark beeinträchtigen. Die Autorinnen und Autoren vermuteten, dass Gene, die mit Exosomen in Verbindung stehen, einen erkennbaren Fingerabdruck in den Blutzellen von Menschen mit ITP hinterlassen könnten. Indem sie ablesend ermitteln, welche Gene stärker oder schwächer aktiv sind, hofften sie, Muster zu finden, die Patienten von gesunden Probanden unterscheiden und Hinweise auf die Krankheitsentstehung liefern.
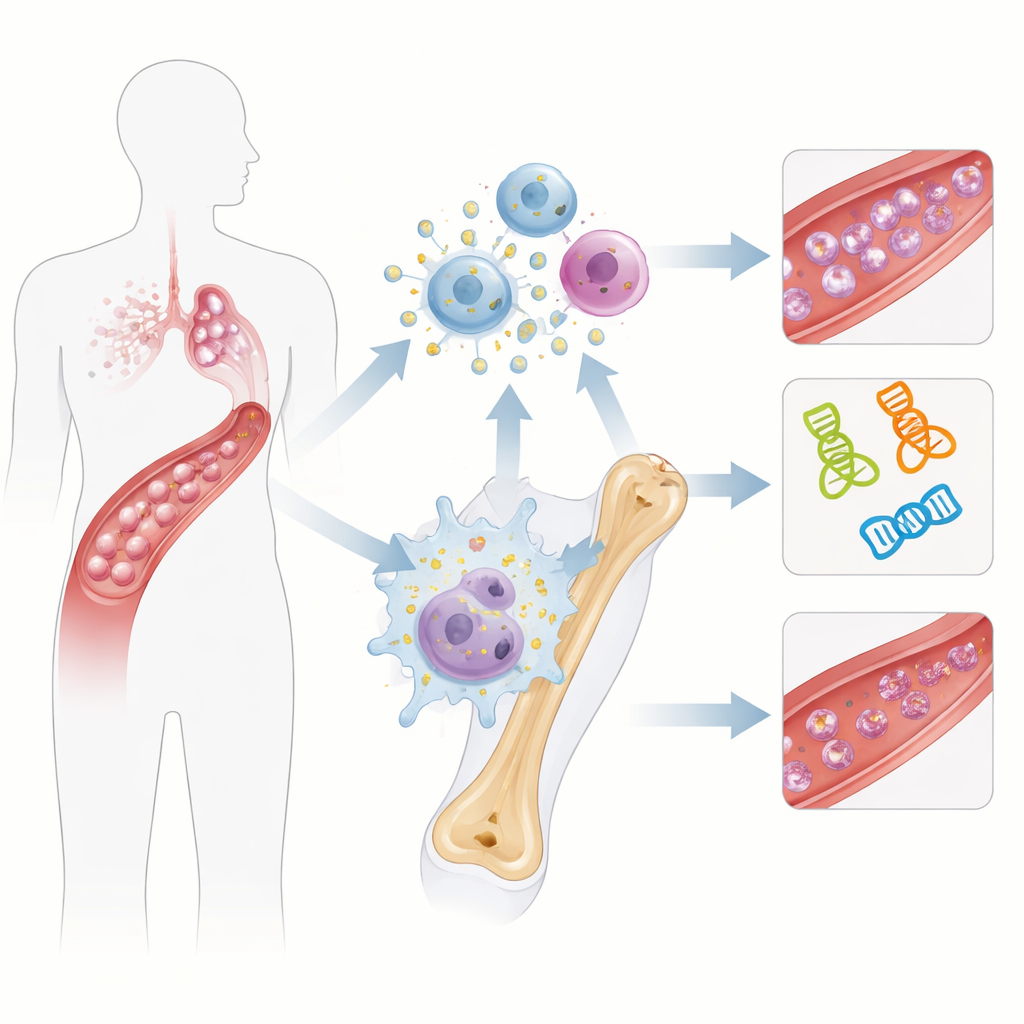
Durchforsten von Tausenden Genen
Das Team begann mit öffentlichen Datenbanken, die Genaktivitätsprofile von T‑Zellen — einer Art weißer Blutkörperchen — von ITP‑Patienten und gesunden Kontrollen enthielten. Sie verglichen diese Profile mit einer kuratierten Liste von Genen, die als exosombezogen bekannt sind. Mithilfe statistischer Methoden identifizierten sie zunächst Gene, die bei ITP hoch- oder herunterreguliert sind. Anschließend erzeugten sie Netzwerke, die zeigen, welche Gene dazu neigen, gemeinsam ein- oder ausgeschaltet zu werden, und suchten nach größeren Gruppen, die mit Exosomenaktivität verknüpft sind. Aus Tausenden von Kandidaten reduzierten sie die Liste auf 23 Gene, die sowohl bei ITP verändert waren als auch starke Verbindungen zu exosombezogenen Netzwerken aufwiesen.
Ein Kernsatz vielversprechender Marker
Um diese Liste weiter zu verfeinern, wandten die Forschenden zwei Methoden des maschinellen Lernens an, die darauf ausgelegt sind, aus komplexen Daten die informativsten Merkmale herauszufiltern. Beide Verfahren identifizierten unabhängig voneinander dieselben vier Gene: GABARAPL1, SLC39A14, HIBADH und GSR. Diese Gene sind an Prozessen wie zellulärem Recycling (Autophagie), dem Umgang mit dem Spurenelement Zink, dem Energiehaushalt und dem Schutz vor oxidativem Schaden beteiligt. Das Team erstellte dann ein einfaches Vorhersagewerkzeug, das die Aktivitätsniveaus dieser vier Gene kombiniert, um einzuschätzen, ob eine Probe von einer Person mit ITP oder von einer gesunden Kontrolle stammt. In dem kleinen verwendeten Datensatz trennte dieser Score die beiden Gruppen recht gut, was darauf hindeutet, dass diese Gene wichtige Aspekte der Erkrankung erfassen.
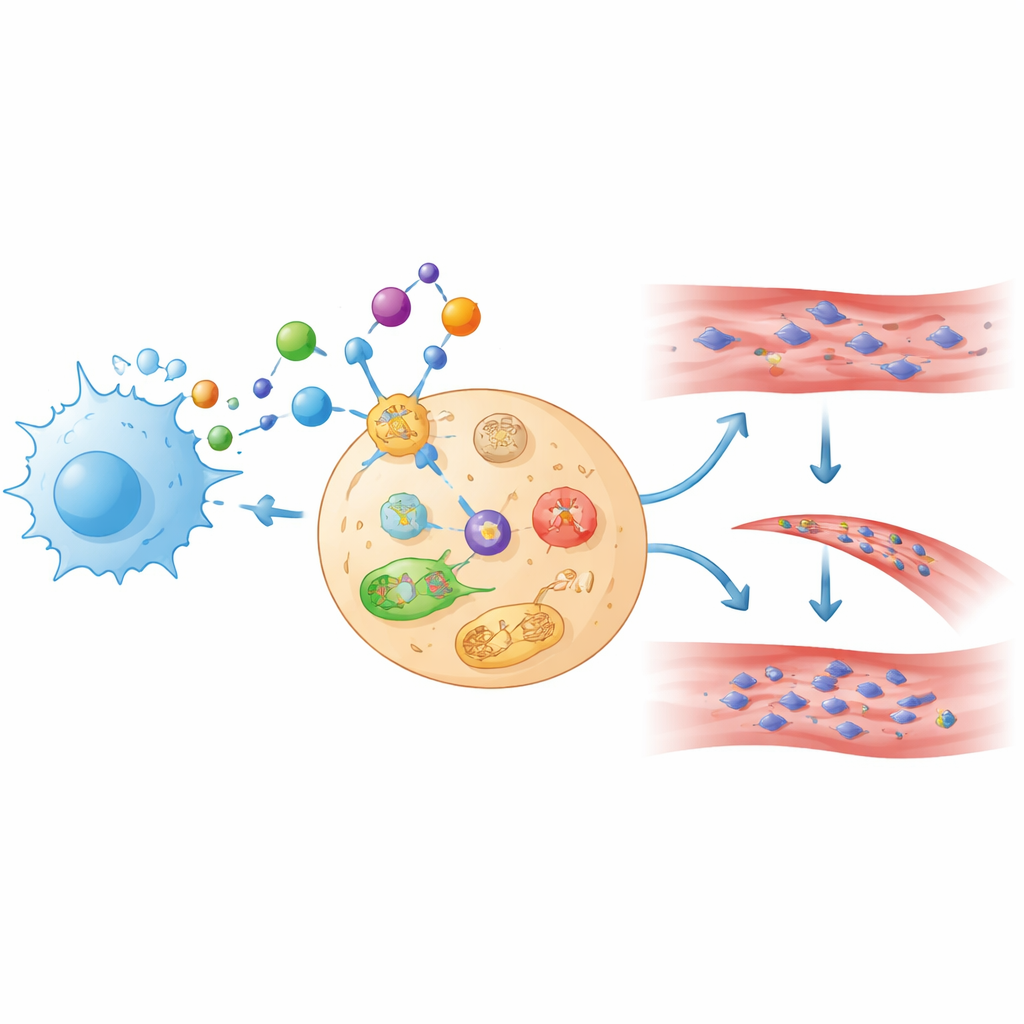
Prüfung der Kandidaten
Bioinformatische Vorhersagen können irreführend sein, wenn sie nicht in Proben aus der Praxis überprüft werden, daher bestimmten die Autorinnen und Autoren die Aktivität der vier Gene in Blutproben von 20 ITP‑Patienten und 20 gesunden Freiwilligen. Drei Gene — GABARAPL1, SLC39A14 und GSR — waren bei den Patienten deutlich weniger aktiv, während HIBADH keinen konsistenten Unterschied zeigte. Dieselben drei Gene verhielten sich auch in zusätzlichen, unabhängigen Genexpressionsdatensätzen ähnlich. Computeranalysen deuteten darauf hin, dass sie an Kreuzungen von Signalwegen liegen, die mit RNA‑Verarbeitung, zellulärem Stress und Proteinabbau verbunden sind. Ein Screening von Wirkstoff‑Gen‑Datenbanken und Docking‑Simulationen legte nahe, dass vorhandene Verbindungen physisch an Proteine binden könnten, die von zwei dieser Gene codiert werden — ein erster Hinweis für mögliche Repositionierungsstudien von Medikamenten, wobei daraus noch keine Therapieempfehlungen ableitbar sind.
Was das für die zukünftige Versorgung bedeuten könnte
Diese Arbeit liefert keinen sofort einsetzbaren Diagnosetest, aber sie rückt drei exosombezogene Gene — GABARAPL1, SLC39A14 und GSR — als besonders vielversprechende Kandidaten in den Fokus. Ihre verringerte Aktivität bei ITP‑Patienten, beobachtet sowohl in Datenbanken als auch in tatsächlichen Blutproben, legt nahe, dass sie dazu beitragen könnten, zu erklären, warum Thrombozyten zerstört werden oder sich nicht richtig entwickeln. Da die Studie vergleichsweise wenige Teilnehmende umfasste und stark auf rechnerische Methoden setzte, sollten die Ergebnisse als Ausgangspunkt für weitergehende labor- und klinische Forschung gesehen werden. Bestätigen und erweitern künftige Studien diese Befunde, könnte das Messen der Genaktivität dieser Gene oder der Exosomen, die deren Signale transportieren, Ärzten schließlich helfen, ITP genauer zu diagnostizieren und Therapien zu entwickeln, die das Immunsystem wieder in ein gesünderes Gleichgewicht bringen.
Zitation: Lou, F., Chen, Z., Yuan, Z. et al. Exploring exosome-related genes as candidate biomarkers in primary immune thrombocytopenia through transcriptomics and preliminary experimental validation. Sci Rep 16, 14322 (2026). https://doi.org/10.1038/s41598-026-43618-1
Schlüsselwörter: immunthrombozytopenie, Exosomen, Biomarker, Thrombozytenerkrankungen, Genexpression