Clear Sky Science · de
3DViT-GAT: ein einheitliches atlasbasiertes 3D-Vision-Transformer- und Graph-Learning‑Framework zur Erkennung der Major Depression anhand struktureller MRT-Daten
Warum Hirnschnitte die Diagnose von Depression verändern könnten
Major-Depressive-Disorder betrifft Hunderte Millionen Menschen, dennoch stellen Ärztinnen und Ärzte die Diagnose meist durch Gespräche mit Patientinnen und Patienten und durch Beobachtung des Verhaltens. Dieser Ansatz ist unverzichtbar, kann aber subjektiv und uneinheitlich sein. In dieser Studie wird untersucht, ob detaillierte Hirnscans kombiniert mit moderner künstlicher Intelligenz eine objektivere Unterstützung der Diagnostik bieten können — indem ein Computer darauf trainiert wird, feine strukturelle Veränderungen im Gehirn zu erkennen, die mit Depression in Verbindung stehen.
Mit moderner Bildgebung ins Gehirn blicken
Die Forschenden konzentrieren sich auf strukturelle MRT, eine Scan‑Methode, die die Anatomie des Gehirns in hoher Detailtiefe zeigt, bis hin zu winzigen dreidimensionalen Einheiten, sogenannten Voxel. Frühere Computermethoden untersuchten oft jeden Voxel einzeln oder stützten sich auf von Expertinnen und Experten erstellte Zusammenfassungen. Diese Ansätze sind nützlich, können aber breitere Muster über mehrere Hirnregionen hinweg übersehen. Das Team zielt stattdessen darauf ab, diese Muster automatisch im gesamten Gehirn zu erlernen und nutzt dafür einen großen öffentlichen Datensatz mit mehr als zweitausend Personen mit und ohne diagnostizierte Depression, die an vielen Krankenhäusern und Forschungseinrichtungen erhoben wurden.
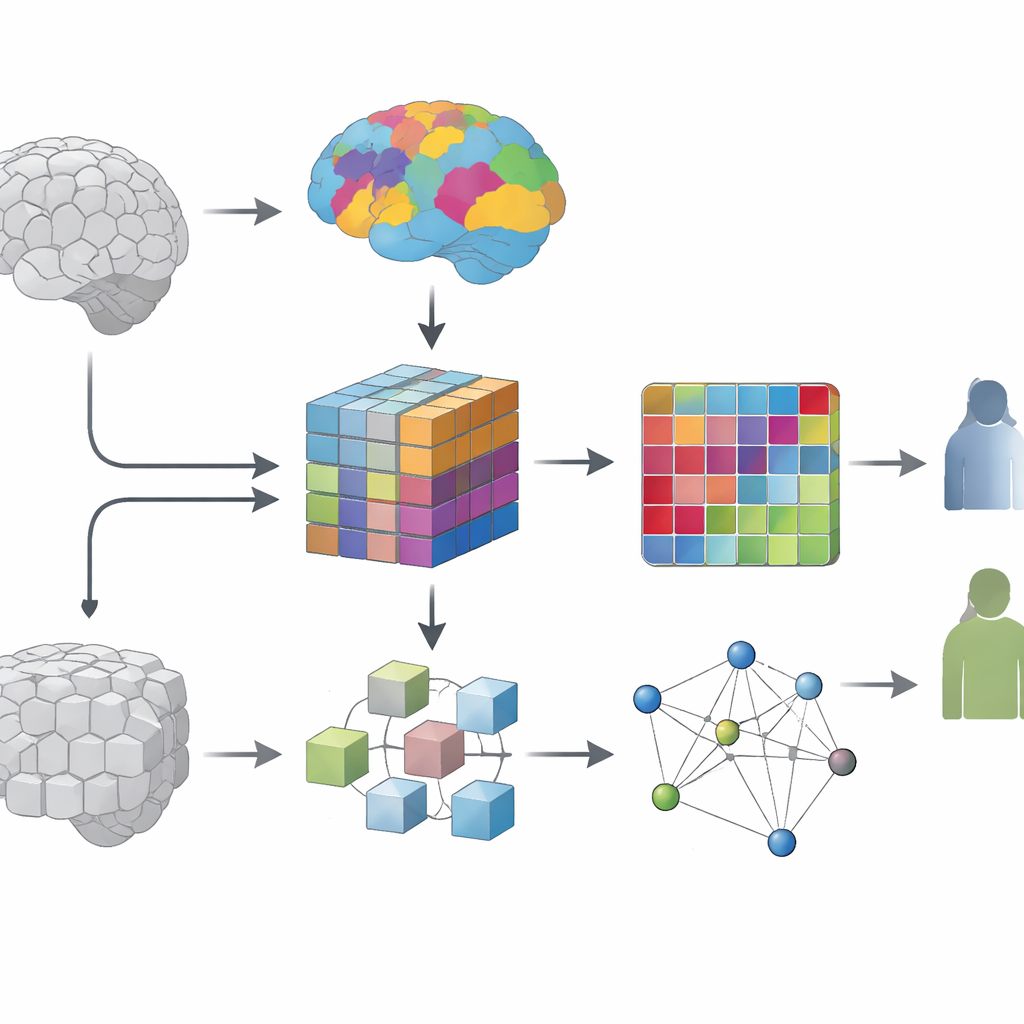
Dem Modell beibringen, Hirnregionen zu sehen, nicht nur Pixel
Eine zentrale Frage dieser Arbeit ist, wie man das Gehirn in sinnvolle Teile zerlegt, damit der Computer sie analysieren kann. Eine Möglichkeit ist, den Scan in gleichmäßige Würfel zu zerschneiden, wie Brot in identische Stücke. Eine andere ist, bestehenden Hirn‑Landkarten (Atlanten) zu folgen, die Voxel in Regionen gruppieren, von denen bekannt ist, dass sie ähnliche Struktur oder Funktion teilen. Die Autorinnen und Autoren vergleichen diese beiden Strategien systematisch. In beiden Fällen verwenden sie eine Art Deep‑Learning‑Modell, einen Vision‑Transformer, angepasst für 3D‑Daten, um jede Region in einen kompakten numerischen Fingerabdruck zu verwandeln, der sowohl lokale Details als auch längerreichende Zusammenhänge innerhalb der Region erfasst.
Regionen in ein Netzwerk von Verbindungen verwandeln
Gehirne sind nicht bloß Ansammlungen isolierter Bereiche — sie bilden Netzwerke. Um das abzubilden, erstellt das Team für jede Teilnehmerin bzw. jeden Teilnehmer ein personalisiertes Netzwerk. Jeder Knoten in diesem Netzwerk entspricht einer Hirnregion, und die Stärke der Verbindung zwischen zwei Knoten spiegelt wider, wie ähnlich ihre gelernten Fingerabdrücke sind. Das Ergebnis ist ein Graph, der zusammenfasst, wie die Hirnregionen einer Person strukturell zueinander in Beziehung stehen. Ein zweiter KI‑Modelltyp, ein Graph Attention Network, lernt dann, welche Regionen und Verbindungen die wichtigsten Informationen zur Unterscheidung von depressiven Patientinnen bzw. Patienten und gesunden Kontrollpersonen liefern, und hebt so die informativsten Pfade hervor.
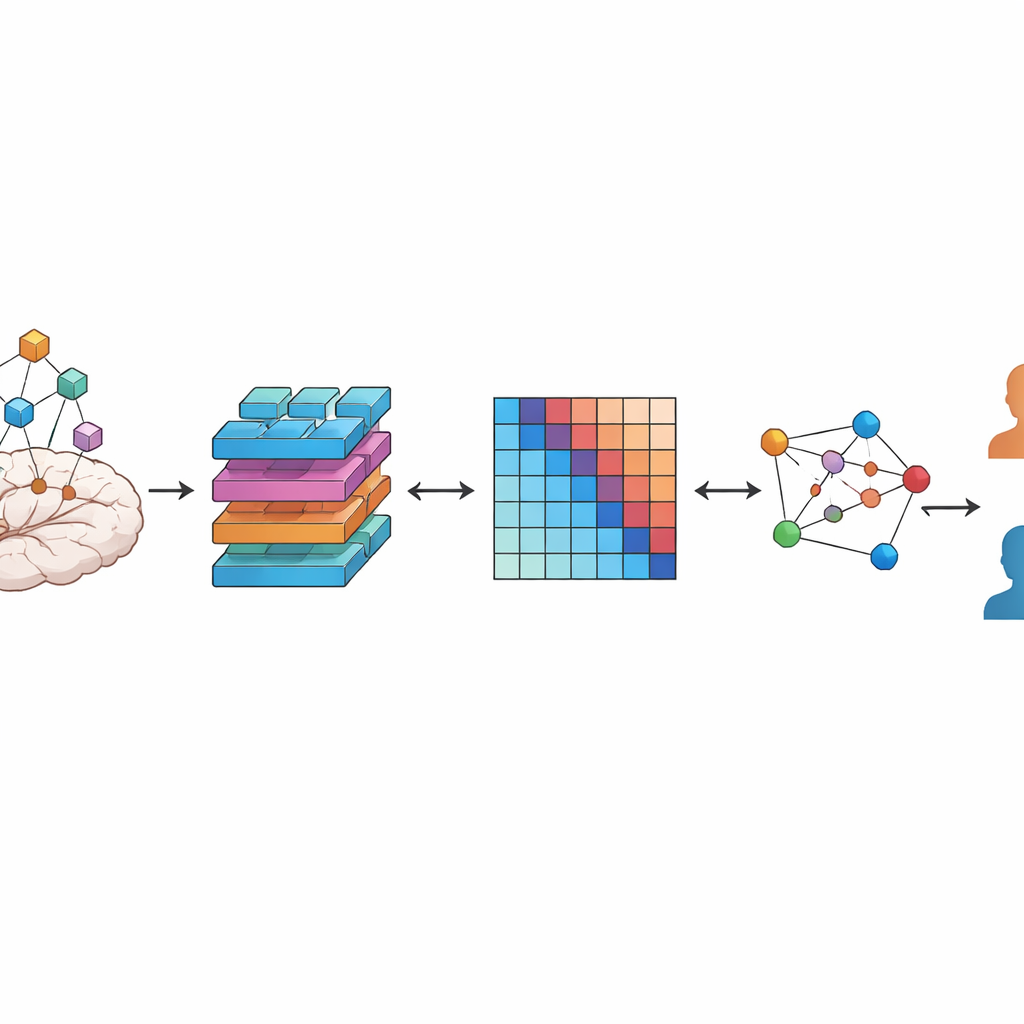
Wie gut das System funktioniert und was es offenbart
Bei umfangreichen Tests mit stratifizierter 10‑fach‑Kreuzvalidierung erreichte das kombinierte Transformer‑plus‑Graph‑System eine Genauigkeit von etwa 81,5 Prozent, mit hoher Sensitivität (korrekte Identifikation von Personen mit Depression) und solider Spezifität (korrekte Identifikation gesunder Kontrollen). Wichtig ist, dass Modellvarianten, die atlasdefinierte Hirnregionen nutzten, konstant bessere Leistungen erzielten als solche, die auf gleichmäßigen Würfeln basierten, obwohl die würfelbasierte Methode eine ähnliche Rechenkomplexität aufwies. Das deutet darauf hin, dass das Einbeziehen vorhandenen anatomischen Wissens — statt das Gehirn als einheitlichen Block zu behandeln — dem Modell hilft, klarere, robustere Signale zu finden, die mit Depression zusammenhängen. Folgeanalysen der trainierten Modelle zeigten Spitzen in fronto‑parietalen, sensomotorischen, okzipitalen, zerebellaren sowie frontal‑insulären Regionen und stimmen mit früheren Studien überein, die diese Bereiche mit Veränderungen von Stimmung, Denken und Bewegung bei Depression in Verbindung bringen.
Was das für die Zukunft der Diagnostik bedeutet
Für Nicht‑Spezialistinnen und Nicht‑Spezialisten lautet die Schlussfolgerung: Die Autorinnen und Autoren haben eine Pipeline zur Analyse von Hirnscans entwickelt, die zwei Dinge gleichzeitig leistet — sie berücksichtigt die bekannte Anordnung des Gehirns und erlaubt leistungsfähigen KI‑Modellen zugleich, neue Muster in der Beziehung zwischen Regionen zu entdecken. Ihre Ergebnisse zeigen, dass diese atlasgesteuerte, netzwerkbasierte Sicht des Gehirns Depression in MRT‑Scans genauer erkennen kann als viele frühere Ansätze. Obwohl die Methode noch nicht bereit ist, klinische Untersuchungen zu ersetzen, rückt sie das Feld näher an objektive bildgebende Werkzeuge, die eines Tages eine frühere und zuverlässigere Diagnose unterstützen, Behandlungswirkungen überwachen und unser Verständnis darüber vertiefen könnten, wie Depression die Struktur und Netzwerke des Gehirns verändert.
Zitation: Alotaibi, N.M., Alhothali, A.M. & Ali, M.S. 3DViT-GAT: a unified atlas-based 3D vision transformer and graph learning framework for major depressive disorder detection using structural MRI data. Sci Rep 16, 11595 (2026). https://doi.org/10.1038/s41598-026-42108-8
Schlüsselwörter: Major-Depressive-Disorder, Gehirn‑MRT, Deep Learning, Vision-Transformer, Graph-Neuronale Netze