Clear Sky Science · de
Gewebe- und Reife-spezifische DNA-Methylierungsdynamik von Gonadotropin-Genen beim Makrelen-ähnlichen Scomber japonicus mittels kostengünstiger, gezielter Bisulfit-Sequenzierung
Warum die Fruchtbarkeit von Fischen uns alle betrifft
Meeresfrüchte auf unseren Tellern und gesunde Meeresökosysteme hängen beide davon ab, dass Fische unter sich erwärmenden Gewässern und wachsender Aquakultur zuverlässig reproduzieren können. Diese Studie blickt in den Körper der Makrelenartigen Scomber japonicus — einer wichtigen kommerziellen Art — und untersucht, wie kleine chemische Markierungen auf der DNA dabei helfen, Fortpflanzungshormone ein- und auszuschalten, während die Fische heranwachsen. Außerdem stellt die Arbeit eine schnellere, günstigere Methode vor, um diese DNA-Marken zu verfolgen, und schafft damit Möglichkeiten für klügere, nachhaltigere Aquakultur.
Kleine Schalter auf der DNA
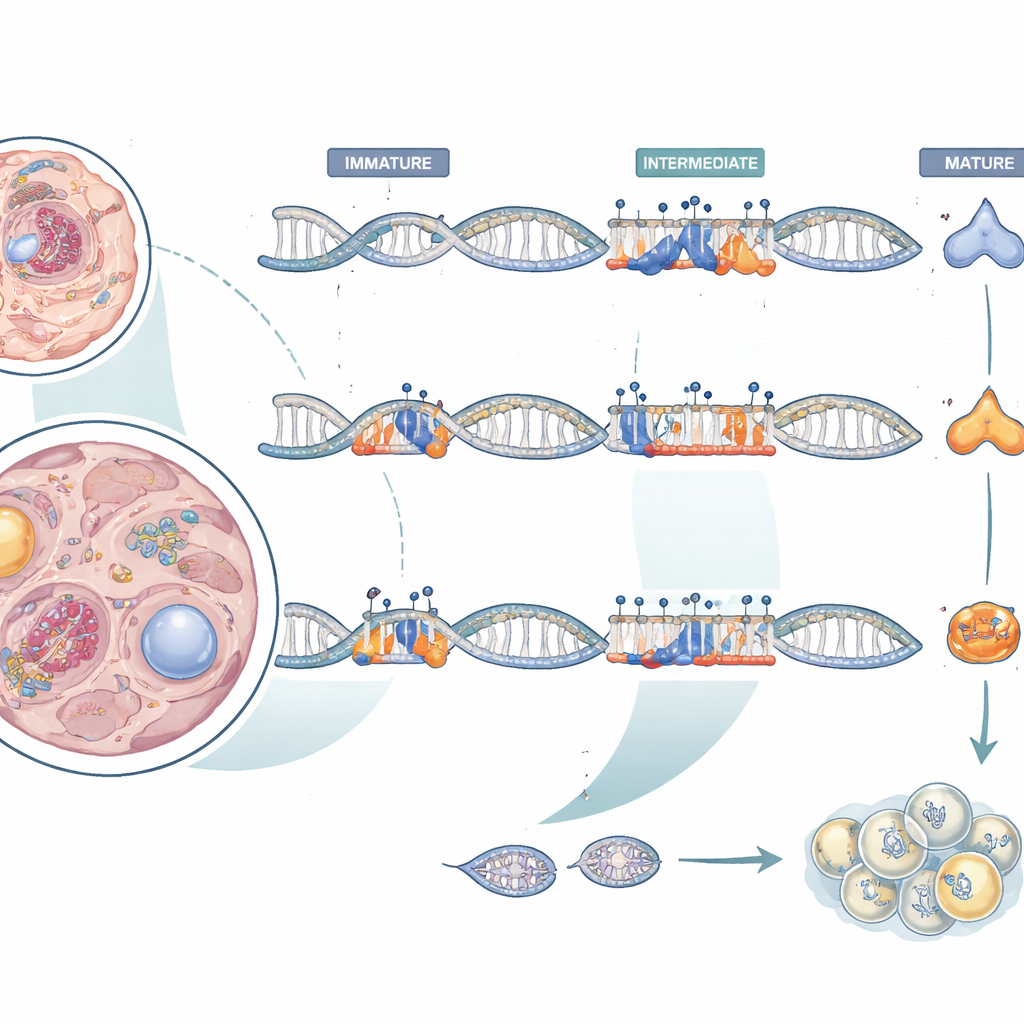
Unsere Gene sind von einer zusätzlichen Kontrollschicht aus chemischen Markern umhüllt, die die Genaktivität erhöhen oder verringern können, ohne den genetischen Code selbst zu verändern. Ein solcher Marker, die DNA-Methylierung, wirkt oft wie ein Dimmer: Wird sie in der Nähe eines Gens angebracht, neigt dieses dazu, leiser zu werden. Die Autoren konzentrierten sich auf zwei Hormone, die in der Hypophyse des Gehirns gebildet werden — das Follikelstimulierende Hormon (FSH) und das Luteinisierende Hormon (LH) — die gemeinsam die Ei- und Spermienproduktion steuern. Indem sie die Methylierung rund um die DNA dieser Hormone in verschiedenen Geweben und Lebensstadien von gefarmten Makrelen untersuchten, fragten sie, wie sich dieser chemische Code verändert, wenn Fische von der Jugend zur Geschlechtsreife übergehen.
Eine schnellere Methode, den chemischen Code zu lesen
Die detailgetreue Erfassung von Methylierung ist üblicherweise langsam und teuer. Traditionelle Ansätze sequenzieren ein DNA-Fragment nach dem anderen, was die Anzahl der analysierbaren Tiere oder Gewebe einschränkt. In dieser Studie passte das Team eine ursprünglich für Pflanzen entwickelte Methode der gezielten Bisulfit-Sequenzierung für Fische an. Sie befestigten kurze Identifikations-Tags an vielen DNA-Fragmenten und sequenzierten diese gemeinsam auf einem Hochdurchsatzsequenzierer, um anschließend mit Software Proben und Zielregionen auseinanderzuhalten. So konnten sie 2.880 DNA-Ziele von 96 Fischen über fünf Gewebe — Gonade, Leber, Gehirn, Hypothalamus und Hypophyse — zu einem Bruchteil der Kosten und des Aufwands klassischer Methoden analysieren, dabei jedoch mit ausreichender Tiefe, um feine Methylierungsunterschiede zu erkennen.
Wie sich Hormon-Gene mit der Reife verändern
Das grobe Muster war, dass die Methylierung rund um die FSH- und LH-Gene stark vom Gewebetyp und davon abhängig war, ob die Fische unreif oder in der Fortpflanzungsperiode waren. In den meisten Geweben blieb die Methylierung in der Nähe des FSH-Gens hoch und relativ stabil. In unreifen Gonaden war sie jedoch niedriger, und in reifen Hypophysen verloren bestimmte Stellen Methylierung, sodass dieses Gewebe am wenigsten methyliert und am aktivsten in der FSH-Produktion war. Das LH-Gen zeigte in der Hypophyse den entgegengesetzten Trend: Der Bereich innerhalb des Gens selbst war bei reifen Fischen stärker methyliert, obwohl die LH-Spiegel höher waren. Dieser Befund unterstreicht, dass Methylierung kein einfacher „Aus“-Schalter ist — ihre Wirkung hängt davon ab, wo sie sitzt und welche Proteine dort binden wollen.
Eine versteckte Bremse innerhalb des Hormon-Gens
Um zu untersuchen, wie lokale DNA-Elemente die LH-Produktion formen, testeten die Forscher kurze Abschnitte des LH-Gens in kultivierten Zellen mit einem lichterzeugenden Reportersystem. Das Entfernen eines winzigen zehn Basenpaare langen Segments innerhalb des ersten Introns — eines nichtkodierenden Abschnitts im Gen — ließ das Reportersignal ansteigen, was darauf hindeutet, dass dieses Stück normalerweise als Bremse der Genaktivität wirkt. Dieses Segment überlappt eine vorhergesagte Bindungsstelle für ein verbreitetes Regulationsprotein, bekannt als Sp1. Interessanterweise war die nahegelegene DNA-Methylierung an dieser Stelle im Allgemeinen gering und änderte sich mit der Reifung kaum, was darauf hindeutet, dass die Stärke dieser Bremse entweder durch kleine, schwer nachweisbare Methylierungsverschiebungen oder durch andere nahegelegene Kontrollstellen feinjustiert wird. Das Team maß außerdem Gene, die Methylierungsmarker hinzufügen und entfernen, und fand heraus, dass deren Aktivität sich gewebespezifisch mit der Reifung veränderte — ein Hinweis auf ein aktives Umgestalten des chemischen Codes und nicht nur auf altersbedingte Veränderungen.
Was das für Fische und die Fischzucht bedeutet
Zusammengefasst zeigt die Studie, dass sich die chemischen Markierungen auf der DNA rund um Schlüsselhormone der Fortpflanzung in bestimmten Geweben ändern, wenn Makrelen-ähnliche Fische in die Fortpflanzungsphase kommen, und dass ein kleines internes Element im LH-Gen als eingebaute Bremse der Hormonproduktion wirken kann. Gleichzeitig beweist die verbesserte Sequenziermethode, dass es nun praktikabel ist, diese epigenetischen Muster über Hunderte von Zielen und viele Individuen hinweg zu erfassen. Für Nicht-Spezialisten ist die Quintessenz: Die Fruchtbarkeit von Fischen wird nicht nur von Genen gesteuert, sondern auch von einer flexiblen chemischen Ebene, die auf den inneren Zustand und möglicherweise auf die Umwelt reagiert. Das Verständnis und gegebenenfalls die Lenkung dieser Ebene könnte Züchtern helfen, gesunde, zuverlässig laichende Fische zu produzieren und gleichzeitig den Druck auf Wildbestände zu verringern.
Zitation: Galotta, M., Ogino, Y., Nagano, N. et al. Tissue and maturation specific DNA methylation dynamics of gonadotropin genes in chub mackerel (Scomber japonicus) using cost-effective targeted bisulfite sequencing. Sci Rep 16, 12222 (2026). https://doi.org/10.1038/s41598-026-40580-w
Schlüsselwörter: Fischreproduktion, DNA-Methylierung, Gonadotropinhormone, Epigenetik in der Aquakultur, gezielte Bisulfit-Sequenzierung