Clear Sky Science · de
Genomassemblierung und Annotation der in Japan gehaltenen Nacktmull-Art Heterocephalus glaber
Ein kleines unterirdisches Säugetier mit großen Geheimnissen
Der Nacktmull mag wie ein runzeliges, rosafarbenes Kuriosum aussehen, doch er fasziniert Wissenschaftler, weil er langsam altert, gegen Krebs resistent ist und in stickigen unterirdischen Tunneln mit sehr wenig Sauerstoff überlebt. Um zu verstehen, wie dieses Tier diese Fähigkeiten erzielt, brauchen Forscher nicht nur einen genetischen Bauplan, sondern mehrere Versionen aus verschiedenen Populationen. Diese Studie präsentiert eine neue, hochwertige Karte der DNA des Nacktmulls aus einer in Japan gehaltenen Kolonie und vergleicht sie mit bestehenden Karten, um subtile genetische Unterschiede aufzudecken, die seinem ungewöhnlichen Lebensstil und dem langen, gesunden Leben zugrunde liegen könnten.
Warum eine genetische Karte nicht ausreicht
Bisher stützte sich ein Großteil der Forschung am Nacktmull-Genom auf ein einziges Referenzgenom, das als Standard für die gesamte Art galt. Individuen und Populationen können sich jedoch in wichtigen Punkten unterscheiden, und diese Unterschiede gehen verloren, wenn nur ein einziges Beispiel verwendet wird. Frühere Arbeiten deuteten an, dass Nacktmulle, die in verschiedenen Regionen Ostafrikas leben, genetisch so unterschiedlich sein können wie eng verwandte Arten, und dass Flüsse Populationen trennen und die Fortpflanzung einschränken können. Dennoch gab es nicht genügend vollständige Genome, um zu sehen, wie ihre DNA entlang der Chromosomen oder innerhalb bestimmter Gene tatsächlich variiert.
Aufbau eines neuen Genoms aus einer japanischen Kolonie
Das Team konzentrierte sich auf eine langjährig in Laboren gehaltene Kolonie in Japan, die auf Tiere zurückgeht, die vor Jahrzehnten im nordöstlichen Afrika gesammelt wurden. Sie extrahierten sorgfältig DNA aus dem Muskel eines einzelnen Männchens und nutzten zwei moderne Sequenzieransätze: sehr lange Reads einer Plattform, um große DNA-Abschnitte zu überbrücken, und große Mengen kürzerer Reads einer anderen Plattform zur Fehlerkorrektur. Spezialisierte Software setzte diese Teile zu einem Genom mit 2,56 Milliarden "Buchstaben" zusammen — ähnlich groß wie das menschliche Genom — und Tests zeigten, dass mehr als 95 % der standardmäßigen Säugetiergene vollständig vorhanden sind. Die Forschenden nutzten dann eine Kombination aus bestehenden RNA-Daten und Protein-Datenbanken, um 26.714 proteinkodierende Gene vorherzusagen und nahezu allen wahrscheinliche Funktionen zuzuweisen.
Gene finden, die zuvor übersehen wurden
Mit dieser neuen Karte stellten die Wissenschaftler eine einfache Frage: Welche Gene erscheinen hier, die im früheren Nacktmull-Referenzgenom nicht richtig erfasst waren? Beim Vergleich ihrer vorhergesagten Proteine mit denen von Mensch, Maus, Meerschweinchen und zwei früheren Nacktmull-Genomen fanden sie 417 Genmodelle, die klare Entsprechungen in anderen Säugetieren hatten, im älteren Nacktmull-Annotat jedoch fehlten oder unvollständig waren. Die meisten dieser Regionen existierten zwar bereits in der älteren Sequenz, wurden aber nicht als vollständige Gene erkannt, was bedeutet, dass die neue Arbeit Lücken füllt, statt die frühere Karte zu widerlegen. Insgesamt wurden 417 zuvor unentdeckte Genmodelle katalogisiert und damit das Werkzeugset für Forschende, die die Biologie des Nacktmulls untersuchen, erweitert.
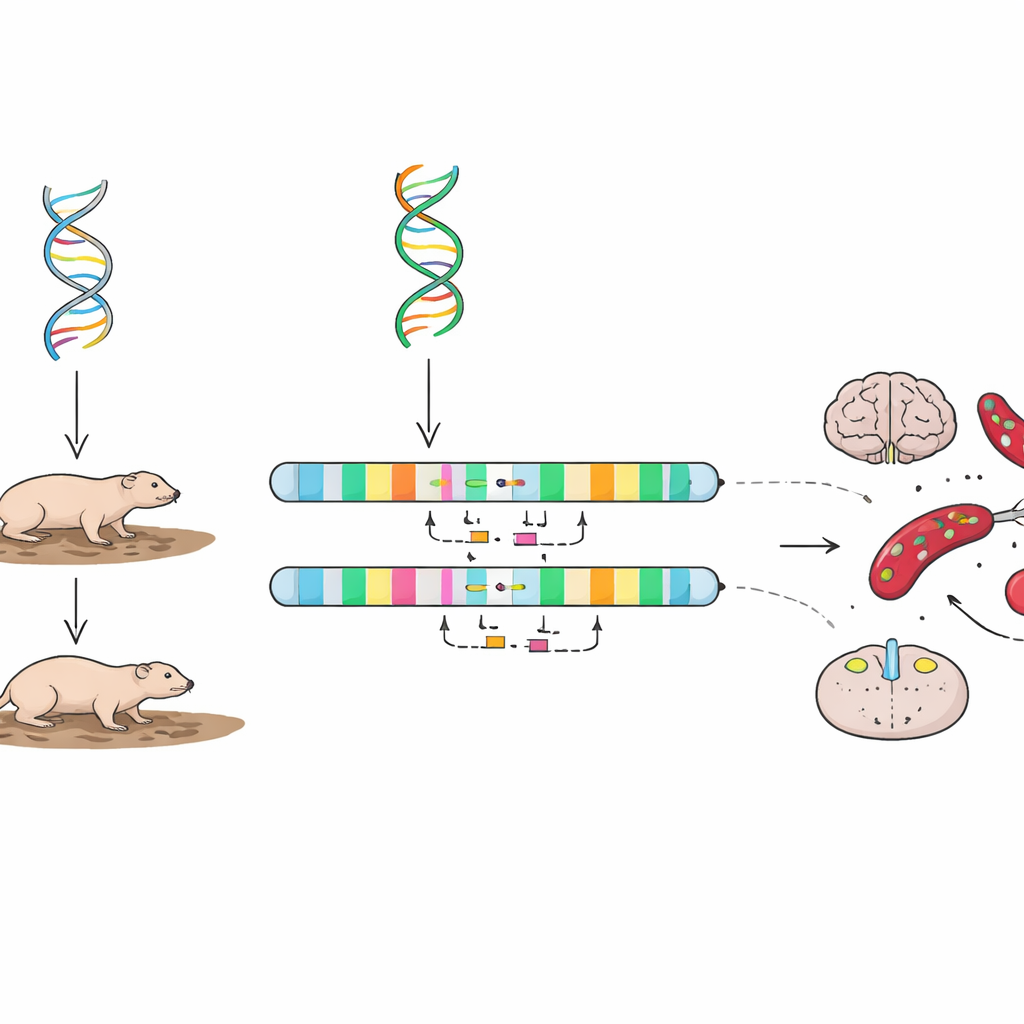
Subtile DNA-Veränderungen und ihre mögliche Bedeutung
Die Studie zoome dann auf die Ebene ganzer Chromosomen hinaus, um zu sehen, wie das neue Genom mit älteren verglichen werden kann. Mithilfe grafischer "Punktdiagramme", die übereinstimmende DNA-Abschnitte ausrichten, sahen die Autorinnen und Autoren überwiegend gerade, saubere Diagonalen — ein Hinweis darauf, dass die Gesamtstruktur des Genoms zwischen Individuen sehr ähnlich ist. Eine Handvoll vermeintlicher Umkehrungen und Umordnungen trat auf, doch bei näherer Prüfung zeigte sich, dass viele davon nahe Lücken in der älteren Assemblierung liegen, was auf technische Artefakte statt auf echte biologische Veränderungen hindeutet. Betrachtet man kleinere strukturelle Veränderungen wie kurze Insertionen und Deletionen, war die Zahl der Unterschiede zwischen Nacktmull-Genomen deutlich geringer als die, die üblicherweise zwischen Labormausstämmen beobachtet werden, was darauf hindeutet, dass diese gehaltene Population auf struktureller Ebene relativ einheitlich ist.
Genetische Anpassungen in Verbindung mit Verhalten, Sauerstoff und Altern
Über die großräumige Struktur hinaus untersuchten die Forschenden Veränderungen in den tatsächlichen Proteinsequenzen, die von Genen codiert werden. Sie übertrugen ihre Genannotationen auf das ältere Referenzgenom und identifizierten 177 Transkripte mit besonders ausgeprägten Sequenzunterschieden. Der Vergleich mit ähnlichen Analysen in Mäusen hob 77 Gene hervor, deren Variation für Nacktmulle charakteristisch zu sein scheint. Viele dieser Gene sind an der Wahrnehmung und Reaktion von Zellen auf chemische Botenstoffe beteiligt, darunter Rezeptoren für Serotonin, ein stimmungsrelevantes Signal im Gehirn, und für L-DOPA, eine Substanz, die mit Bewegung und Belohnung zusammenhängt. Andere beeinflussen Hormonwege, die die Produktion roter Blutkörperchen und den Stoffwechsel steuern. Diese Unterschiede könnten soziale Interaktionen in dicht besiedelten Kolonien beeinflussen, den Tieren helfen, mit niedrigem Sauerstoff umzugehen, oder zu ihrer ungewöhnlichen Reaktion auf Altern und Zellschädigung beitragen.
Eine neue Grundlage zur Entschlüsselung eines bemerkenswerten Tieres
Am Ende beansprucht diese Arbeit nicht, die genauen Gene zu identifizieren, die Nacktmulle langlebig, krebsresistent oder tolerant gegenüber erstickenden Tunneln machen. Stattdessen bietet sie ein deutlich vollständigeres und sorgfältig überprüftes Genom aus einer gut dokumentierten Kolonie, beschreibt die Übereinstimmungen und Unterschiede zu früheren Karten und hebt eine fokussierte Auswahl an Genen hervor, deren subtile Veränderungen die besondere Biologie des Tieres prägen könnten. Dieses reichere genetische Referenzwerk wird künftigen Studien ermöglichen, spezifische DNA-Veränderungen mit Verhalten, Krankheitsresistenz und Lebensdauer zu verknüpfen und uns näher daran bringen, die Geheimnisse gesunden Alterns zu verstehen — und vielleicht eines Tages zu nutzen —, die unter der Oberfläche dieser unterirdischen Nagetiere verborgen liegen.
Zitation: Toga, K., Oka, K., Tanaka, H. et al. Genome assembly and annotation of the naked mole rat Heterocephalus glaber reared in Japan. Sci Data 13, 705 (2026). https://doi.org/10.1038/s41597-026-06996-9
Schlüsselwörter: Nacktmull-Genom, gesundes Altern, Hypoxietoleranz, soziales Verhalten bei Tieren, genetische Variation