Clear Sky Science · de
Anwendung von Machine Learning und Deep Learning zur Vorhersage von Depressionen anhand von Hirn-MRT und zur Identifizierung depressionsbezogener Gehirnbiologie
Warum Gehirnscans und Algorithmen für die Stimmungslage wichtig sind
Depressionen betreffen Hunderte Millionen Menschen weltweit, dennoch fehlen Ärztinnen und Ärzten weiterhin objektive Tests, die zuverlässig anzeigen, wer gefährdet ist, oder die helfen, Therapien zu individualisieren. Diese Studie stellte eine einfache, aber dringliche Frage: Können detaillierte Gehirnscans, kombiniert mit modernen Rechnerverfahren, ein verlässliches Signal für Depressionen liefern? Durch die Analyse von Tausenden von Hirn‑MRT‑Bildern aus der UK Biobank und den Vergleich herkömmlicher Machine‑Learning‑Methoden mit Deep‑Learning‑Ansätzen untersuchten die Forschenden, wie viel Information über Depressionen tatsächlich in der Struktur der grauen Substanz steckt.
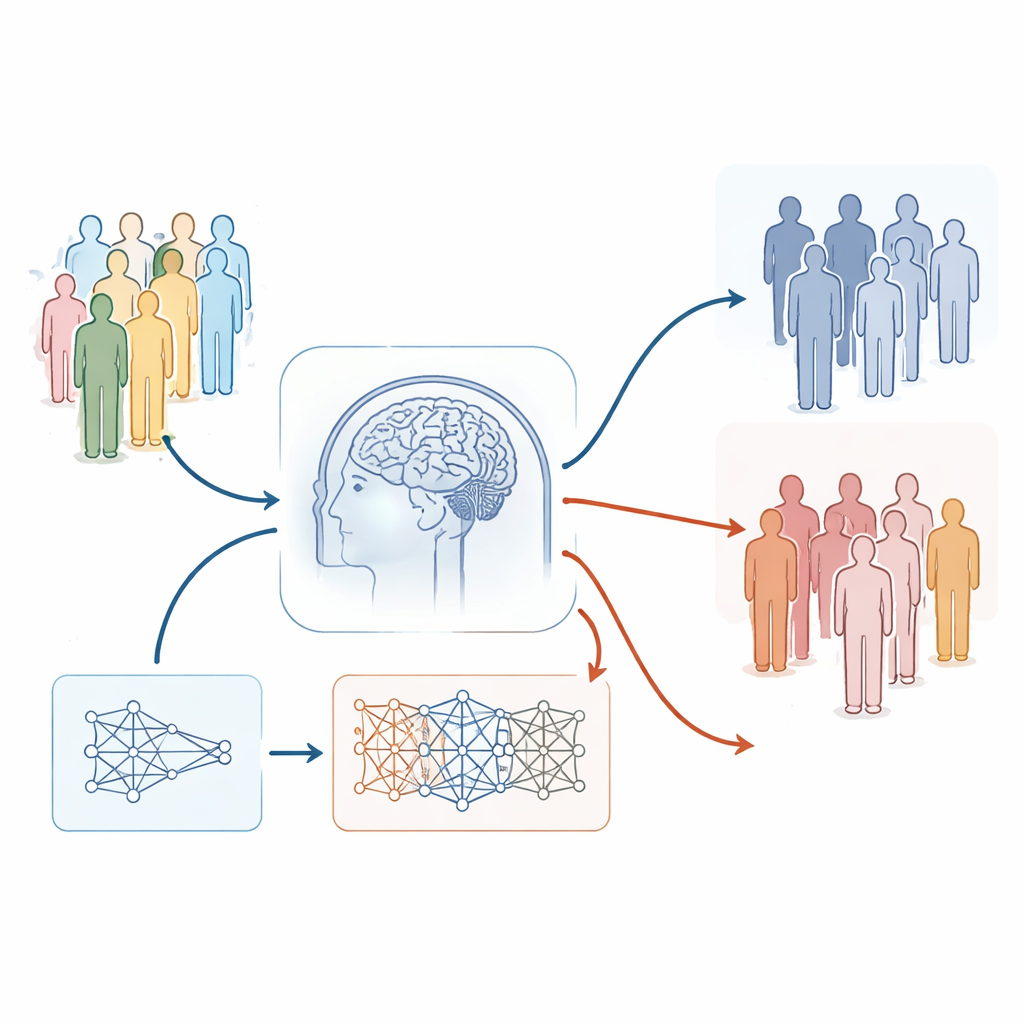
Auf der Suche nach Mustern in Tausenden von Hirnscans
Das Team nutzte strukturelle MRT‑Aufnahmen aus der UK Biobank und konzentrierte sich auf Personen mit und ohne Vorgeschichte einer Major Depression. Sie arbeiteten mit mehr als 1.400 Personen mit Depression und über 29.000 sorgfältig geprüften Kontrollen und wählten davon einen ausgeglichenen Teilbestand für Training und Testen ihrer Modelle aus. Anstatt das Gehirn in große Regionen zu mitteln, behielten sie ein fein aufgelöstes, dreidimensionales Gitter winziger Einheiten – Voxels – über die graue Substanz bei. Dieser Ansatz bewahrt subtile, lokale Unterschiede in der Hirnstruktur, die bei starker Vereinfachung verloren gehen könnten. Alle Bilder wurden verarbeitet und in eine gemeinsame Vorlage gebracht, sodass jedes Voxel sinnvoll über Individuen hinweg verglichen werden konnte.
Vergleich eines klassischen Modells mit Deep‑Learning
Die Forschenden trainierten zwei Arten von Prädiktoren. Das eine war ein statistischer Machine‑Learning‑Ansatz namens BLUP‑Modell, das linear Informationen aus Hunderttausenden von Voxels zu einem einzigen gehirnbasierten Risikoscore kombiniert. Das andere war ein modernes Deep‑Learning‑Modell (ein 3D‑ResNet), das versucht, komplexe Muster direkt aus den MRI‑Volumina zu lernen. In einer unabhängigen Gruppe von fast 2.500 Personen zeigte der BLUP‑Score eine moderate, aber verlässliche Fähigkeit, Betroffene von Kontrollen zu unterscheiden. Personen mit Depression hatten tendenziell leicht höhere Scores, und jeder Standard‑Schritt (Standardabweichung) im BLUP‑Score war mit etwa 28 % höheren Odds verbunden, an einer Major Depression zu leiden. Im Gegensatz dazu schnitt das Deep‑Learning‑Modell nur geringfügig besser als Zufall ab und hielt nach strengeren statistischen Prüfungen nicht stand.
Was der Gehirn‑Score über Schlüsselregionen verrät
Um den Gehirn‑Score besser interpretierbar zu machen, zerlegten die Autoren ihn nach anatomischen Regionen. Sie fragten, welche Bereiche, isoliert betrachtet, am stärksten zur Vorhersage beitrugen. Mehrere Regionen, denen zuvor eine Rolle bei Depressionen zugeschrieben wurde – wie Hippocampus und Amygdala – zeigten Signale in die erwartete Richtung, ebenso Teile des Thalamus, Kleinhirns sowie bestimmte frontale und temporale Areale. Keine dieser regionsspezifischen Effekte war jedoch stark genug, um nach Korrektur für die große Anzahl getesteter Bereiche statistisch signifikant zu bleiben. Eine kleine klinische Stichprobe, die mit anderer Ausrüstung gescannt wurde, zeigte überwiegend konsistente Effekt‑richtungen, hatte aber nicht die nötige Größe, um eine feste Bestätigung zu liefern.
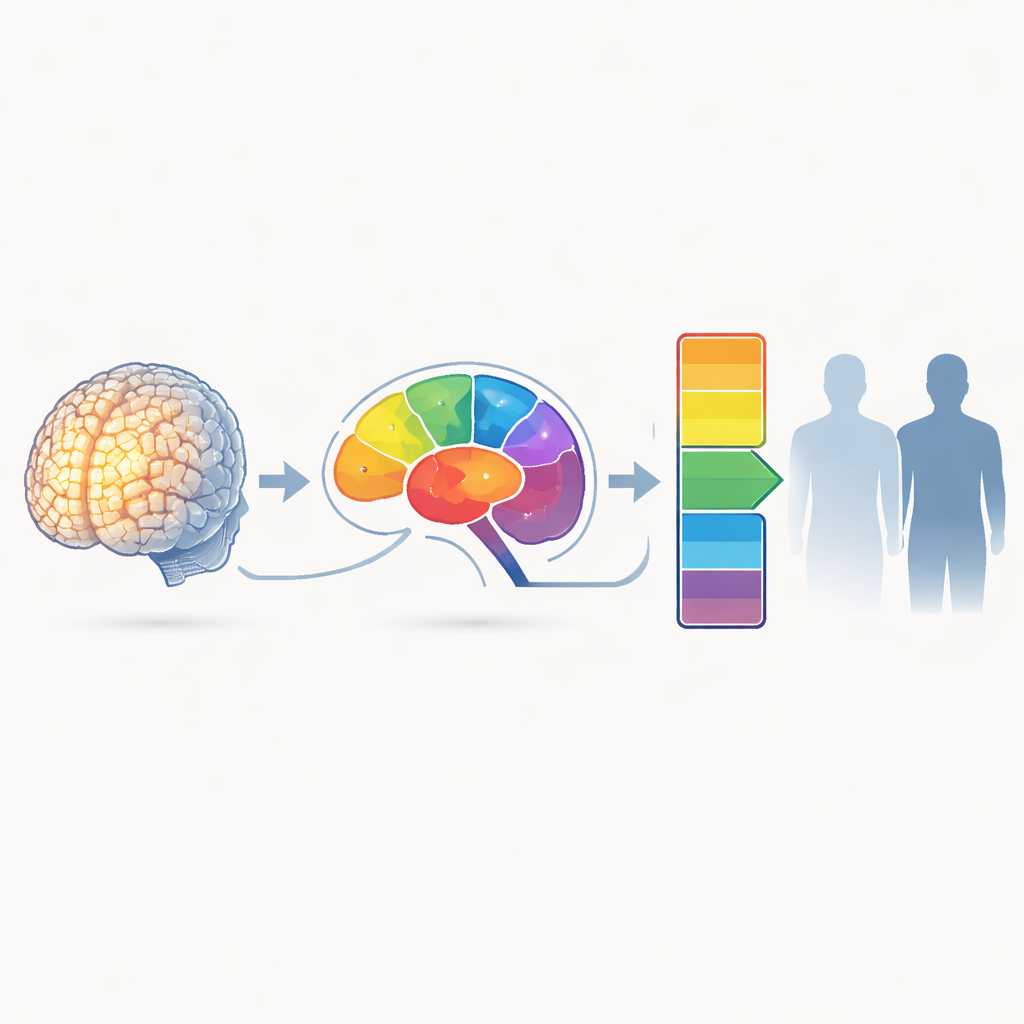
Abwägung von Gehirnstruktur gegenüber genetischem Risiko
Da Gene ebenfalls Depressionen beeinflussen, verglich das Team ihren gehirnbasierten Score mit einem polygenen Score, der das Risiko über viele genetische Varianten zusammenfasst. Gehirn‑ und genetischer Score waren mäßig korreliert, was darauf hindeutet, dass sie teilweise dieselbe biologische Verwundbarkeit erfassen. Wichtig ist, dass die Hinzunahme des Gehirn‑Scores zum genetischen Score nur eine sehr kleine Verbesserung der Vorhersagegenauigkeit brachte. Die Autoren schätzten außerdem, dass die graue Substanzstruktur in ihrer Stichprobe insgesamt nur etwa 6 % der Variation erklärt; selbst in einem idealen Szenario würde dies die Leistung eines rein struktur‑basierten Hirnprädiktors auf einem relativ bescheidenen Niveau begrenzen.
Was das für künftige Tests und Behandlungen bedeutet
Für die allgemeine Leserschaft lautet die Kernaussage: Aktuelle strukturelle Hirn‑MRT, selbst analysiert mit ausgefeilten Methoden, kann noch nicht als verlässlicher eigenständiger Test für Depressionen dienen. Die Leistung des BLUP‑Modells war statistisch eindeutig, aber weit entfernt von der Genauigkeit, die für klinische Entscheidungen erforderlich wäre; Deep‑Learning übertraf einfachere Methoden nicht. Dennoch liefert die Arbeit wertvolle Hinweise darauf, welche Hirnareale und Merkmale am informativsten sind und wie Hirnstruktur mit Genen und Lebenserfahrungen zusammenhängt, die die psychische Gesundheit formen. Die Autorinnen und Autoren argumentieren, dass künftige Fortschritte wahrscheinlich aus der Kombination mehrerer Gehirndatenarten, genetischer Informationen und Umweltfaktoren sowie aus der Fokussierung auf spezifische Mustersymptome statt auf Depression als eine einzige breite Kategorie kommen werden.
Zitation: Jiang, JC., Brianceau, C., Delzant, E. et al. Applying machine-learning and deep-learning to predict depression from brain MRI and identify depression-related brain biology. Transl Psychiatry 16, 171 (2026). https://doi.org/10.1038/s41398-026-03889-8
Schlüsselwörter: Depression, Hirn‑MRT, Machine Learning, Neuroimaging, genetisches Risiko