Clear Sky Science · zh
印度抗菌素抗性基因组图谱:来自多物种监测研究的发现
为什么印度的超级细菌与我们息息相关
耐抗生素的“超级细菌”正成为全球日益严重的担忧,但我们对这些病菌在世界许多地区如何演化和传播仍知之甚少。该研究对印度医院中的危险细菌进行了深入分析,读取其完整DNA以理解它们如何躲避我们最强的药物。研究结果不仅揭示了这些微生物难以被杀死的原因,也检验了快速的基于DNA的方法能否可靠地取代较慢的实验室检测——这一点可能影响全球感染的诊治方式。
更仔细地审视医院感染
研究人员在2022年至2024年间收集了来自印度北部和西部大型医院的266份细菌样本。大多数样本来自血液,也包括尿液和肺部感染样本,且多数来自重症监护病房,这里患者最为脆弱。团队重点关注了已知的主要问题菌株,例如Escherichia coli、Klebsiella pneumoniae、Acinetobacter baumannii、Pseudomonas aeruginosa、耐甲氧西林的Staphylococcus aureus(MRSA)和耐万古霉素的Enterococcus(VRE)。每份样本在此之前都已做过标准的抗生素敏感性测试——在实验室将细菌暴露于药物以观察哪些药物仍然有效。科学家随后对细菌基因组进行测序以绘制完整的耐药基因图谱,并将DNA“预测”的结果与试验管中的实际表现进行比较。
基因与试验结果不一致的情况
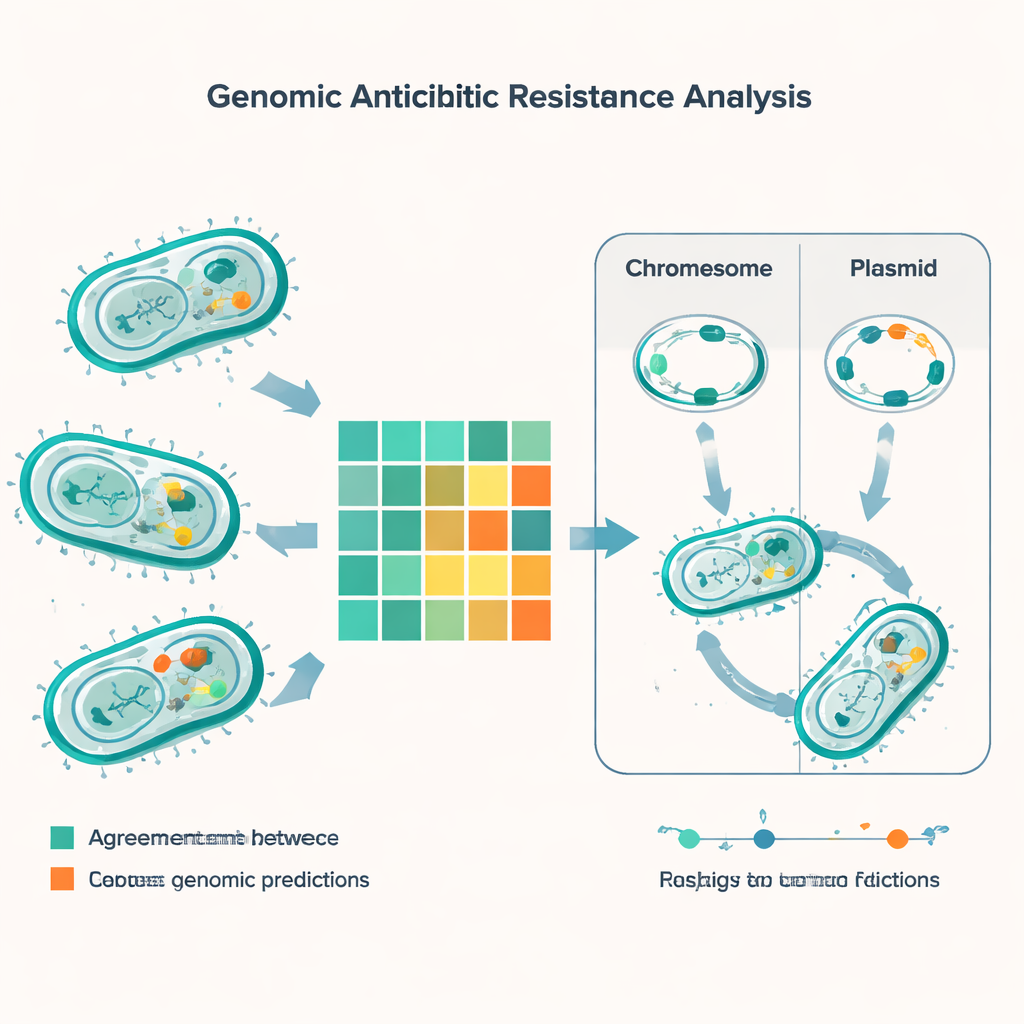
通过将基因预测与56种不同抗生素的实验室结果进行匹配,研究进行了超过5000次比较。大多数情况下,基于基因组的方法与传统检测一致,但约有600次不匹配值得注意。最常见的错误类型是基因组工具预测细菌将表现出耐药性,而实验室检测却显示仍可治疗。这类情况在米诺环素、粘菌素(colistin)和庆大霉素等药物中较为常见,尤以E. coli为甚。相反的错误——实验显示耐药但基因并不能清楚解释的情况——虽不如前者频繁,但更令人担忧,因为这可能导致漏检耐药。这类“非常重大”的差异在肠道相关细菌粪肠球菌(enterococci)中尤为突出,尤其涉及广泛使用的青霉素类药物和复方新诺明(甲氧苄啶‑磺胺甲噁唑)。
隐匿在细菌DNA中的武器库
基因组调查在主要物种中发现了密集的耐药基因库。所有常见的革兰氏阴性病原体至少携带一种β‑内酰胺酶基因,该基因可分解青霉素及相关药物,且许多菌株同时携带多种此类基因。臭名昭著的NDM型碳青霉烯酶——能够使最后一线抗生素失效——在E. coli、Klebsiella、Acinetobacter和Pseudomonas中广泛存在。研究还发现了帮助细菌抵抗强效“多肽”类抗生素(如粘菌素)的基因,以及使MRSA对甲氧西林耐药的经典mecA基因和肠球菌中的万古霉素耐药簇。通过比较被称为序列类型的DNA指纹,团队将部分耐药基因与已知的高风险细菌谱系联系起来,这些谱系已在印度和全球范围内传播。
通过可移动DNA进行基因共享
故事的关键不仅在于细菌携带哪些基因,还在于这些基因位于何处。许多耐药基因位于称为质粒的小型DNA环上,细菌可以像交换卡片一样互相转移这些质粒。使用专门软件,研究人员在样本中预测出约1400个质粒,且在E. coli和Klebsiella中多样性尤其高。在这些物种中,大量耐药基因——包括若干关键的β‑内酰胺酶——位于质粒上,使其更容易在菌株之间甚至物种之间传播。其他耐药特性则整合在细菌染色体中,这意味着即便丢失质粒也可持续存在。团队还登记了可移动遗传元件——能够跳动并携带耐药基因的短DNA片段,强调了另一条快速传播的途径。
对未来治疗的启示
对非专业读者来说,核心信息是:读取细菌DNA可以大大帮助对抗超级细菌,但该技术尚不完美。基因组工具倾向于“过度判定”耐药性,这样做比漏判危险菌更安全,但可能促使医生使用比实际需要更强的药物。与此同时,少量病例显示实验室检测发现了现有基因目录无法完全解释的耐药,突显了我们知识中的重要盲点。通过在印度医院构建耐药基因、质粒和可移动元件的详细地图,本研究为更好、更快的基于DNA的诊断和更合理的抗生素使用奠定了基础——这不仅对印度有意义,对任何面临超级细菌威胁的地区亦然。
引用: Gheewalla, N., Karthikeyan, V., Jadhav, Y. et al. Genomic landscape of antimicrobial resistance in India: findings from a multi-species surveillance study. npj Antimicrob Resist 4, 13 (2026). https://doi.org/10.1038/s44259-026-00185-9
关键词: 抗菌素耐药性, 基因组测序, 医院感染, 耐药细菌, 质粒介导的耐药