Clear Sky Science · zh
DANST 利用深度领域对抗神经网络实现空间转录组学的细胞类型解卷积
在细胞的邻里中看见细胞
人类组织就像拥挤的城市,由许多不同的细胞类型构成,各司其职。新的“空间转录组学”技术可以测量组织切片中哪些基因处于活跃状态,但每次测量通常会混合来自相邻多个细胞的信号。本文介绍了 DANST,一种能够拆分这些混合信号的智能计算方法。通过告诉我们器官和肿瘤中存在哪些细胞类型以及它们的位置,DANST 帮助科学家更好地理解组织如何构建、疾病如何扩散以及治疗应针对何处。 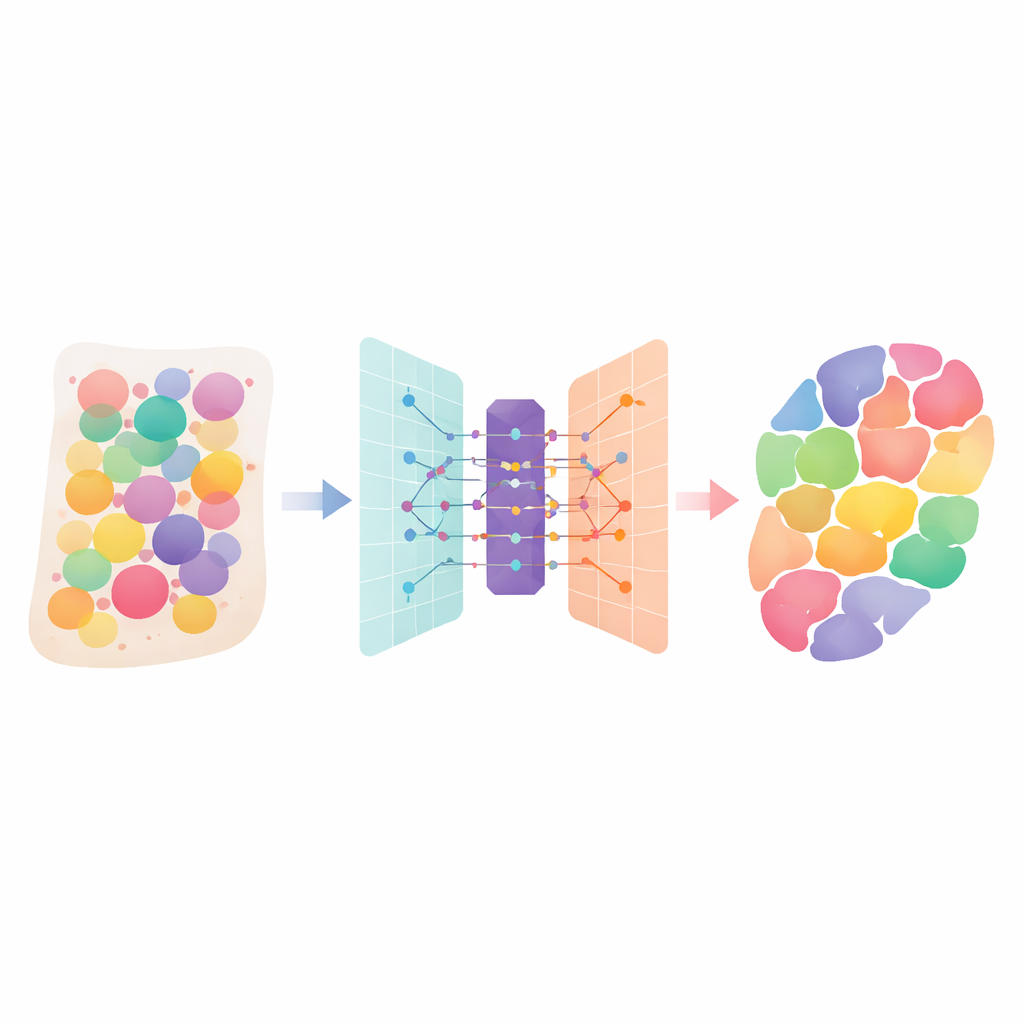
解开细胞人群的挑战
现代基因检测工具要么能非常精确地查看单个细胞,要么能捕捉组织的整体布局,但很少两者兼顾。常用的空间技术在相对较大的“点”上记录基因活性,一个点可以覆盖多个细胞。结果就像听到合唱,但无法分辨谁唱了哪些音符。为了解读这些数据,研究人员需要“解卷积”方法来估计每种细胞类型对每个点的贡献比例。许多现有方法使用单细胞数据作为参考,但它们面临困难,因为这两类数据来自不同实验,在质量、噪声或分辨率上不能完美匹配。
在数据世界之间架起桥梁
DANST 通过在单细胞数据和空间数据之间建立桥梁来解决这种不匹配。首先,它利用详细的单细胞谱系模拟出许多带有已知细胞类型比例的人工混合点。同时,它根据真实空间点在组织中的位置和基因模式对它们进行分组,并使用到这些分组的距离为每个模拟点分配一个“伪”位置。这一步创造了一个连接图谱,人工点和真实点共享一个共同的空间框架,使方法能够学习特定组织邻域中混合信号应有的表现。 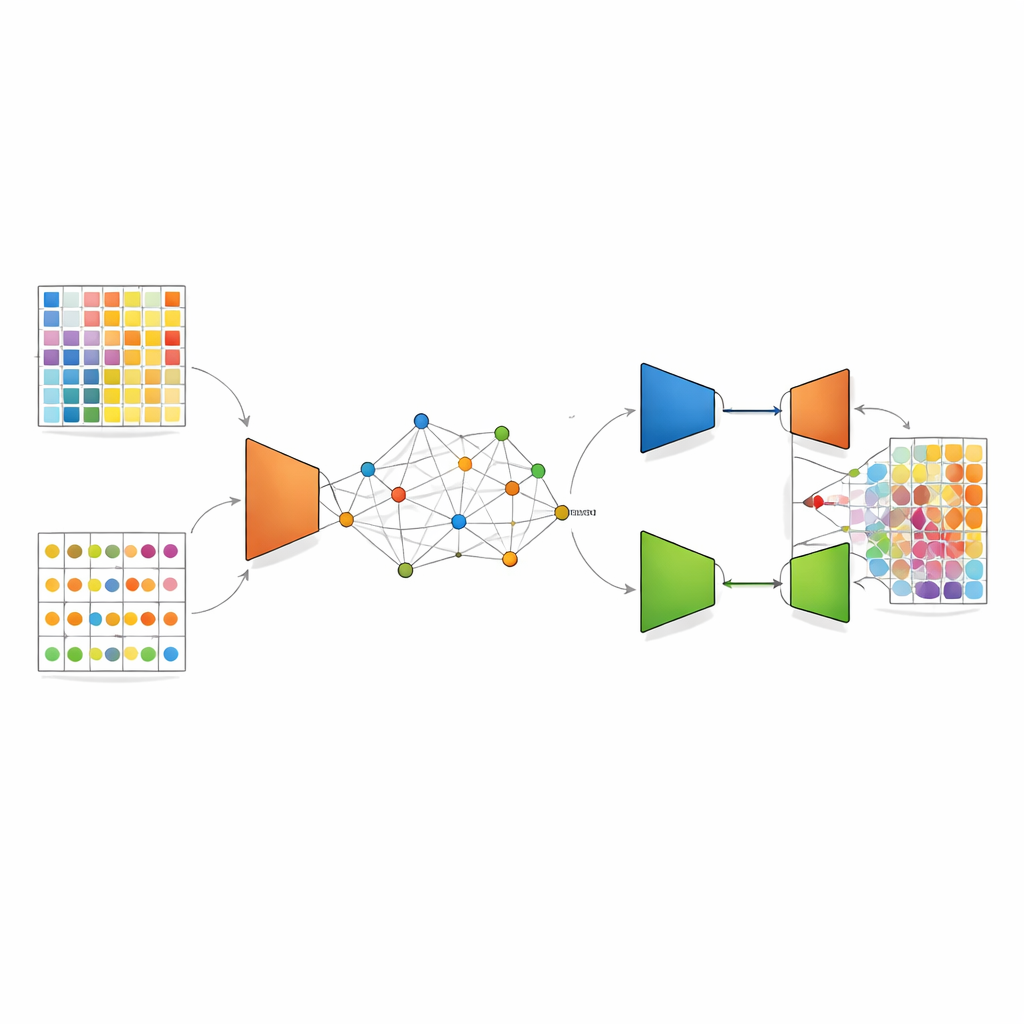
清理信号并对齐领域
一旦建立了这个联合图谱,DANST 就应用一种称为变分自编码器的深度学习方法。该网络将真实和模拟点的基因模式压缩为精炼的内部表示,然后尝试重建它们,从而实现去噪并强调重要特征。在此基础上,作者添加了一个对抗组件:第二个网络试图区分一个精炼后的模式是来自真实空间数据还是模拟数据,而特征提取器则学习去“欺骗”它。这种“拉锯战”促使模型朝向对两种数据源都有效的特征发展,使得从已知细胞类型比例的模拟点中获得的知识能够可靠地迁移到组成未知的真实组织点上。
在心脏、大脑和肿瘤上的测试
团队在人工基准和来自小鼠与人类的真实生物样本上测试了 DANST。与几种领先方法相比,DANST 在合成数据集中更准确地恢复了细胞类型比例,并且在不同组织与平台上保持了其优势。在一个小鼠大脑数据集中,它清晰地重建了皮层的分层结构并与专家定义的解剖区域一致。在另一块小鼠脑切片中,它捕捉到了如海马等区域的精细模式。尤其值得注意的是,在人类乳腺癌组织中,DANST 描绘了各种免疫细胞、支持细胞和对激素敏感的腔上皮细胞在肿瘤区域内外的排列。这些图谱与已知生物学相符,并提示了临床相关特征,例如激素依赖性,以及在某些免疫细胞稀少处可能较差的预后。
这对生物学和医学意味着什么
对非专业人士而言,DANST 可被视为一种强大的“翻译者”,它将模糊、重叠的信号转化为关于组织中细胞分布的清晰图像。通过在空间上可靠地分离细胞类型,它使研究人员更清晰地观察健康器官的组织方式以及疾病如何重塑这种组织。在癌症中,这可以揭示肿瘤细胞与免疫细胞在特定区域的相互作用,从而指导靶向疗法并帮助预测患者结局。随着更多空间和单细胞数据集的出现,像 DANST 这样的工具将成为解码支撑健康与疾病的细胞邻里结构的关键手段。
引用: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
关键词: 空间转录组学, 细胞类型解卷积, 深度学习, 肿瘤微环境, 单细胞 RNA 测序