Clear Sky Science · zh
整合多组学分析识别与DNA损伤相关的基因CLSPN作为胃癌生物标志物
这项研究为何重要
胃癌仍然是全球致死率很高的癌症之一,主要原因在于常常发现较晚且缺乏可靠的早期警示信号。本研究深入剖析DNA受损时留下的“划痕”——即相关基因的变化,识别出名为CLSPN的基因作为有前景的标志物,可能帮助临床更早检测胃癌、评估其侵袭性,并有望更精确地制定治疗方案。
在胃肿瘤中寻找危险信号
研究者从一个简单的假设出发:如果DNA损伤推动了胃癌发生,那么参与应对这些损伤的基因可能蕴含关于病人发病与疾病进展的重要线索。为验证这一点,他们整合了多组大型数据集,包括整体(bulk)RNA测序(测量肿瘤样本中基因的平均表达)、单细胞RNA测序(逐个细胞分析数千个细胞)以及空间转录组学(将基因表达映射回组织切片)。他们还汇总了一份已知与DNA损伤相关的基因名单。利用这些资源,研究团队筛选出与胃癌及患者生存显著相关的DNA损伤相关基因。
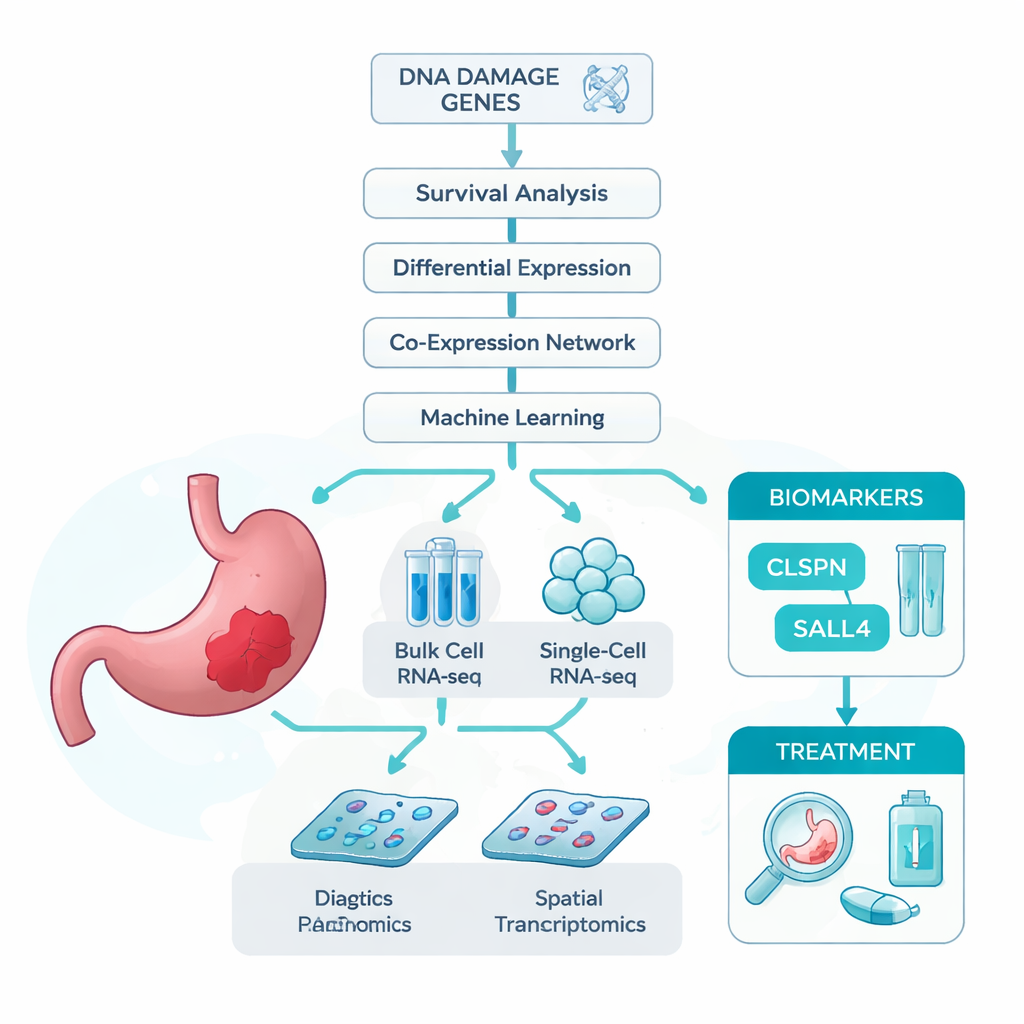
用智能算法筛选关键基因
由于癌症中有成千上万的基因发生变化,团队采用了一系列统计学和机器学习工具来缩小候选范围。他们首先筛除在肿瘤中异常表达且与患者生存明显相关的基因,然后将这些基因按共表达模式进行分组,并与DNA损伤基因名单交叉验证。多步筛选最终得到13个有力候选基因。为了判定哪些基因在区分肿瘤与正常组织上最具价值,研究者训练了七种不同的机器学习模型,每个模型按基因的分类效用进行排序。在所有模型中,有两个基因——CLSPN和SALL4——始终名列前茅,准确率接近或超过97%,ROC曲线下面积超过0.96,表明这些基因具有出色的诊断潜力。
在肿瘤内部聚焦CLSPN
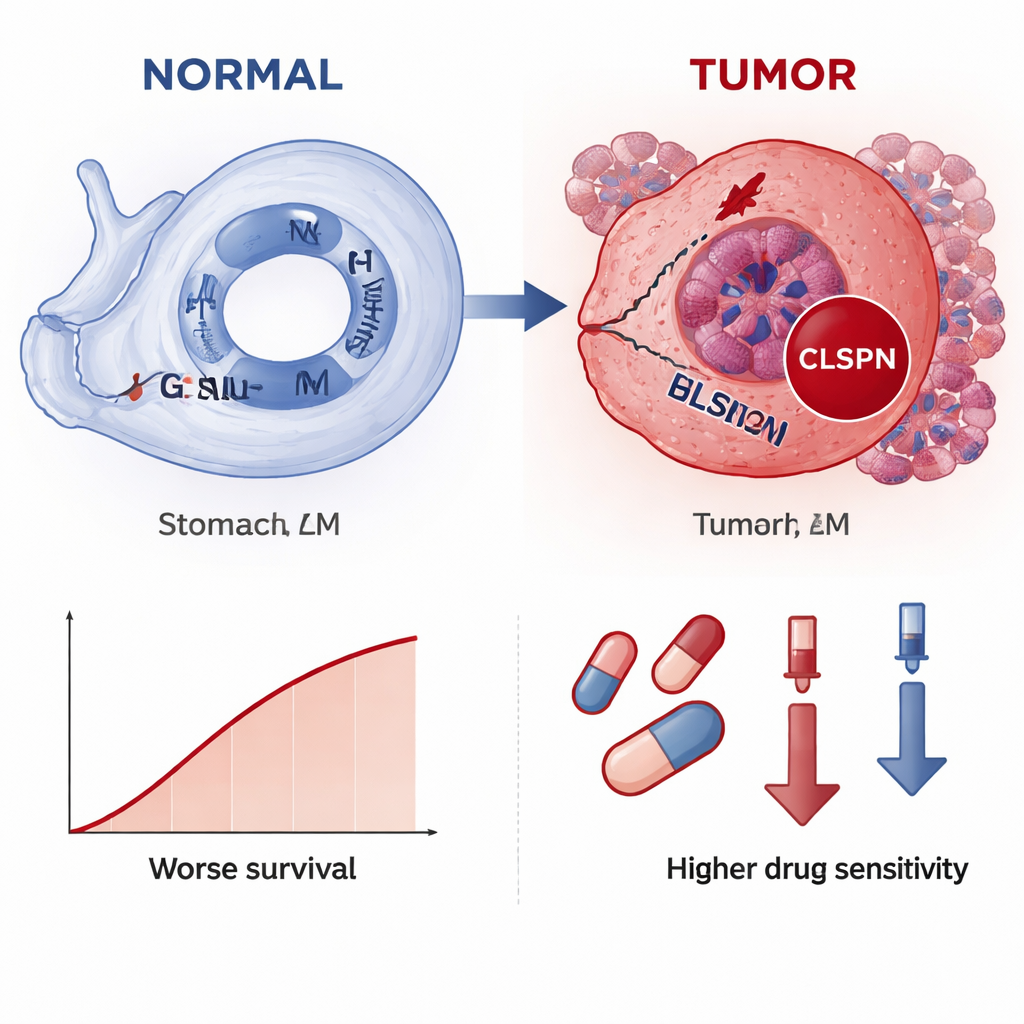
在这两种领先基因中,CLSPN在整体上最具信息量,因此作者对其进行了更深入的分析。在超过3万细胞的单细胞数据中,CLSPN在肿瘤细胞中的活跃度明显高于邻近的正常或间质细胞,指向其特异性的肿瘤角色。对患者组织切片的空间映射显示了类似模式:CLSPN表达在病理学上被识别为癌变的区域聚集。当团队将肿瘤细胞分为“高CLSPN”和“低CLSPN”两组时,高表达组在与DNA复制、细胞分裂和修复相关的通路上表现出更强的活性——这些过程在过度或错位激活时可助长失控增殖。伪时间分析(重建细胞在假想时间线上的变化)显示,随着肿瘤细胞进展,CLSPN水平往往上升,提示CLSPN上调可能是细胞向更恶性状态转变的一部分。
与免疫系统和治疗反应的关联
研究还探讨了CLSPN与肿瘤微环境及潜在疗法的关系。CLSPN高表达的肿瘤呈现出不同的免疫细胞组成,尤其是在巨噬细胞以及某些T细胞和NK细胞的分布上,暗示CLSPN可能有助于塑造免疫抑制性环境。药物敏感性建模显示,CLSPN表达更高的肿瘤对若干化疗药物和靶向药物可能更为敏感——CLSPN水平越高,预测抑制生长所需的剂量越低。更为重要的是,当作者对70例真实患者的组织样本进行免疫染色时,CLSPN蛋白在癌组织中的表达明显高于正常胃组织,并且与肿瘤体积更大、浸润更深、淋巴结转移以及较短的总体生存期相关联。
这对患者意味着什么
通俗地说,本研究表明CLSPN像胃癌的一个红色警示灯:它主要在肿瘤细胞中亮起,在病情更进展的情况下更为强烈,并预示着更差的预后。由于CLSPN既可在RNA水平检测,也可通过医院常规的免疫组织化学方法检测,因此它有潜力成为一个实用的生物标志物,帮助病理医生确认胃癌、按风险对患者分层并可能辅助用药选择。尽管在常规临床应用前仍需更多的临床验证,这项工作强调了通过多层数据解读DNA损伤足迹,能够为胃癌的早期诊断和更个性化治疗发掘新工具。
引用: Ma, Q., Yang, X., Sun, N. et al. Integrating multi-omics analysis identifies DNA damage-related gene CLSPN as a biomarker in gastric cancer. Sci Rep 16, 7789 (2026). https://doi.org/10.1038/s41598-026-39387-6
关键词: 胃癌, DNA损伤, CLSPN, 生物标志物, 单细胞分析