Clear Sky Science · zh
用于共聚焦显微数据集细菌识别的新型卷积神经网络
为什么更快发现病菌很重要
当医生试图确定引起感染的细菌时,时间至关重要。传统的实验室检测可能需要数小时甚至数天,并且依赖受过高度训练的专家通过肉眼检查显微镜图像。本研究提出了一种新的计算机视觉系统,称为 CM-Net,它可以自动读取专用显微镜图像,快速区分两种常见且具有医学重要性的细菌,同时识别细胞是存活还是死亡。该工作指明了通往更快速、更可靠诊断的方向,未来有望在医院和研究实验室广泛应用。
把发光的细菌变成有用的图像
研究人员起始于一种强大的成像工具——共聚焦激光扫描显微镜。简单来说,这种显微镜使用聚焦激光和荧光染料,使细菌根据存活状态呈现不同颜色。存活细胞呈绿色,而死亡细胞呈红色。通过以非常薄的层扫描样品,显微镜能够构建出清晰、细致的细菌图像。团队研究了两种常见引发院内感染的物种:杆状的大肠埃希菌(Escherichia coli)和球状的金黄色葡萄球菌(Staphylococcus aureus)。这些高质量图像构成了 CM-Net 需要学习理解的原始材料。
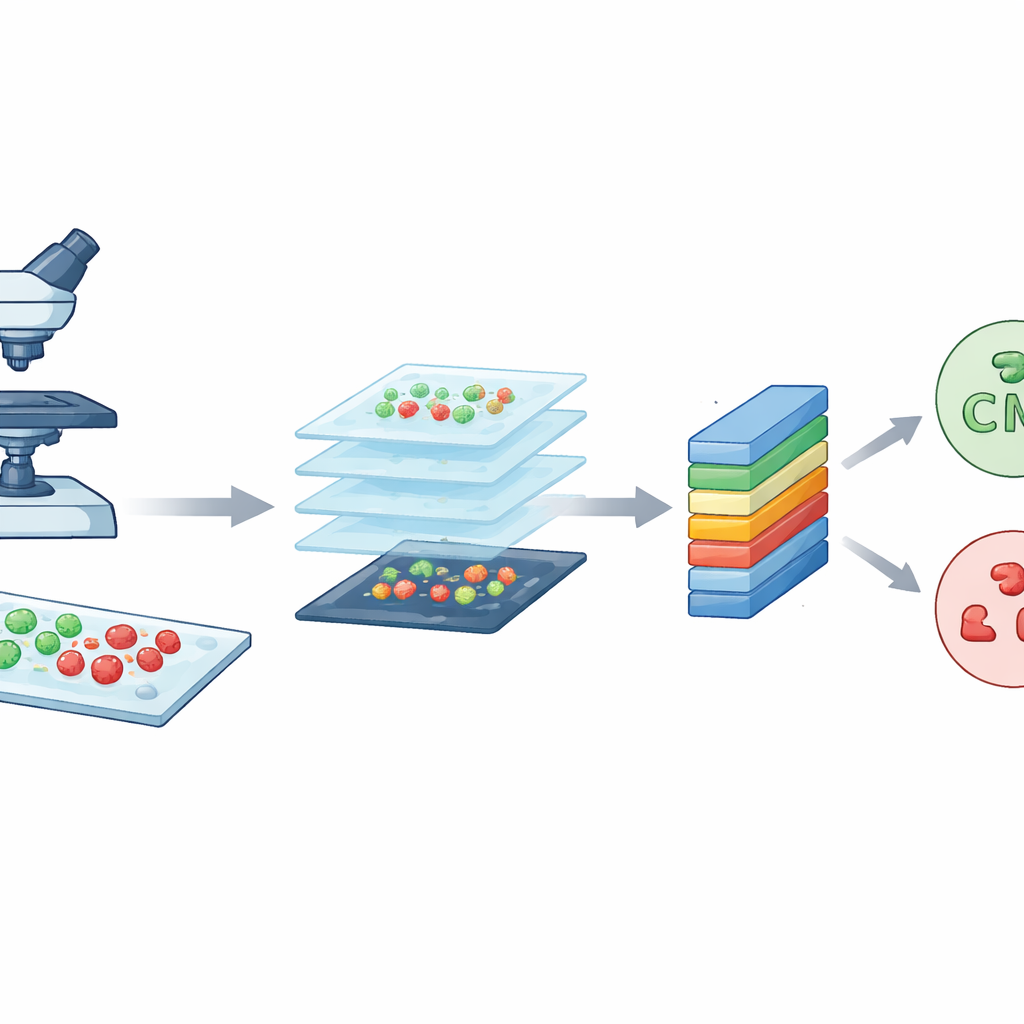
将大图切成许多小块
尽管每张共聚焦图像细节丰富,但尺寸也很大,约为 3000 x 3000 像素。直接在如此巨大的图像上训练模型会很慢且需要大量计算资源。为了解决这一问题,团队将每张大图切成许多较小的方形块,每块 224 x 224 像素,这是图像分析中的标准尺寸。这个过程称为数据增强,既减轻了计算负担,又成倍增加了训练样本数量。在每种细菌类型原始各 300 张图像的基础上,他们总共生成了 7,066 个小块。这些小块捕捉了载玻片不同区域的局部形状、颜色和纹理模式,为模型提供了多样且平衡的学习样本。
数字观察者如何学习“看见”
CM-Net 是为细菌显微图像专门设计的深度学习模型,而非从通用照片库改造而来。它属于卷积神经网络这一擅长从图像中发现模式的程序类别。CM-Net 将每个图像小块通过一系列处理阶段。早期阶段寻找边缘和斑点等简单视觉线索;更深的阶段将这些线索组合成更复杂的模式,用以区分杆状与球状以及存活与死亡细胞。网络采用诸如批量归一化等技术,以维持内部信号的稳定,以及一种裁剪形式的激活函数以防止极端响应导致学习不稳定。后期层将提取的信息压缩并做出最终的细菌类型与细胞状态判断。
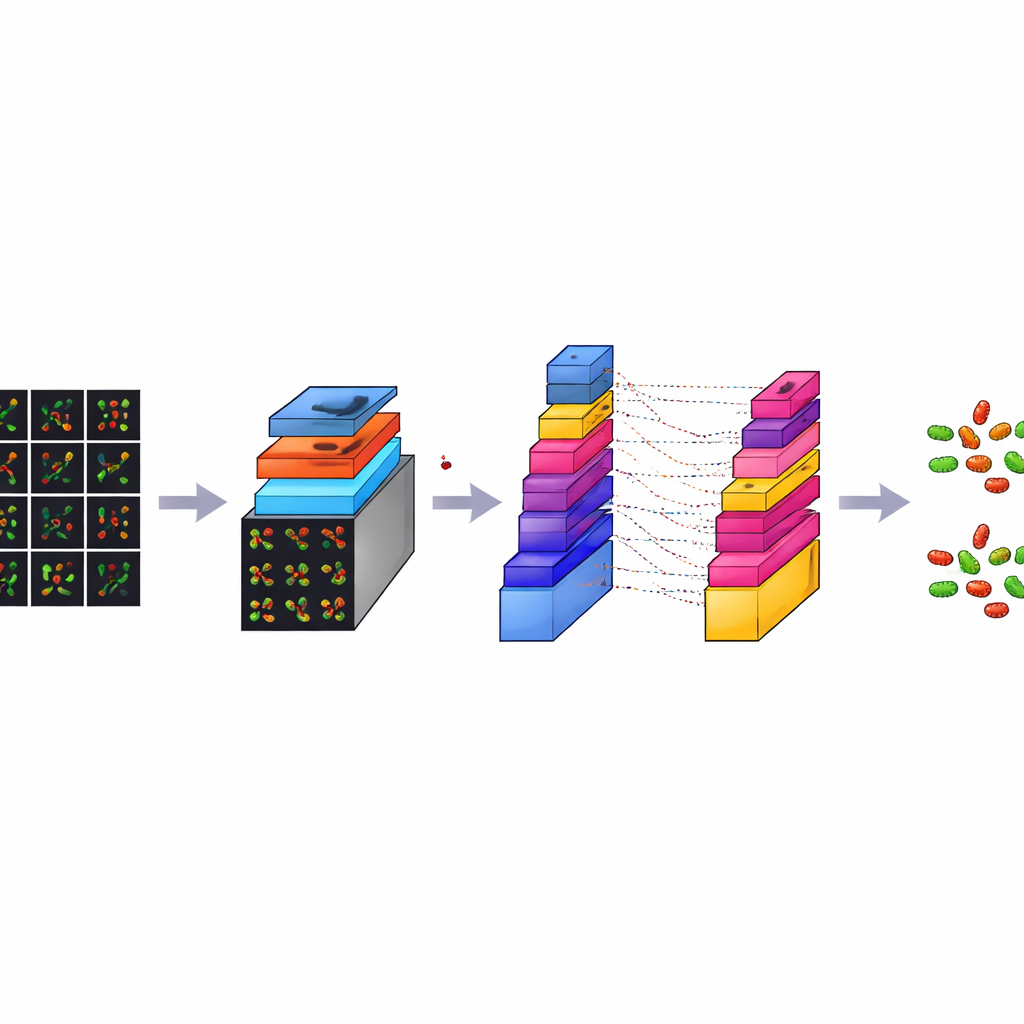
胜过多种现成的流行模型
为了评估 CM-Net 的表现,作者进行了 30 次训练和测试,每次都对数据进行新的训练/测试划分。他们测量了准确率(模型整体正确的频率)、灵敏度(对目标的检测能力)、特异性(避免误报的能力)以及若干其他标准指标。CM-Net 平均约达到 96% 的准确率,灵敏度和特异性也约为 96%,并在两类之间体现出良好平衡。与若干常用的预训练模型(包括 GoogLeNet、MobileNetV2、ResNet18 和 ShuffleNet)相比,CM-Net 所需的内部参数更少、内存占用更低,同时运行速度也更快。可视化工具显示 CM-Net 更关注图像中的细菌本体而非随机背景特征,支持其正在学习具有生物学意义的线索这一结论。
这对未来实验室工作意味着什么
通俗地说,该研究表明,专门构建的深度学习系统能够以准确、高效且与人类专家关注点一致的方式“读取”复杂的细菌显微图像。目前,CM-Net 仅在两种细菌和一种显微镜类型的数据上进行了训练,因此在将其作为通用诊断工具推广之前仍需更多工作。作者计划将其扩展到更多物种、不同的细胞状态以及更大、更具多样性的数据集。尽管如此,结果表明类似 CM-Net 的系统最终或可帮助实验室更快识别感染、指导治疗决策,并向缺乏专门成像经验的用户开放微生物学实验的自动化分析。
引用: Al-Jumaili, A., Al-Jumaili, S., Alyassri, S. et al. Novel convolutional neural network for bacterial identification of confocal microscopic datasets. Sci Rep 16, 8123 (2026). https://doi.org/10.1038/s41598-026-38861-5
关键词: 细菌图像分类, 共聚焦显微镜, 深度学习, 卷积神经网络, 医学诊断