Clear Sky Science · zh
使用 PiCNoR 的序列切片显微图像自动且稳健的非刚性配准
在不丢失细节的情况下以 3D 观察组织
现代生物学常常依赖将薄薄的组织切片重建为器官或大脑的完整三维视图。但当每一张显微切片被切割、染色和成像时,可能会发生拉伸、撕裂或位移。如果这些切片未能正确对齐,最终的三维图像可能会产生误导。本文介绍了一种称为 PiCNoR 的新计算方法,帮助科学家更准确、自动地对齐此类图像,从而在三维重建中保留胚胎和大脑中的细微结构。
为什么切片对齐如此困难
为了构建三维视图,研究人员对来自同一组织块的一系列超薄切片进行成像。理论上,每一片应当像整齐叠放的纸牌那样完美重合。但现实中,每片在切割和染色过程中都可能以不同方式发生形变。颜色可能变化、局部可能被拉伸、特征也会位移。传统的“刚性”对齐方法假定整张切片只发生平移或旋转,这通常不够用。更灵活的“弹性”方法也存在,但它们可能运行缓慢、需要专家仔细调整,或对图像亮度高度敏感,而亮度在切片间会变化。
一种新方法:协同工作的局部片段
PiCNoR 采用一种不同且更局部化的视角。它并不试图一次性弯曲整张图像,而是先根据图像中的特征模式将每张切片划分为许多区域。在每个区域内,方法使用稳健的特征检测器在相邻两片之间找到匹配点,并估计该区域需要如何旋转和平移以对齐。这些局部运动随后会经过合理性检查并被温和地合并,从而使切片中的每个像素获得一个平滑融合自周围区域的信息的位移。结果是一种既灵活又受控、符合现实的“非刚性”对齐。
让数据决定合适的复杂度
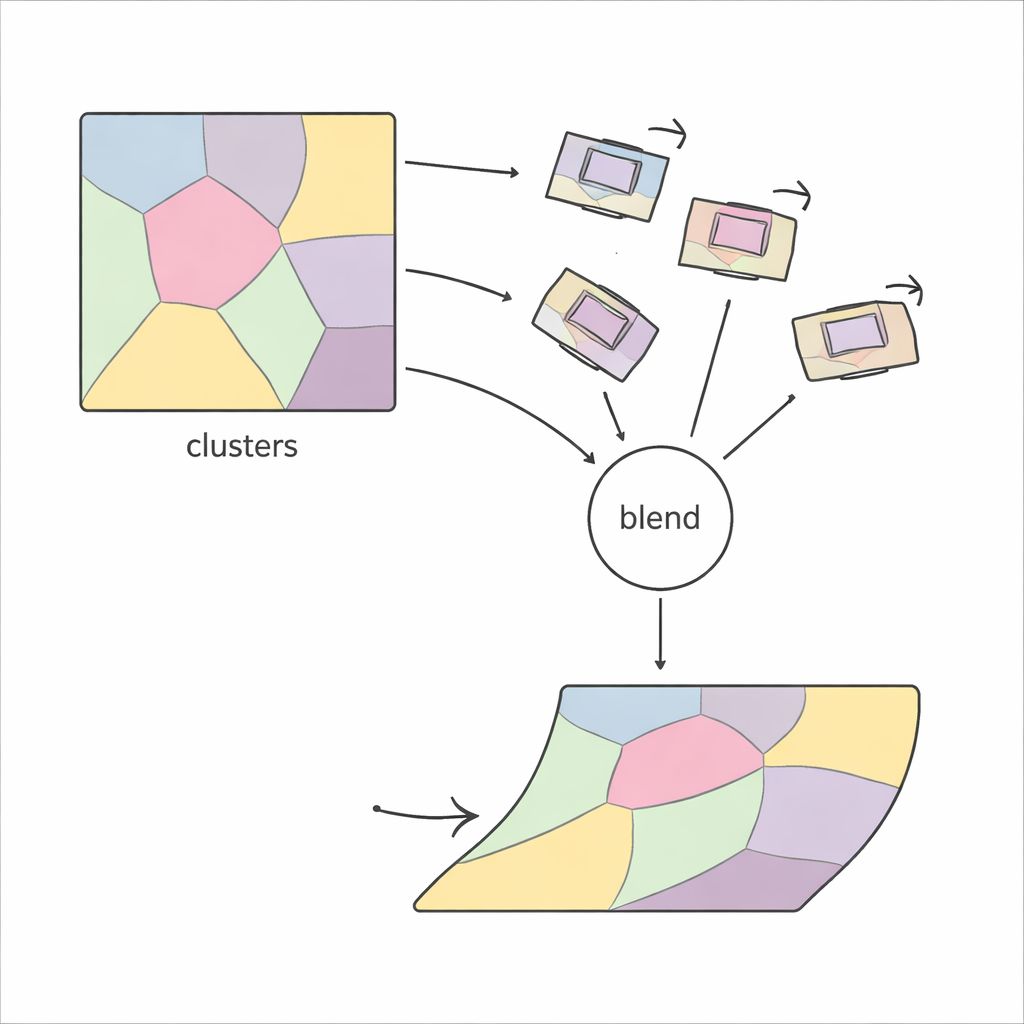
基于区域的方法面临的一个关键挑战是决定使用多少区域:区域太少,方法无法纠正细微形变;区域太多,则会变得不稳定且缓慢。以往的方法常依赖反复试验,通过反复检查视觉质量来调整。PiCNoR 避免了这种人工调参,采用了一种称为贝叶斯信息准则的统计工具,自动在细节量和过拟合风险之间进行权衡。实践中,这意味着算法可以自动决定给定数据集所需的区域数量,无需人工监督,从而节省时间并减少偏差。
保持结果可靠且高效
并非所有估计出的局部运动都是值得信赖的——有些可能被噪声或错误匹配扭曲。PiCNoR 通过将每个区域表示为图中的节点来处理这一问题,相邻区域相互影响。那些在旋转或平移上看起来不现实的运动将被相邻更可靠运动的加权平均所替代。一个紧凑的数学表示有助于高效地组合这些运动。最后,每个像素的移动被计算为区域运动的概率加权混合,确保区域之间的过渡保持平滑,不会在组织中产生突兀的折皱或折叠。
在真实生物数据上的验证
研究人员在三组迥然不同的数据集上测试了 PiCNoR:京都收藏的人类胚胎切片,一组果蝇神经索的电子显微镜堆栈,以及来自大鼠海马的新光学显微镜堆栈。在这些实例中,PiCNoR 一贯比标准刚性方法和常用的非刚性方法产生更好的切片重叠。它在三维视图中保持了细小结构的连续性,避免了其他工具有时会出现的夸张畸变。重要的是,它在使用的局部区域比某些竞品更少的同时,计算成本仍然对大规模堆栈保持可行。
这对未来 3D 显微镜意味着什么
对非专业读者来说,结论是 PiCNoR 提供了一种更可靠的方式,将二维显微镜图像堆栈转化为忠实的三维重建。通过自动选择对齐应达到的细节程度并防止糟糕的局部校正,它在保持组织真实形状的同时使处理时间可控。这让生物学家和病理学家更容易信任他们在三维中看到的内容,无论是在研究胚胎发育还是大脑细胞排列方面,并为更准确、自动化地分析复杂显微数据集奠定了基础。
引用: Adi, P.M., Shabani, H. & Mansouri, M. Automated and robust nonrigid registration of serial section microscopic images using PiCNoR. Sci Rep 16, 7559 (2026). https://doi.org/10.1038/s41598-026-38548-x
关键词: 3D 显微镜, 图像配准, 脑成像, 组织学, 非刚性对齐