Clear Sky Science · zh
使用近似 k-mer 匹配的集成 BSI 细菌识别芯片
为何更快的病原体检测至关重要
对于接受救命干细胞移植的患者来说,血流中的感染可能在数小时内将康复变为医疗急症。医生清楚每一分钟都很重要,但现有用于查找致病细菌的实验室工具往往缓慢或需要强大的计算资源。本研究提出了一种微小、能效高的计算芯片——称为 PC-CAM——能够实时快速扫描患者样本中的 DNA,并在病床旁即刻标出危险细菌。
拯救肠道治疗后的感染风险
一些移植患者会出现一种严重并发症,移植的免疫细胞攻击患者的肠道。一种有前景的治疗是粪菌移植,即将供体的健康肠道微生物引入患者体内。虽然这能挽救肠道功能,但有时会带来额外危险:肠道中的有害细菌可能溢出进入血流,引发危及生命的感染。要有效治疗这些感染,医生必须迅速识别存在哪些细菌种类,但传统检测可能需要数小时到数天,且可能漏检不熟悉的菌株。
从慢速基因组拼接到快速 DNA 片段匹配
现代 DNA 测序仪能近乎实时地读取血液或粪便样本中的遗传物质。瓶颈不再是读取 DNA,而是如何解释这些数据。传统方法先尝试从数百万短片段重建完整基因组,然后再将这些组装后的基因组与参考库比对——这是计算量极大的过程。作者用更简单的策略取代了这一流程:他们把 DNA 切成固定长度的短片段,称为 k-mer,并直接在已知细菌序列的数据库中查找这些片段。系统并不要求逐字逐句的完全匹配,而是容许一定数量的差异,这使其能应对测序误差和自然突变带来的变异。 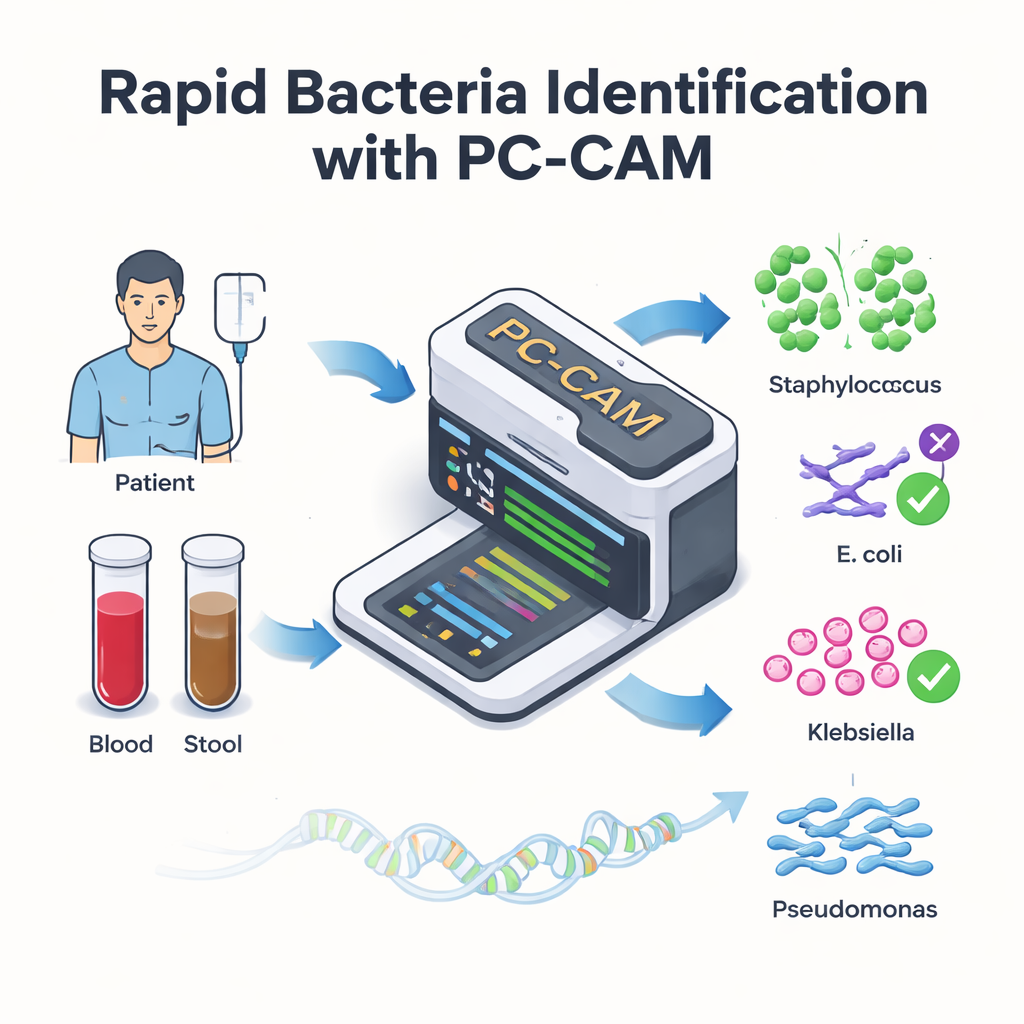
为 DNA 搜索而设计的智能存储芯片
PC-CAM 的核心是一种特殊类型的存储器,称为内容可寻址存储(content-addressable memory),它可以将输入数据与其存储的所有内容同时比较。研究人员设计了一个可调节的“近似搜索”版本(ACAM),它可以接受近似匹配而非精确匹配。每个短 DNA 片段被编码并以行为单位存入该存储器。当来自患者样本的新片段到达时,芯片通过所有行同时发起一条搜索线并测量微小电信号的放电速度。通过调节两个控制电压,系统设定可容许的不匹配阈值,从而调节匹配的宽容程度。该硬件级比较使芯片能够比通用计算机更快、更省能地筛选模式。
芯片识别真实细菌的表现如何
团队在接受过粪菌移植的患者的真实数据集上测试了 PC-CAM,将血液和粪便中检测到的细菌与完整的软件基因组分析结果进行了比较。即便芯片仅存储了每个细菌基因组中一小部分经过精心挑选的片段,其结果在很大程度上与计算成本更高的方法一致,能在多个患者中正确识别关键病原体。在使用来自不同细菌和不同比错率的模拟 DNA 读序的扩展实验中,随着容忍差异程度的提高,芯片的灵敏度(捕获真实匹配的能力)上升,而在非常高的容忍度下其特异性(避免误报的能力)下降。作者展示了简单的后处理步骤——例如要求多个片段一致或丢弃弱匹配——可以降低这些假阳性率。 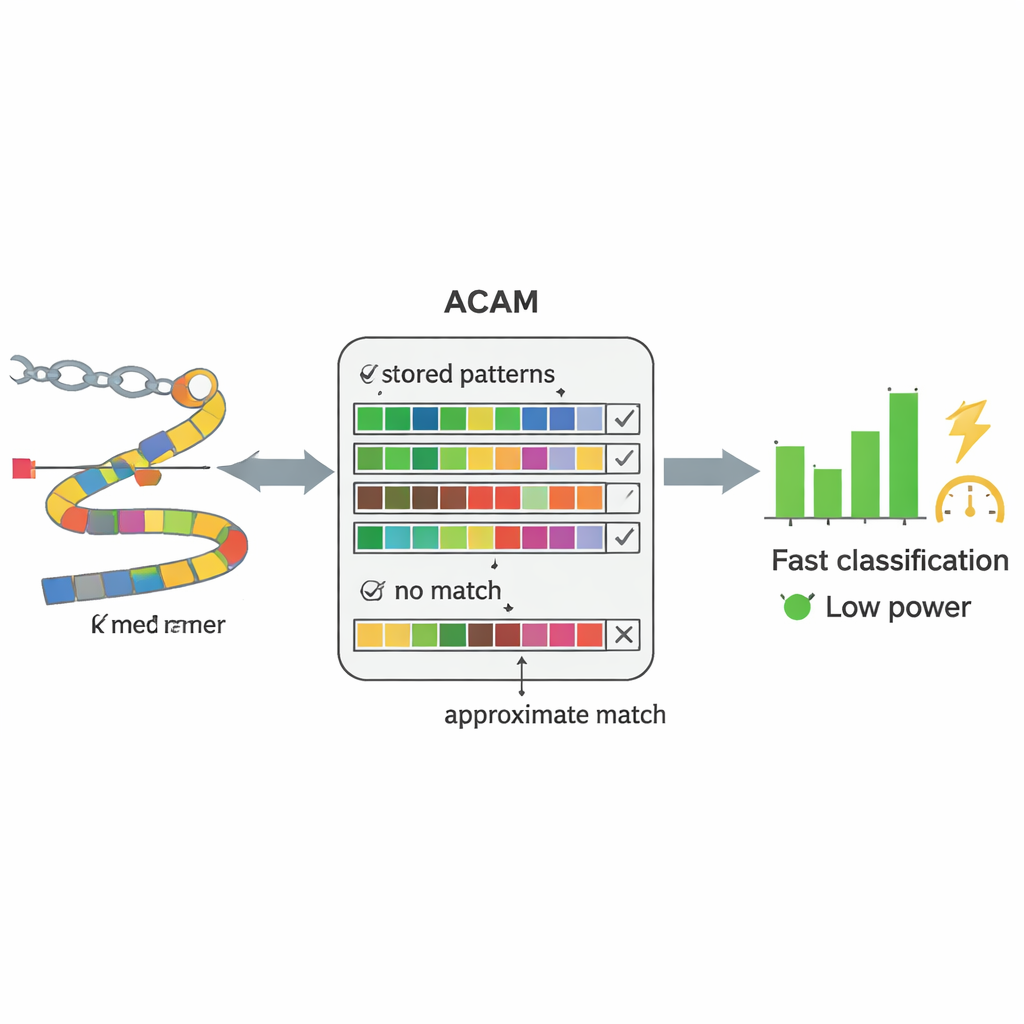
体积微小、速度快且功耗低的硬件
PC-CAM 将 ACAM 存储与一颗小型 RISC-V 处理器集成在仅几平方毫米、采用标准 65 纳米工艺制造的芯片上。实测硬件表明,它每秒可分类约 960,000 条短 DNA 读序,功耗约为 1.27 毫瓦——低于许多数字手表。当与在高端桌面处理器上运行的领先软件工具比较时,对于此类分类任务,芯片大约快 1,900 倍。尽管由于存储了每个基因组的稀释版本其准确度略有下降,作者认为在速度和功耗是首要约束(如急救护理或便携设备)时,这种权衡是可以接受的。
这对患者及更广泛应用的意义
简单来说,该研究表明,一块微小的低功耗芯片可以作为细菌 DNA 的专用搜索引擎,几乎瞬间识别血液或粪便样本中的危险病原。尽管它不能取代大型实验室中的全面基因分析,但可以就现场哪种细菌存在提供快速指导,帮助医生更早、更准确地选择抗生素。相同的方法还可扩展用于监测抗生素耐药性、检查食品与水源污染或监测农作物病害——所有这些都能借助紧凑的硬件将复杂的 DNA 分析从数据中心带到决策发生的现场。
引用: Garzón, E., Galindo, V., Harary, Y. et al. Integrated BSI bacteria identifier-on-chip using approximate k-mer matching. Sci Rep 16, 5722 (2026). https://doi.org/10.1038/s41598-026-36497-z
关键词: 血流感染, 快速病原体检测, DNA 测序, 芯片实验室, 微生物组