Clear Sky Science · zh
ONCOPLEX:一种受肿瘤学启发的超图模型,整合多种生物学知识以预测癌症驱动基因
这项研究为何重要
癌症由少数几处强有力的基因改变驱动,这些改变隐藏在成千上万无害变异之中。识别那些真正危险的“驱动”基因对于更好的诊断和靶向治疗至关重要,但这类似于在人群嘈杂的环境中找出为首的几个人。本文提出了 ONCOPLEX —— 一个新的人工智能框架,它不再逐个基因地考察,而是在基因所共同参与的生物通路背景中进行分析,从而更准确地定位真正推动肿瘤生长的基因。
在基因的生物邻域中观察癌症基因
当前大多数方法在癌症基因组中扫描那些出现频率异常或在简单基因网络中显得突出的突变。这些方法有帮助,但生物学很少如此单一。基因通常在通路中成组发挥作用,控制细胞生长、DNA 修复及其他诸多过程。ONCOPLEX 接受这种复杂性,将基因表示为节点,将通路表示为可以包含多个基因的重叠群组。这种称为超图的结构使模型能够直接考虑多基因关系,而不是将它们拆成许多独立的成对关系。
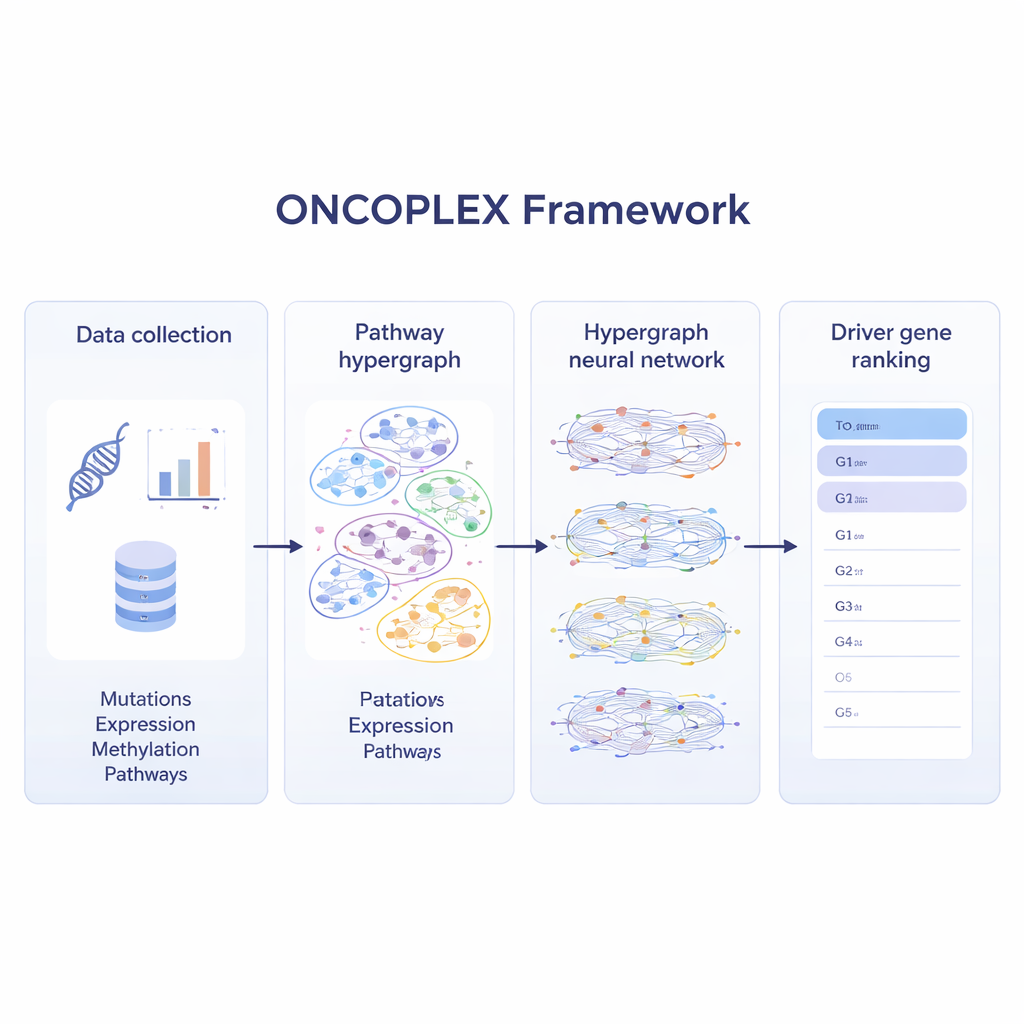
融合多层次的癌症数据
为了充分利用现代癌症数据集,ONCOPLEX 结合了关于每个基因的多类信息。它使用突变频率、基因表达变化、DNA 的化学标记(甲基化)以及一套丰富的生物学特征,如进化保守性和功能注释。这些特征附加在超图中的每个基因上。一个专门的神经网络随后沿着通路传递信息,使每个基因的表示既受自身数据影响,也受其共事基因行为的塑造。模型在训练时利用已知的癌症驱动基因,同时也从大量未标注但可能重要的基因中学习。
在多种癌症中优于现有工具
研究人员在癌症基因组图谱(The Cancer Genome Atlas)数据上测试了 ONCOPLEX,既在将多种肿瘤类型合并分析的总体任务中评估,也在包括乳腺、肺、肝、膀胱和头颈等 11 种单独癌症类型上逐一检验。他们将其与多种领先的基于图和基于超图的方法进行了比较。总体来看,ONCOPLEX 在将已知驱动基因与更常见的非驱动基因区分开以及将可能的驱动基因排在列表前列方面表现更佳。在最高排名的基因上其优势尤为明显——这些基因的准确识别对于后续实验和临床转化最有价值。
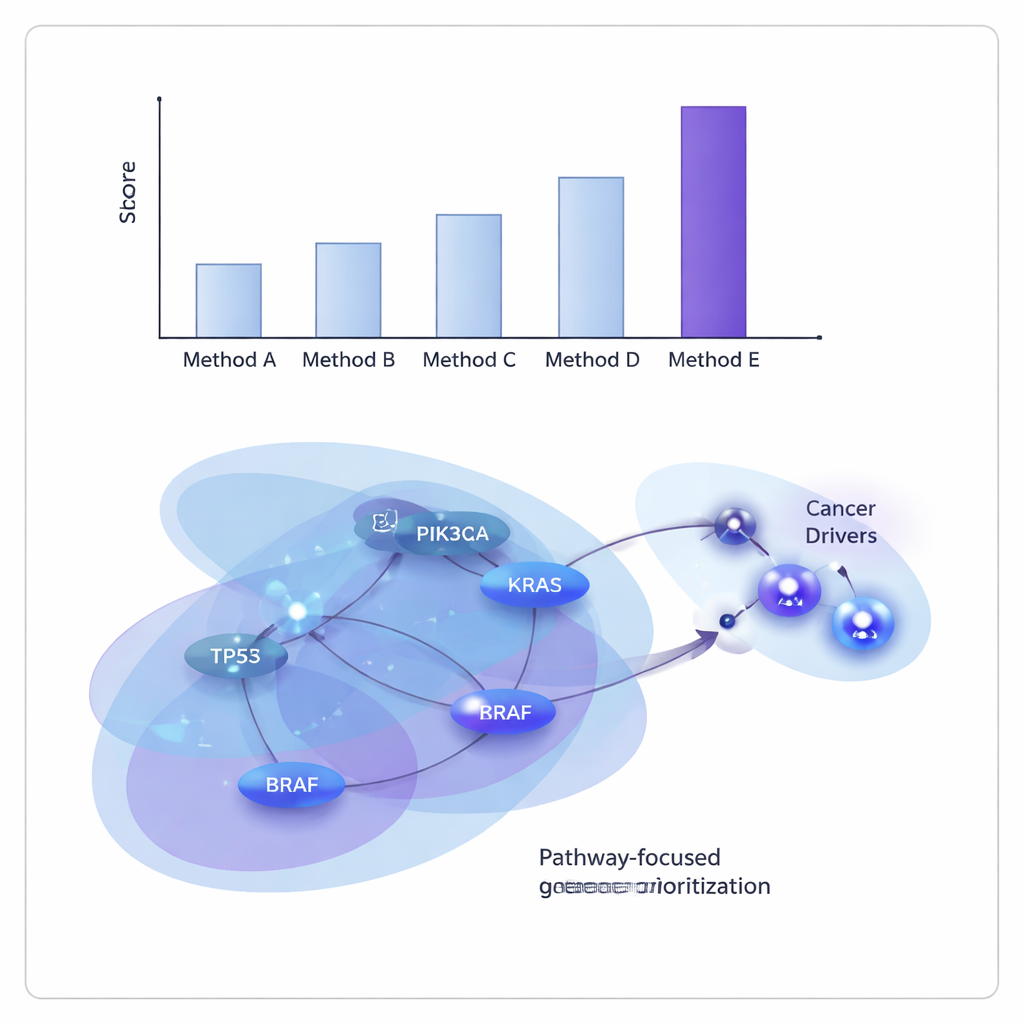
揭示共享与癌种特异性的罪魁祸首
超越原始性能指标,ONCOPLEX 的排序基因列表恢复了许多熟悉的癌症基因,如 KRAS、BRAF 以及 PI3K–AKT 信号通路的成员,证实模型捕捉到了已确立的生物学事实。它还突出了一些在特定癌种中尚未被牢固认定为驱动基因的有前景候选者,例如乳腺癌中的 GRB2 与 MAPK3,以及胃癌中的 SHC1。团队对最高排名基因进行通路富集分析时,发现了强烈的已知癌症通路信号,包括 ErbB 信号通路和 PI3K–AKT–mTOR,以及免疫相关通路,表明 ONCOPLEX 正在定位与临床相关的网络。
优势、局限与未来方向
研究表明,随着更丰富的生物学特征被持续引入,ONCOPLEX 的预测稳定改进,展示了在以通路为中心的框架中融合多数据源的价值。与此同时,研究也揭示了一项局限:由于许多癌症共享大量通路,模型有时更偏向那些广泛作用的“泛癌”基因,而非真正特异于某一肿瘤类型的基因。作者建议未来工作应改进通路信息的使用方式,以便更清晰地区分共有信号与癌种特异信号。
这对患者与临床医生意味着什么
对非专业读者而言,关键点是 ONCOPLEX 提供了一种更符合生物学真实情况的方式来寻找驱动癌症的基因。通过在基因所处的“朋友圈”——即通路内而非孤立地——进行观察,它提高了识别既有知名又被忽视的驱动基因的能力,即便是在目前了解甚少的癌种中亦然。此类工具可帮助研究人员优先确定实验室研究对象,引导新药靶点的寻找,并最终支持更精确、考虑通路信息的肿瘤治疗策略。
引用: Alotaibi, E.M., Alkhnbashi, O.S. & Tran, V.D. ONCOPLEX: an oncology-inspired hypergraph model integrating diverse biological knowledge for cancer driver gene prediction. Sci Rep 16, 5164 (2026). https://doi.org/10.1038/s41598-026-36127-8
关键词: 癌症驱动基因, 超图神经网络, 多组学整合, 通路分析, 精准肿瘤学