Clear Sky Science · zh
使用因果图学习在苜蓿(Medicago sativa L.)中拆分直接与多效性SNP效应
这对农场与食物意味着什么
苜蓿是现代农业的主力作物,为奶牛提供饲料并有助于改善土壤健康。然而,要育成更优良的苜蓿——在冬季依然健壮、抗损伤并提供高质量饲料——往往受制于其基因复杂性。本研究提出了一种新方法,能够把冗长且令人困惑的DNA标记列表转化为清晰的因果图谱,显示哪些基因组片段真正驱动重要的茎部性状,哪些只是随行标记。
从松散关联到因果关系
传统的全基因组关联研究(GWAS)扫描基因组以寻找与性状(如茎色或越冬存活)同时出现的DNA变异,称为SNP。然而在苜蓿中,这种情况尤为复杂:它具有四套染色体长臂,大片段DNA通常整块联动,且种群高度混合。这产生了一种“相关性的迷雾”,使得许多标记看似重要,但只有少数真正影响性状。作者认为育种者需要的不仅是简单的统计关联;他们需要知道哪些标记位于从基因型到可观测性状的实际因果路径上。
新框架如何工作
研究者构建了一个两阶段框架,将现代机器学习与因果图理论相结合。首先,他们使用称为双重机器学习(Double Machine Learning)的技术,在500个苜蓿基因型中筛选约2400个SNP。该步骤利用基因组的主成分作为代理变量,去除了家系背景与地理等隐藏因素的影响。结果是更清晰地看到在考虑这些混杂影响后,哪些标记仍然对茎部性状如茎色具有直接效应。在这一筛选结果中,强而稳定的信号主要出现在第2和第4号染色体上,且关键标记的效应量置信区间明确不包含零,表明可能具有真实的因果影响。
把标记变成遗传路线图
在第二阶段,团队使用一种称为PC算法的因果图学习算法,将最有前景的标记连接成有向网络。在这些图中,节点代表SNP和性状,箭头表示最可能的影响方向。通过删除与基本生物学相冲突的边(例如,性状不能改变基础DNA)并仅保留那些直接指向性状的SNP,作者得到紧凑且生物学上合理的图谱。这些“向日葵”网络呈分层结构:内环是直接父本(Direct Parent)SNP,直接连接到性状;外环是上游枢纽(Upstream Hub)SNP,影响多个父本但不直接接触性状。
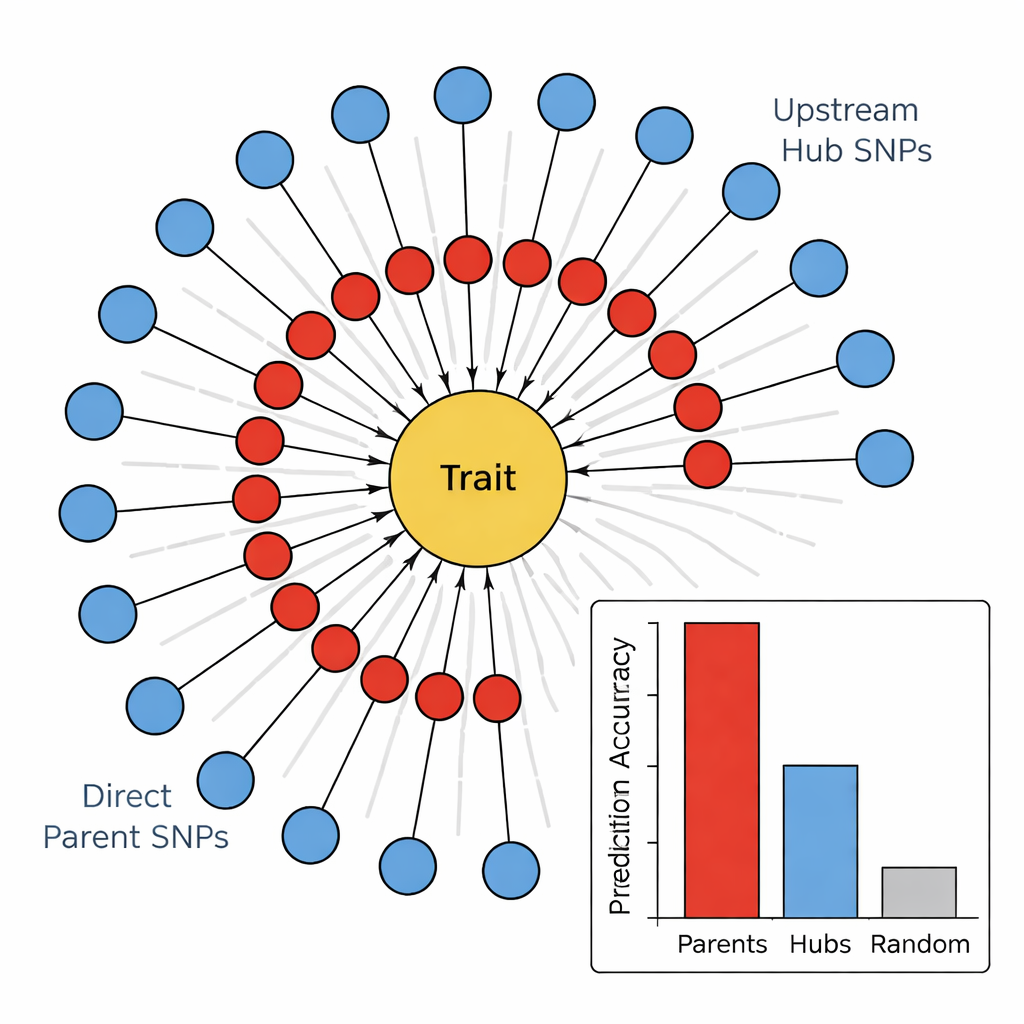
基因组中的执行者与指挥者
为检验这种层级是否有意义,作者比较了不同标记组预测四项茎相关性状(茎色、茎胀、茎强度和越冬损伤)的能力。在所有性状上,直接父本SNP始终是最好的预测因子,通常解释的变异量比随机标记或上游枢纽多好几倍。相反,枢纽虽然在网络中高度连接,但表现出较弱甚至负向的预测能力。当研究者将这些SNP与已知基因关联时,出现了一种模式:直接父本往往对应直接作用于细胞壁、色素或损伤响应的酶或结构蛋白;而枢纽更常对应转录因子和调控蛋白,广泛调节多条通路。
这对未来苜蓿育种的意义
对育种者和遗传学家而言,该研究提供了一种方法,能穿透嘈杂的关联结果,聚焦于真正能改变特定性状的DNA变异。作者展示了将去混杂的筛选与因果图相结合,可作为防止过拟合的内置保护,把冗长的候选列表转化为与已知生物学一致的小型、可解释网络。在实践中,直接父本SNP可作为高精度标记,用于选择具有更好茎部性状或越冬存活能力的植株;而上游枢纽指示可能重塑更广泛抗逆反应的主开关,但也可能伴随权衡。这样的基因组结构视角为复杂作物中更可靠的基因组选择奠定了基础,并便于将未来的数据层次(如基因表达和代谢组学)整合进连贯的因果模型,以解释植物表现。
引用: Lee, Y., Medina, C.A. & Xu, Z. Disentangling direct and pleiotropic SNP effects in alfalfa (Medicago sativa L.) using causal graph learning. Sci Rep 16, 5216 (2026). https://doi.org/10.1038/s41598-026-35876-w
关键词: 苜蓿遗传学, 因果图学习, 基因组选择, 植物育种, 多倍体作物