Clear Sky Science · zh
石蝇Rhopalopsole triangulispina Mo and Li, 2025(石蝇目:Leuctridae)染色体级基因组组装
为何一种微小的溪流昆虫很重要
在世界各地湍急的山区溪流中,一类名为石蝇的小而脆弱的昆虫默默地反映着水体的健康状况。它们的若虫阶段对污染极为敏感,因此若在溪流中发现它们,通常意味着水质清洁且含氧充足。尽管具有这样的生态重要性,科学家对许多石蝇的详细基因构成仍知之甚少。本研究提供了一种石蝇Rhopalopsole triangulispina的高质量染色体级DNA图谱,为理解这些昆虫的进化以及它们如何帮助我们更好地保护淡水生态系统打开了新窗口。
清澈快速流水中的生命
隶属于Nemouroidea超科的石蝇是该类昆虫中最为多样和丰富的群体之一,生活在寒冷、洁净的溪流、湖泊和池塘中,常常隐藏在岩石或沉积物之间。它们的若虫依赖良好的水质:温度、含氧量、化学污染,乃至底质类型,都可能决定其能否繁衍生存。正因为这种敏感性,科学家在评估河流和溪流健康时常把它们当作天然的“环境传感器”。在Nemouroidea中,Leuctridae科和Rhopalopsole属在亚洲山地地区尤其常见,包括中国在内,已知Rhopalopsole种类超过60种。尽管物种丰富,基因参考图谱——尤其是完全注释的基因组——一直缺失,限制了我们研究它们的进化或在水质监测中应用基因组学工具的能力。
从零起步构建基因图谱
为填补这一空白,研究团队在中国南部的一个保护山地自然保护区采集了成虫Rhopalopsole triangulispina。经仔细保存样本后,提取了高质量的DNA和RNA(RNA反映了哪些基因处于活跃状态)。研究者使用多种前沿测序技术生成了基因组的不同视图:非常准确的长读长DNA序列(PacBio HiFi)、大量短读序列(Illumina),以及能够捕捉DNA在细胞核内折叠与相互作用的特殊数据(Hi-C)。这些数据类型的结合使团队能够将昆虫的遗传物质组装成长而连续的序列,然后利用Hi-C信息把它们排列成13条类似染色体的结构,称为拟染色体。
基因组揭示了什么
组装完成的基因组约为3.47亿个DNA“字母”长度,其中近97%被定位到13条拟染色体上。质量检测表明该组装既高度完整又极为准确,错误率估计低于每一千万个碱基中出现一次,且超过95%的测序读取能映射回该组装。近一半的基因组由重复DNA组成——这些重复序列多次出现,常反映移动遗传元件或“跳跃基因”,它们在进化过程中塑造了基因组。在此基础上,团队预测了12,857个蛋白编码基因和超过2,400个非编码RNA基因,后者包括参与核糖体构建、RNA加工和指导蛋白质合成的分子。通过将这些基因与大型国际数据库比对,研究者得以为绝大多数基因分配可能的功能,并将许多基因关联到已知的生物学通路。
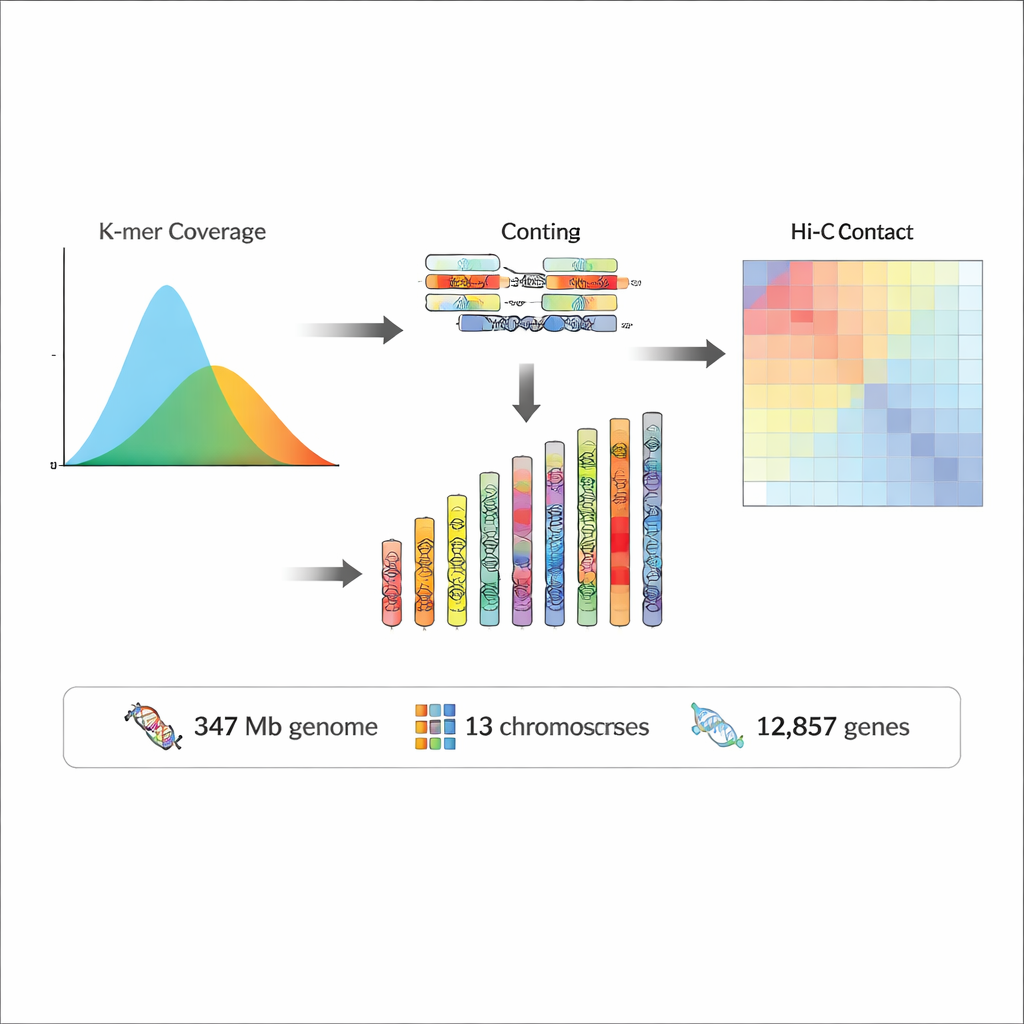
为进化与生态研究提供的新资源
除了对基因的编目外,这一基因组还可作为未来研究的参考手册。科学家现在可以探索哪些基因帮助石蝇适应寒冷、湍急的水体,它们在分子层面如何应对污染或气候变化,以及不同石蝇谱系之间的亲缘关系。迄今为止,大多数关于Nemouroidea的进化研究依赖于形态特征、线粒体DNA或部分基因集。这个完整且注释完善的基因组为重建石蝇的进化树并与其他具有截然不同生活方式的昆虫基因组进行比较,提供了更丰富、更精确的基础。由于所有原始数据和注释均已公开,全球研究者可以重新分析这些信息,将其与其他数据集整合,并构建用于生物监测的新工具。
从DNA蓝图到更清洁的溪流
对非专业读者来说,关键结论是:我们现在拥有一种作为淡水健康前线守护者的石蝇物种的详细染色体级蓝图。该基因组将帮助科学家理解这些昆虫如何生活与适应,追溯其深层进化历史,并设计更敏感的基于DNA的方法来在河流和溪流中检测它们。在实践中,这意味着对污染和环境变化的更早预警系统。通过揭示山间溪流中一种微小昆虫的遗传基础,这项工作最终有助于保护人类和生态系统赖以生存的清洁水源。
引用: Lin, A., Cao, J., Murányi, D. et al. Chromosome-level genome assembly of the stonefly Rhopalopsole triangulispina Mo and Li, 2025 (Plecoptera: Leuctridae). Sci Data 13, 292 (2026). https://doi.org/10.1038/s41597-026-06631-7
关键词: 石蝇基因组, 淡水生物指示物, 染色体级组装, 昆虫进化, 环境DNA