Clear Sky Science · zh
法国与智利沿海水体环境梯度的元条形码与宏基因组数据
变迁海域中的隐秘生命
在全球海岸线上,从平静的潟湖到雄伟的峡湾,微观生命始终在适应不断变化的环境。这些微小生物驱动着支撑渔业、水质乃至气候的碳与养分循环。然而许多沿海水域,尤其像潟湖和峡湾这样复杂的地区,在基因层面上仍几乎未被探索。本研究旨在改变这一状况,构建一个来自法国和智利沿海的丰富且开放的微生物数据集,为理解海洋生物如何应对多变环境提供新的视角。
海岸线:天然的试验场
沿海水域很少保持稳定。暴雨、河流注入、蒸发与潮汐可能在短距离和短时间内改变温度与盐度。为微观藻类提供养分的浓度可能暴涨或骤降,人类活动又带来额外干扰。这种变化形成了筛选不同微生物群落并促使新适应性出现的斑块化栖息地。为捕捉这种复杂性,研究者在法国与智利海岸采样了26个地点,包括潟湖、河口、峡湾、港口、海滩、近岸水域以及一个近海站点。部分法国地点按月采样、持续一年以追踪季节变化,而智利地点在南部秋季采样,提供了对比鲜明的沿海世界的广泛时点。 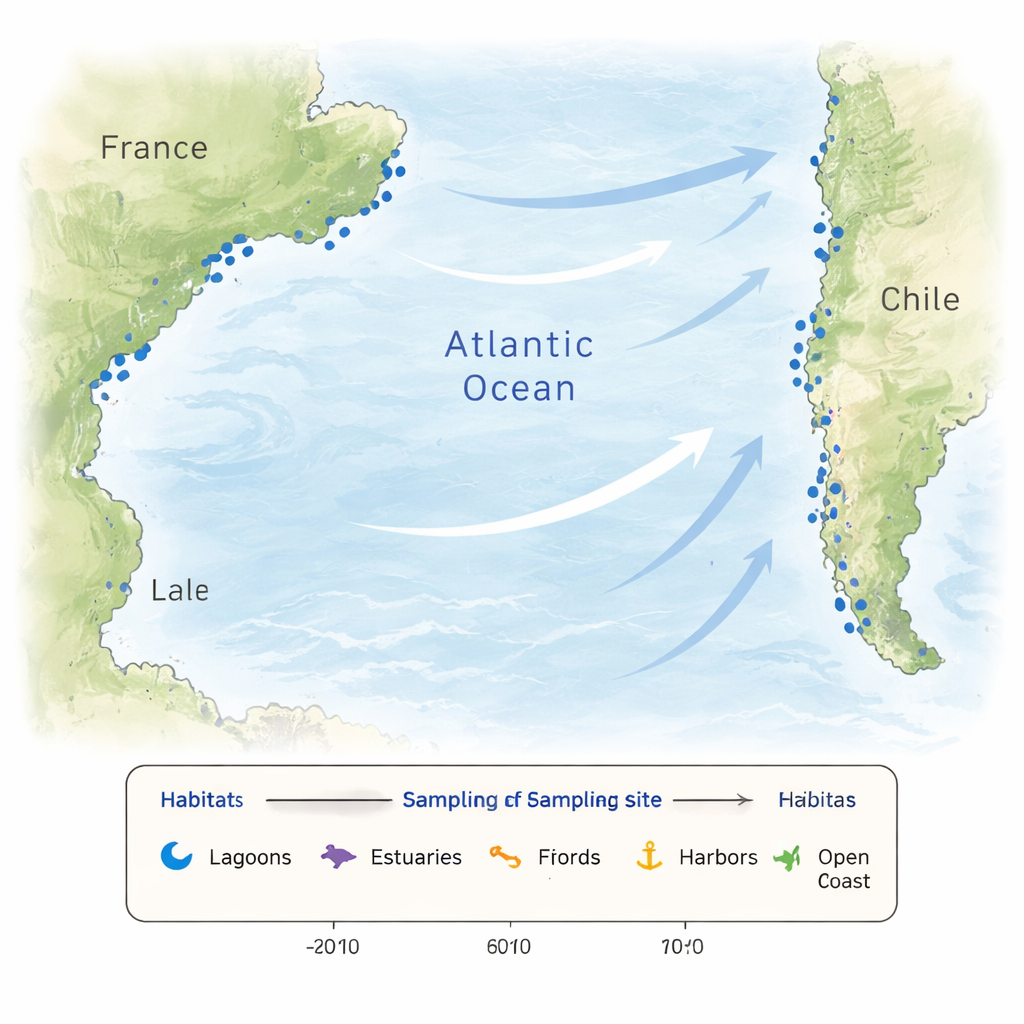
从一桶海水到DNA指纹
在每个采样点,团队收集了大量海水,主要来自日照层表层,同时在选定的峡湾和近海水域取样更深的水层。他们测量了诸如温度、盐度与养分等基本环境参数,以及叶绿素(藻类的替代指标)、溶解有机物、细菌生产力与呼吸等生物活性指标。在实验室中,微生物被浓缩在细滤膜上并提取其DNA。一类测试针对标准标志基因(16S rRNA),该基因类似于识别细菌与古菌的条形码。这种元条形码方法揭示了超过53,000个不同的DNA变体,并显示有些样本之间共享的变体少至三种,凸显了邻近群落间的高度差异性。
从基因汤中重建基因组
第二条分析路径更为宏大:整体枪击式宏基因组测序,对样本中所有DNA同时测序。利用先进的组装与划分方法,团队重建了1,372个基因组草案,即宏基因组组装基因组(MAGs)。许多基因组无法与已知物种匹配,只有约4%与已有正式描述的微生物物种对齐。在某些类群中,例如适应极端环境的某些细菌与古菌,超过一半的预测蛋白缺乏已知功能。研究者还构建了一个包含超过2300万非冗余基因的大型基因目录,发现约31%在主要参考数据库中没有匹配。这表明沿海水域中存在大量未被表征的生物学储备。
极端栖息地,新的工具
一些地点,尤其是法国的高盐潟湖,凸显为遗传新颖性的热点。在那里的盐度在几个月内可从接近正常海水波动到超过海水两倍的水平。这类压力条件可能有利于所谓的耐极端微生物,它们携带在高盐或高温下仍能发挥作用的酶。这类酶在清洁剂、生物燃料、污染治理与食品加工等工业中愈发受到追捧。通过将详细的环境测量与基因和基因组数据相结合,这个数据集有助于定位最可能发现这些罕见生物与生物化学工具的区域。 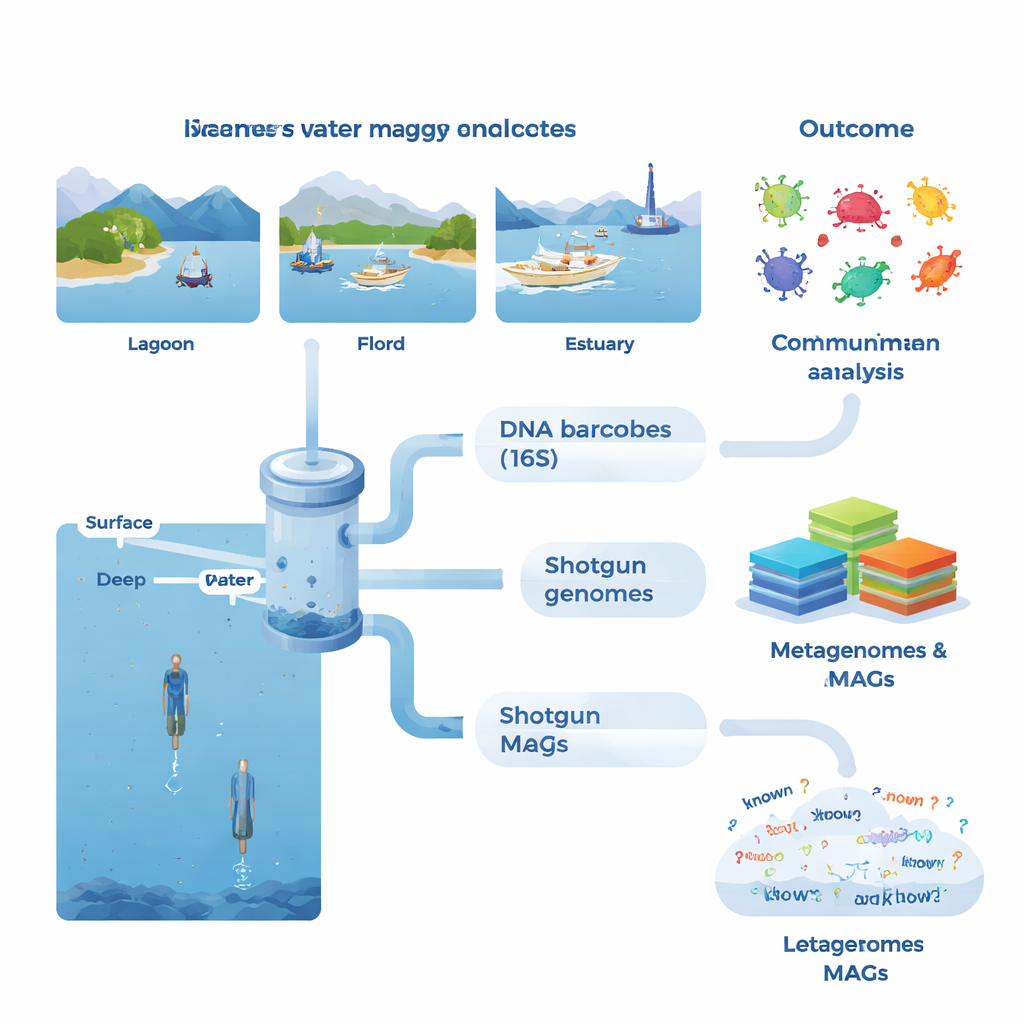
为海洋未来提供的公共资源
这项工作并非仅提出单一发现,而是提供了一个经过严格验证的开放资源,供其他科学家挖掘。所有DNA序列、基因组重建、基因目录与环境测量数据均公开存档,连同用于处理这些数据的计算代码也一并提供。对非专业读者而言,关键信息是:沿海微生物既多样又充满惊喜,尤其是在被忽视的环境如潟湖与峡湾。随着研究者利用这些数据,他们将更有能力理解沿海微生物如何响应变暖、污染与扰动,并发掘出可能惠及生物技术与环境管理的新基因。
引用: Maeke, M.D., Hassenrück, C., Aguilar-Muñoz, P. et al. Metabarcoding and metagenomic data across aquatic environmental gradients along the coasts of France and Chile. Sci Data 13, 29 (2026). https://doi.org/10.1038/s41597-026-06572-1
关键词: 沿海微生物群落, 宏基因组学, 潟湖与峡湾, 海洋生物多样性, 环境DNA