Clear Sky Science · zh
AF2BIND:利用 AlphaFold2 的配对表示预测小分子结合位点
在蛋白质的汪洋中寻找药物靶点
现代药物常通过附着在细胞内蛋白表面的微小凹槽或裂隙来发挥作用。尽管如今我们拥有庞大的蛋白结构目录,但要事先判断小分子(潜在药物)到底会粘在哪仍然令人意外地困难。本研究介绍了 AF2BIND——一个简单但强大的计算工具,它挖掘了里程碑式蛋白结构预测器 AlphaFold2 的内部数据层,以在数千种人类蛋白中突出可能的药物结合位点。其目标是缩小新药搜索范围,并揭示传统方法易忽视的隐含功能热点。
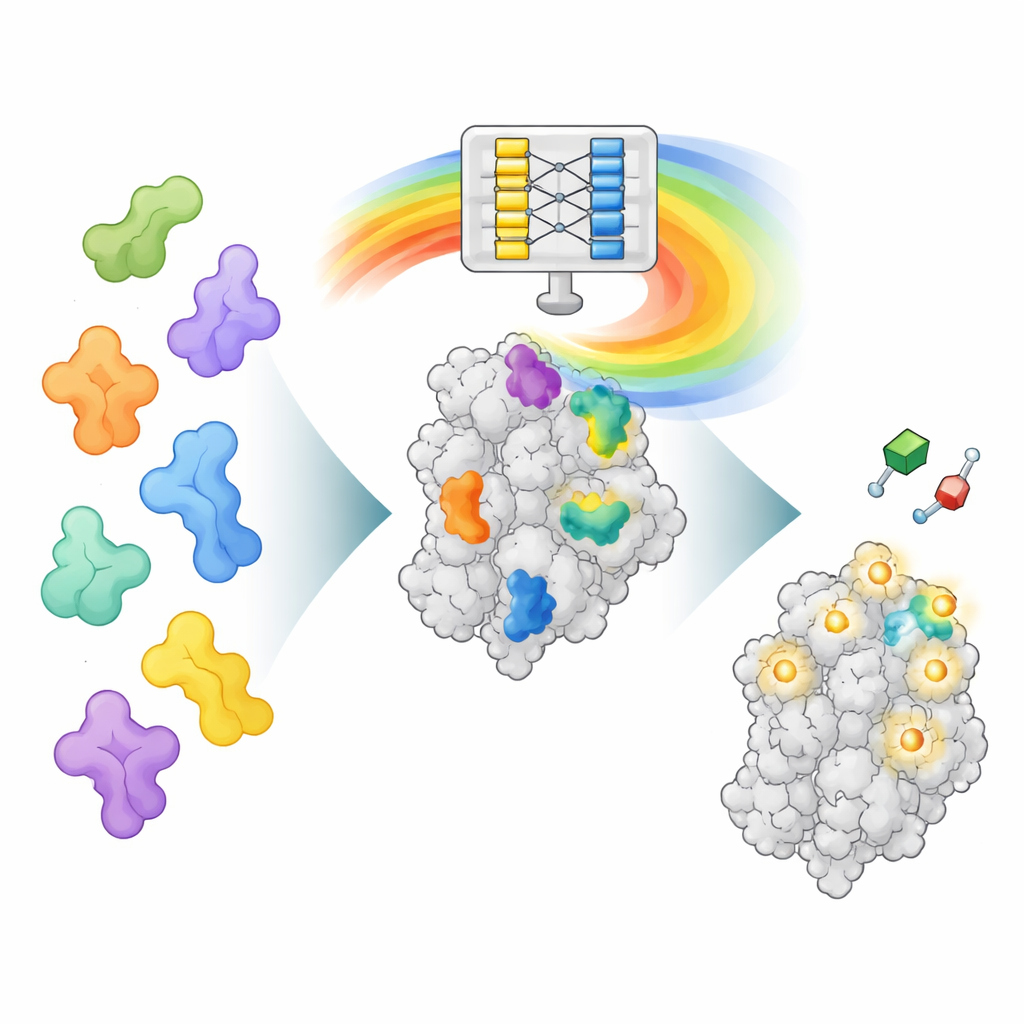
解读 AlphaFold “内部思路”的新方式
AlphaFold2 的训练目标是预测氨基酸链如何折叠成三维蛋白,而不是寻找药物结合位置。然而,在学习蛋白折叠的过程中,它也学到了关于蛋白不同部分如何相互作用的丰富模式。AF2BIND 利用其中一个内部数据层,称为配对表示(pair representation),它编码了每一对氨基酸位置在空间上的关联。作者将蛋白序列及其主链结构输入 AlphaFold2,同时附加 20 个额外的氨基酸——每种类型各一个,作为独立的“诱饵”链。AlphaFold2 随后计算蛋白与每个诱饵残基的相互作用。这些相互作用模式成为一个非常直接的逻辑回归模型的输入,该模型为蛋白的每个位置估计其属于小分子结合位点的概率。
将隐藏信号转化为实用预测
训练 AF2BIND 需要一组精心挑选的大约 1,900 个蛋白–配体结构,这些结构中小分子的结合具有高质量的实验证据。研究人员花了大量努力来避免通过相似性“作弊”:他们在划分数据时确保测试蛋白在整体折叠、序列甚至结合口袋形状上都不与训练集共享。 在这个严格的基准测试中,AF2 的配对表示优于若干替代的神经网络嵌入方法,包括仅基于序列或基于结构条件的序列设计。仅使用配对特征,AF2BIND 在排名靠前的预测中找回了约三分之二的已知结合残基,并在标准分类指标上表现良好,同时对蛋白形状和侧链取向的小幅变化保持稳健。
从诱饵残基中读出化学线索
由于 AF2BIND 是一个简单的线性模型,其决策对现代 AI 系统而言异常透明。每种 20 种诱饵氨基酸都会对给定蛋白位置的最终结合评分贡献一个可测量的分量。通过在大约 2,000 个蛋白–配体复合体中检查这些贡献,作者发现某些诱饵组合在遇到富碳的疏水配体时会更强烈地被激活,而另一些则在面对更极性、亲水的分子时更为显著。换言之,诱饵激活模式类似于一个粗略的化学指纹,表征某个口袋偏好哪类小分子。这表明未来类似 AF2BIND 的方法不仅可能标出药物的结合位置,还能提示最合适的化学性质。
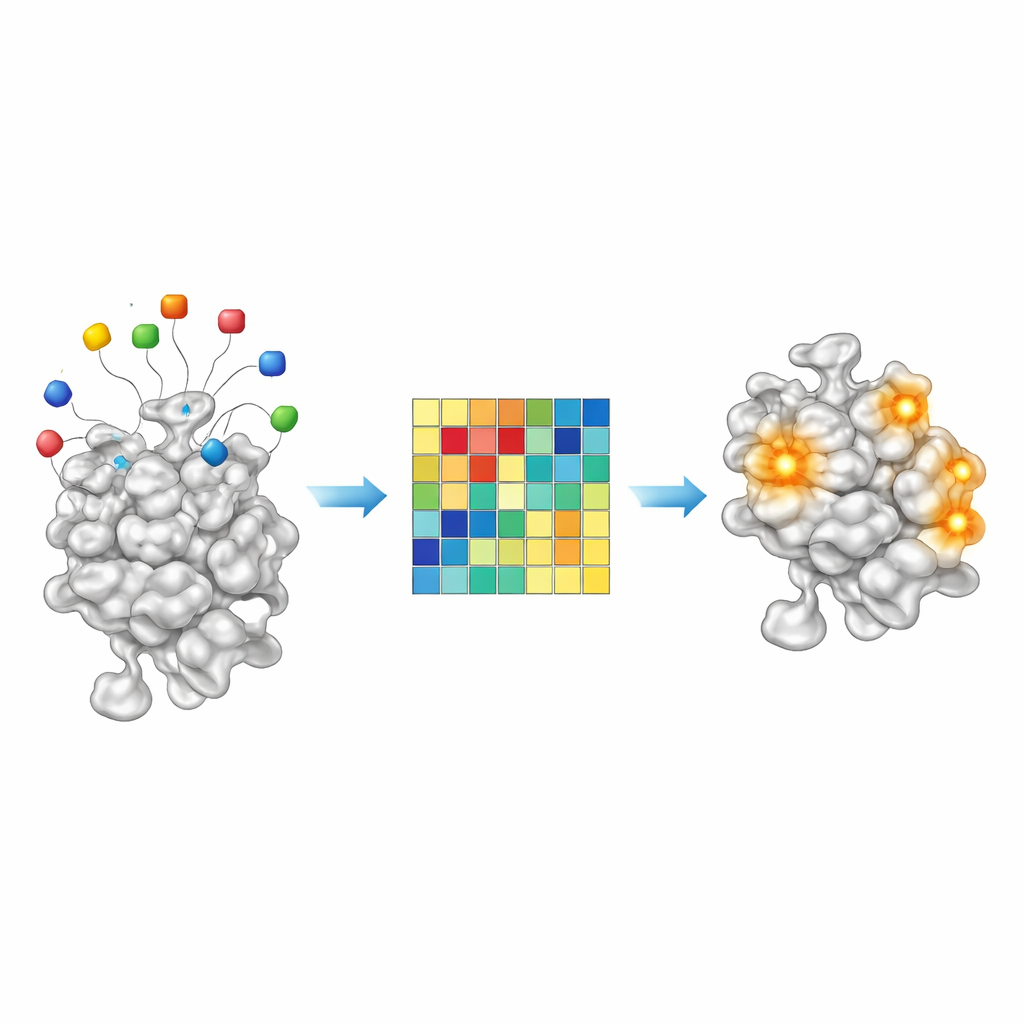
在整个人类蛋白组中扫描新口袋
有了训练好的模型,团队将 AF2BIND 应用于 AlphaFold 预测的整个人类蛋白组结构。去除低置信度区域并将非常大的蛋白切分为可管理的结构片段后,他们将相邻的高分残基聚成候选结合位点。AF2BIND 在超过 13,000 个蛋白中预测出 20,000 多个此类位点。值得注意的是,其中大多数并未与基于同源性的方法(如从相关晶体结构复制配体的 AlphaFill)推断出的口袋重叠,也不与广泛使用的口袋发现工具 P2Rank 重合。许多仅被 AF2BIND 发现的位点比经典的埋藏口袋更浅或更分散,且常与肽、RNA、DNA 或其他蛋白结合的区域重合——这些界面仍可能被小分子所靶向。
对药物发现和疾病研究的影响
为了评估这些新建议位点在药物设计上的潜力,作者使用了一个独立工具,基于口袋大小、封闭性和化学环境来评分“药物可及性”。总体而言,AF2BIND 识别的位点得分高于常见的有吸引力药物靶点阈值,其中包括那些与遗传性疾病相关的蛋白。将结果与在细胞中标记反应性半胱氨酸的化学蛋白质组学实验交叉比对时,AF2BIND 与 P2Rank 一起解释了近一半的可配位区域——两种方法各自捕捉到了对方遗漏的案例。该工作表明,结构预测网络学到的内部表示可以被重新用于大规模绘制可能的药物结合位点,而无需事先知道任何特定配体。对于非专业读者,关键的信息是:那些能预测蛋白形状的 AI 突破也开始揭示药物可能如何和在哪里抓住这些形状,这可能加速新疗法的发现并阐明我们蛋白中此前被隐藏的调控节点。
引用: Gazizov, A., Lian, A., Goverde, C. et al. AF2BIND: predicting small-molecule binding sites using the pair representation of AlphaFold2. Nat Methods 23, 626–635 (2026). https://doi.org/10.1038/s41592-026-03011-2
关键词: 蛋白质结合位点, 药物发现, AlphaFold2, 计算生物学, 结构生物信息学