Clear Sky Science · zh
使用DNA三叉结构建复杂多样的DNA序列
构建新的遗传故事
现代生物学可以以惊人的速度读取和编辑DNA,但实际书写长且定制的遗传序列仍然滞后。这一差距拖慢了从新药设计到更环保材料开发的各个领域。本研究提出了“Sidewinder”(侧向缠绕)方法,一种将DNA片段拼接在一起的新途径,旨在使编写复杂、定制基因像读取一样可靠且可扩展。
为什么DNA组装需要重新思考
每个细胞都依赖DNA运行,DNA是一串编码生命指令的长化学“字母”序列。科学家只能化学合成短的DNA片段,因此更长的基因必须像将切碎的词拼成句子一样,从许多小片段组装而成。现有方法都依赖片段的匹配端点来引导哪些片段互相结合。但这些匹配端点会成为最终DNA的一部分,这意味着为了实现完美组装而对端点的优化会同时改变基因本身。随着设计变得更长更复杂,这种内在的折中会导致更多错误、产率下降以及实际可构建性的限制。
一条不留痕迹的旁路引导
Sidewinder 通过加入第三条在成品中永远不会出现的辅助DNA链来解决这个问题。DNA片段在两端被预先设计为具有两种特性:短的“趾锚”(toeholds),最终形成无缝的连接;以及较长的“条形码”,仅用于与其指定伙伴配对。当在受控温度下混合时,相邻片段上的条形码会互相识别并缠绕成临时的侧向螺旋,形成三叉结,将匹配的趾锚拉到位。随后酶将主要DNA片段封接在一起。最后,辅助条形码被去除,留下干净、连续且无额外疤痕或标签的序列。 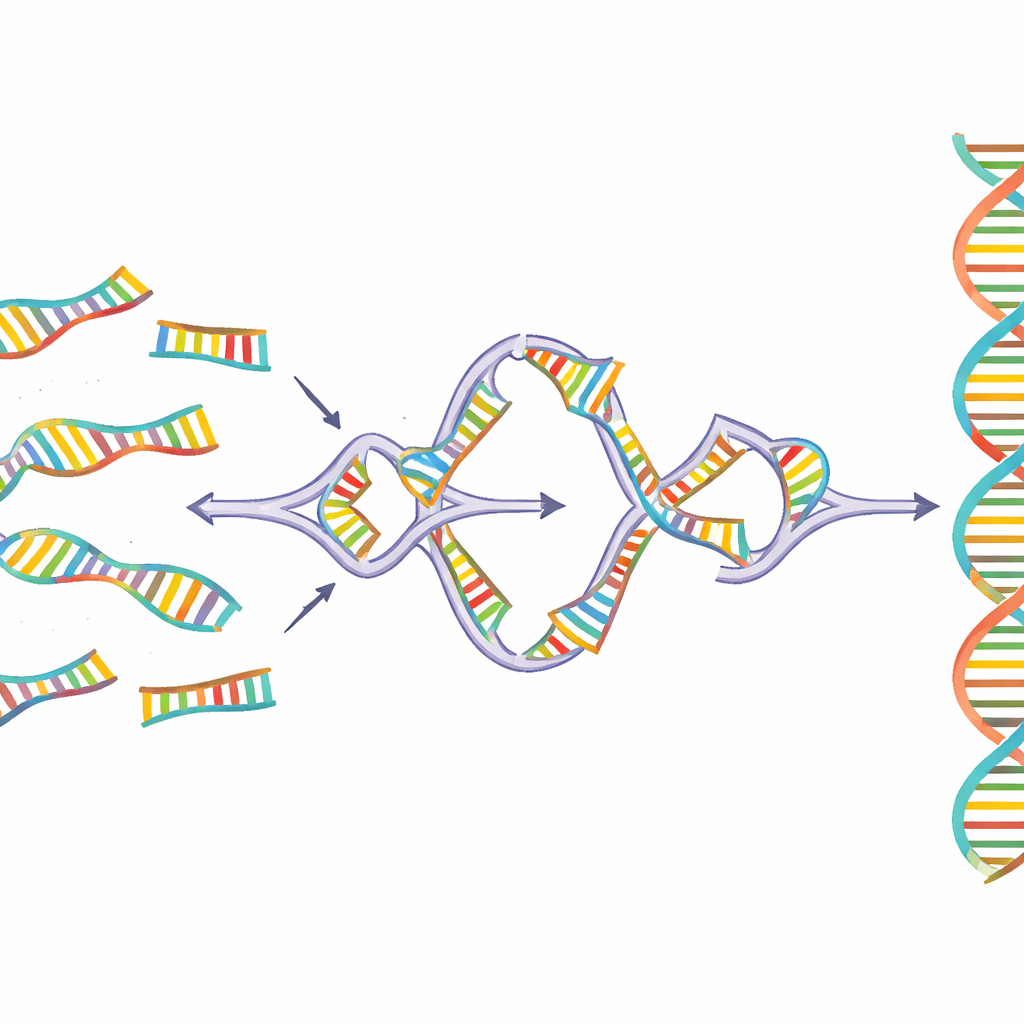
从数十个片段到难拼的基因
为了展示Sidewinder的能力,作者在一次反应中从5、10、20甚至40个独立片段构建了DNA构件。现有的最先进方法在超过少数片段时就会失败,产生混乱的混合物或完全失败,而Sidewinder则稳定地产生单一、正确大小的产物。长读长测序确认,在40片段的测试中,超过96%的读取是真正的Sidewinder产物,且这些产物都按完美顺序组装。团队随后在“困难模式”序列上测试该方法:一个富含G和C碱基的人类基因,以及一个充满重复的类丝蛋白片段。这类序列常常因为自我互粘而击败标准组装方法。即便在所有连接处刻意使用相同趾锚序列(一种几乎不可能被旧技术控制的情况),Sidewinder仍然产生了接近完美的组装结果。
同时构建多种基因与海量变体
由于Sidewinder的条形码明确限定了谁可以与谁配对,多个基因可以在同一试管中构建而不会发生交叉污染。研究者将三种不同颜色标记蛋白的片段混合并在同一环境中组装。使用合适的引物,他们可以有选择地扩增任一基因或整个混合物,测序显示不同设计间的错误交叉极为罕见。 
这对未来生物工程的意义
Sidewinder 的关键成就是将“组装指令”与最终的DNA序列分离开来。通过将引导信息转移到可移除的侧链上,科学家可以设计出极具特异性且可靠的连接方式,而不必牺牲基因本身的序列。其结果是一个通用的方法,能够以与起始片段质量相媲美甚至在某些方面更佳的准确性,构建长、复杂且高度多样的DNA序列。随着人工智能等工具日益提出大胆的新基因设计,像Sidewinder这样的技术可能成为将这些设计转化为用于药物、材料、农业等领域的真实分子的关键手段。
引用: Robinson, N.E., Zhang, W., Ghosh, R. et al. Construction of complex and diverse DNA sequences using DNA three-way junctions. Nature 651, 491–500 (2026). https://doi.org/10.1038/s41586-025-10006-0
关键词: DNA组装, 合成生物学, 基因文库, DNA纳米技术, 蛋白质工程