Clear Sky Science · zh
TONSOKU 防止大型串联重复的形成并抑制 ATR–WEE1 检查点激活
当植物的 DNA 修复出错时
我们自身的基因组,以及作物和肿瘤的基因组,在细胞复制 DNA 的过程中不断受到冲击。通常,修复系统会在问题导致严重后果之前悄然修补。本研究关注当一种以名为 TONSOKU(TSK)的蛋白为核心的系统在一种常用于研究的小杂草植物中缺失时会发生什么。结果是意想不到的大规模 DNA 重复和异常的生长模式——这些发现对植物育种和理解人类疾病都有重要启示。
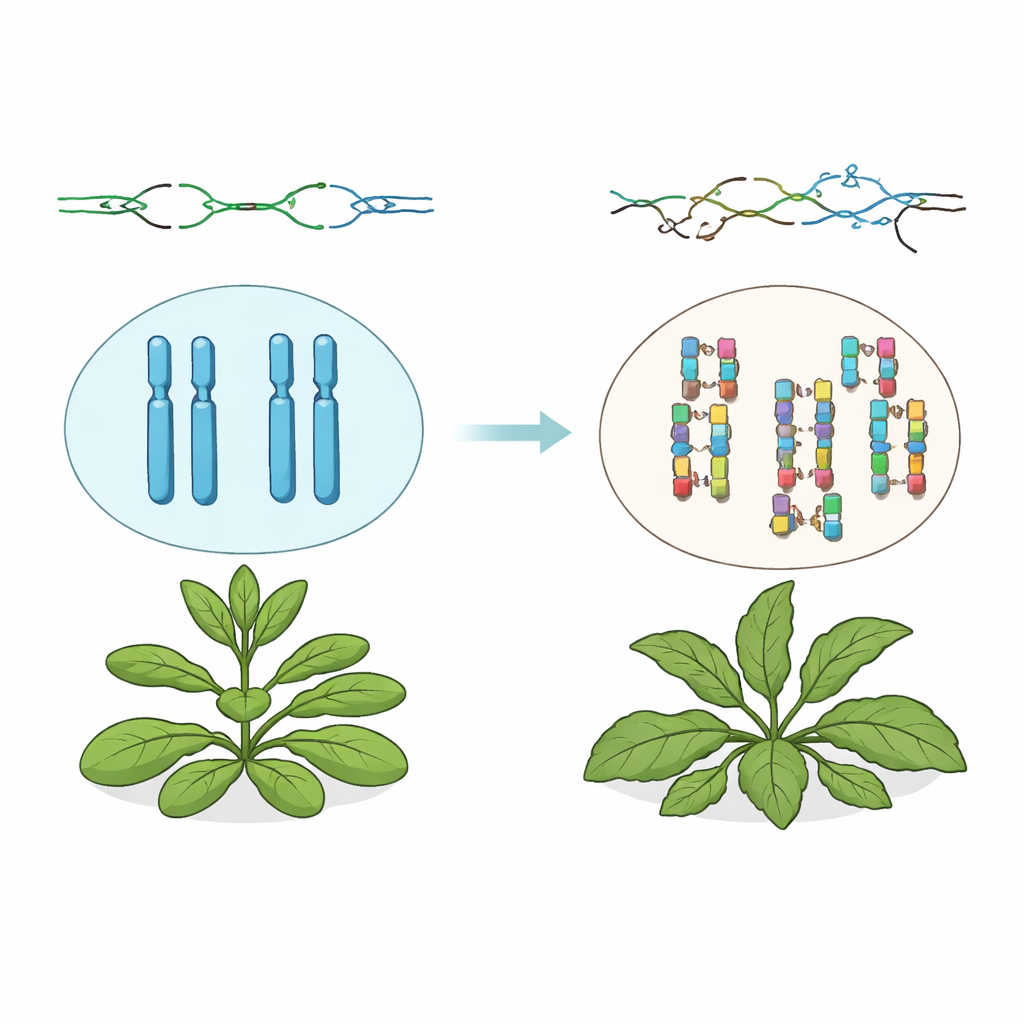
额外的 DNA 副本大量积累
作者使用了缺失功能性 TSK 基因的拟南芥(Arabidopsis thaliana)。尽管这些植物可以存活并繁殖,但其基因组讲述了一个戏剧性的故事。通过全基因组测序,研究团队发现小尺度的突变仍在正常范围内,但大段 DNA 经常被连续复制——即所谓的串联重复。这些被复制的片段长度从不到一千个碱基到近一百五十万个碱基不等,通常使基因组总体大小增加约 7%。许多重复是个体特有的,表明这些事件在植物生长过程中以及各代之间反复独立地产生。
重复重塑基因及其活性
这些额外的 DNA 片段并非空载。当被重复的区域包含基因时,这些基因往往变得更为活跃,因为拷贝数增加了。通过将 DNA 测序与 RNA(基因活性的读出)测量结合,研究者表明处于重复区域内的基因通常产生的 RNA 比正常植物中对应基因多出数倍。这种表达增强还可能外溢,影响重复区外的基因。随着时间推移,这类拷贝数变化能以重大方式改变性状——这是农作物驯化长期利用的机制,亦常见于人类肿瘤中。
备用修复途径造成了损伤
为弄清这些重复如何形成,团队对重复片段的端点进行了放大观察。他们看到的模式与一种叫 theta 介导的末端连接(theta-mediated end joining,TMEJ)的应急 DNA 修复途径的指纹相符,该途径依赖一种称为聚合酶 theta 的酶。当依赖 TSK 的高精度修复系统失效时,这一路径介入修补断裂的 DNA。它通过利用极短的互补序列作为“粘合”进行连接,这很容易导致 DNA 片段被重复复制。对超长 DNA 分子的光学绘图证实,额外的片段紧邻其原始拷贝位于染色体上,形成真正的串联重复,而非独立的 DNA 圈状结构。
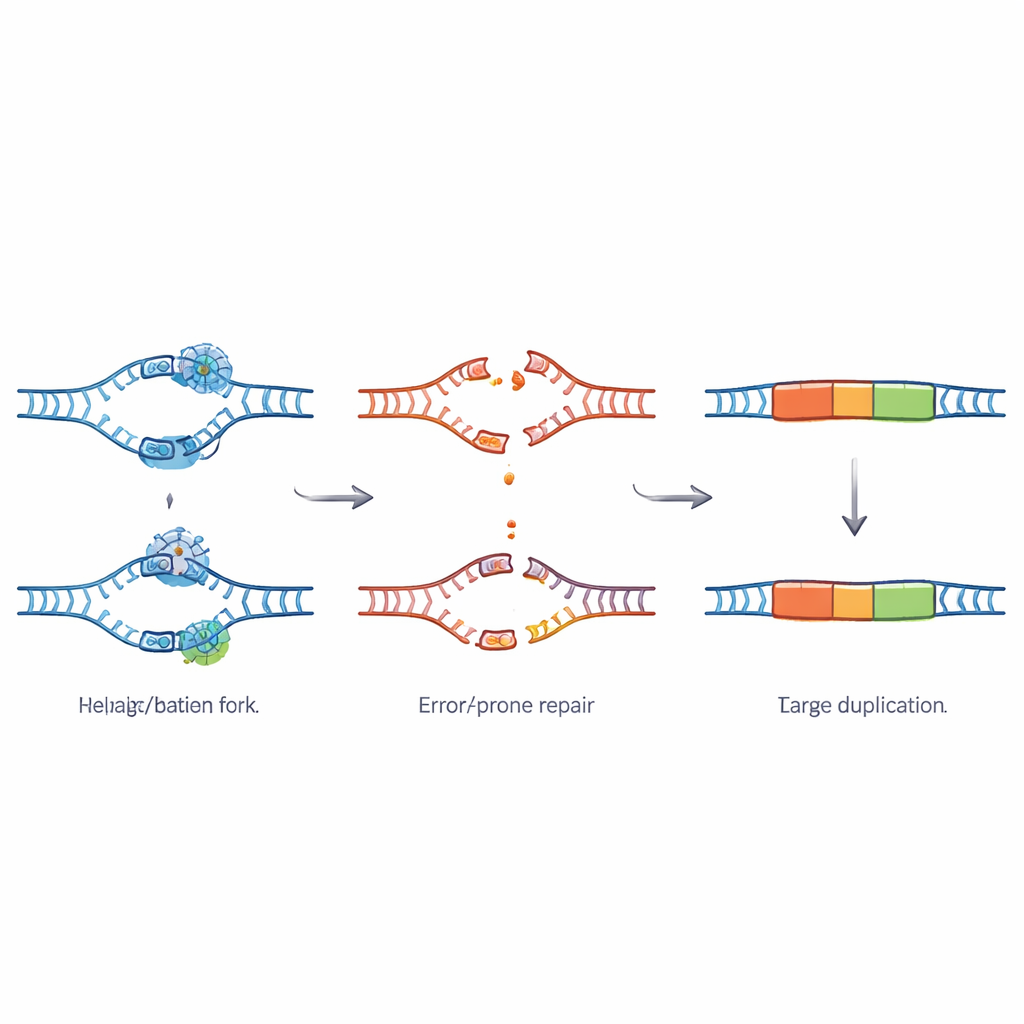
基因组中的应激热点
这些重复区域并非随机分布。它们倾向于出现在细胞分裂过程中较晚复制且被紧密、重复序列包装的异染色质区域。这些区域富含特殊的重复基序和已知会给复制机器带来麻烦的移动 DNA 元件。重复位点的边界也显示出慢性应激的迹象:它们包含更多的天然变异、更长的重复序列、更丰富的转座元件,以及比典型区域更多的 DNA 复制起始位点。所有这些表明这些区域是复制经常停滞或断裂的热点,尤其是在缺失 TSK 时。
从受损的 DNA 到奇形植物
没有 TSK 的拟南芥不仅携带受损的基因组;它们的外观也异常。许多植株表现出叶片和花朵的扭曲模式、粗壮或分裂的茎以及异常的分枝。研究者探究这些可见奇特性是否由重复本身导致,或由细胞对持续 DNA 损伤的警报系统反应所致。通过使植物 DNA 损伤反应中的关键参与者失能——那些感应复制停滞并使细胞周期暂停的蛋白——他们在很大程度上恢复了正常的植物形态,尽管重复仍在形成。这表明发育缺陷主要由 DNA 损伤反应的慢性激活引起,而非直接由额外的 DNA 拷贝所致。
为何这超越了一种杂草的重要性
这项工作揭示了一条此前被忽视的通路:当一种保守的修复途径失效时,大型 DNA 串联重复如何产生,将复制应激、易出错的修复与有形的形态改变联系起来。类似 TONSOKU 的蛋白及其修复系统在包括人类在内的动物中也存在。在某些癌症中,基因组中散布着与这些植物中观察到的大小惊人相似的大型串联重复,并且强烈依赖研究中提到的相同应激感知通路。理解 TSK 类功能丧失如何将平衡从稳定的 DNA 维护推向失控的重复,可能有助于阐明如何设计新的植物性状以及某些肿瘤如何进化并对治疗作出反应。
引用: Thomson, G., Poulet, A., Huang, YC. et al. TONSOKU prevents the formation of large tandem duplications and restrains ATR–WEE1 checkpoint activation. Nat Commun 17, 2874 (2026). https://doi.org/10.1038/s41467-026-70906-1
关键词: 基因组稳定性, 串联重复, DNA 复制应激, DNA 修复途径, 植物发育