Clear Sky Science · zh
SMART:使用图神经网络和度量学习的空间多组学聚合
把组织看作邻里地图
我们的身体由繁忙的细胞社区构成,基因、蛋白质和DNA的包装在特定位置协同工作。新的显微镜和测序工具现在可以直接在薄切组织片内读取这些分子层,但将这类多层次的空间数据转化为关于器官组织方式的清晰图景,是一个巨大的计算挑战。本研究介绍了SMART,一种计算方法,帮助科学家将这些复杂信号融合为反映不同细胞群落位置与排列的详尽地图。
为什么绘制细胞邻里图很难
现代“空间多组学”技术可以同时测量多种分子信息——例如RNA、细胞表面蛋白以及染色质开放性——并记录每次测量在组织切片中的精确位置。每一种组学提供了关于细胞行为的不同视角,但它们噪声大、维度高且不自然对齐。此外,同一类型的细胞并不总是聚成团簇;它们可以在器官中呈散落的“岛屿”分布。现有的软件工具常常要么忽略空间布局,要么过度简化不同组学之间的关系,要么难以扩展到新仪器能产生的超大数据集。
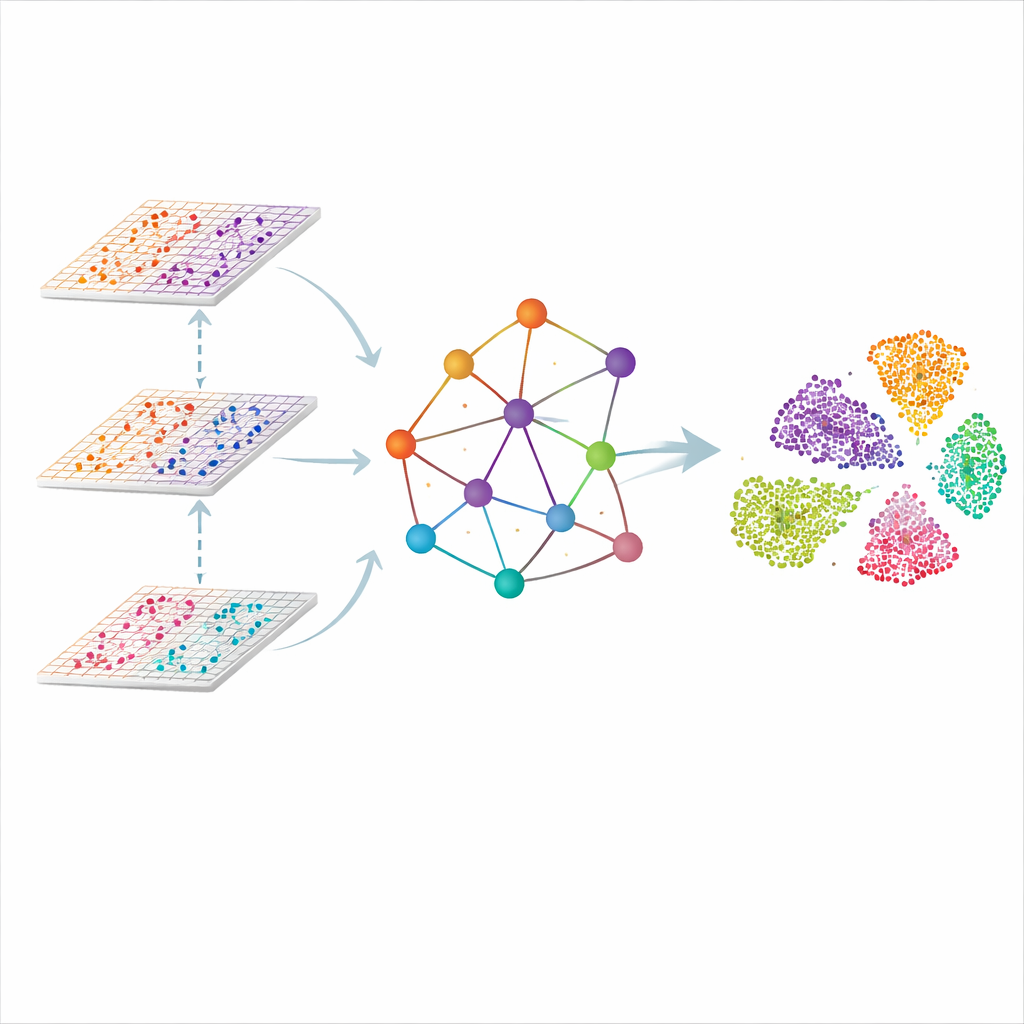
用图来描述组织,而不只是列出细胞
SMART通过将组织中每个测量点视为网络中的一个节点来处理问题。相邻点被连接形成空间图,而每种组学的分子读数首先被压缩为较小的一组协同特征,捕捉总体模式而不是单个基因。然后一种为图设计的神经网络沿连接传递信息,使每个点在“倾听”邻居的同时保留每种组学的贡献。结果是一个共享的低维表示,其中组织中相似的区域——例如大脑的不同层或淋巴结的功能区——会自然地聚集在一起。
教模型什么应该被视为相似
仅仅依靠物理邻近并不够,因为同类型的细胞可能远相互分离。SMART引入了来自人脸识别系统的第二个要素:基于三元组的度量学习。对于每个点,该方法会自动找到另一个分子模式非常相似的点(“正样本”)和一个明显不同的点(“负样本”)。然后调整内部表示,使正样本被拉近而负样本被推远,即使它们在组织切片上相距甚远。这个拉锯过程与一个重构步骤同时进行,迫使SMART保留每个组学层的关键细节,平衡空间连续性与分子特异性。
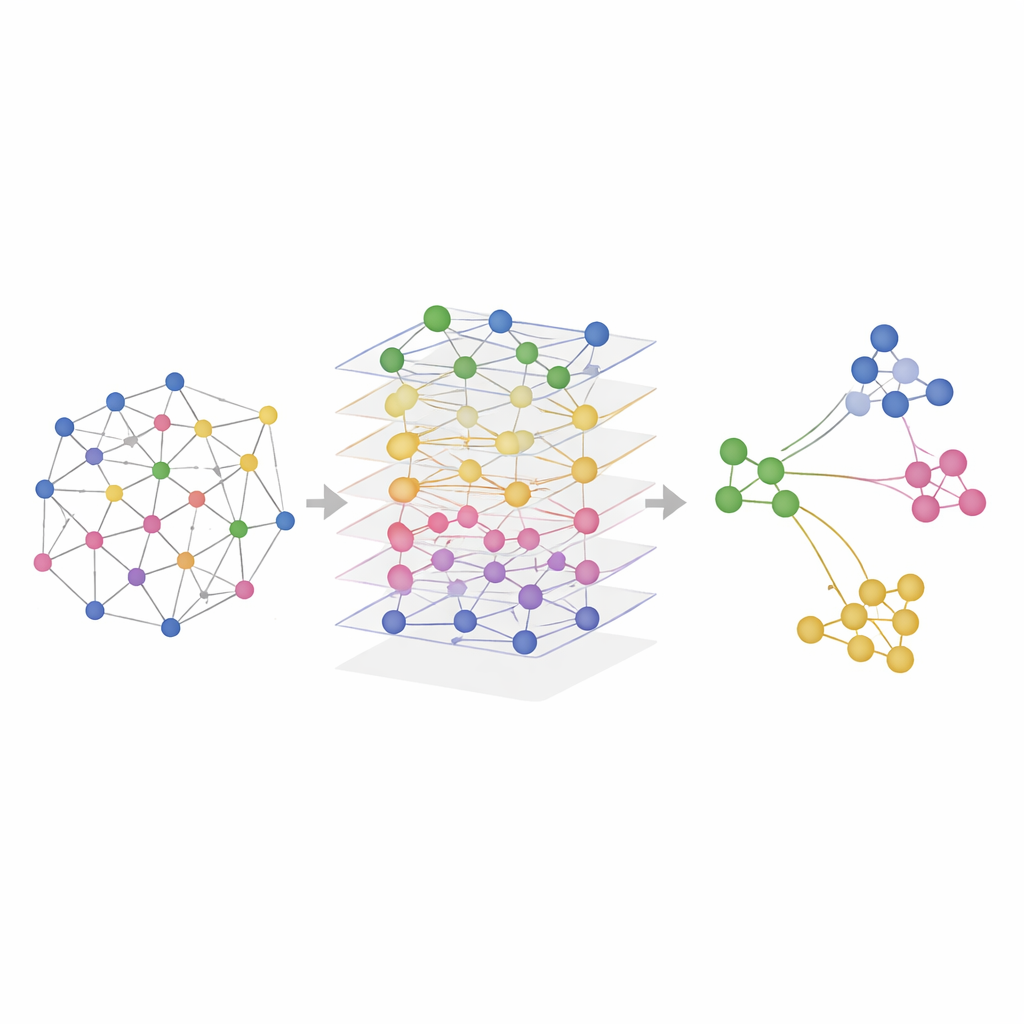
在真实组织中检验SMART
研究人员在模拟数据和真实实验数据上测试了SMART,这些实验测量了小鼠大脑、小鼠脾脏、人类淋巴结和扁桃体中RNA、蛋白和染色质可及性等组合。在已知真实空间区域的受控模拟中,SMART最准确地恢复了真实模式并保持了各组学层内的关系。在真实数据集中,SMART持续比其他方法更清晰地识别精细的解剖结构——例如特定的大脑区域或淋巴器官中的免疫细胞区——同时保持较低的计算需求。一个相关版本SMART‑MS将相同思路扩展到多张组织切片,校准同一器官的切片并修正实验间的技术差异。
为下一波空间生物学提供快速地图
简而言之,SMART是为下一代分子图谱构建的制图引擎。通过将组织布局的网络式建模与内置的“什么应被视为相似”的判断相结合,它可以将庞大且混乱的空间多组学测量转化为连贯的器官邻里地图,帮助研究者更容易发现特定细胞类型与微环境的位置、它们在发育或疾病过程中的变化,以及新实验技术之间如何相互契合。随着空间数据在规模和复杂性上的持续增长,像SMART和SMART‑MS这样的工具将是把原始测量转化为生物学洞见的关键。
引用: Du, Z., Chen, Q., Huang, W. et al. SMART: spatial multi-omic aggregation using graph neural networks and metric learning. Nat Commun 17, 2876 (2026). https://doi.org/10.1038/s41467-026-70821-5
关键词: 空间多组学, 图神经网络, 组织微环境, 数据整合, 单细胞生物学