Clear Sky Science · zh
TANGO:冷冻电子断层扫描中粒子分析与整理
以3D观察细胞,然后理解分子群落
冷冻电子断层扫描让科学家能够将活细胞在运动中快速冷冻并以三维形式捕捉它们,几乎像是在原子尺度上暂停一部电影。但当成千上万个微小的分子“斑点”被绘制到细胞内部后,会出现一个新问题:我们如何理解谁与谁相邻、哪些分子组成团队,以及在这座拥挤的分子城市中重要的模式藏在哪儿?这项研究介绍了TANGO——一个将原始3D粒子地图转化为可读故事的软件框架,帮助阐明分子如何排列与协同工作。
从冰中的点到分子邻里地图
冷冻电子断层扫描从在显微镜中倾斜冷冻样品并记录大量二维图像开始。这些图像被合成为一个称为断层图的三维体积,其中单个分子复合体呈现为模糊的斑点。现有方法已经利用这些数据通过平均多份实例来锐化分子形状,但它们在很大程度上忽视了同样丰富的宝藏:每个粒子的精确位置和方向。TANGO正是为利用这些被忽视的信息而构建。它将所有粒子视为空间中的点,每个点都有一个方向,并分析它们相对于彼此的位置与取向。通过这样做,它不仅仅询问“这个分子看起来怎样?”,而是追问“这些分子在细胞中如何组织在一起?” 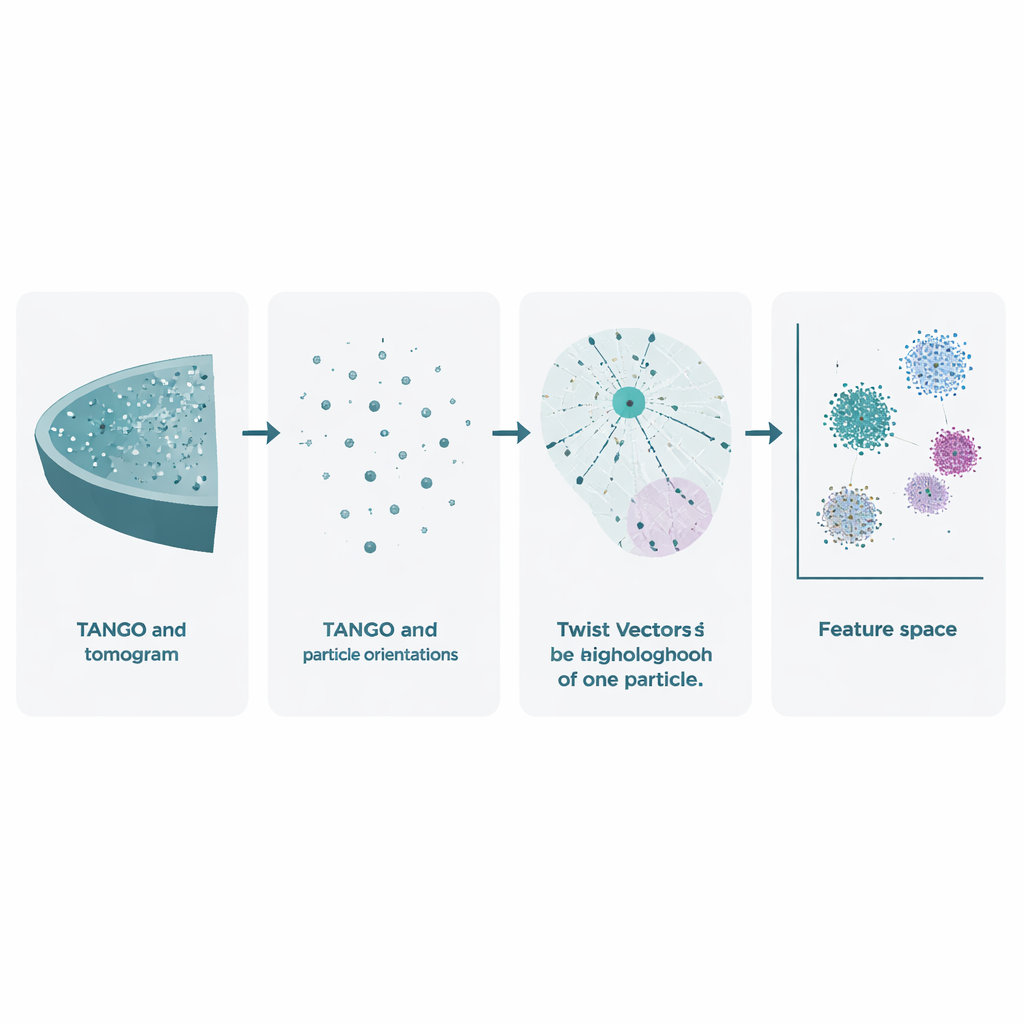
用新描述子捕捉扭转与转动
TANGO的核心思想是“扭转向量”。对于任一给定粒子,软件查看在所选半径内的所有邻居,并记录两件事:每个邻居在三维空间中的位置以及其相对中心粒子的旋转情况。这些位置与角度的组合关系被编码为简明的数值描述,称为扭转描述子。由于TANGO始终将邻域重新定向到一个共同的参考系,这些描述子不受整个样品在显微镜中如何旋转的影响。这就使得能够在不同断层图与实验之间以一致的方式比较局部邻域。
清理嘈杂数据并重建分子组装体
真实的实验数据通常很混乱:自动挑选方法可能包含许多错误粒子,并且难以跟踪哪些小片段属于哪些大结构。TANGO通过将扭转关系网络转化为图结构来应对这一点,在该图中粒子为节点,邻域链接为边。通过分析节点如何连接,TANGO可以将粒子重新归组到它们正确的母体组装中,并丢弃不符合预期几何形状的异常值。作者展示了该方法能够准确地恢复细胞核包膜中核孔的环状结构、微管的管状排列以及未成熟HIV类病毒颗粒的大致球形外壳。在每种情况下,TANGO既清理了粒子列表,又恢复了哪些片段属于同一组装体,通常与细致的人工整理相当或有所改进。
在晶格中识别细微缺陷与模式
许多病毒与细胞结构形成重复晶格,类似于曲面上的分子铺砖。TANGO利用其扭转描述子来衡量这些模式的规则性,并检测它们弯曲或断裂的位点。一个关键要素是“角度评分”,它在比较取向时尊重内建对称性,例如六聚体的六重对称。应用于成熟的HIV衣壳时,TANGO能够在大片六聚体中检测出用于闭合锥形外壳的五聚体。在未成熟的HIV晶格中,它将有序区域与畸变区域区分开来,并将低角度评分与外壳的不规则、断裂区域相关联。对合成染色质和核糖体数据的类似分析揭示了堆叠的核小体、螺旋状的DNA–蛋白排列,以及重复出现的核糖体对,类似于先前描述的翻译状态。 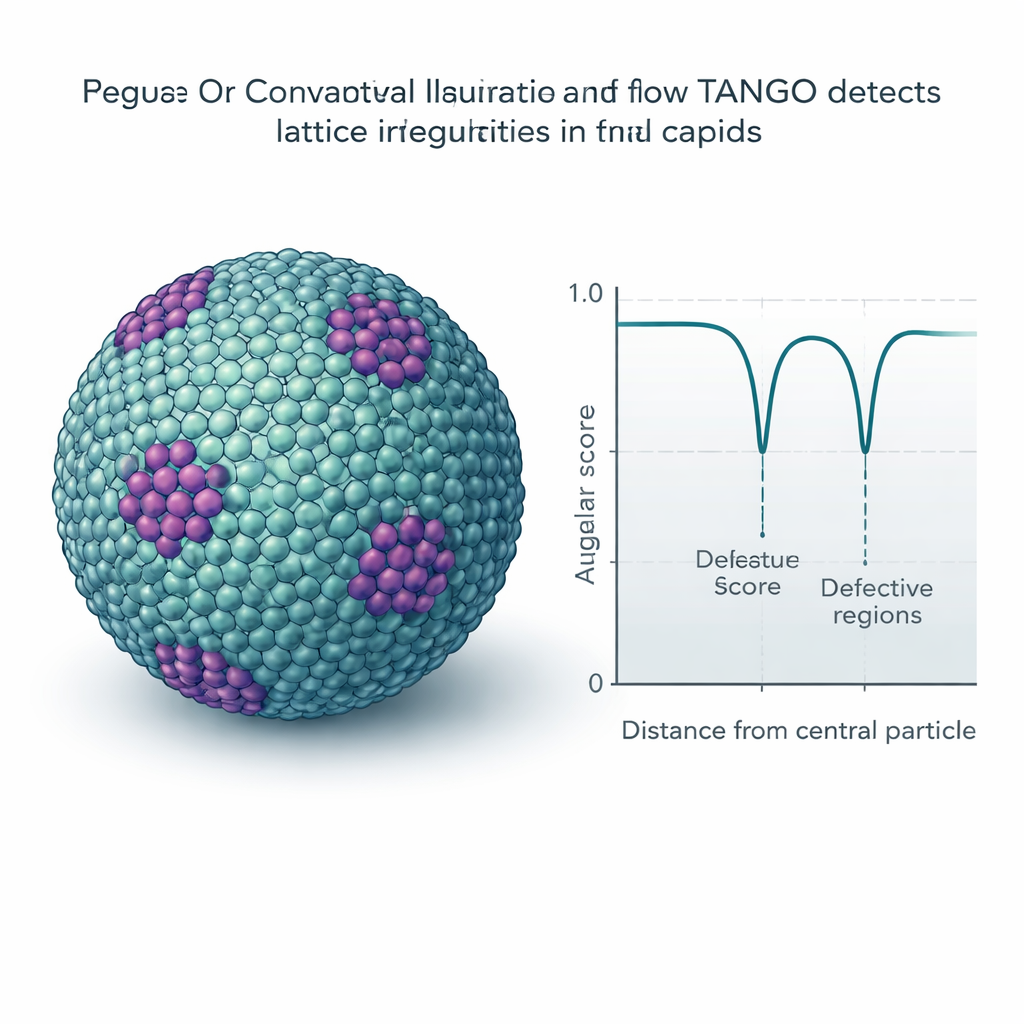
用于探索细胞结构的灵活工具箱
TANGO以开源Python软件实现,并配有图形界面,使用户可以在无需大量编程的情况下测试不同的邻域形状、滤波器和特征。由于其模块化设计,研究者可以插入自己的几何度量或模式描述子,并立即在相同工作流中使用它们。对新手而言,这降低了探索空间组织的门槛;对专家而言,它提供了一个能够随着新想法和数据集扩展的框架。
这对理解活细胞为何重要
简而言之,这项工作为生物学家提供了一种方法,从单个分子的静态图像迈向这些分子在细胞内如何排列与协作的动态地图。通过将“谁靠近谁”和“它们如何取向”这些关系编码为稳健的数值特征,TANGO将嘈杂的3D显微数据转化为可以聚类、比较并进行统计检验的模式。这能揭示隐藏的组装体、 pinpoint(定位)病毒外壳的缺陷,并发现与疾病或药物作用相关的罕见分子排列。随着冷冻电子断层扫描的广泛应用,像TANGO这样的工具将帮助把密集的粒子云转化为关于生命内部协作的清晰见解。
引用: Schreiber, M., Turoňová, B. TANGO: Analysis and curation of particles in cryo-electron tomography. Nat Commun 17, 1557 (2026). https://doi.org/10.1038/s41467-026-69195-5
关键词: 冷冻电子断层扫描, 空间组织, 分子晶格, 病毒衣壳, 核糖体