Clear Sky Science · zh
跨多种哺乳动物组织与细胞系的小非编码RNA绝对定量图谱
为何微小的RNA分子重要
在每个细胞内,大量微小的RNA分子参与决定哪些基因被开启或关闭。这些小型非编码RNA像遗传程序的调光开关,塑造发育、器官功能和疾病进程。然而,尽管测序技术日益强大,科学家仍然难以准确测定这些分子在不同细胞和组织中的真实数量。本研究提出了一种更精确的计数方法,并构建了一个详尽的图谱,展示它们在多种哺乳动物组织和常用实验室细胞系中的真实丰度。
更清晰的小RNA计数方法
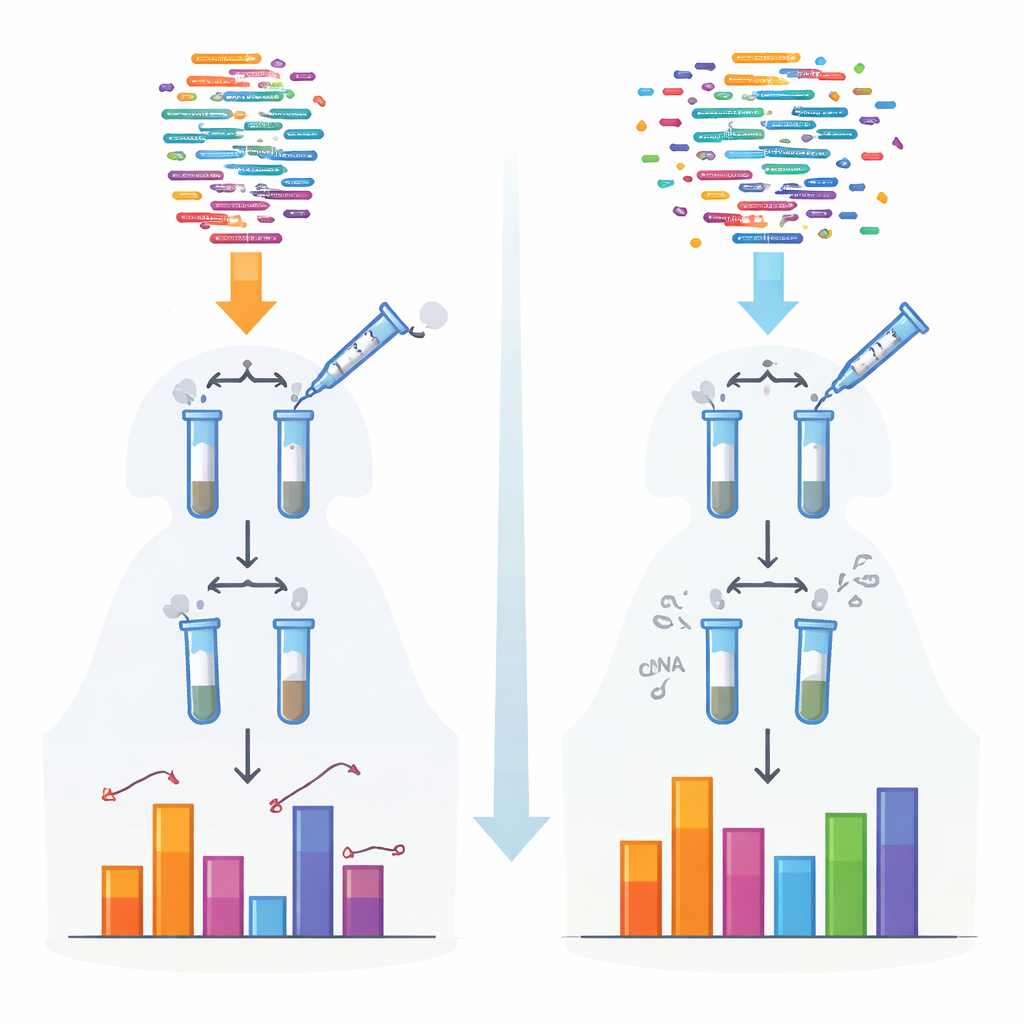
传统的小RNA测序方法依赖于将接头片段连接到分子上再进行读取的酶。这些酶偏好特定的形状和化学末端,因此某些RNA被高效捕获而其他的则被遗漏或低估。这种偏差在某些类别上尤为严重,例如携带保护性化学帽的piRNA和植物小RNA。作者开发了一种名为4NBoost的新方案,对接头设计和反应条件进行了重新设计以平衡这种偏好,并加入了内建的分子条码以区分真实分子和扩增过程中产生的拷贝。
把一个方案变成量化工具
为了将4NBoost从相对读数转换为实际测量工具,团队在已知浓度下加入了精心设计的合成“spike‑in” RNA,覆盖极宽的浓度范围。通过比较测序器读取每个spike‑in的次数与最初添加的量,他们建立了将读取计数转换为绝对分子数的标准曲线。不同spike‑in混合物和加入的对照RNA测试表明,4NBoost能在多个数量级上准确追踪丰度,包括带有麻烦化学修饰的RNA。即便从仅1纳克的总RNA起始,方法依然忠实地捕获了小RNA的全貌。
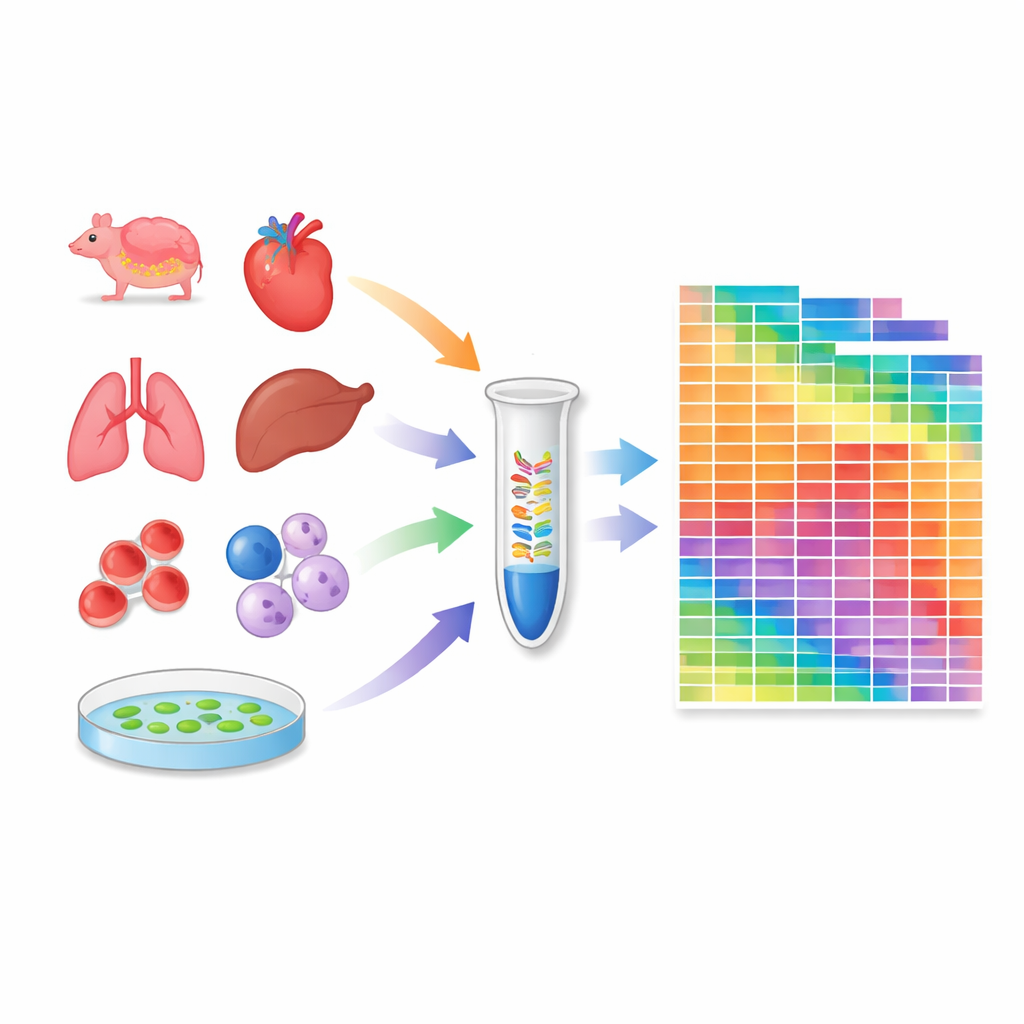
跨组织与细胞系构建图谱
借助这一校准后的方案,研究者分析了259个样本:来自小鼠的20个组织、食蟹猴的18个组织、24个人类与小鼠的常用细胞系,以及模式植物拟南芥的若干组织。对每个样本,他们估算了数千种microRNA和piRNA的绝对分子数。这揭示了每种情境下存在多少不同的microRNA物种,以及它们在组织与物种间的总量如何变化。一些细胞系和器官拥有特别丰富的microRNA谱系,而另一些如血细胞则由少数高度丰富的物种主导。该图谱还暴露了小鼠与猴子组织间的显著差异,强调小RNA调控可能具有物种特异性。
修正旧数据并修订常见假设
将新图谱与使用传统方法构建的流行小RNA数据库比较时,出现了显著的不匹配。若干重要的microRNA家族——例如miR‑19和miR‑29——比以前认为的更为丰富,而另一些——如广泛研究的let‑7和miR‑10家族——则常被高估。研究还重新评估了每个前体发夹中哪一条“臂”在细胞中被使用,发现一些当前注释标注了错误的主要链。为挽救大量已有的偏倚数据集,作者训练了一个机器学习模型,学习传统测量如何偏离4NBoost,然后用数学方法对其进行校正,使结果更能反映真实丰度。
一个用于探索小RNA的公共资源
所有4NBoost测量结果和校正模型都通过一个名为SmRNAQuant的在线平台免费提供。研究者可以浏览或下载特定组织、细胞系或microRNA的绝对小RNA水平,也可以上传使用常见试剂盒制备的数据以获得偏差校正值。对于非专业读者,核心信息是:计数很重要——小RNA拷贝数上的微小差异可能意味着基因调控是否发生。通过提供更可靠的数字和修复旧数据的方法,这项工作为理解小RNA如何影响正常生理与疾病奠定了更坚实的定量基础。
引用: Xiao, W., Zheng, Y., Zhang, H. et al. An absolute quantification atlas of small non-coding RNAs across diverse mammalian tissues and cell lines. Nat Commun 17, 2314 (2026). https://doi.org/10.1038/s41467-026-68812-7
关键词: microRNA 定量, 小非编码 RNA, RNA 测序偏差, 组织表达图谱, 机器学习校正