Clear Sky Science · tr
Microhomoloji aracılı uç birleştirme baskın hedeflemesi yoluyla fare embriyolarında CRISPR hassasiyetinin optimize edilmesi
Neden daha keskin gen düzenlenmiş fareler önemli?
CRISPR gibi gen düzenleme araçları, insan hastalıklarını modelleyen fareler yaratmayı son derece kolaylaştırdı, ancak gizli bir sorun var: hayvanların ilk neslindeki genetik değişiklikler sıklıkla karışık ve düzensiz oluyor. Bu, deneyleri yavaşlatıyor, güvenilirliğini düşürüyor ve daha fazla hayvan kullanılmasına yol açıyor. Bu çalışma, fare embriyolarında CRISPR kırılmalarını yüksek düzeyde öngörülebilir sonuçlara yönlendiren bir yöntem sunuyor; böylece çoğu kurucu fare aynı, iyi tanımlanmış mutasyonla doğuyor—gen düzenleme araştırmasına daha temiz bir biyoloji ve daha iyi etik getiriyor.
Karışık DNA onarımlarının zorluğu
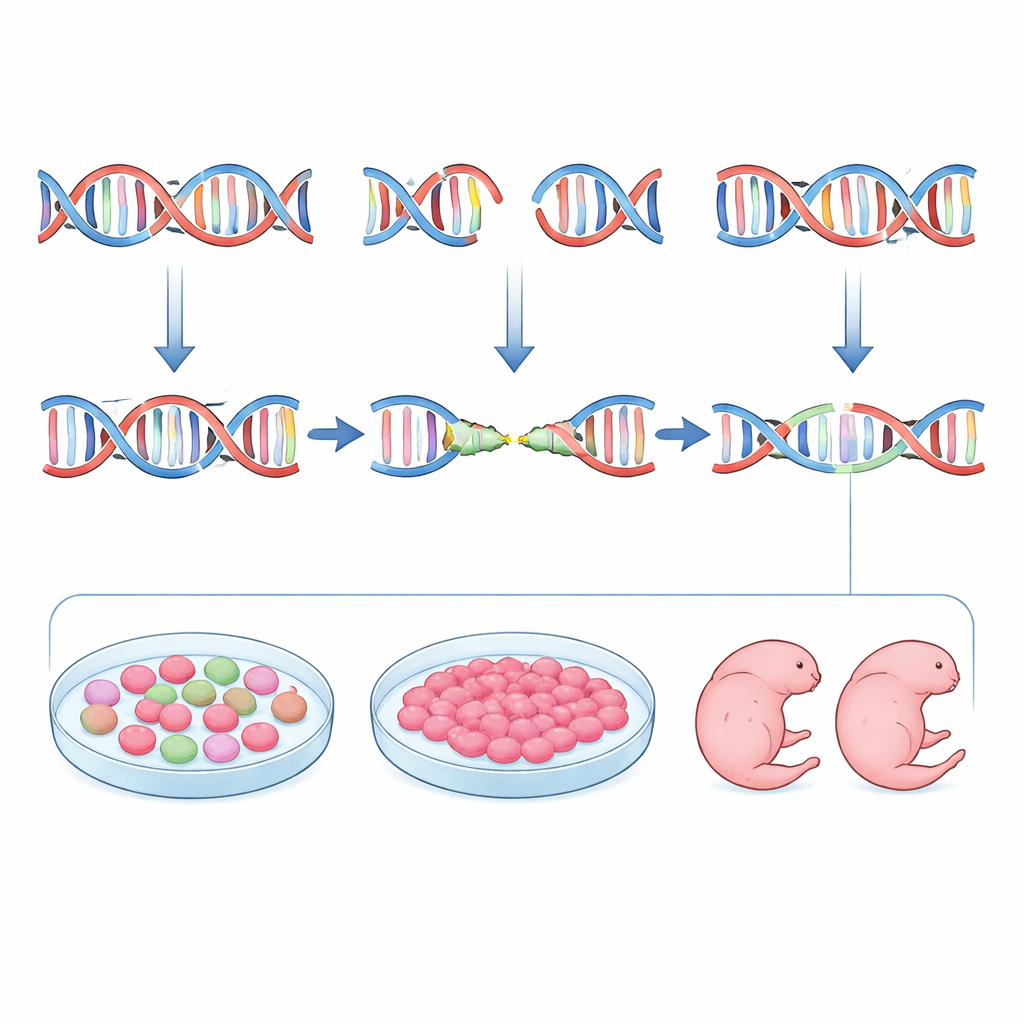
CRISPR DNA’yı kestiğinde, hücre kırığı kendi onarım sistemleriyle yamamak zorunda kalır. En yaygın yol olan homolog olmayan uç birleştirme hızlıdır ama hassas değildir; kesme bölgesinde küçük eklemeler ve silinmelerin karışımını üretir. Diğer bir yol olan mikrohomoloji aracılı uç birleştirme, kısa eşleşen dizileri kılavuz olarak kullanarak genellikle belirli biçimlerde DNA parçalarını siler. Her ikisi de hassas ama yavaş olan homolojiye dayalı yoldan çok daha etkilidir. Standart CRISPR deneylerinde bilim insanları genellikle bir kılavuz RNA’nın ne kadar güçlü kestiğine ve kaç hedef dışı siteye sahip olduğuna odaklanır; hangi onarım yolunun tercih edileceğine veya hangi kesin mutasyonun ortaya çıkacağına çok daha az dikkat ederler. Sonuç olarak birçok kurucu fare farklı hücrelerde farklı mutasyon mozaikleri taşır ve araştırmacıları temiz, tek tip bir genotiple çalışabilmek için bir sonraki nesle çiftleştirmeye zorlar.
CRISPR kılavuzlarını seçmenin daha akıllı yolu
Yazarlar, kılavuzları yalnızca güç ve güvenlik için değil, aynı zamanda öngörülebilirlik için de tasarlayarak bu senaryoyu değiştirmeyi hedeflediler. Çalışmaya hücre kültürlerinde CRISPR kaynaklı mutasyonların büyük veri setleriyle eğitilmiş bir makine öğrenmesi aracı olan inDelphi ile başladılar. inDelphi yalnızca bir bölgenin ne sıklıkla düzenleneceğini söylemez; ortaya çıkabilecek tüm ekleme ve silinmelerin listesini ve her birinin ne sıklıkta görüneceğini, özellikle mikrohomolojiyle yönlendirilen olaylara dikkat ederek tahmin eder. Ekip, işlev kaybı hayvanları albino yapan fare tirozinaz (Tyr) genini taradı ve off-target risklerini düşük tutarken güçlü, tekrarlanabilir mikrohomoloji aracılı silinmeleri desteklemesi öngörülen kılavuz RNA’ları seçti. Ardından fare embriyolarını düzenleyip derin dizileme ile ortaya çıkan mutasyonları ölçtüler. Genel olarak, inDelphi’in her kılavuz için favori genotipi embriyolarda tahmin edildiği benzer sıklıkta ortaya çıktı ve daha güçlü mikrohomoloji özelliklerine sahip kılavuzlar gerçekten daha uniform mutasyon desenleri üretti.
Kök hücreleri provada kullanmak
Yine de yalnızca tahmin yeterli değildi. Ekip inDelphi öngörüleri ile gerçek düzenleme desenlerini karşılaştırdığında yalnızca orta düzeyde bir uyuşma buldu. Bu boşluğu kapatmak için pratik bir ara adım eklediler: her kılavuzu erken embriyolarla birçok özelliği paylaşan fare embriyonik kök hücrelerinde test etmek. Bu hücreleri CRISPR bileşenleriyle transfekte ettikten sonra düzenlenmiş hücreleri sıraladılar ve hedef bölgeleri dizilediler. Kök hücrelerindeki mutasyon desenleri, bilgisayar modelinden çok daha yakın bir şekilde embriyolardaki desenlerle eşleşti. Kök hücrelerinde tek baskın bir silinme üreten kılavuzlar tipik olarak blastosistlerde ve daha ileri embriyolarda da aynı davranışı gösterdi. inDelphi’in sıralamasını bu kök hücre “prova”sıyla birleştirerek araştırmacılar, mikrohomoloji aracılı onarımı yönlendiren ve mutant alellerin çeşitliliğini en aza indiren kılavuzları güvenilir şekilde seçebildiler.
Göz renginden kayıp uzuvlara
Yazarlar boru hattını canlı hayvanlarda denediler. Tyr geni için yüksek, orta ve düşük öngörülen hassasiyeti temsil eden üç kılavuz seçip düzenlenmiş embriyoları bakıcı annelere aktardılar. Gelişimin 11.5. gününde göz pigmentasyonunu incelediler ve her embriyoyu ayrı ayrı dizilediler. Mikrohomoloji lehine güçlü kılavuz çoğunlukla albino olan ve genin her iki kopyasında sıklıkla tek bir baskın küçük silinme taşıyan, çok az varyasyon gösteren embriyolar üretti. Daha az optimize edilmiş bir kılavuz ise pigment kaybı ve kısmi pigmentasyonun karışımı ile daha karmaşık bir mutasyon setine bağlı sonuçlar verdi. Ardından aynı yaklaşımı, işlev kaybı uzuvsuz embriyolarla sonuçlanan Fgf10 genine uyguladılar. Kök hücrelerde spesifik dört bazlık bir silinmeyi yüksek olasılıkla vereceği öngörülen ve doğrulanan bir kılavuz seçerek, gelişimin 15.5. günündeki embriyoları bir şekilde tek tip uzuvsuz ve beklenen silinmelerle güçlü şekilde zenginleşmiş olarak ürettiler. Her iki gen için de inDelphi tahminlerinde, kök hücrelerde, erken embriyolarda ve daha ileri embriyolarda aynı birkaç mutasyon türü baskın çıktı.
Daha az hayvanla daha temiz genetik
Pratik açıdan çalışma, farelerde CRISPR deneyleri tasarlamak için yeni bir şablon sunuyor. Bilgisayarla tasarlanmış bir kılavuzdan doğrudan embriyo düzenlemeye hızla geçmek yerine yazarlar entegre bir boru hattını öneriyor: mikrohomoloji aracılı silinmeleri ve çerçeve kaymalarını destekleme olasılığı yüksek kılavuzları seçmek için inDelphi ve off-target araçlarını kullanın, bu kılavuzları verim ve mutasyon uniformitesini doğrulamak için embriyonik kök hücrelerde test edin ve sadece en iyi performans gösterenleri embriyo çalışmalarına ilerletin. Bu strateji, hücreleri ezici çoğunlukla aynı, iyi tanımlanmış mutasyonu paylaşan kurucu fareler veriyor; bunlar özellikle tekrar eden silinme türündeki değişikliklerin neden olduğu insan hastalıklarını modellemede hemen kullanılabilir hale geliyor ve çiftleştirilmesi ve taranması gereken hayvan sayısını azaltıyor. Sonuç, daha keskin, daha tekrarlanabilir genetikler ve güçlü hastalık modellerine daha etik bir erişim yolu.
Atıf: Lkhagvadorj, K., Okamura, E., Taki, T. et al. Optimizing CRISPR precision in mouse embryos via microhomology-mediated end joining-dominant targeting. Commun Biol 9, 371 (2026). https://doi.org/10.1038/s42003-026-09771-z
Anahtar kelimeler: CRISPR, fare modelleri, genom düzenleme, DNA onarımı, hastalık modelleme