Clear Sky Science · tr
DANST, derin alan adversarial sinir ağları kullanarak mekânsal transkriptomikte hücre tipi dekonküvolüsyonunu sağlıyor
Hücreleri Komşulukları İçinde Görmek
İnsan dokuları, her biri kendi rolünü oynayan birçok farklı hücre tipinin bulunduğu kalabalık kentler gibidir. Yeni “mekânsal transkriptomik” teknolojiler, bir doku dilimi boyunca hangi genlerin aktif olduğunu ölçebiliyor, ancak her bir ölçüm genellikle birden çok komşu hücrenin sinyallerini karıştırıyor. Bu makale, bu karışımları ayıran akıllı bir hesaplama yöntemi olan DANST’i tanıtıyor. Hangi hücre tiplerinin bulunduğunu ve organlarda veya tümörlerde nerede yer aldıklarını söyleyerek, bilim insanlarının dokuların nasıl yapılandığını, hastalıkların nasıl yayıldığını ve tedavilerin en iyi nereye yönlendirilebileceğini daha iyi anlamalarına yardımcı oluyor. 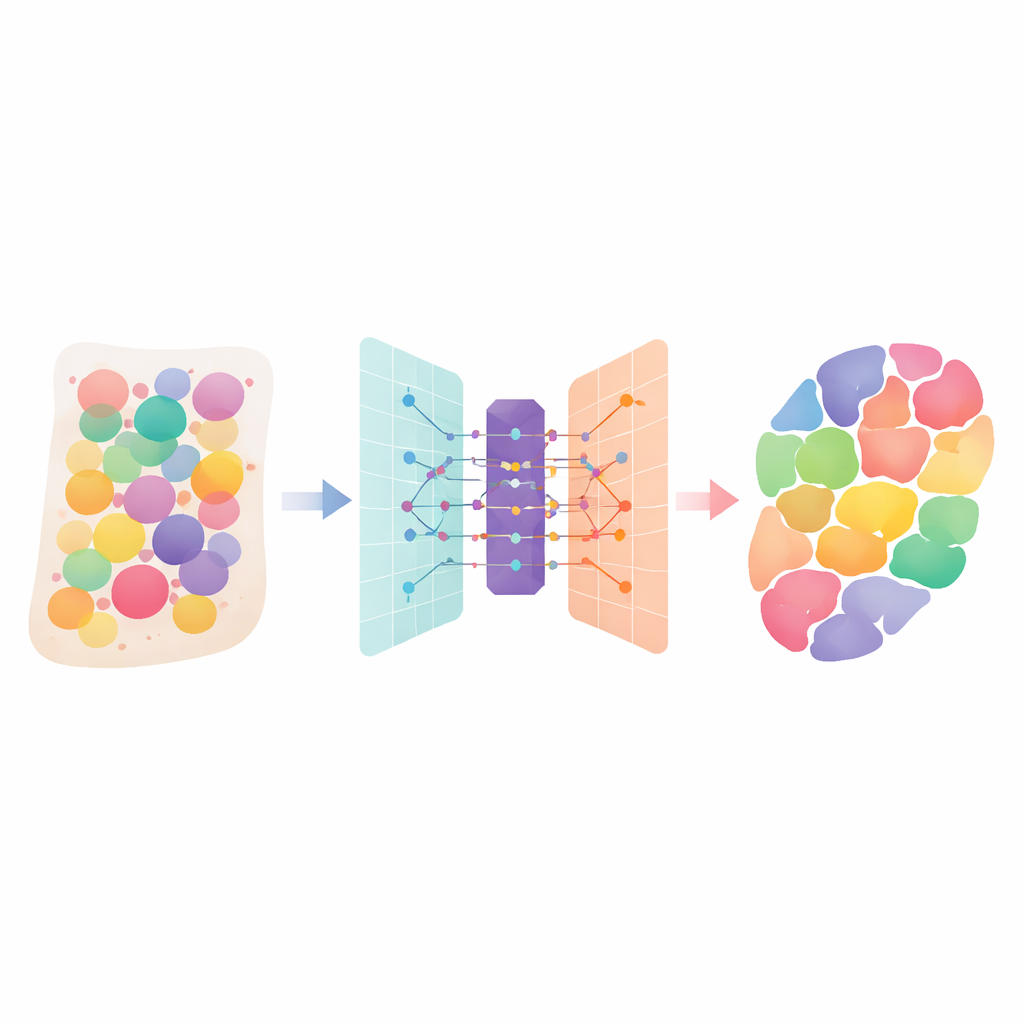
Hücre Kalabalıklarını Çözmenin Zorluğu
Modern gen-okuma araçları ya tek hücre düzeyinde çok hassas bakabiliyor ya da bir dokunun tüm düzenini yakalayabiliyor, nadiren her ikisini birden yapabiliyor. Yaygın mekan teknolojileri, birkaç hücreyi kapsayabilen nispeten büyük “noktalarda” gen aktivitesini kaydeder. Sonuç, kimin hangi notaları söylediğini bilemediğiniz bir koroyu duymaya benziyor. Bunu anlamlandırmak için, araştırmacıların her noktanın hangi hücre tiplerinin ne kadar katkıda bulunduğunu tahmin eden “dekonküvolüsyon” yöntemlerine ihtiyacı var. Mevcut birçok yaklaşım referans olarak tek hücre verilerini kullanıyor, ancak iki veri türü farklı deneylerle toplandığı ve kalite, gürültü veya çözünürlük açısından tam olarak örtüşmediği için zorlanıyorlar.
Veri Dünyaları Arasında Bir Köprü Kurmak
DANST, tek hücre verileri ile mekânsal veriler arasındaki bu uyumsuzluğu bir köprü kurarak ele alıyor. Önce, ayrıntılı tek hücre profillerini kullanarak bilinen hücre tipi oranlarına sahip çok sayıda yapay karışık nokta (spot) simüle ediyor. Aynı zamanda, gerçek mekânsal noktaları hem dokudaki konumlarına hem de gen desenlerine göre grupluyor ve bu gruplara olan uzaklıkları kullanarak her simüle edilmiş noktaya bir “sözde” konum atıyor. Bu adım, yapay ve gerçek noktaların ortak bir mekânsal çerçeve paylaştığı bağlı bir harita oluşturuyor; böylece yöntem, karışık sinyallerin dokunun belirli mahallelerinde nasıl görünmesi gerektiğini öğrenebiliyor. 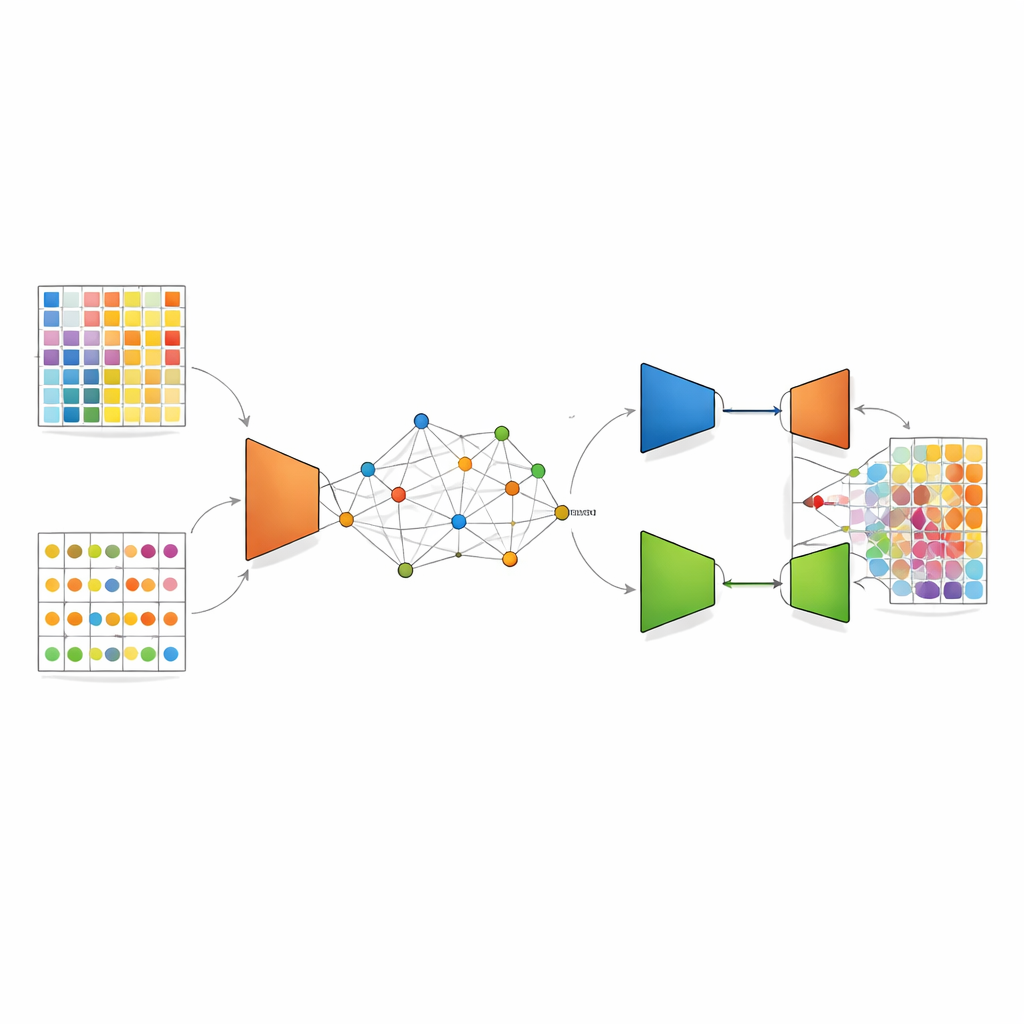
Sinyalleri Temizlemek ve Alanları Hizalamak
Bu ortak harita hazır olduğunda, DANST varyasyonel otoenkoder olarak adlandırılan bir tür derin öğrenme uyguluyor. Bu ağ, gerçek ve simüle edilmiş noktaların gen desenlerini rafine edilmiş bir iç temsile sıkıştırıyor ve sonra bunları yeniden oluşturmaya çalışıyor; böylece veriyi etkin biçimde gürültüden arındırıyor ve önemli özellikleri vurguluyor. Bunun üzerine yazarlar bir adversaryal bileşen ekliyor: ikinci bir ağ, rafine edilmiş bir desenin gerçek mekânsal veriden mi yoksa simüle edilmiş veriden mi geldiğini ayırt etmeye çalışırken, özellik çıkarıcı onu yanıltmayı öğreniyor. Bu “güç mücadelesi”, modeli her iki veri kaynağı için de iyi çalışan özelliklere yönlendiriyor; böylece bilinen hücre tipi oranlarına sahip simüle edilmiş noktalardan elde edilen bilgi, bileşimi bilinmeyen gerçek doku noktalarına güvenilir şekilde aktarılabiliyor.
Kalp, Beyin ve Tümörlerde Test Etme
Ekip, DANST’i hem yapay kıyaslamalarda hem de fare ve insanlardan alınan gerçek biyolojik örneklerde test etti. Önde gelen birkaç yönteme kıyasla DANST, sentetik veri setlerinde hücre tipi oranlarını daha doğru biçimde geri çıkardı ve çok farklı dokular ve platformlar çapında üstünlüğünü korudu. Bir fare beyni veri setinde korteksin katmanlı organizasyonunu net şekilde yeniden inşa etti ve uzman tarafından tanımlanmış anatomik bölgelerle eşleşti. Ayrı bir fare beyin diliminde hipokampus gibi alanlardaki ince desenleri yakaladı. En önemlisi, insan meme kanseri dokusunda DANST, çeşitli bağışıklık hücrelerinin, destek hücrelerinin ve hormon-duyarlı luminal hücrelerin tümör bölgeleri içinde ve çevresinde nasıl düzenlendiğini izledi. Bu haritalar bilinen biyolojiyle uyumluydu ve hormon bağımlılığı gibi klinik açıdan ilgili özellikleri ve belirli bağışıklık hücrelerinin az olduğu yerlerde muhtemel daha kötü prognoz gibi bulguları öne sürdü.
Biyoloji ve Tıp İçin Anlamı
Uzman olmayan biri için DANST, bulanık ve üst üste binen sinyalleri dokuda hangi hücrelerin nerede yaşadığına dair net bir resme çeviren güçlü bir çevirmen olarak görülebilir. Hücre tiplerini mekânda güvenilir şekilde ayırarak, araştırmacılara sağlıklı organların nasıl düzenlendiğine ve hastalığın bu düzeni nasıl yeniden şekillendirdiğine dair daha keskin bir görüş sunuyor. Kanserde bu, tümör hücreleri ile bağışıklık hücrelerinin belirli bölgelerde nasıl etkileştiğini ortaya koyabilir; bu da hedefe yönelik tedavileri yönlendirebilir ve hasta sonuçlarını tahmin etmeye yardımcı olabilir. Daha fazla mekânsal ve tek hücre veri seti erişilebilir oldukça, DANST gibi araçlar sağlık ve hastalığın temelindeki hücresel mahalleleri çözmek için vazgeçilmez hale gelmeye adaydır.
Atıf: Zhang, X., Wu, Z., Wang, T. et al. DANST enables cell-type deconvolution in spatial transcriptomics using deep domain adversarial neural networks. Commun Biol 9, 388 (2026). https://doi.org/10.1038/s42003-026-09659-y
Anahtar kelimeler: mekânsal transkriptomik, hücre tipi dekonküvolüsyonu, derin öğrenme, tümör mikroçevresi, tek hücre RNA dizileme